peptides
spectra
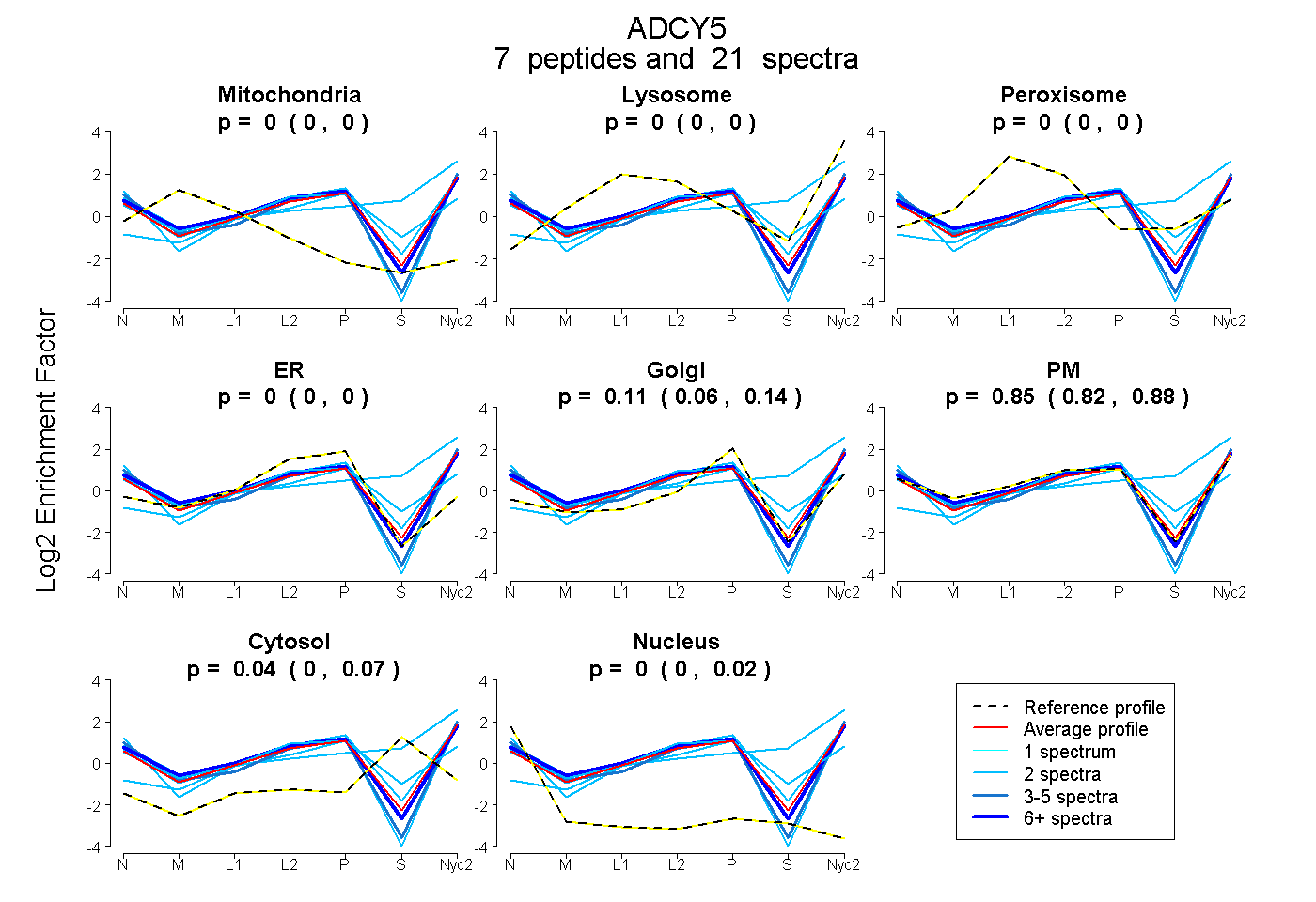
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.062 | 0.140
0.824 | 0.879
0.000 | 0.068
0.000 | 0.022
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
21 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.106 0.062 | 0.140 |
0.852 0.824 | 0.879 |
0.039 0.000 | 0.068 |
0.003 0.000 | 0.022 |
| 2 spectra, APPAGGSGSSAAAAAAAGGTEVRPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.058 | 0.854 | 0.000 | 0.088 | ||
| 2 spectra, LASVGWR | 0.000 | 0.521 | 0.000 | 0.000 | 0.082 | 0.000 | 0.396 | 0.000 | ||
| 3 spectra, LLLSVLPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.037 | 0.924 | 0.000 | 0.039 | ||
| 2 spectra, VHCGVLGLR | 0.000 | 0.000 | 0.052 | 0.154 | 0.000 | 0.603 | 0.191 | 0.000 | ||
| 2 spectra, LLHNILPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.077 | 0.861 | 0.062 | 0.000 | ||
| 2 spectra, LDFLWK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.997 | 0.000 | 0.003 | ||
| 8 spectra, QAFQETR | 0.000 | 0.000 | 0.000 | 0.000 | 0.056 | 0.939 | 0.000 | 0.005 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
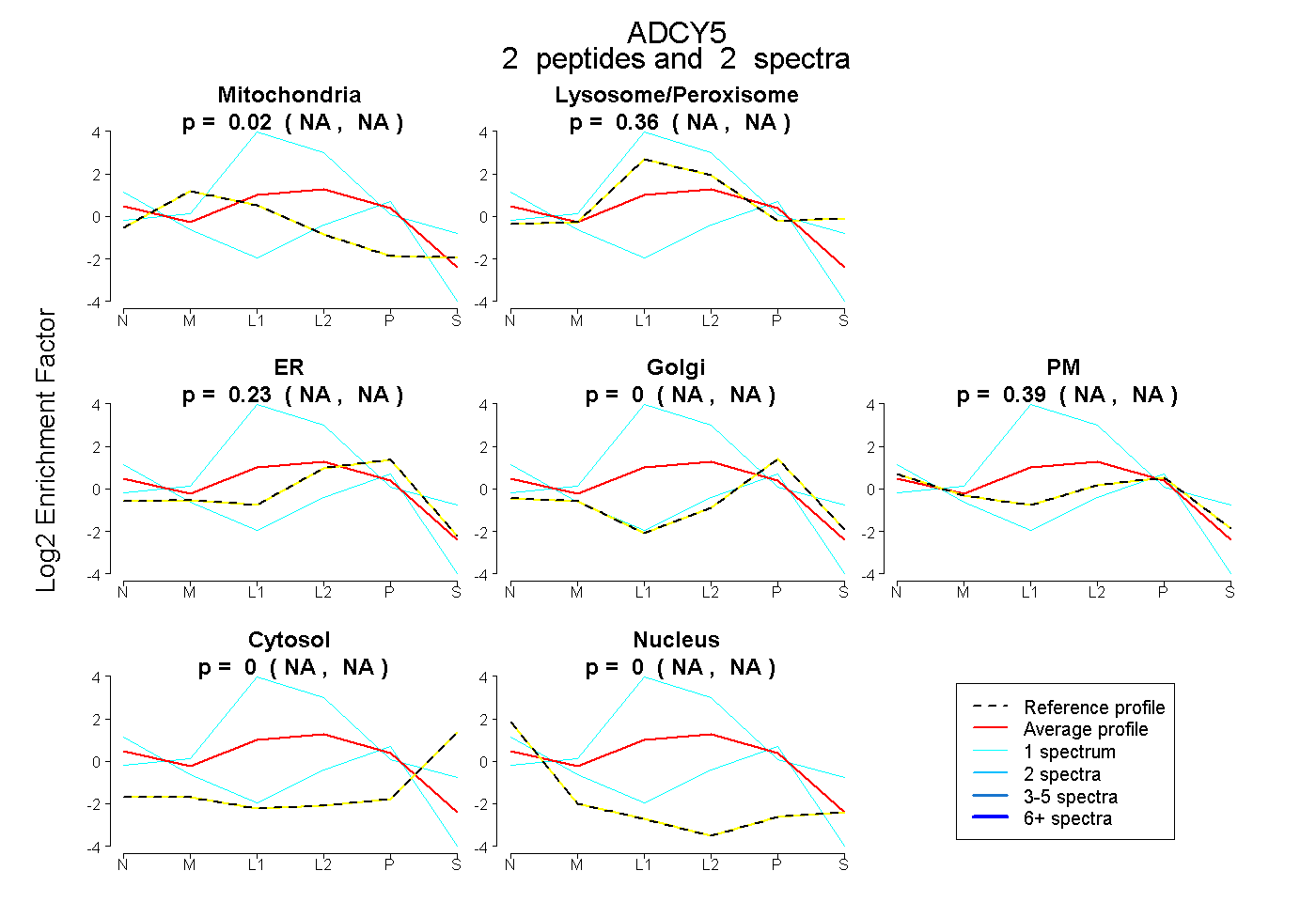 |
0.023 NA | NA |
0.360 NA | NA |
0.229 NA | NA |
0.000 NA | NA |
0.389 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
25 spectra |
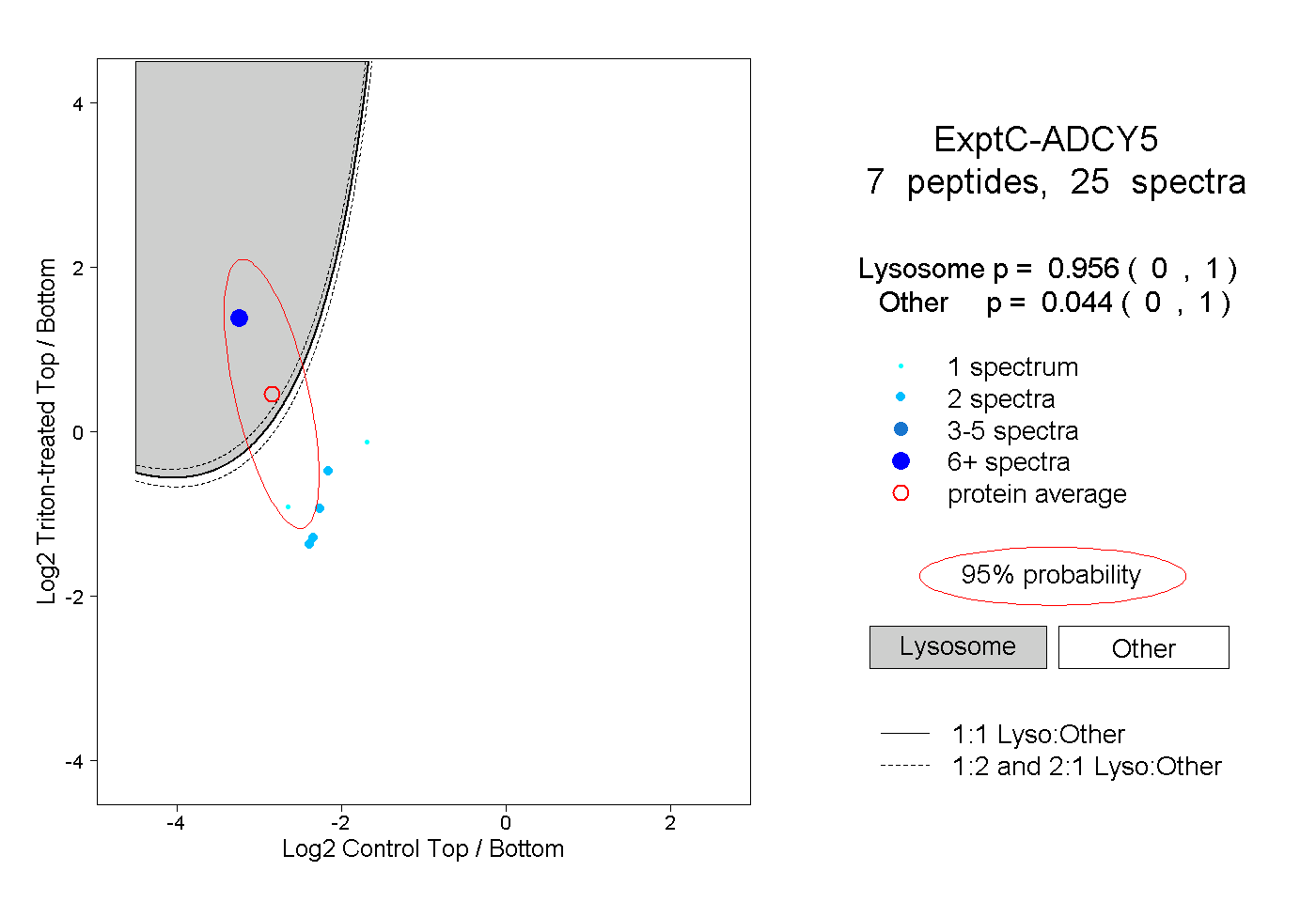 |
0.956 0.000 | 1.000 |
0.044 0.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
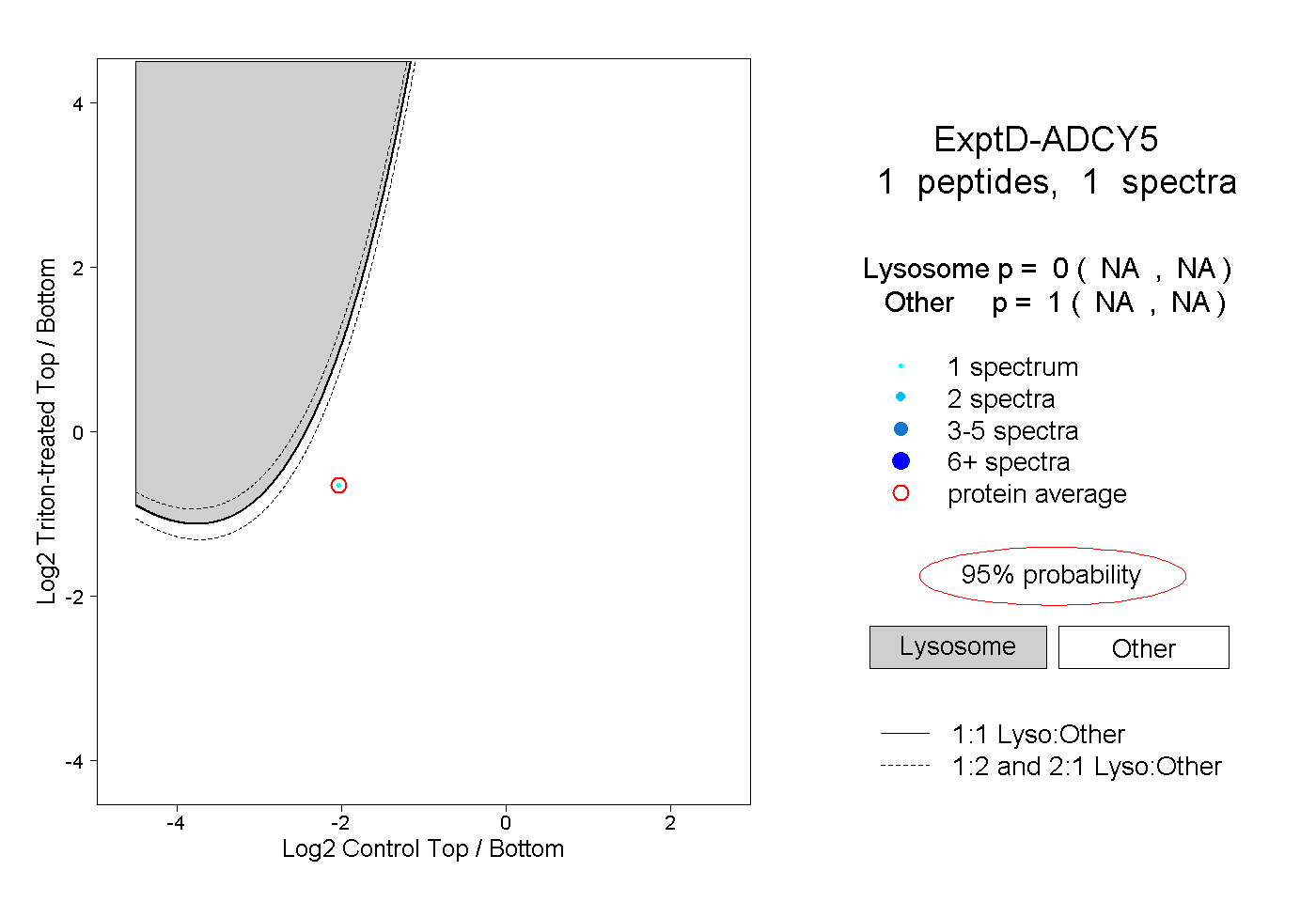 |
0.000 NA | NA |
1.000 NA | NA |