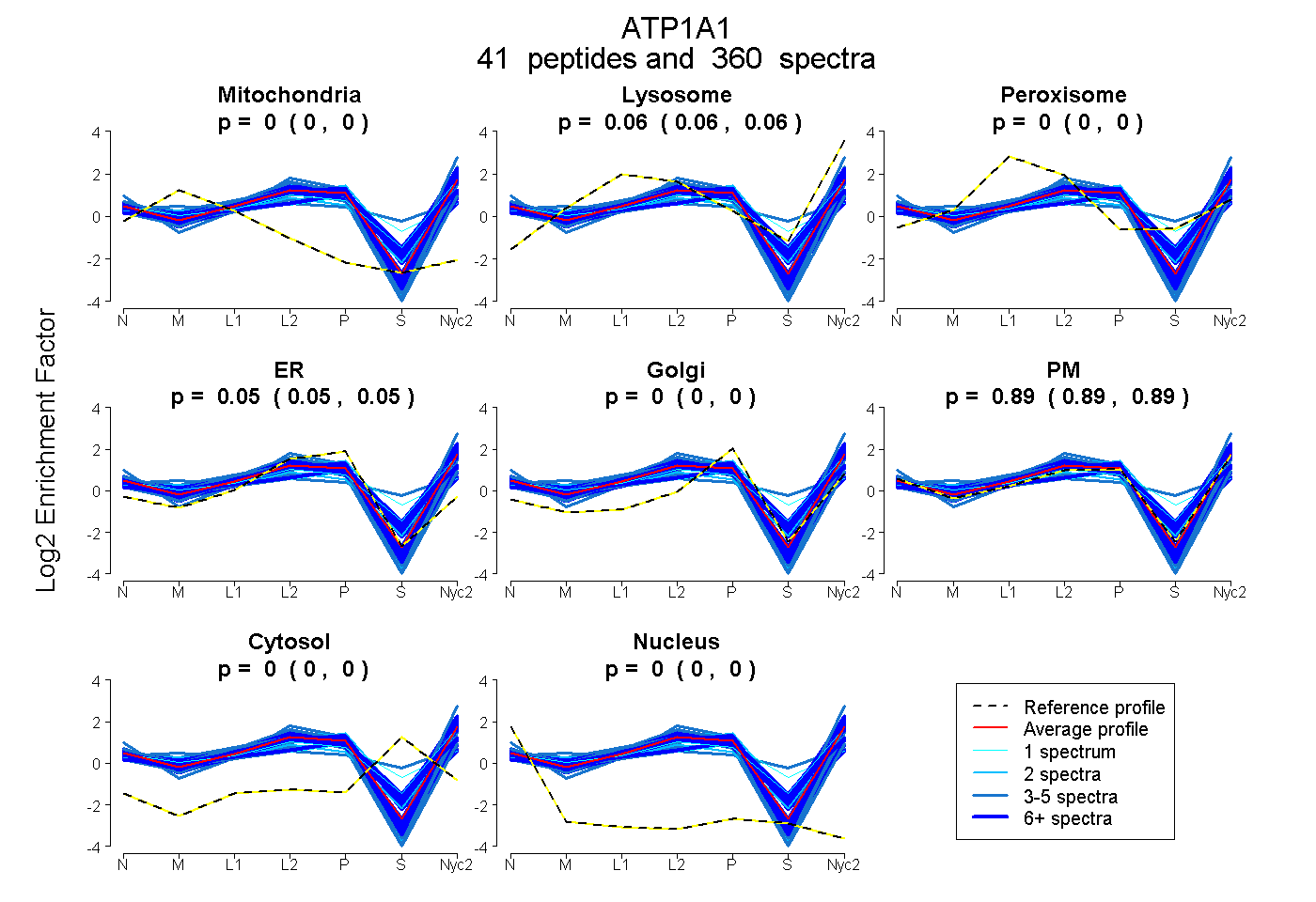
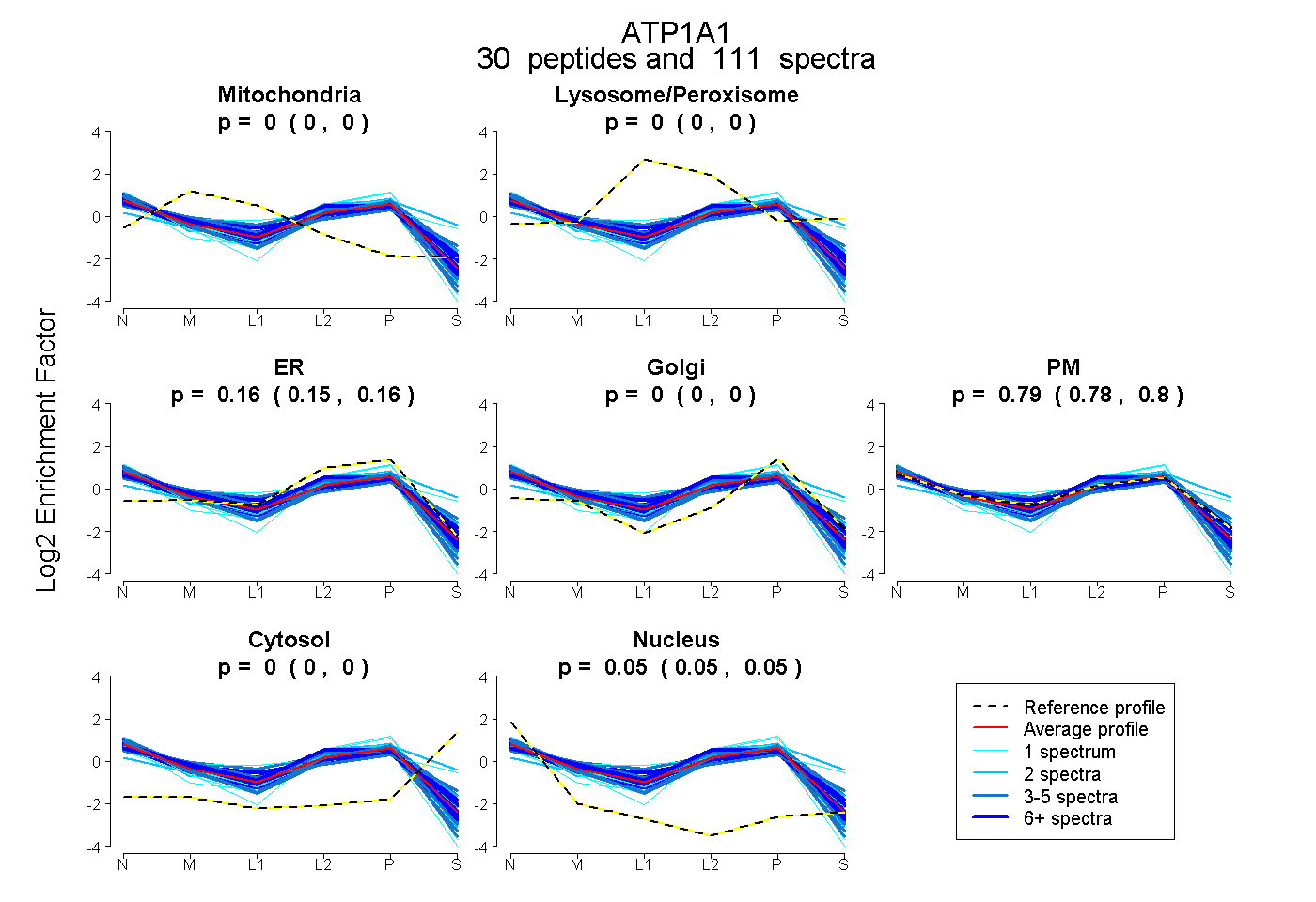
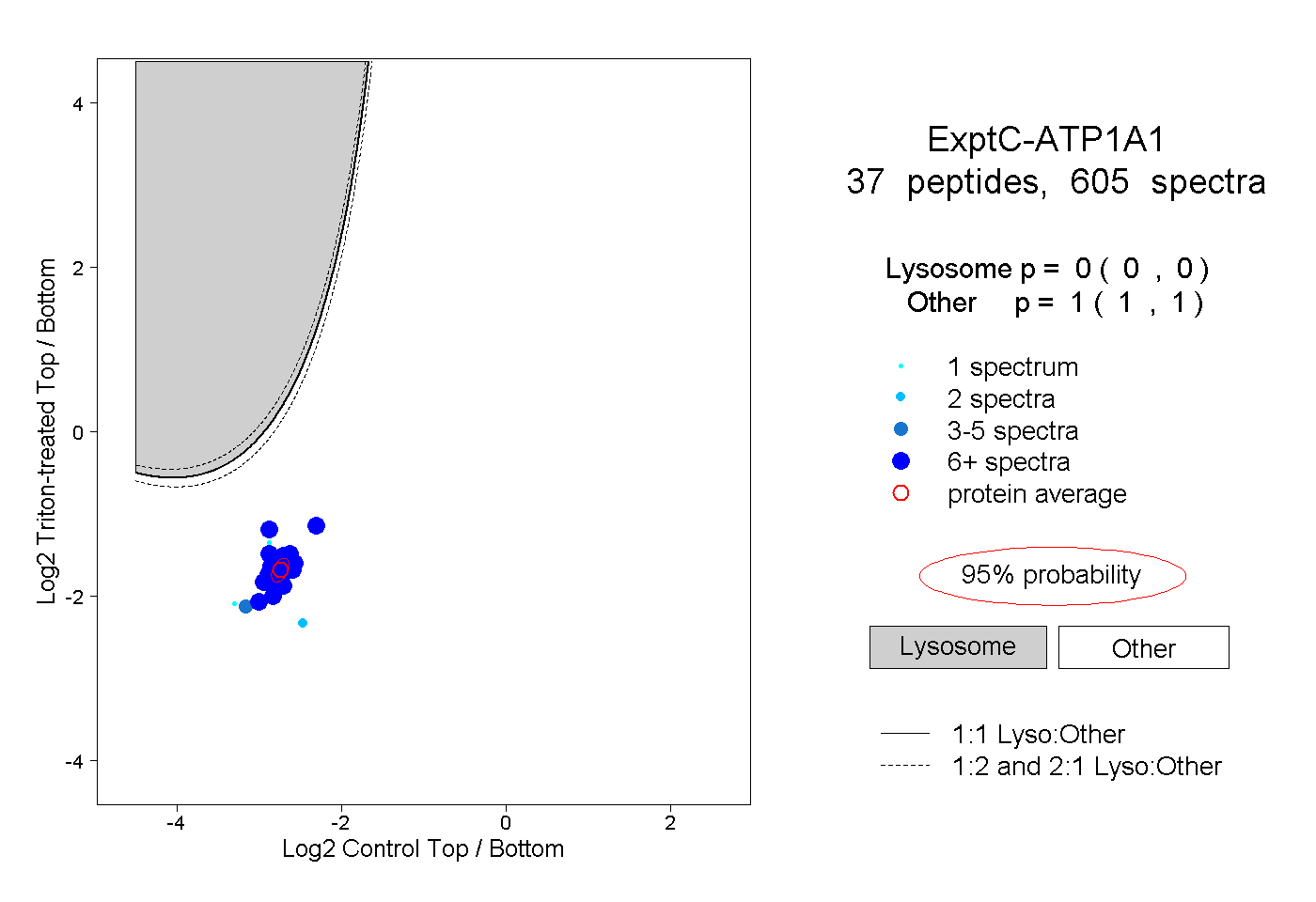
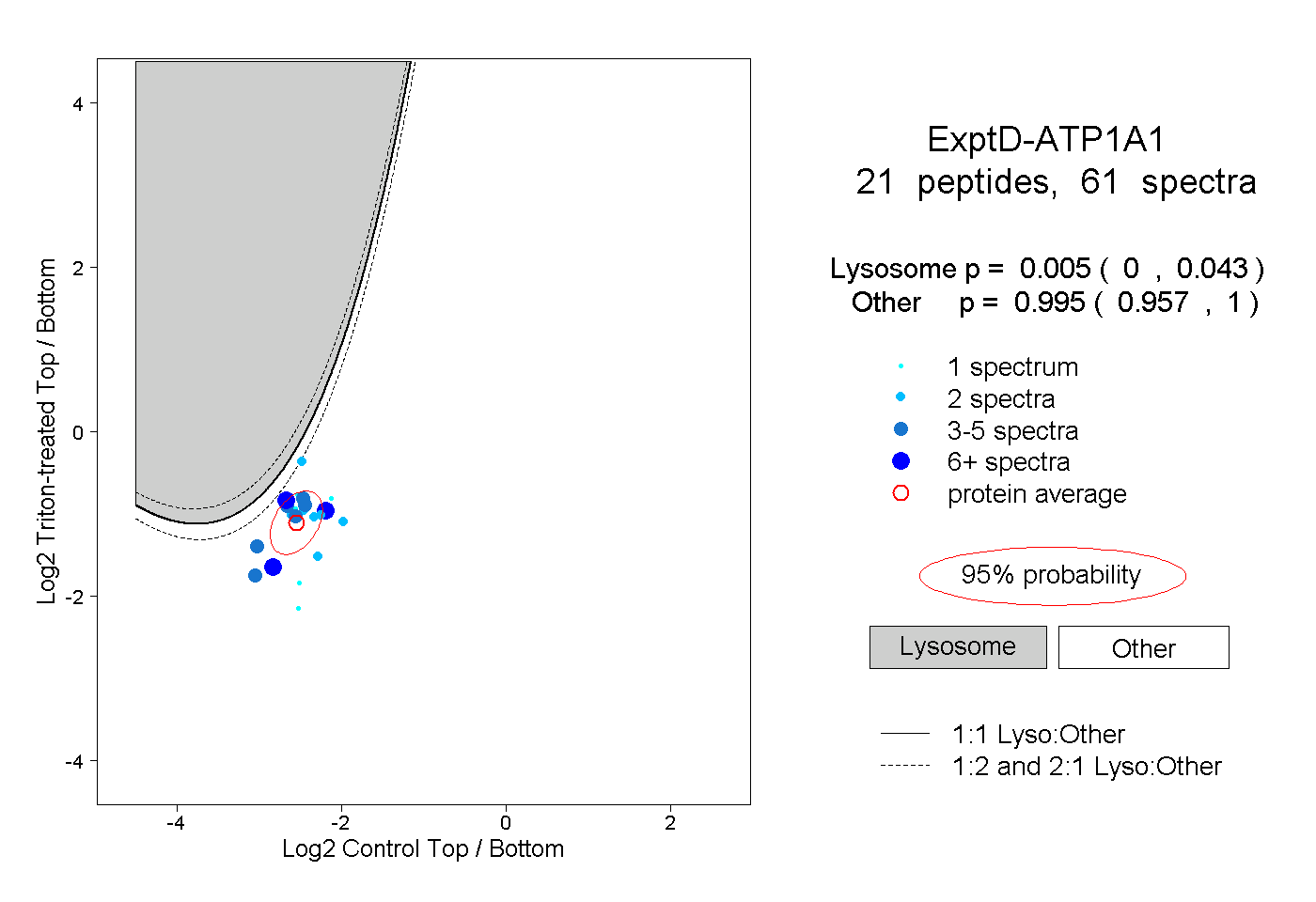
| 2 spectra, RPGGWVEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, IAGLCNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, LNIPVNQVNPR |
|
0.015 |
|
|
|
|
|
|
|
0.985 |
| 2 spectra, GLTPAR |
|
0.001 |
|
|
|
|
|
|
|
0.999 |
| 2 spectra, GIVVYTGDR |
|
0.015 |
|
|
|
|
|
|
|
0.985 |
| 3 spectra, LSLDELHR |
|
0.007 |
|
|
|
|
|
|
|
0.993 |
| 2 spectra, IISANGCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TGTLTQNR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GVGIISEGNETVEDIAAR |
|
0.032 |
|
|
|
|
|
|
|
0.968 |
| 7 spectra, HLLVMK |
|
0.002 |
|
|
|
|
|
|
|
0.998 |
| 5 spectra, LIIVEGCQR |
|
0.042 |
|
|
|
|
|
|
|
0.958 |
| 4 spectra, SPDFTNENPLETR |
|
0.010 |
|
|
|
|
|
|
|
0.990 |
| 3 spectra, AAVPDAVGK |
|
0.003 |
|
|
|
|
|
|
|
0.997 |
| 1 spectrum, IVEIPFNSTNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VIMVTGDHPITAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, VDNSSLTGESEPQTR |
|
0.013 |
|
|
|
|
|
|
|
0.987 |
| 2 spectra, ETWDDR |
|
0.168 |
|
|
|
|
|
|
|
0.832 |
| 2 spectra, YHTEIVFAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, YGTDLSR |
|
0.069 |
|
|
|
|
|
|
|
0.931 |
| 2 spectra, EVSMDDHK |
|
0.005 |
|
|
|
|
|
|
|
0.995 |
| 3 spectra, AVFQANQENLPILK |
|
0.025 |
|
|
|
|
|
|
|
0.975 |