peptides
spectra
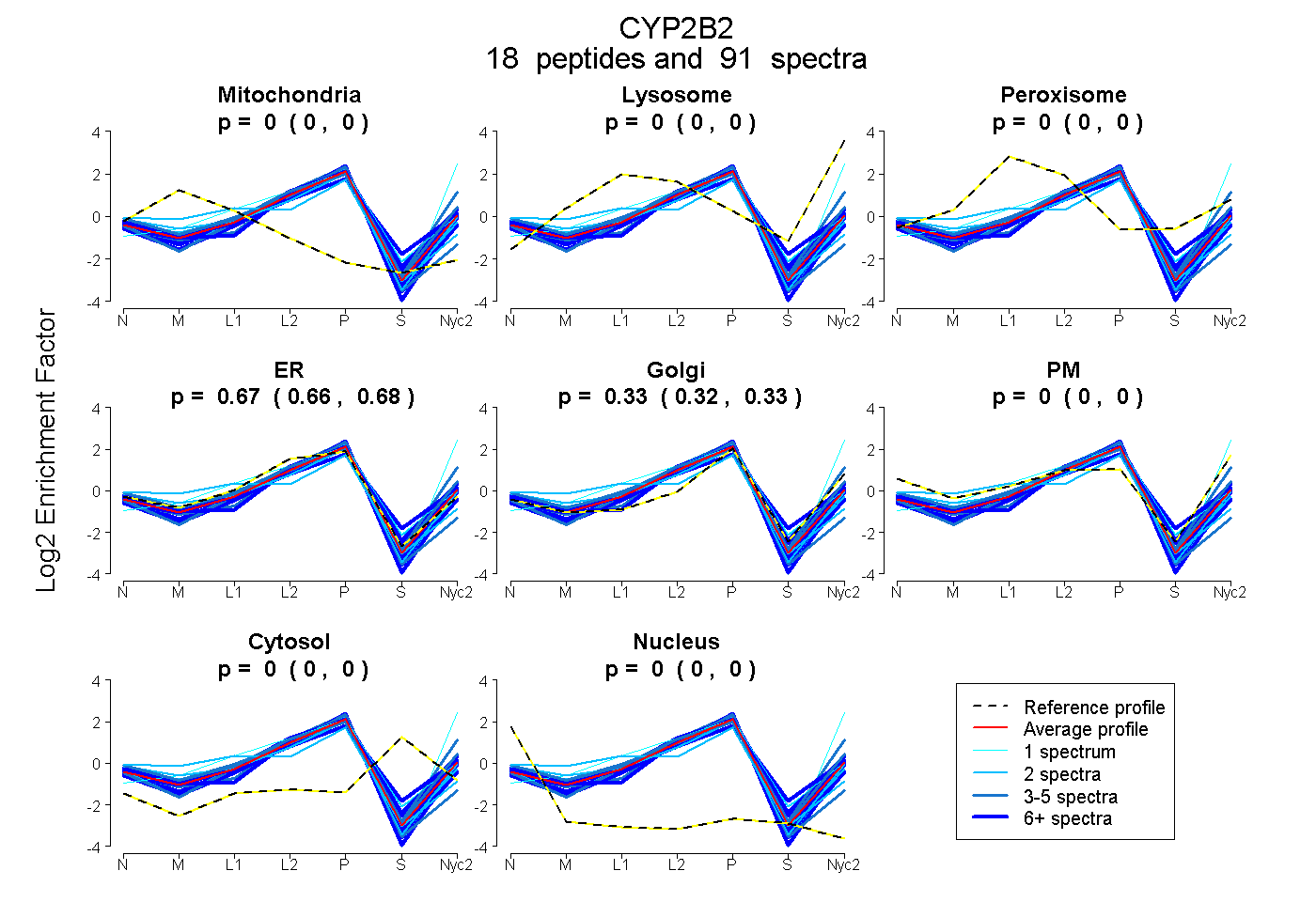
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.664 | 0.681
0.318 | 0.334
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
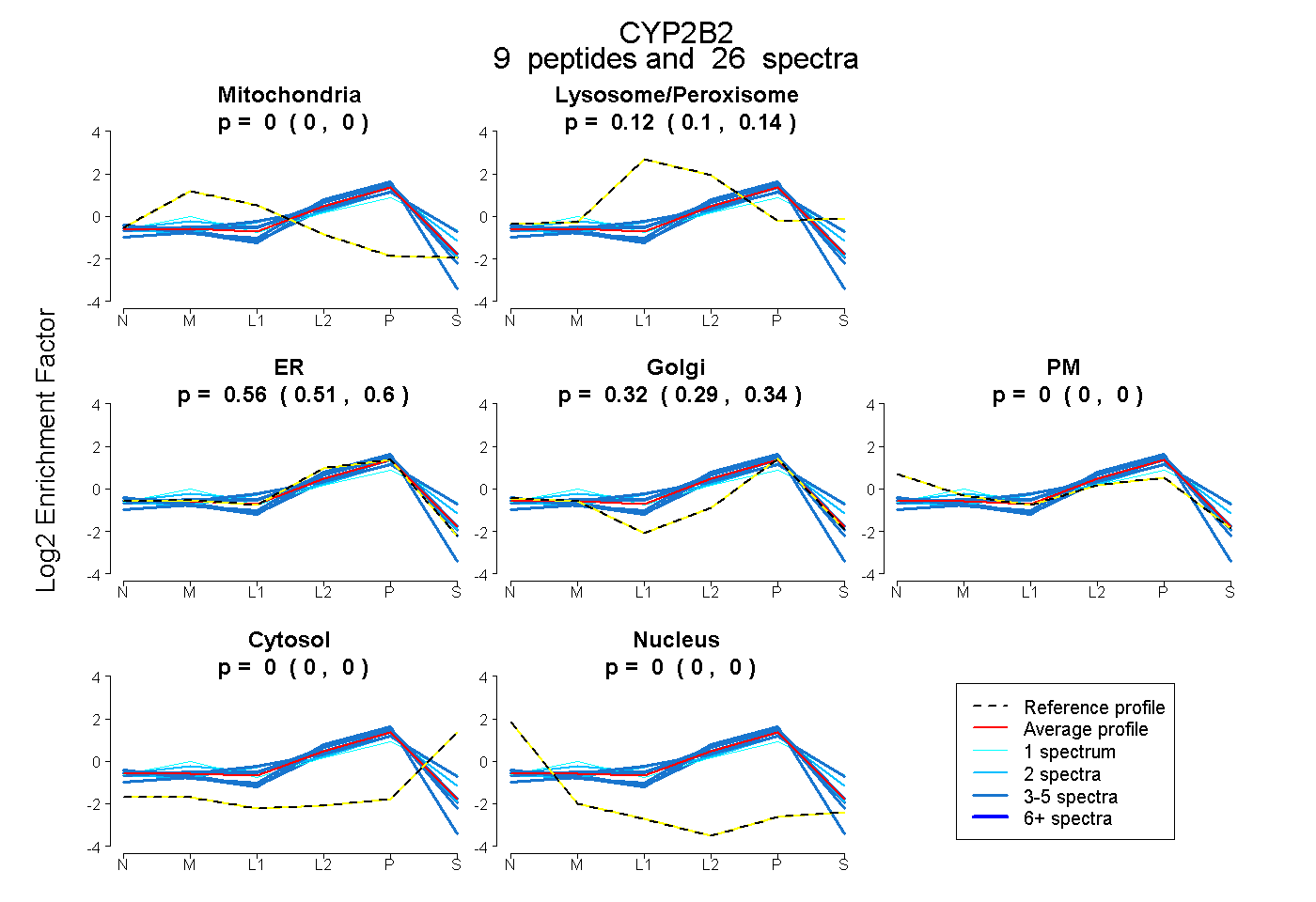
0.000 | 0.000
0.101 | 0.139
0.514 | 0.604
0.286 | 0.340
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
91 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.673 0.664 | 0.681 |
0.327 0.318 | 0.334 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
26 spectra |
 |
0.000 0.000 | 0.000 |
0.122 0.101 | 0.139 |
0.562 0.514 | 0.604 |
0.316 0.286 | 0.340 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, GGLLNSFMQFR | 0.000 | 0.327 | 0.000 | 0.602 | 0.000 | 0.071 | 0.000 | |||
| 2 spectra, EIDQVIGSHRPPSLDDR | 0.000 | 0.315 | 0.086 | 0.599 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, ATLDPSAPR | 0.000 | 0.015 | 0.644 | 0.324 | 0.000 | 0.017 | 0.000 | |||
| 4 spectra, GTIAVIEPIFK | 0.000 | 0.401 | 0.000 | 0.586 | 0.000 | 0.014 | 0.000 | |||
| 2 spectra, EALVGQAEDFSGR | 0.000 | 0.148 | 0.606 | 0.246 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, LLELFYR | 0.000 | 0.000 | 0.948 | 0.028 | 0.000 | 0.000 | 0.024 | |||
| 4 spectra, FADLAPIGLPHR | 0.000 | 0.154 | 0.553 | 0.293 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, ICLGEGIAR | 0.000 | 0.044 | 0.844 | 0.112 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, MPYTDAVIHEIQR | 0.000 | 0.000 | 0.780 | 0.165 | 0.000 | 0.055 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
11 spectra |
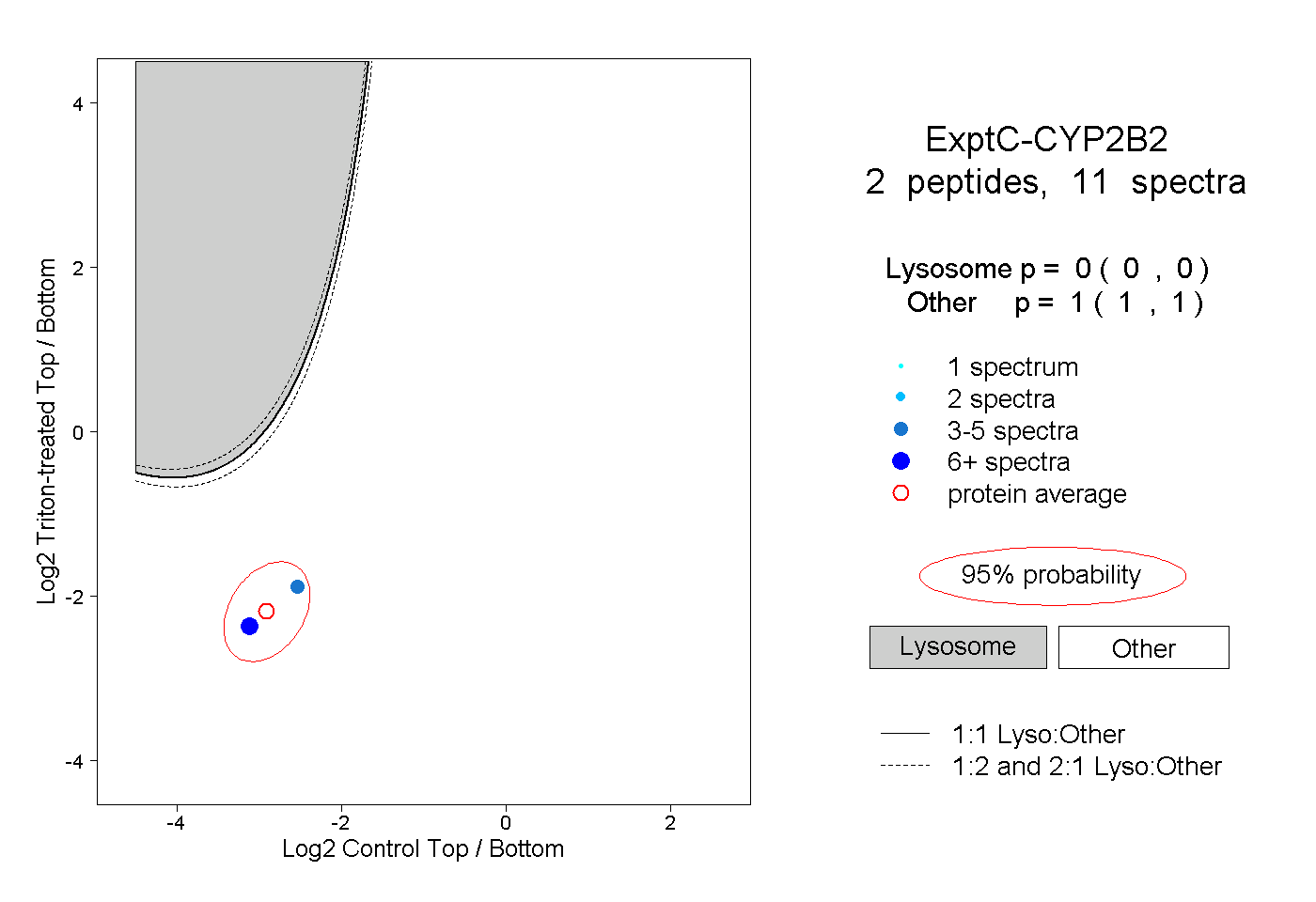 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
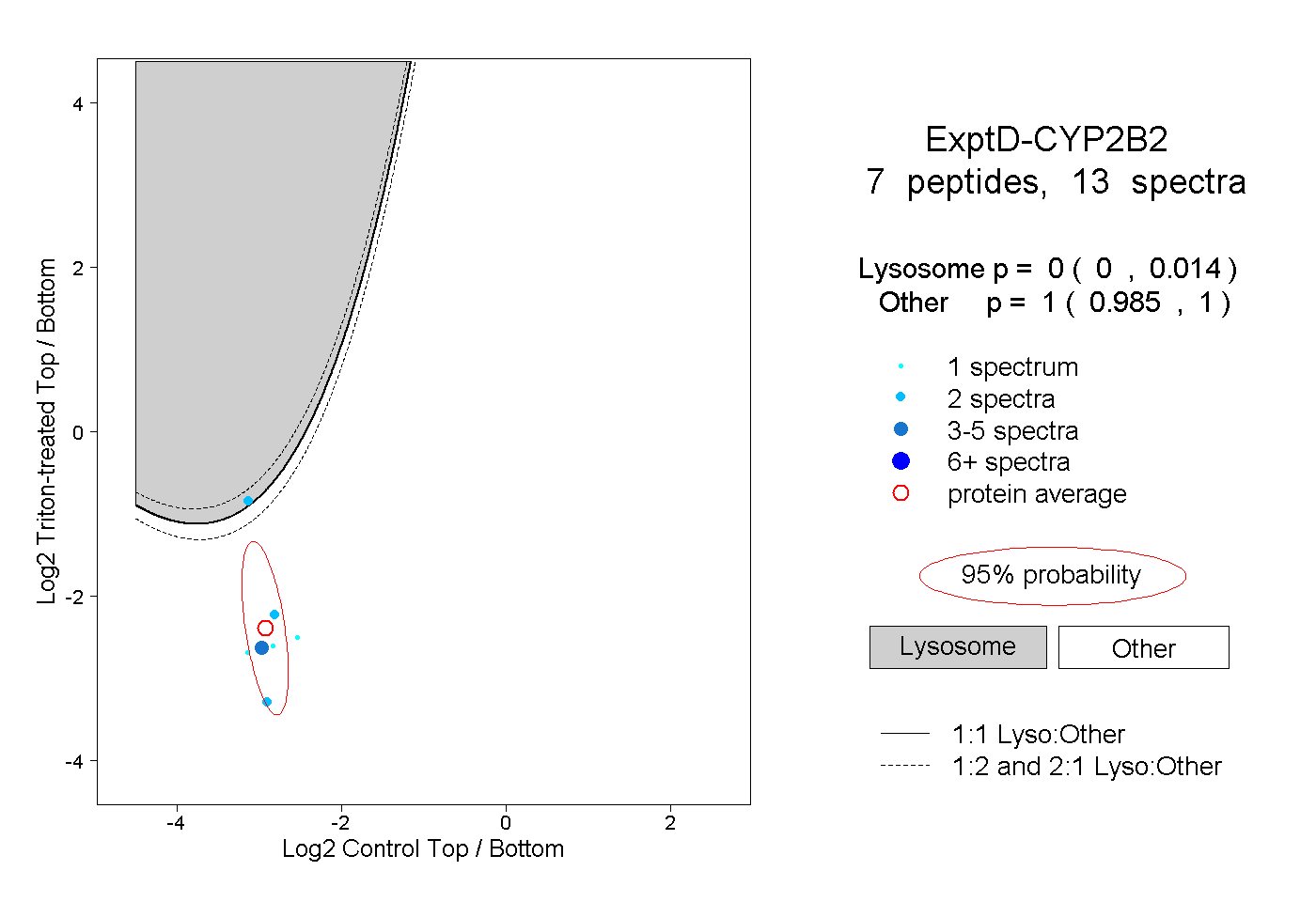 |
0.000 0.000 | 0.014 |
1.000 0.985 | 1.000 |