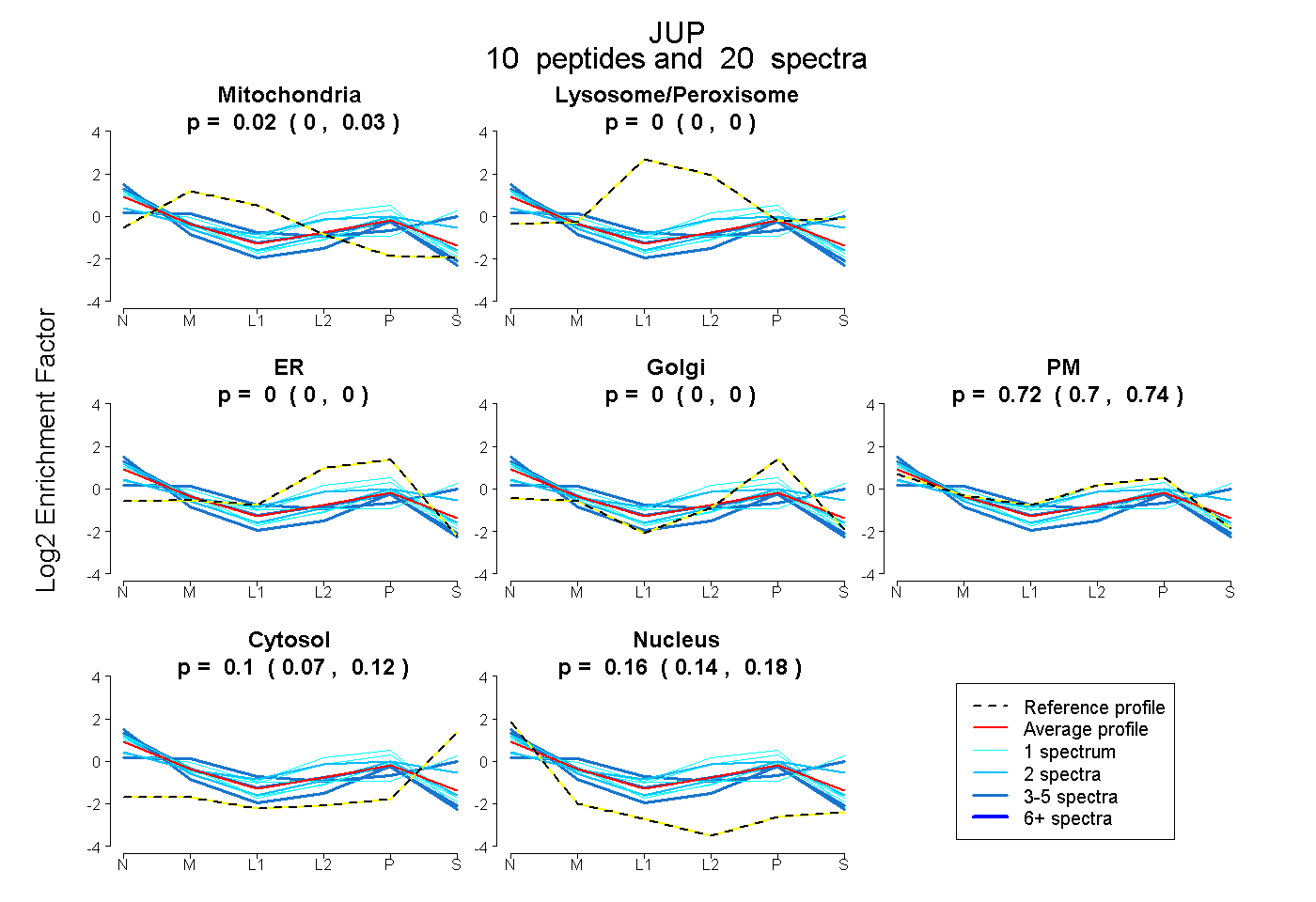
peptides
spectra

0.042 | 0.050
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.732 | 0.738
0.000 | 0.000
0.216 | 0.220
peptides
spectra
0.000 | 0.034
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.705 | 0.738
0.071 | 0.117
0.145 | 0.178
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
64 spectra |
 |
0.046 0.042 | 0.050 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.735 0.732 | 0.738 |
0.000 0.000 | 0.000 |
0.218 0.216 | 0.220 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
20 spectra |
 |
0.018 0.000 | 0.034 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.723 0.705 | 0.738 |
0.095 0.071 | 0.117 |
0.163 0.145 | 0.178 |
| 4 spectra, GLLDEDDTCGR | 0.000 | 0.000 | 0.000 | 0.158 | 0.448 | 0.000 | 0.395 | |||
| 1 spectrum, LLNQPNQWPLVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.969 | 0.000 | 0.031 | |||
| 3 spectra, LVQLLVK | 0.020 | 0.000 | 0.000 | 0.000 | 0.738 | 0.000 | 0.243 | |||
| 1 spectrum, SGGIPALVR | 0.000 | 0.000 | 0.000 | 0.100 | 0.618 | 0.000 | 0.281 | |||
| 2 spectra, ATIGLIR | 0.000 | 0.000 | 0.000 | 0.088 | 0.656 | 0.018 | 0.238 | |||
| 1 spectrum, LLNDEDPVVVTK | 0.005 | 0.000 | 0.000 | 0.133 | 0.596 | 0.000 | 0.266 | |||
| 1 spectrum, LADGLQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.905 | 0.000 | 0.095 | |||
| 1 spectrum, NEGTATYAAAVLFR | 0.138 | 0.099 | 0.000 | 0.000 | 0.330 | 0.388 | 0.046 | |||
| 2 spectra, NLALCPANHAPLQEAAVIPR | 0.000 | 0.103 | 0.000 | 0.000 | 0.663 | 0.233 | 0.000 | |||
| 4 spectra, HVAAGTQQPYTDGVR | 0.210 | 0.071 | 0.000 | 0.000 | 0.379 | 0.340 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
140 spectra |
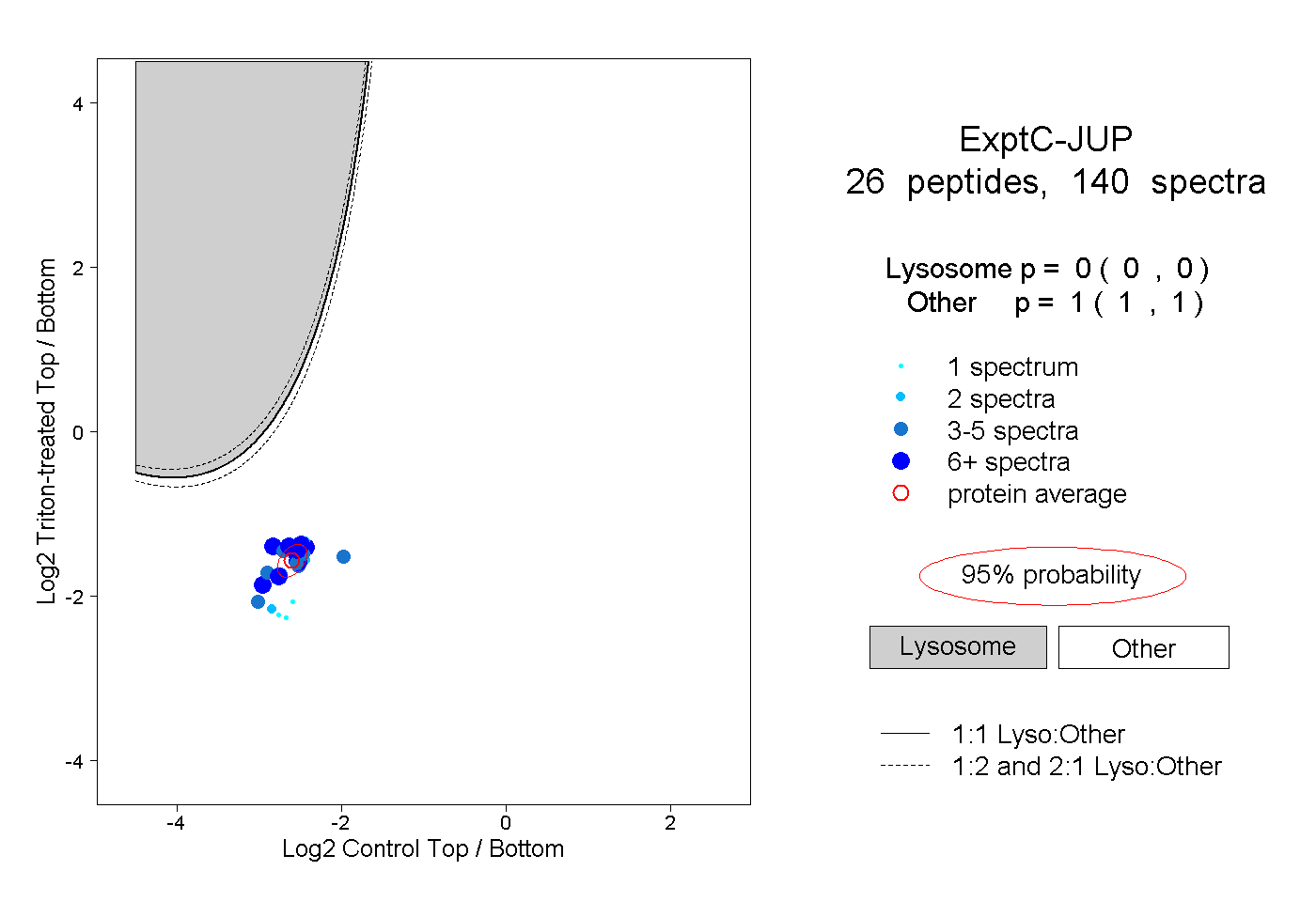 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
15 spectra |
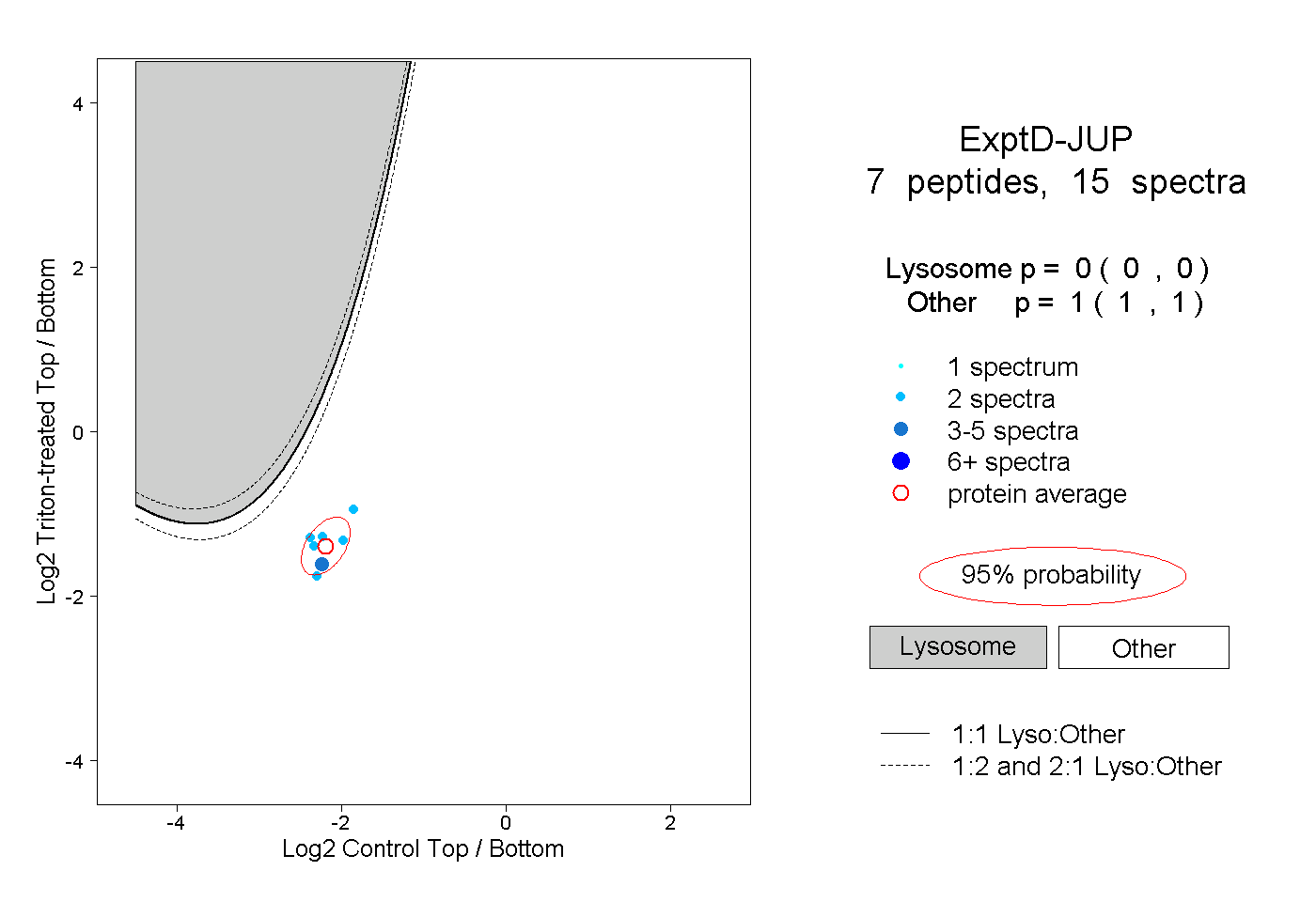 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |