peptides
spectra
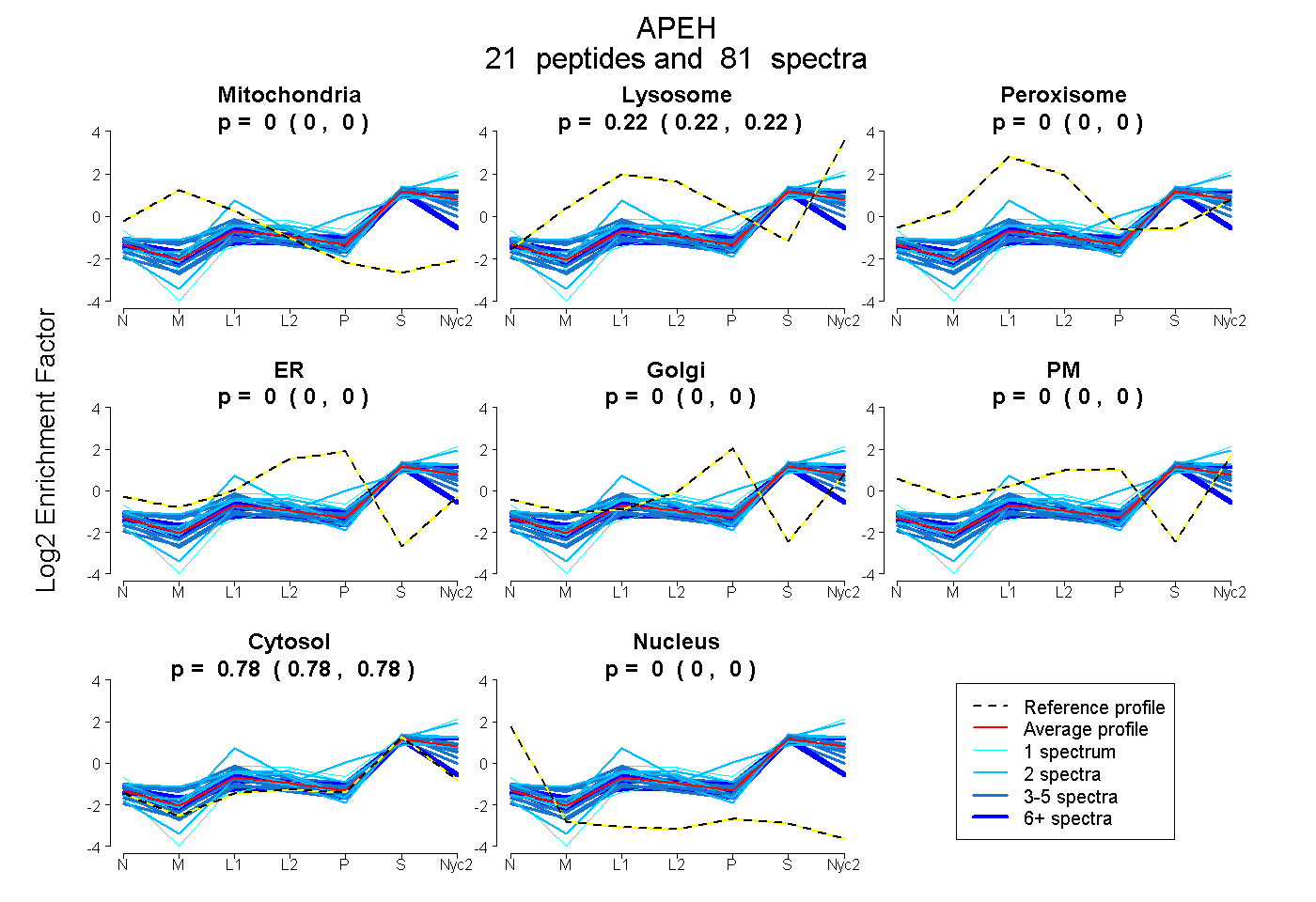
0.000 | 0.000
0.217 | 0.223
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.777 | 0.783
0.000 | 0.000
peptides
spectra
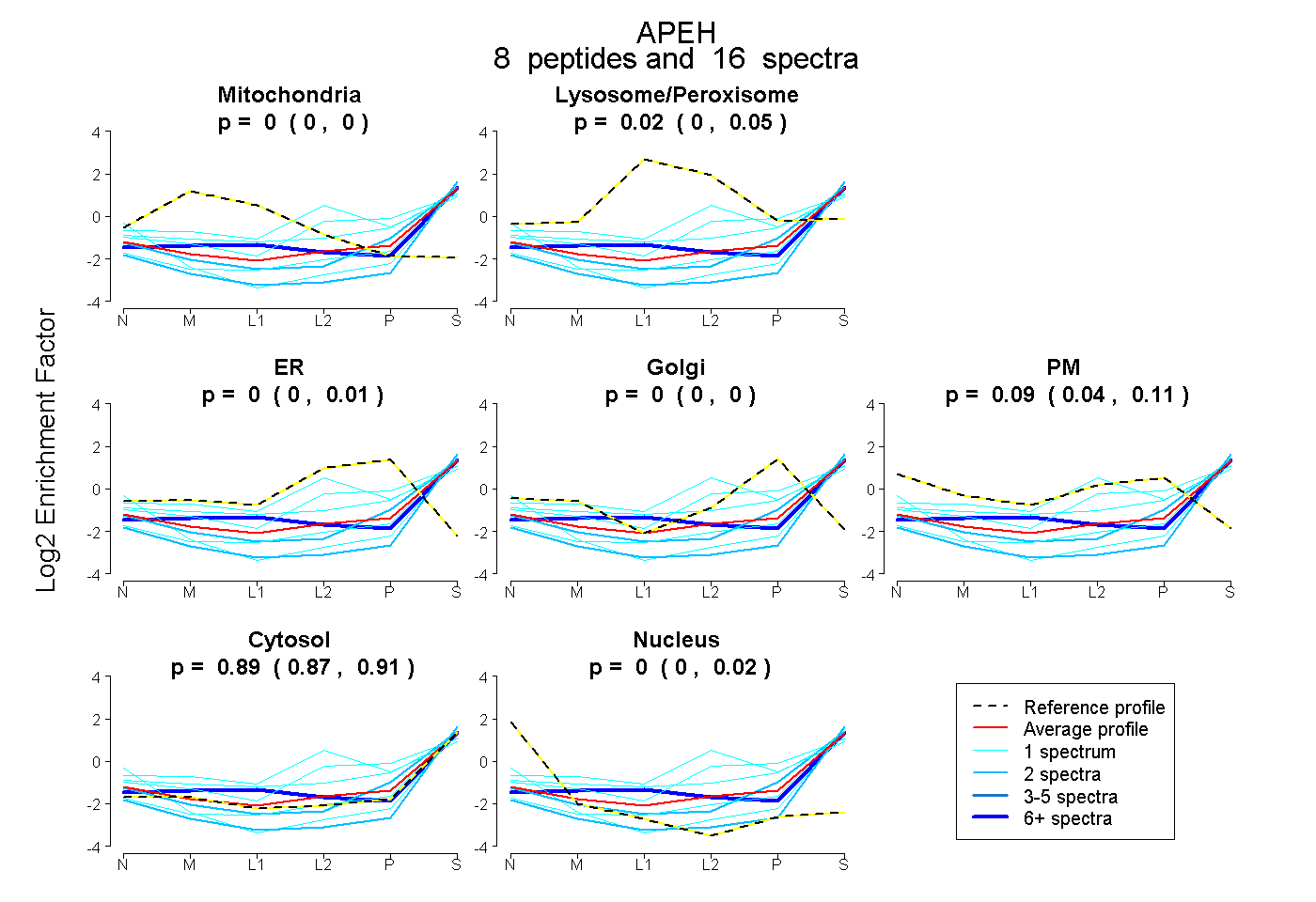
0.000 | 0.000
0.000 | 0.051
0.000 | 0.010
0.000 | 0.001
0.040 | 0.110
0.866 | 0.905
0.000 | 0.017
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
81 spectra |
 |
0.000 0.000 | 0.000 |
0.220 0.217 | 0.223 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.780 0.777 | 0.783 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
16 spectra |
 |
0.000 0.000 | 0.000 |
0.018 0.000 | 0.051 |
0.000 0.000 | 0.010 |
0.000 0.000 | 0.001 |
0.092 0.040 | 0.110 |
0.890 0.866 | 0.905 |
0.000 0.000 | 0.017 |
| 2 spectra, LSPDQCR | 0.000 | 0.000 | 0.000 | 0.080 | 0.000 | 0.903 | 0.018 | |||
| 1 spectrum, QFLEVWEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 1 spectrum, TPVLLMLGQEDR | 0.000 | 0.304 | 0.180 | 0.000 | 0.029 | 0.487 | 0.000 | |||
| 7 spectra, DVQFAVEQVLQEEHFDAR | 0.016 | 0.122 | 0.000 | 0.000 | 0.000 | 0.862 | 0.000 | |||
| 1 spectrum, GELLSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.763 | 0.237 | |||
| 2 spectra, VTSVVVDIVPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.943 | 0.057 | |||
| 1 spectrum, VVFDSAQR | 0.000 | 0.217 | 0.000 | 0.155 | 0.000 | 0.627 | 0.000 | |||
| 1 spectrum, TVHTEWTQR | 0.000 | 0.075 | 0.310 | 0.000 | 0.000 | 0.615 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
104 spectra |
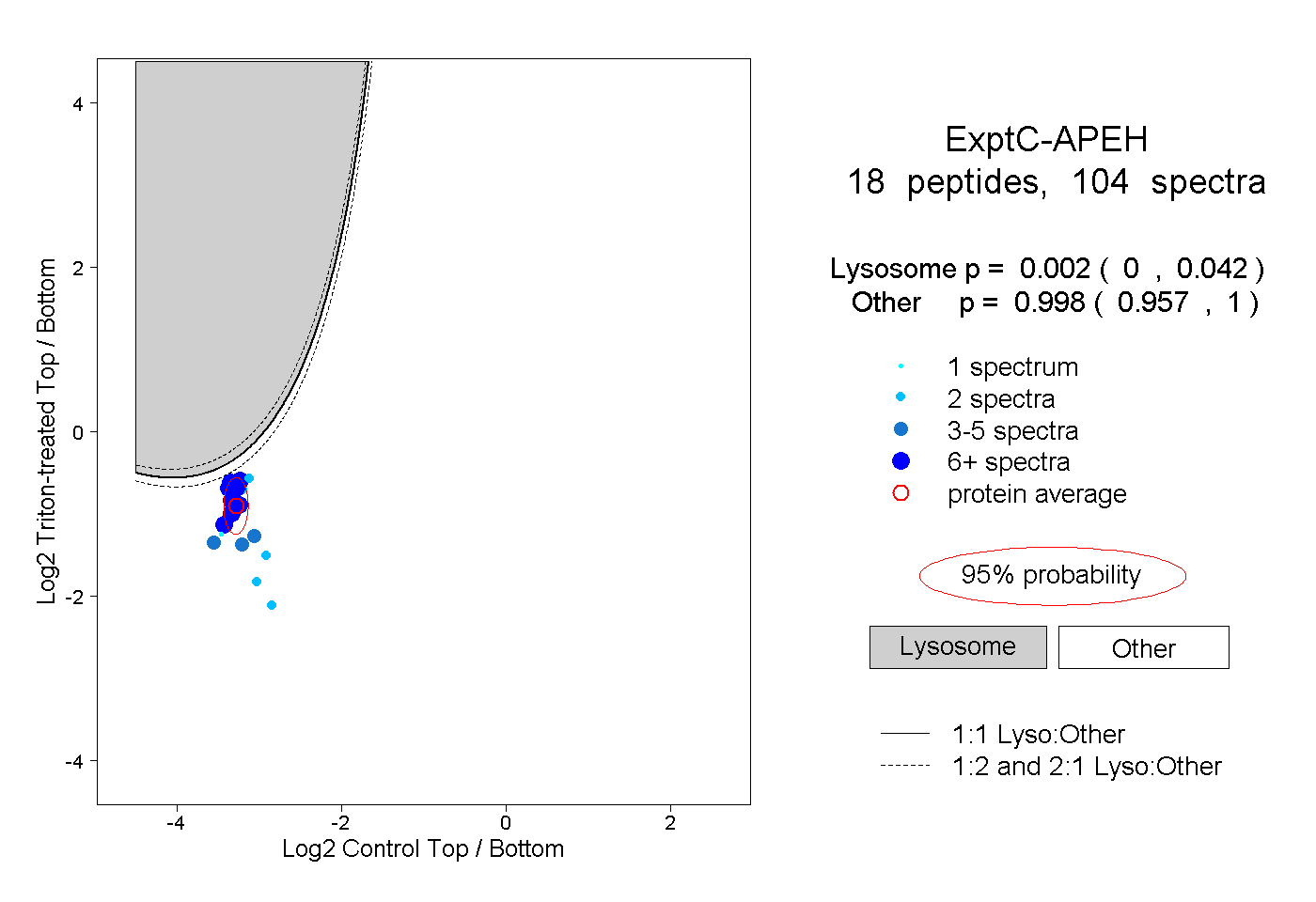 |
0.002 0.000 | 0.042 |
0.998 0.957 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
11 spectra |
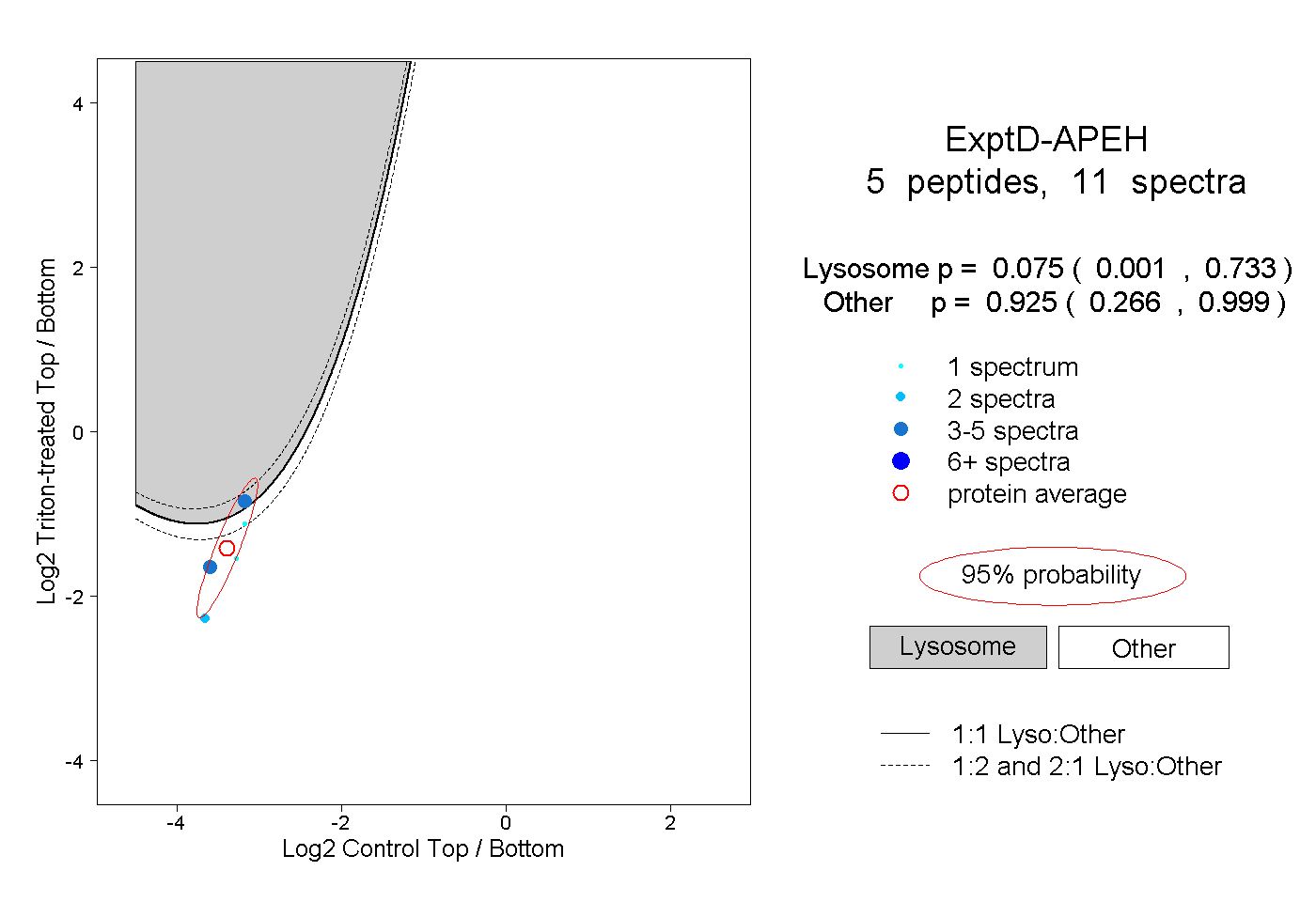 |
0.075 0.001 | 0.733 |
0.925 0.266 | 0.999 |