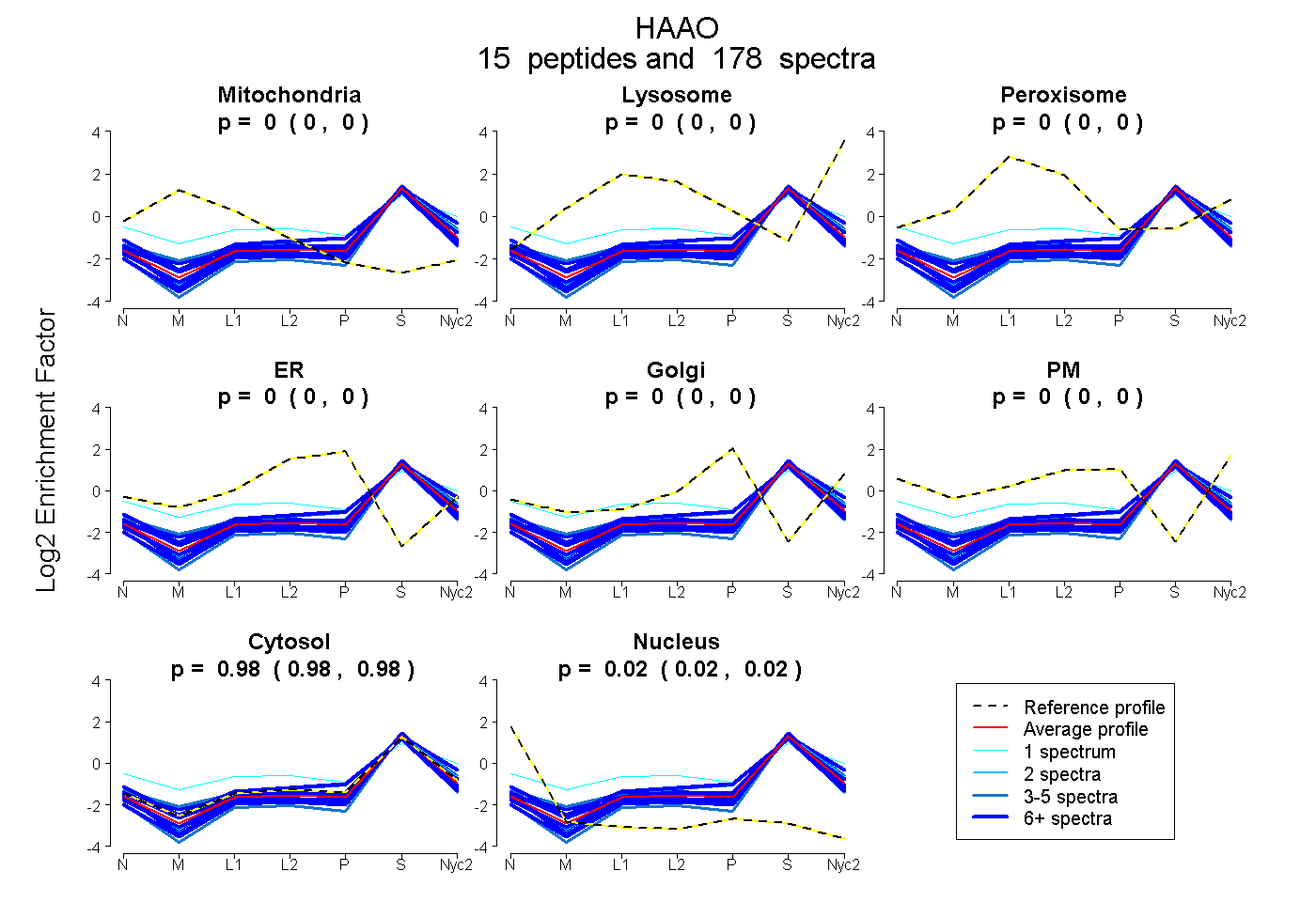
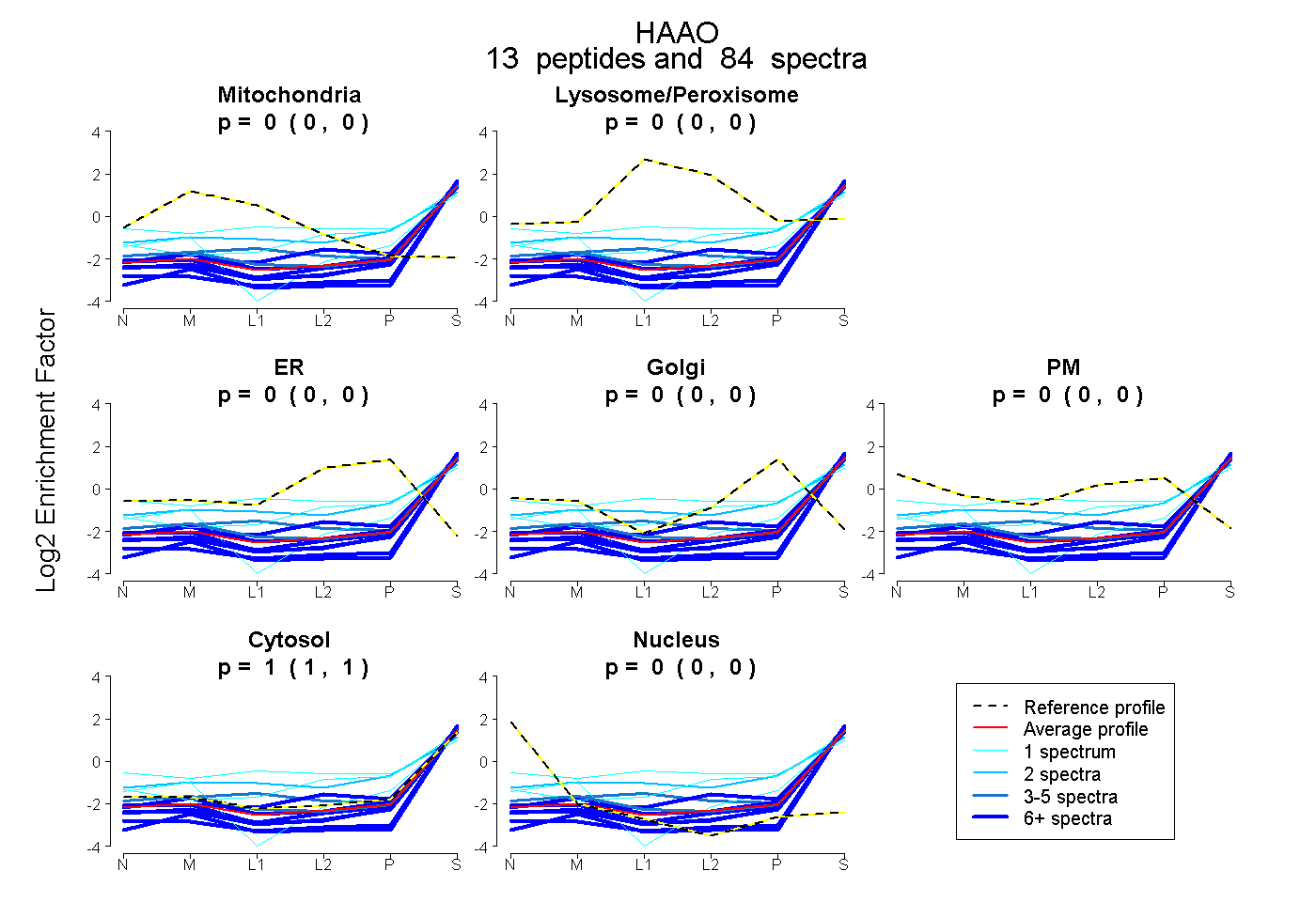
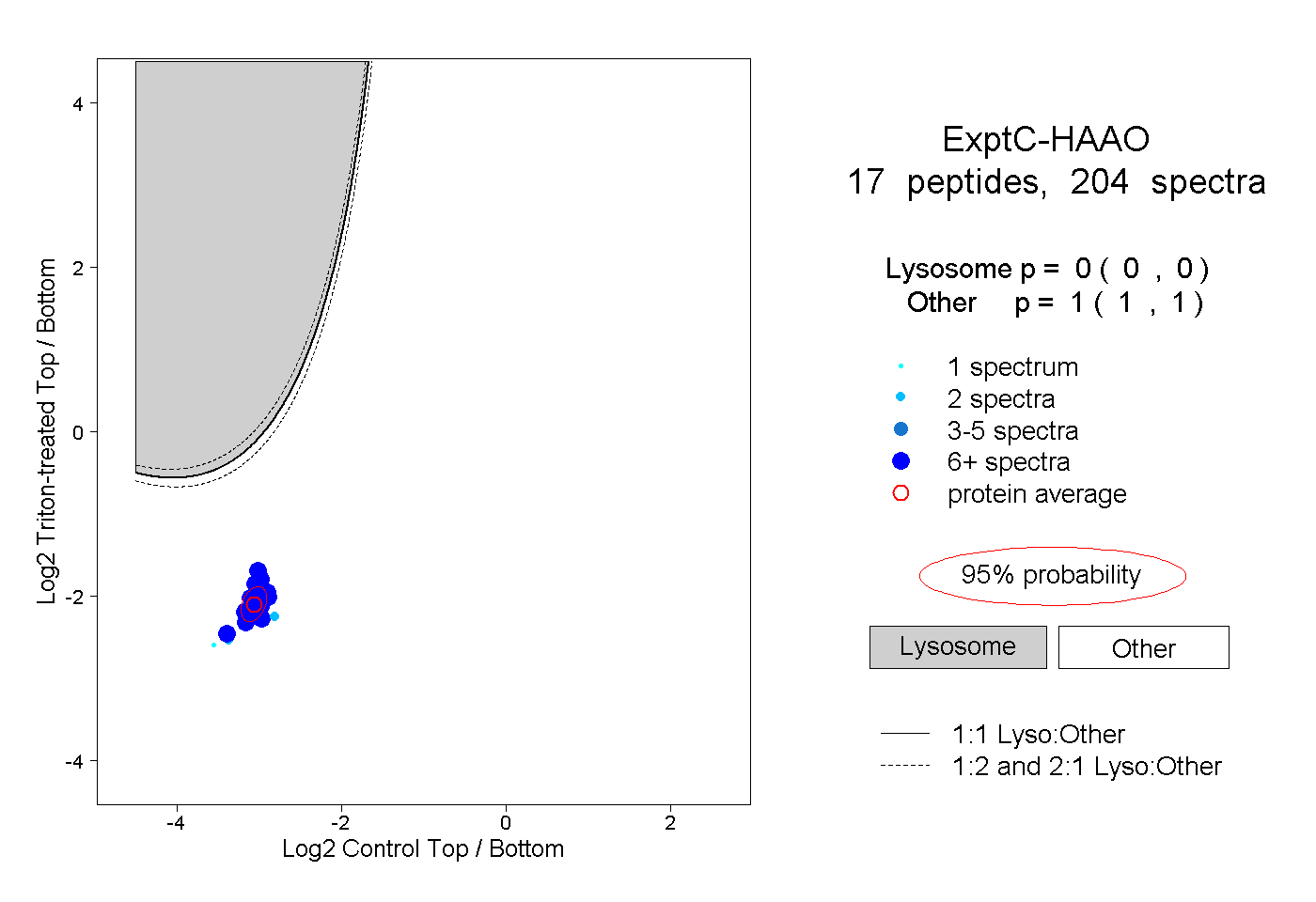
| 2 spectra, DLGTQLAPIIQEFFHSEQYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 25 spectra, LMHQEQLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, TGKPNPDQLLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, QGEIFLLPAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 16 spectra, SVMEPMSLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, METELDGLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, VLEQGEHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 18 spectra, SWVEENR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, ASFQPPVCNK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, AQGSVALSVTQDPACK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YYVGDTEDVLFEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, AWLESHSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, EPPFPLSTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, QDVDVWLWQLEGSSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, VPHSPQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 26 spectra, IMFVGGPNTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, FANTMGLVIER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |