peptides
spectra
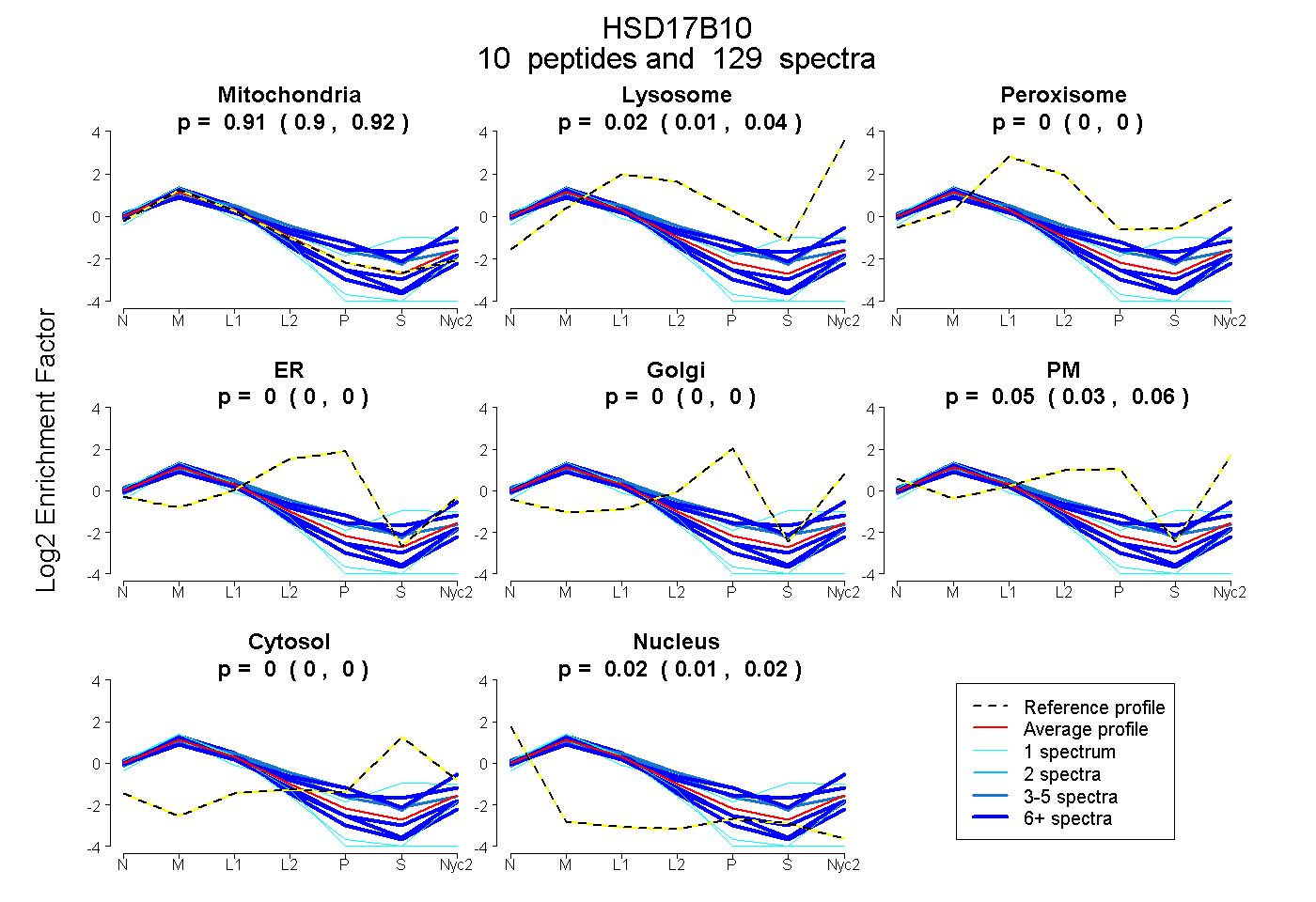
0.901 | 0.917
0.009 | 0.036
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.032 | 0.063
0.000 | 0.000
0.011 | 0.023
peptides
spectra
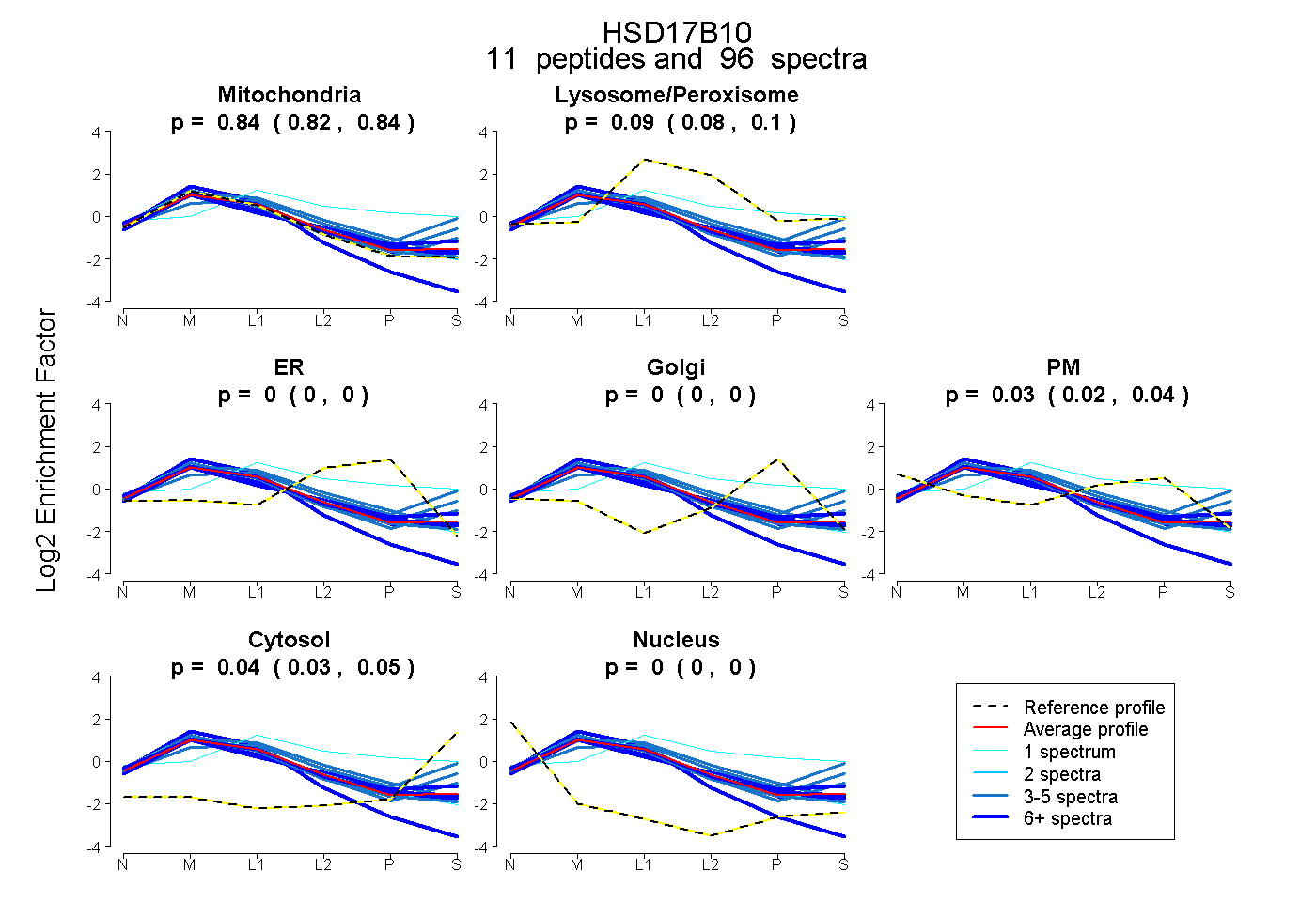
0.824 | 0.845
0.084 | 0.100
0.000 | 0.000
0.000 | 0.000
0.019 | 0.039
0.033 | 0.049
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
129 spectra |
 |
0.910 0.901 | 0.917 |
0.023 0.009 | 0.036 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.050 0.032 | 0.063 |
0.000 0.000 | 0.000 |
0.018 0.011 | 0.023 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
96 spectra |
 |
0.836 0.824 | 0.845 |
0.092 0.084 | 0.100 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.031 0.019 | 0.039 |
0.042 0.033 | 0.049 |
0.000 0.000 | 0.000 |
| 10 spectra, GGIVGMTLPIAR | 0.859 | 0.019 | 0.000 | 0.000 | 0.098 | 0.024 | 0.000 | |||
| 1 spectrum, LVGQGATAVLLDVPNSEGETEAK | 0.873 | 0.018 | 0.000 | 0.000 | 0.109 | 0.000 | 0.000 | |||
| 1 spectrum, GVIINTASVAAFEGQVGQAAYSASK | 0.053 | 0.637 | 0.000 | 0.196 | 0.014 | 0.101 | 0.000 | |||
| 18 spectra, DLAPIGIR | 0.962 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.038 | |||
| 3 spectra, IDVAVNCAGIAVAIK | 0.780 | 0.115 | 0.000 | 0.000 | 0.000 | 0.104 | 0.000 | |||
| 3 spectra, LGGNCIFAPANVTSEK | 0.457 | 0.333 | 0.000 | 0.000 | 0.000 | 0.210 | 0.000 | |||
| 17 spectra, NQVHTLEDFQR | 0.829 | 0.064 | 0.000 | 0.000 | 0.088 | 0.019 | 0.000 | |||
| 4 spectra, GLVAVITGGASGLGLSTAK | 0.678 | 0.151 | 0.000 | 0.000 | 0.000 | 0.170 | 0.000 | |||
| 4 spectra, NFLASQVPFPSR | 0.951 | 0.000 | 0.000 | 0.019 | 0.030 | 0.000 | 0.000 | |||
| 30 spectra, LVAGVMGQNEPDQGGQR | 0.715 | 0.117 | 0.000 | 0.074 | 0.000 | 0.094 | 0.000 | |||
| 5 spectra, EVQAALTLAK | 0.730 | 0.147 | 0.123 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
363 spectra |
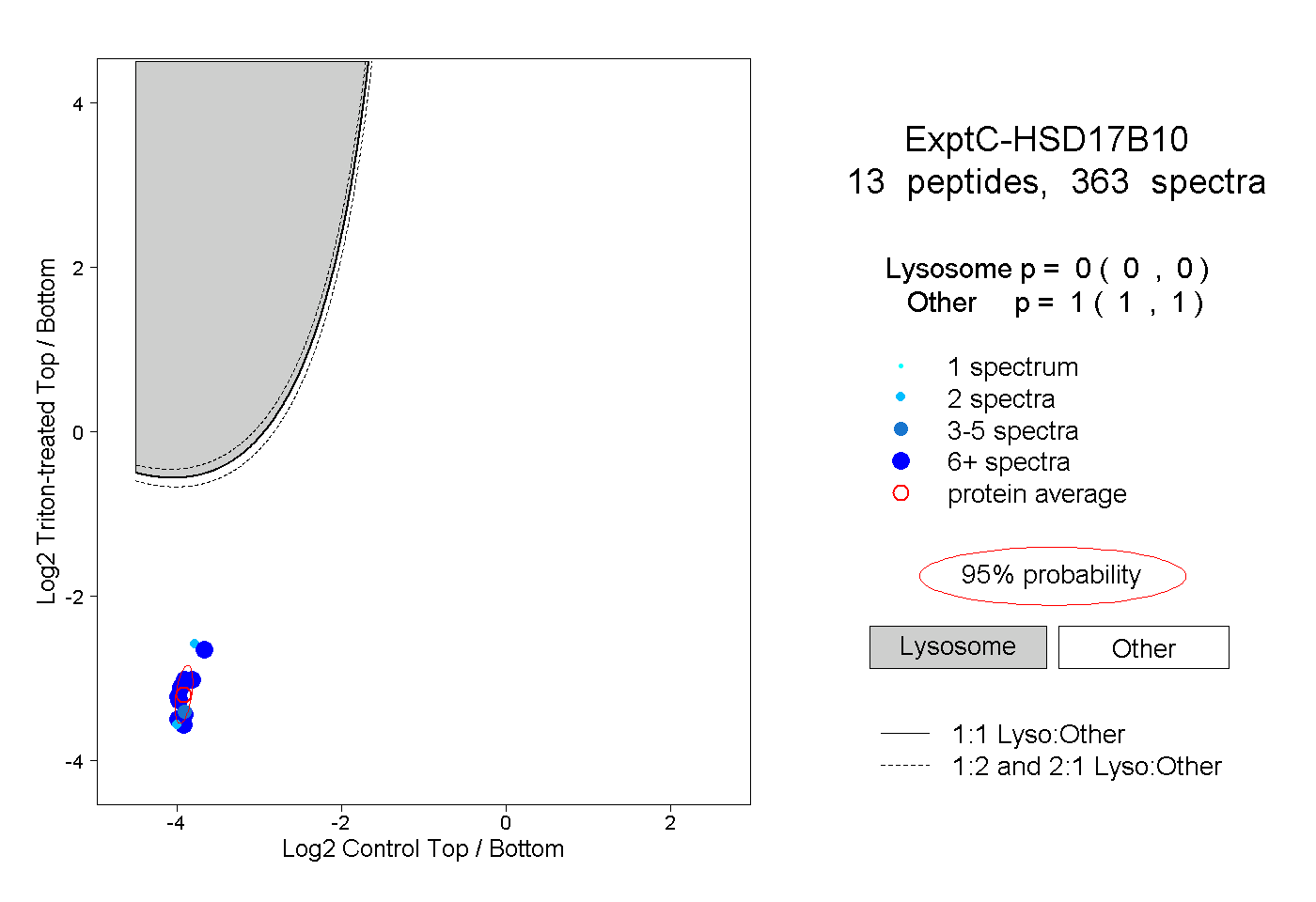 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
19 spectra |
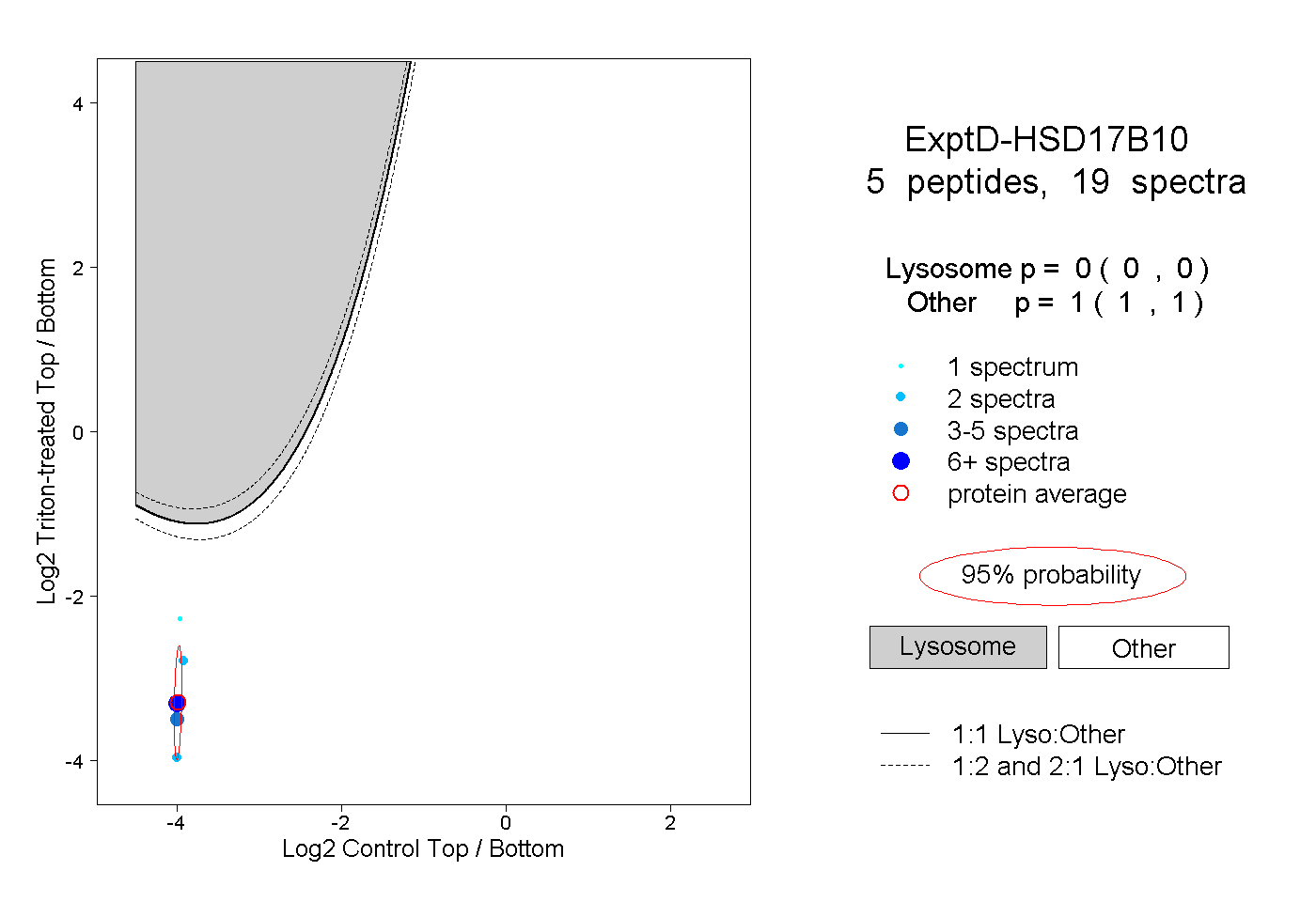 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |