peptides
spectra
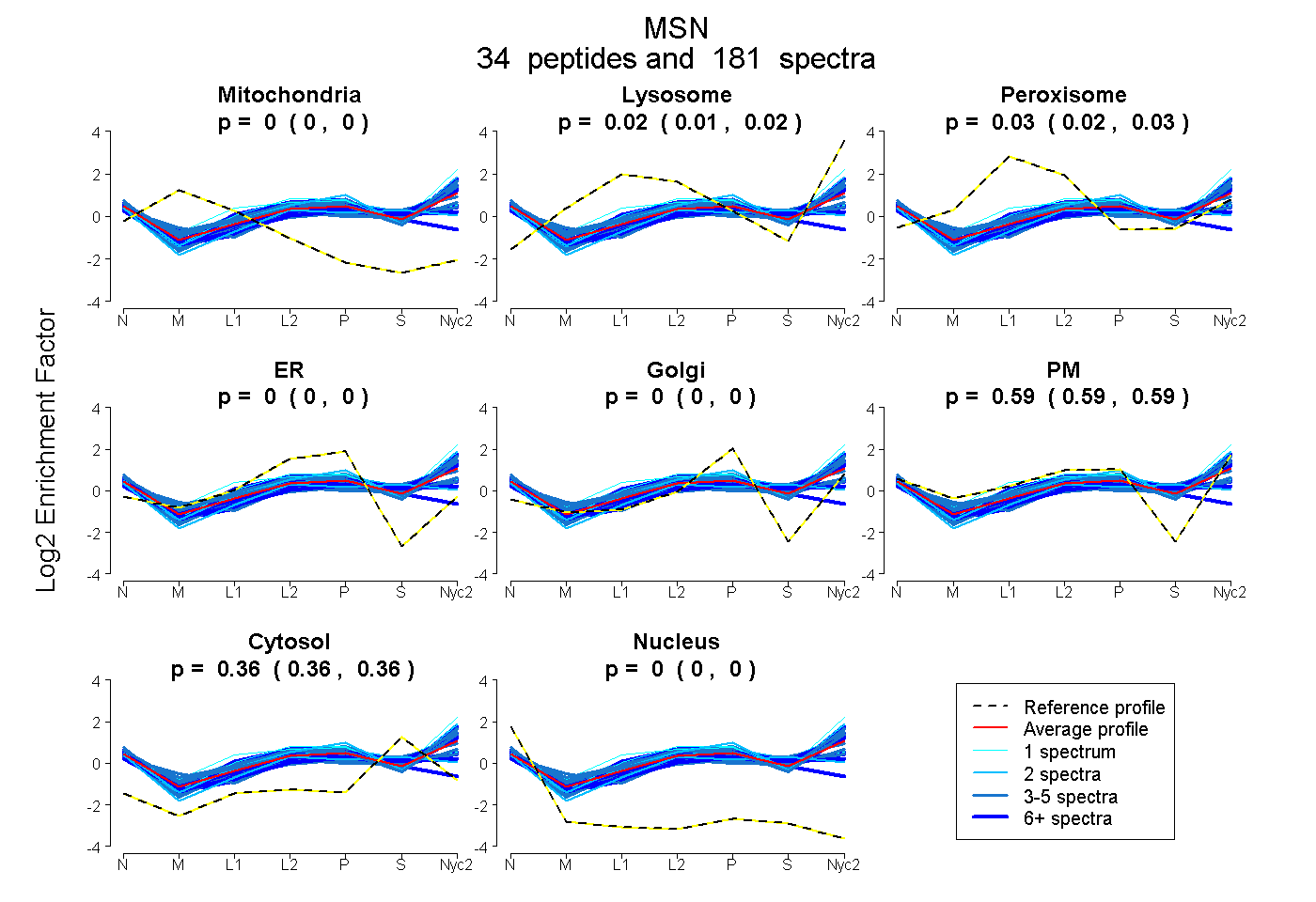
0.000 | 0.000
0.015 | 0.023
0.024 | 0.030
0.000 | 0.000
0.000 | 0.000
0.588 | 0.591
0.363 | 0.364
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
181 spectra |
 |
0.000 0.000 | 0.000 |
0.019 0.015 | 0.023 |
0.027 0.024 | 0.030 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.590 0.588 | 0.591 |
0.364 0.363 | 0.364 |
0.000 0.000 | 0.000 |
| 1 spectrum, TQEQLASEMAELTAR | 0.000 | 0.143 | 0.000 | 0.000 | 0.000 | 0.603 | 0.253 | 0.000 | ||
| 14 spectra, VLEQHK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.510 | 0.490 | 0.000 | ||
| 5 spectra, APDFVFYAPR | 0.000 | 0.000 | 0.034 | 0.000 | 0.000 | 0.517 | 0.449 | 0.000 | ||
| 2 spectra, AFSTWLK | 0.000 | 0.166 | 0.000 | 0.000 | 0.000 | 0.580 | 0.254 | 0.000 | ||
| 2 spectra, IAQDLEMYGVNYFSIK | 0.000 | 0.125 | 0.000 | 0.000 | 0.000 | 0.477 | 0.398 | 0.000 | ||
| 6 spectra, EDAVLEYLK | 0.000 | 0.104 | 0.000 | 0.000 | 0.000 | 0.574 | 0.322 | 0.000 | ||
| 5 spectra, QLFDQVVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.575 | 0.425 | 0.000 | ||
| 14 spectra, ALELEQER | 0.000 | 0.000 | 0.000 | 0.004 | 0.000 | 0.566 | 0.431 | 0.000 | ||
| 7 spectra, AQMVQEDLEK | 0.000 | 0.129 | 0.000 | 0.000 | 0.000 | 0.607 | 0.265 | 0.000 | ||
| 14 spectra, LFFLQVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.538 | 0.458 | 0.004 | ||
| 1 spectrum, FVIKPIDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.523 | 0.477 | 0.000 | ||
| 2 spectra, VTTMDAELEFAIQPNTTGK | 0.000 | 0.000 | 0.015 | 0.078 | 0.000 | 0.373 | 0.534 | 0.000 | ||
| 7 spectra, AQSEAEK | 0.000 | 0.077 | 0.006 | 0.000 | 0.000 | 0.598 | 0.319 | 0.000 | ||
| 17 spectra, IGFPWSEIR | 0.000 | 0.000 | 0.002 | 0.000 | 0.000 | 0.535 | 0.463 | 0.000 | ||
| 1 spectrum, KPDTIEVQQMK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.551 | 0.449 | 0.000 | ||
| 3 spectra, ESPLLFK | 0.000 | 0.066 | 0.000 | 0.000 | 0.000 | 0.558 | 0.375 | 0.000 | ||
| 14 spectra, ILALCMGNHELYMR | 0.000 | 0.000 | 0.165 | 0.253 | 0.000 | 0.153 | 0.344 | 0.085 | ||
| 4 spectra, YGDFNK | 0.000 | 0.055 | 0.000 | 0.000 | 0.000 | 0.647 | 0.298 | 0.000 | ||
| 4 spectra, ISQLEMAR | 0.000 | 0.128 | 0.000 | 0.000 | 0.000 | 0.613 | 0.260 | 0.000 | ||
| 6 spectra, SGYLAGDK | 0.000 | 0.094 | 0.000 | 0.000 | 0.000 | 0.501 | 0.405 | 0.000 | ||
| 3 spectra, ALLENEK | 0.000 | 0.044 | 0.012 | 0.000 | 0.000 | 0.632 | 0.311 | 0.000 | ||
| 4 spectra, EALLQASR | 0.000 | 0.064 | 0.000 | 0.000 | 0.000 | 0.643 | 0.293 | 0.000 | ||
| 4 spectra, NISFNDK | 0.012 | 0.000 | 0.019 | 0.000 | 0.000 | 0.524 | 0.445 | 0.000 | ||
| 2 spectra, ALTSELANAR | 0.000 | 0.067 | 0.000 | 0.000 | 0.000 | 0.636 | 0.297 | 0.000 | ||
| 6 spectra, ESEAEEWQQK | 0.000 | 0.037 | 0.024 | 0.000 | 0.000 | 0.612 | 0.327 | 0.000 | ||
| 3 spectra, IQVWHEEHR | 0.000 | 0.152 | 0.000 | 0.000 | 0.000 | 0.558 | 0.290 | 0.000 | ||
| 3 spectra, EVWFFGLQYQDTK | 0.000 | 0.069 | 0.000 | 0.000 | 0.000 | 0.597 | 0.334 | 0.000 | ||
| 5 spectra, DQWEER | 0.000 | 0.101 | 0.015 | 0.000 | 0.000 | 0.568 | 0.316 | 0.000 | ||
| 3 spectra, QIEEQTK | 0.000 | 0.022 | 0.000 | 0.000 | 0.000 | 0.496 | 0.482 | 0.000 | ||
| 4 spectra, TTNDMIHAENMR | 0.000 | 0.169 | 0.000 | 0.000 | 0.000 | 0.545 | 0.286 | 0.000 | ||
| 1 spectrum, QEAEEAK | 0.000 | 0.298 | 0.000 | 0.000 | 0.000 | 0.488 | 0.215 | 0.000 | ||
| 3 spectra, AQQELEEQTR | 0.000 | 0.122 | 0.000 | 0.000 | 0.000 | 0.504 | 0.374 | 0.000 | ||
| 9 spectra, ADAMAK | 0.000 | 0.126 | 0.021 | 0.000 | 0.000 | 0.500 | 0.353 | 0.000 | ||
| 2 spectra, VTAQDVR | 0.000 | 0.038 | 0.000 | 0.000 | 0.000 | 0.660 | 0.302 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
52 spectra |
 |
0.000 0.000 | 0.000 |
0.062 0.057 | 0.066 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.647 0.642 | 0.650 |
0.291 0.289 | 0.294 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
312 spectra |
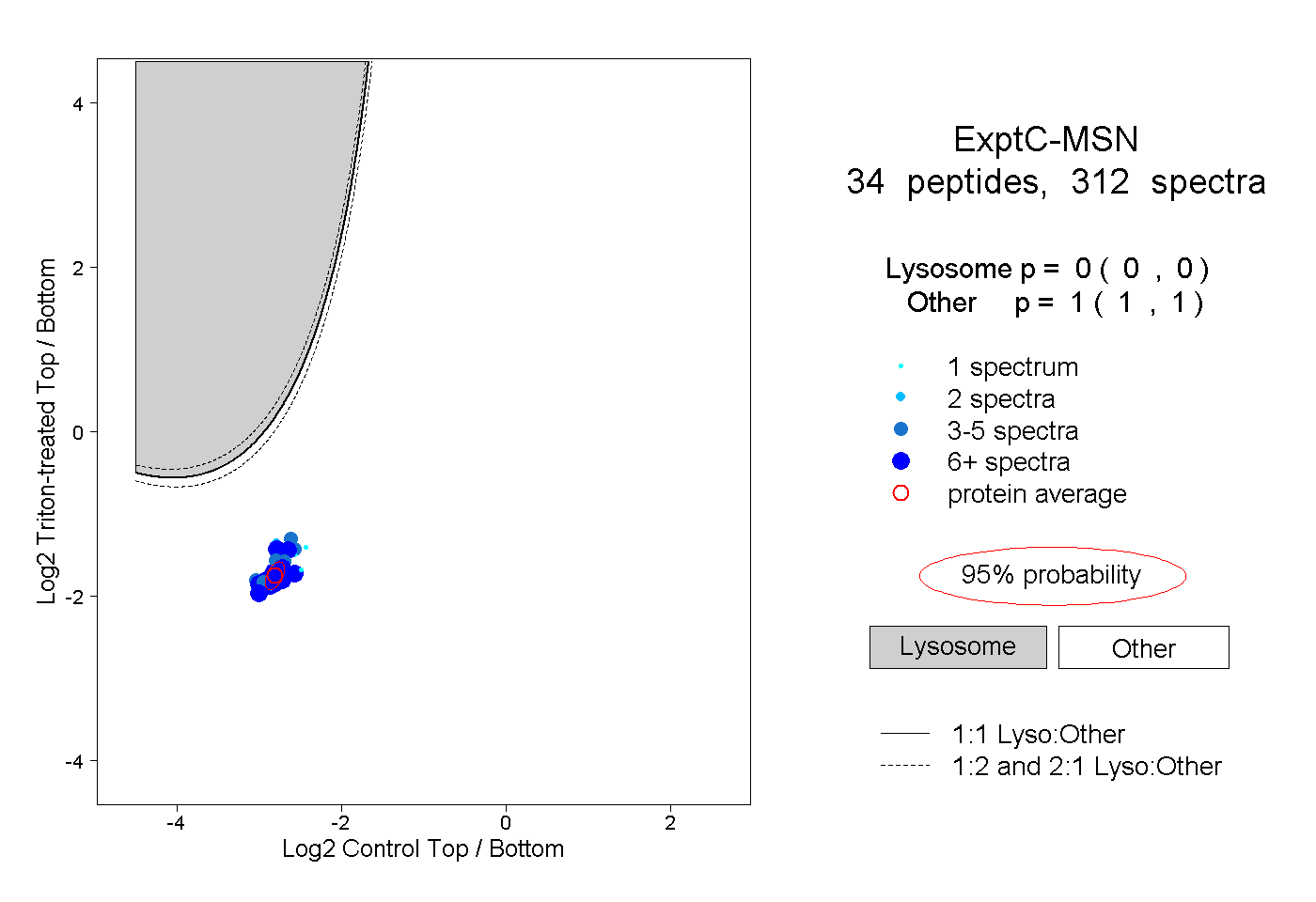 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
21 spectra |
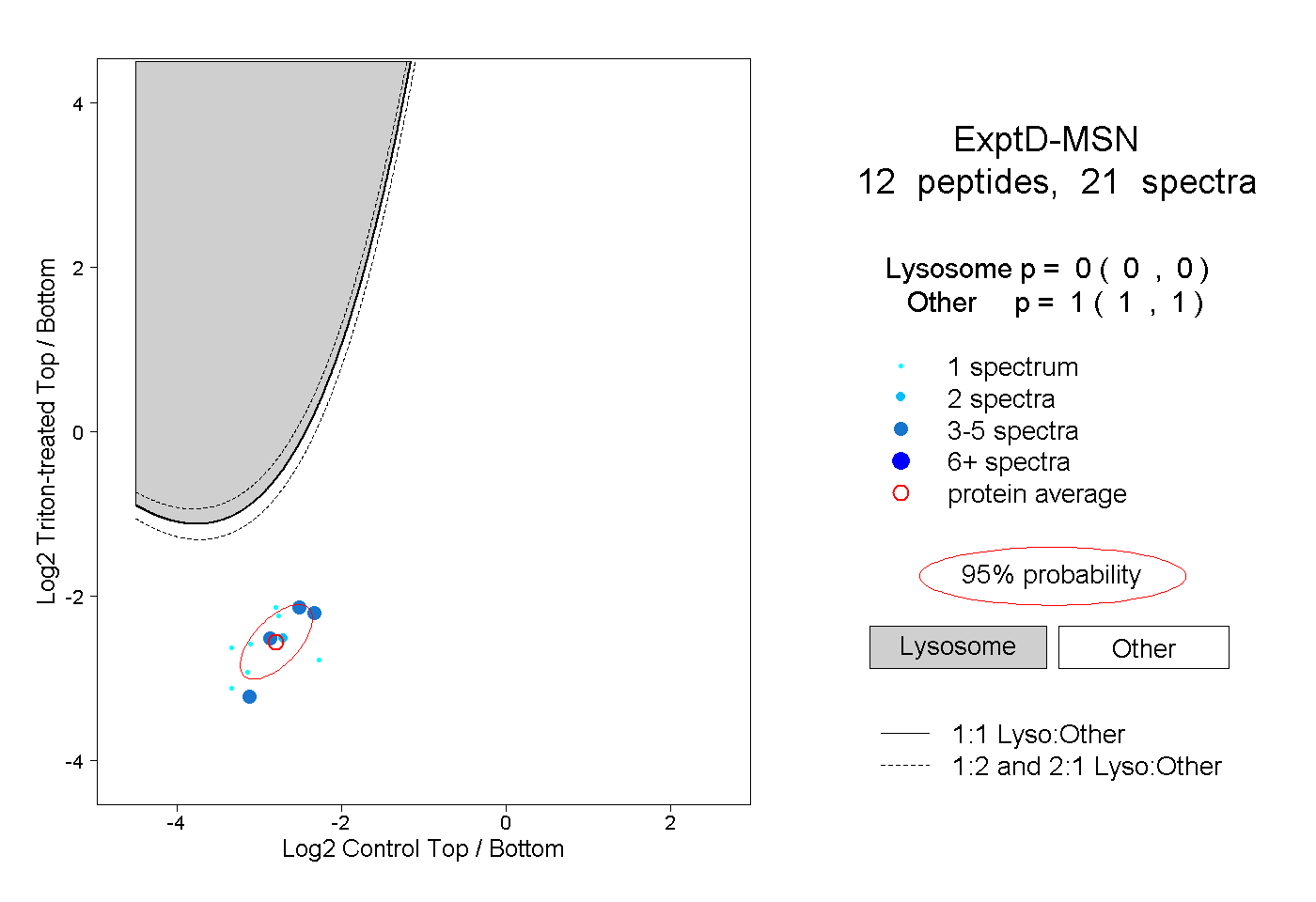 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |