peptides
spectra
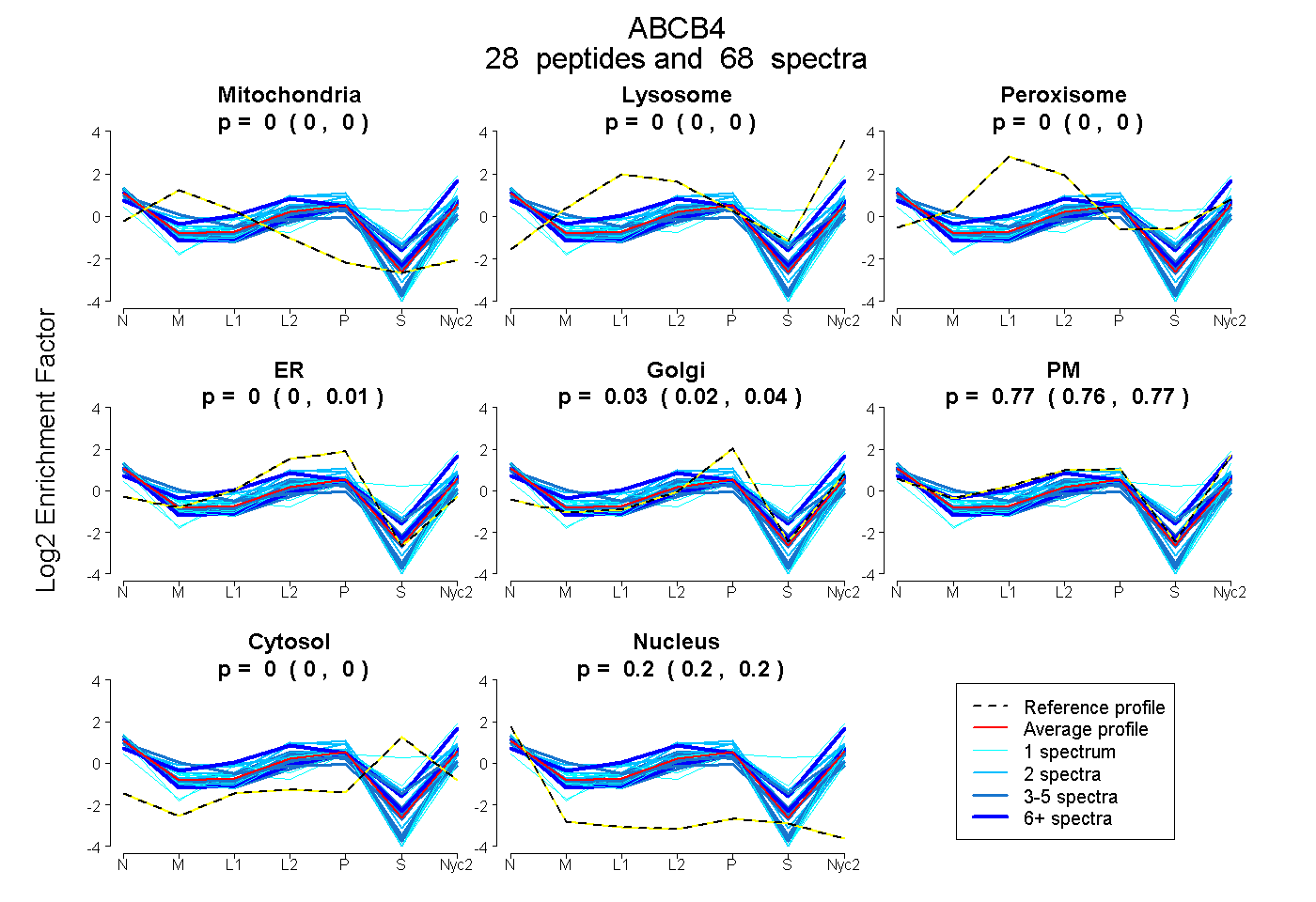
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.007
0.023 | 0.035
0.760 | 0.772
0.000 | 0.000
0.200 | 0.203
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
68 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.007 |
0.031 0.023 | 0.035 |
0.767 0.760 | 0.772 |
0.000 0.000 | 0.000 |
0.202 0.200 | 0.203 |
| 1 spectrum, TVIAFGGQNK | 0.000 | 0.000 | 0.000 | 0.000 | 0.059 | 0.723 | 0.000 | 0.218 | ||
| 4 spectra, LATDAAQVQGATGTR | 0.000 | 0.000 | 0.000 | 0.042 | 0.176 | 0.481 | 0.030 | 0.270 | ||
| 1 spectrum, GAAYVIFDIIDNNPK | 0.000 | 0.000 | 0.000 | 0.116 | 0.102 | 0.513 | 0.000 | 0.269 | ||
| 1 spectrum, MLAGNAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.772 | 0.106 | 0.122 | ||
| 2 spectra, NSTGALSTR | 0.000 | 0.000 | 0.000 | 0.321 | 0.010 | 0.529 | 0.000 | 0.139 | ||
| 2 spectra, GHKPDSIK | 0.059 | 0.000 | 0.000 | 0.000 | 0.000 | 0.835 | 0.024 | 0.082 | ||
| 2 spectra, AGEILTTR | 0.000 | 0.000 | 0.000 | 0.011 | 0.000 | 0.758 | 0.000 | 0.231 | ||
| 3 spectra, QEMGWFDIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.788 | 0.000 | 0.212 | ||
| 1 spectrum, EANAYDFIMK | 0.000 | 0.000 | 0.000 | 0.000 | 0.046 | 0.420 | 0.534 | 0.000 | ||
| 7 spectra, VVQEALDK | 0.000 | 0.021 | 0.056 | 0.000 | 0.000 | 0.819 | 0.104 | 0.000 | ||
| 1 spectrum, LNVQWLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.847 | 0.000 | 0.153 | ||
| 2 spectra, GAQLSGGQK | 0.000 | 0.000 | 0.000 | 0.270 | 0.019 | 0.516 | 0.000 | 0.195 | ||
| 5 spectra, VVSQDEIVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.697 | 0.153 | 0.151 | ||
| 1 spectrum, EANIHPFIETLPQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.025 | 0.756 | 0.000 | 0.218 | ||
| 2 spectra, EGLYFR | 0.003 | 0.000 | 0.000 | 0.388 | 0.000 | 0.475 | 0.000 | 0.134 | ||
| 1 spectrum, SGQTVALVGNSGCGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.725 | 0.253 | 0.022 | ||
| 6 spectra, STVVQLLER | 0.000 | 0.000 | 0.000 | 0.000 | 0.132 | 0.640 | 0.000 | 0.227 | ||
| 4 spectra, AGAVAEEALGAIR | 0.000 | 0.000 | 0.000 | 0.022 | 0.000 | 0.757 | 0.000 | 0.221 | ||
| 4 spectra, GTTELNTR | 0.000 | 0.000 | 0.000 | 0.049 | 0.000 | 0.715 | 0.000 | 0.236 | ||
| 1 spectrum, FDTLVGDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.735 | 0.124 | 0.141 | ||
| 3 spectra, GTQLSGGQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.059 | 0.709 | 0.000 | 0.231 | ||
| 2 spectra, ILEEEMTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.765 | 0.182 | 0.052 | ||
| 2 spectra, ANVPVLQGLSLEVK | 0.000 | 0.000 | 0.000 | 0.060 | 0.000 | 0.679 | 0.000 | 0.261 | ||
| 3 spectra, TVVSLTQER | 0.227 | 0.000 | 0.000 | 0.000 | 0.000 | 0.628 | 0.000 | 0.145 | ||
| 2 spectra, TTIVIAHR | 0.095 | 0.000 | 0.024 | 0.000 | 0.000 | 0.721 | 0.160 | 0.000 | ||
| 3 spectra, IDSFSER | 0.000 | 0.000 | 0.000 | 0.039 | 0.000 | 0.788 | 0.000 | 0.173 | ||
| 1 spectrum, VNLIGPLTLFR | 0.000 | 0.000 | 0.000 | 0.053 | 0.000 | 0.726 | 0.000 | 0.221 | ||
| 1 spectrum, LYDPTEGTISIDGQDIR | 0.000 | 0.000 | 0.000 | 0.170 | 0.000 | 0.553 | 0.000 | 0.276 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
13 spectra |
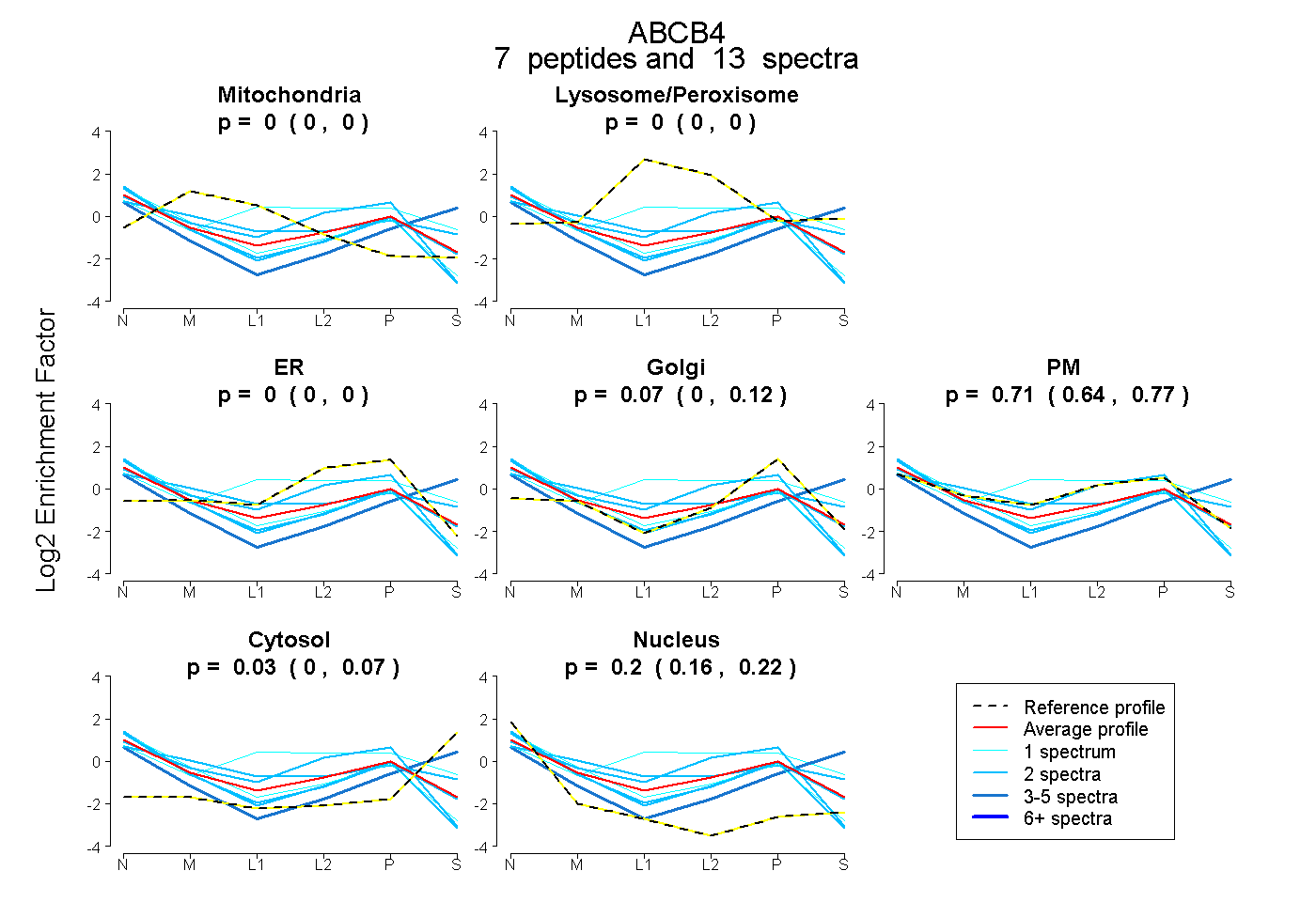 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.067 0.000 | 0.124 |
0.709 0.637 | 0.770 |
0.026 0.000 | 0.071 |
0.198 0.161 | 0.223 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
86 spectra |
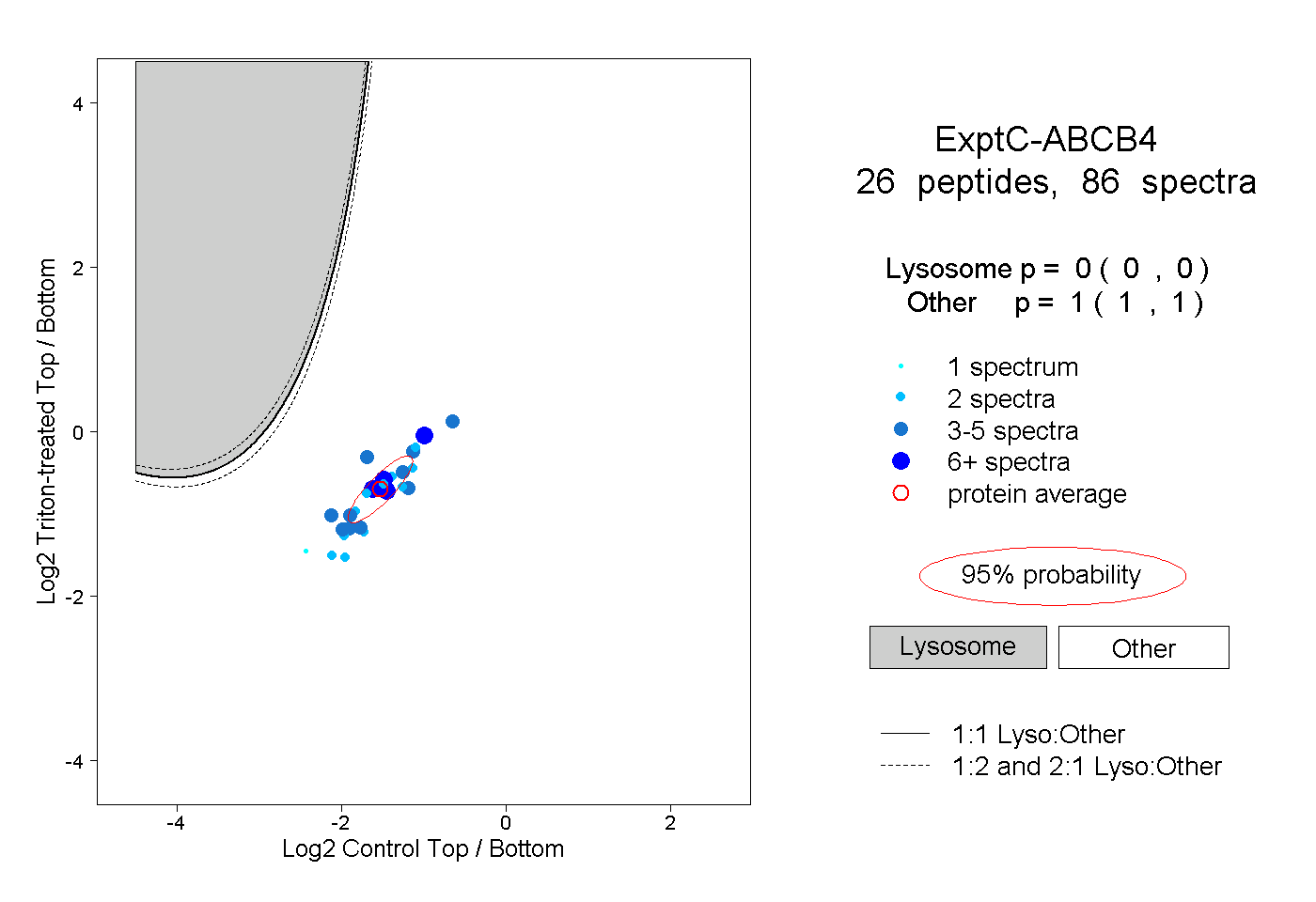 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
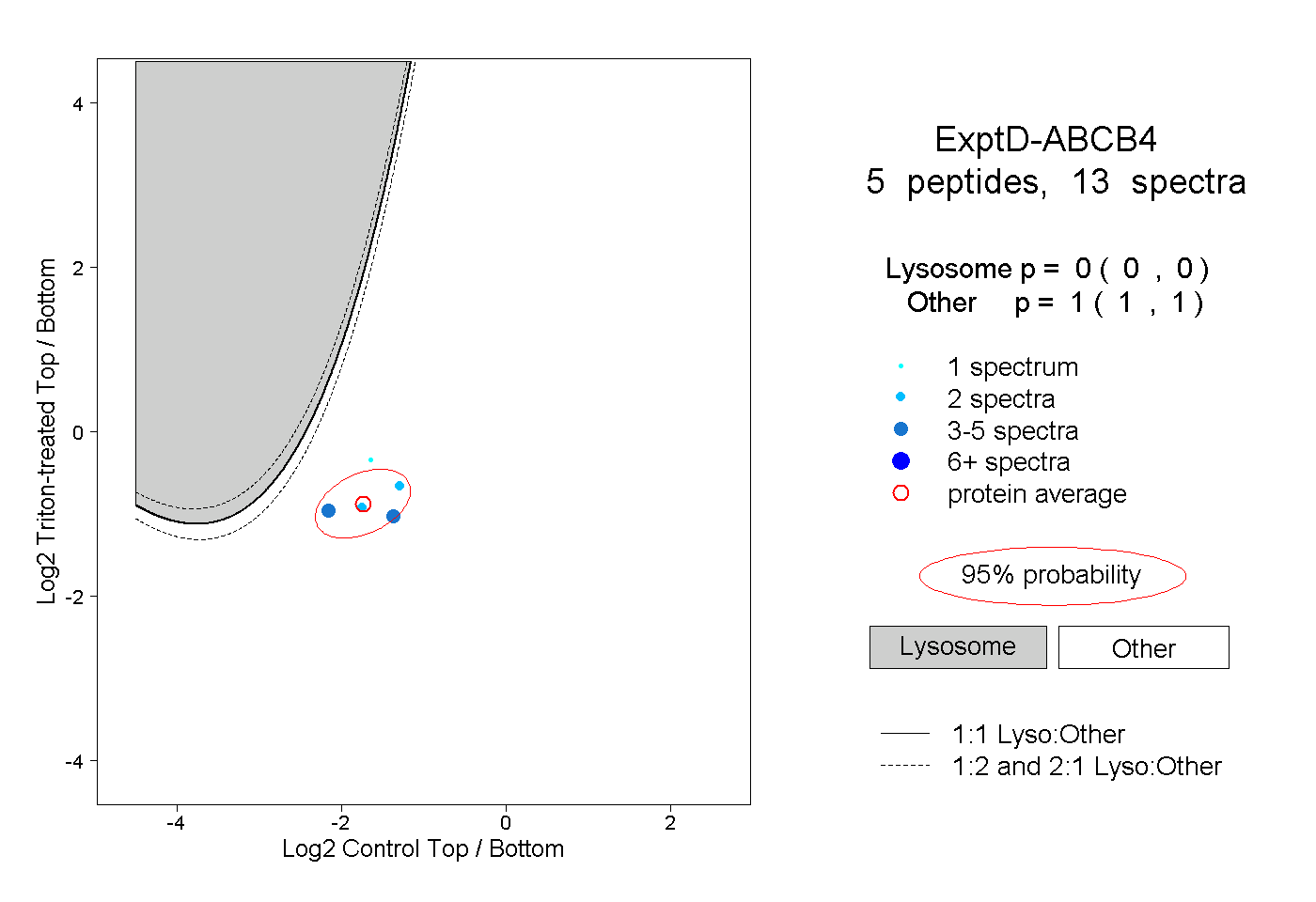 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |