peptides
spectra
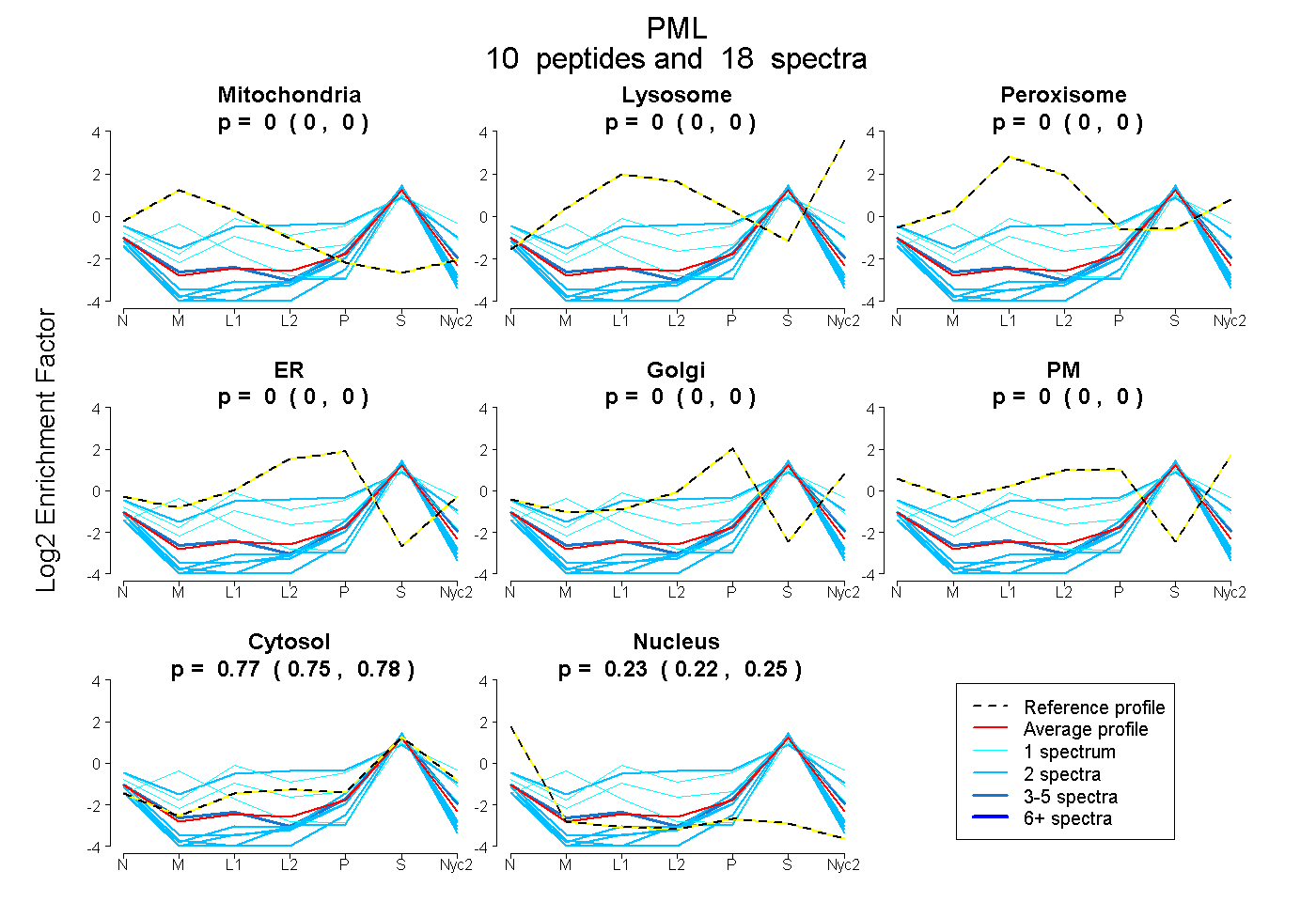
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.750 | 0.780
0.217 | 0.247
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
18 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.766 0.750 | 0.780 |
0.234 0.217 | 0.247 |
| 2 spectra, QIVDAQAACTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.723 | 0.277 | ||
| 1 spectrum, LYASEQEVLDMHGFLR | 0.250 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.679 | 0.071 | ||
| 2 spectra, TPAQTNIYCR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.613 | 0.387 | ||
| 2 spectra, QVIEHVQAQER | 0.000 | 0.000 | 0.160 | 0.157 | 0.000 | 0.000 | 0.668 | 0.015 | ||
| 1 spectrum, IPSASSFK | 0.025 | 0.000 | 0.054 | 0.000 | 0.000 | 0.000 | 0.856 | 0.065 | ||
| 2 spectra, ALDESLAEPHLEDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.615 | 0.385 | ||
| 2 spectra, HEARPLAELR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.677 | 0.323 | ||
| 2 spectra, ELLEAVNVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.639 | 0.361 | ||
| 1 spectrum, TGGALVK | 0.000 | 0.000 | 0.207 | 0.000 | 0.060 | 0.044 | 0.689 | 0.000 | ||
| 3 spectra, EFLDSTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.777 | 0.223 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
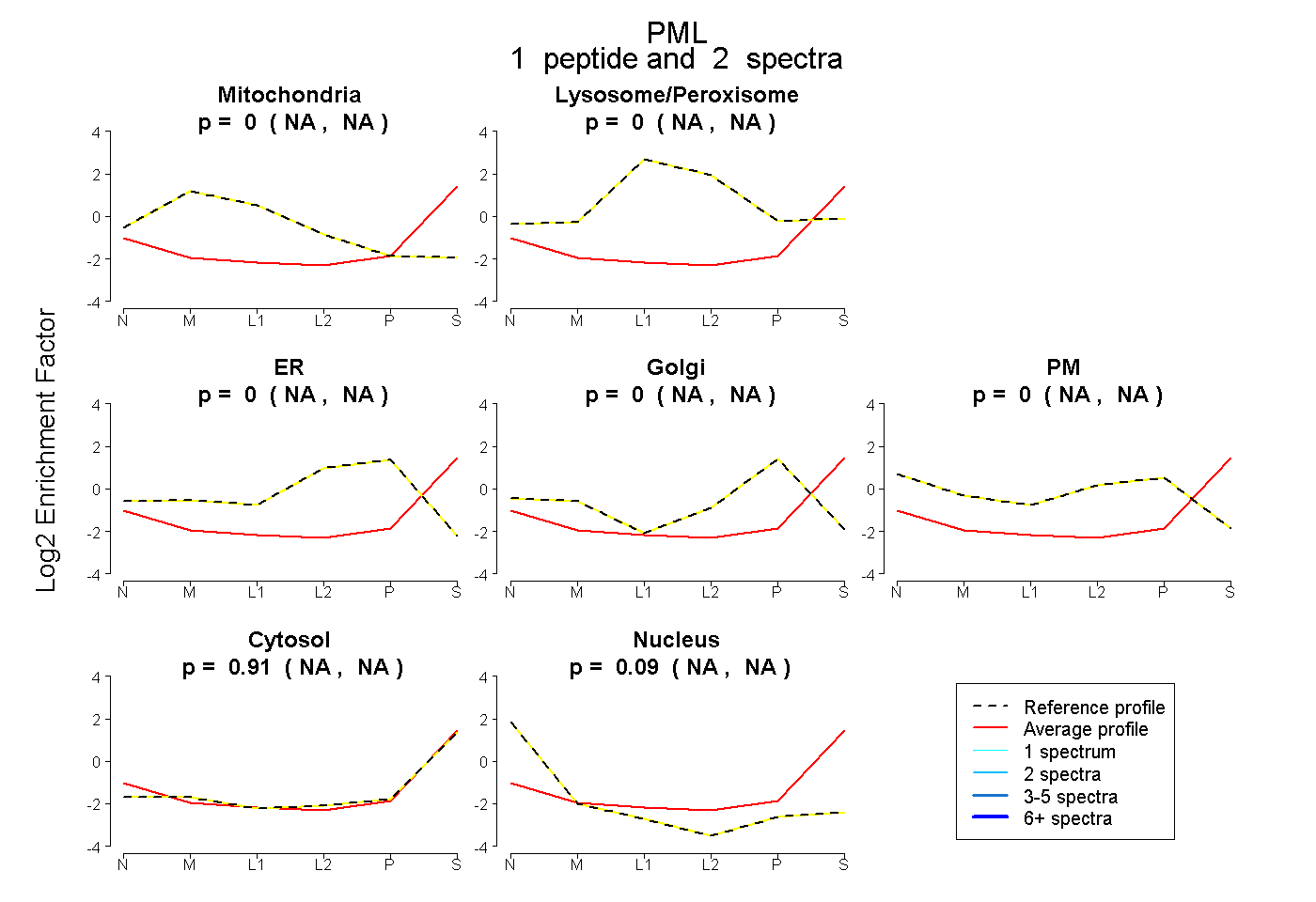 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.910 NA | NA |
0.090 NA | NA |