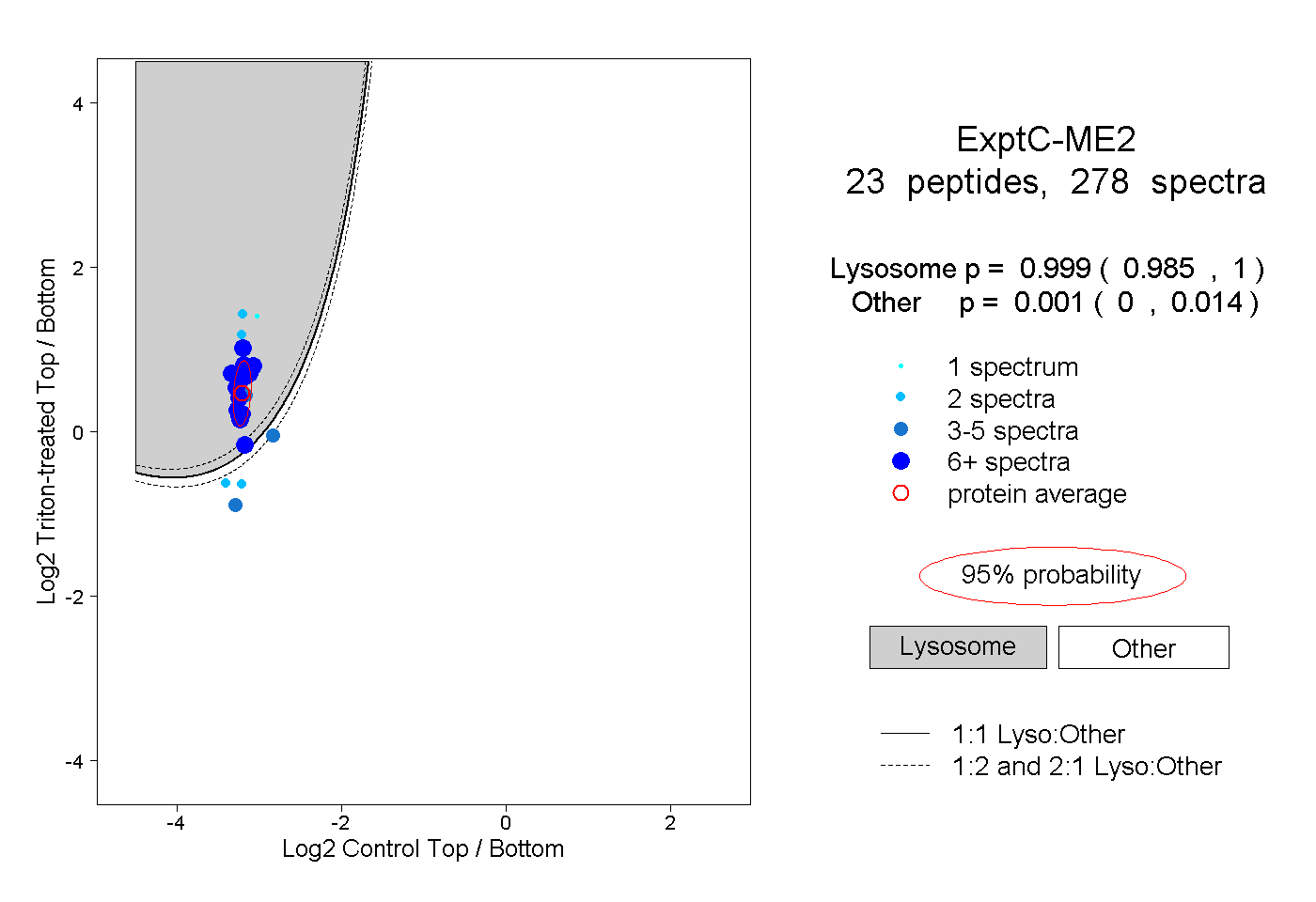
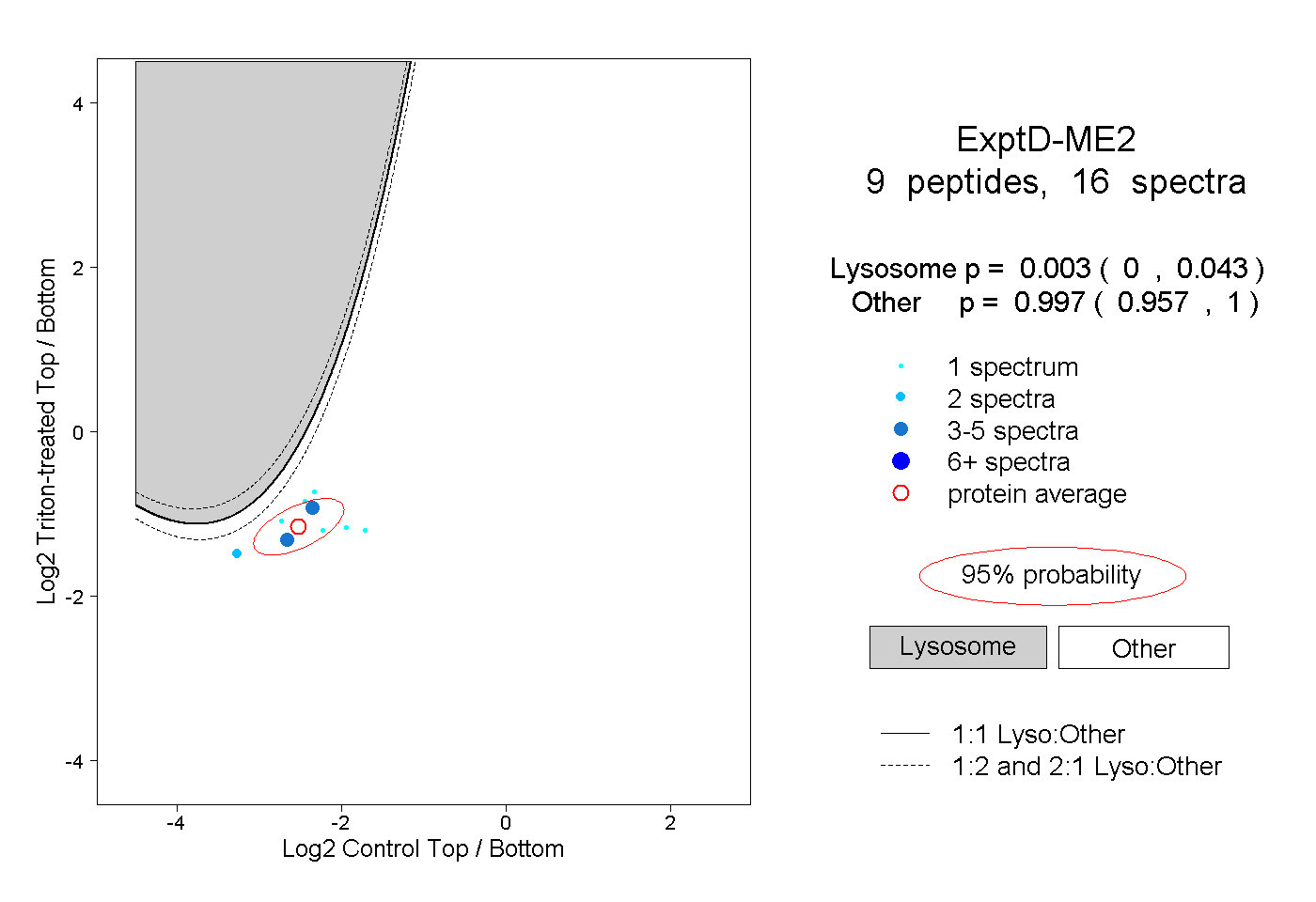
| 10 spectra, GKPLMLNPR |
|
0.988 |
|
|
|
|
|
|
|
0.012 |
| 1 spectrum, LYPSLANIQEVSANIAIK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 8 spectra, DPFYMGLYQK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, HISDTVFLEAAK |
|
0.022 |
|
|
|
|
|
|
|
0.978 |
| 12 spectra, GLFISISDR |
|
0.994 |
|
|
|
|
|
|
|
0.006 |
| 3 spectra, SQLYDDLMDEFMK |
|
0.152 |
|
|
|
|
|
|
|
0.848 |
| 13 spectra, YIYIMGIQER |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, LCLYTACAGIQPEK |
|
0.078 |
|
|
|
|
|
|
|
0.922 |
| 36 spectra, YPEPEDK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 24 spectra, MTSPLEK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, ALTSQLTDEELAQGR |
|
0.999 |
|
|
|
|
|
|
|
0.001 |
| 52 spectra, AVVVTDGER |
|
0.997 |
|
|
|
|
|
|
|
0.003 |
| 18 spectra, GMAFTLQER |
|
0.999 |
|
|
|
|
|
|
|
0.001 |
| 2 spectra, ILGLGDLGVYGMGIPVGK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 3 spectra, GMAFTLEER |
|
0.003 |
|
|
|
|
|
|
|
0.997 |
| 2 spectra, ILFLGAGEAALGIAK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 9 spectra, CLFASGSPFEPVR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 9 spectra, IWMFDK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 10 spectra, NTLIQFEDFGNHNAFR |
|
0.699 |
|
|
|
|
|
|
|
0.301 |
| 25 spectra, IETQDIQALR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 10 spectra, IAEYLYANK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 15 spectra, SIVDNWPENHVK |
|
0.993 |
|
|
|
|
|
|
|
0.007 |
| 8 spectra, NGLLVK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |