peptides
spectra
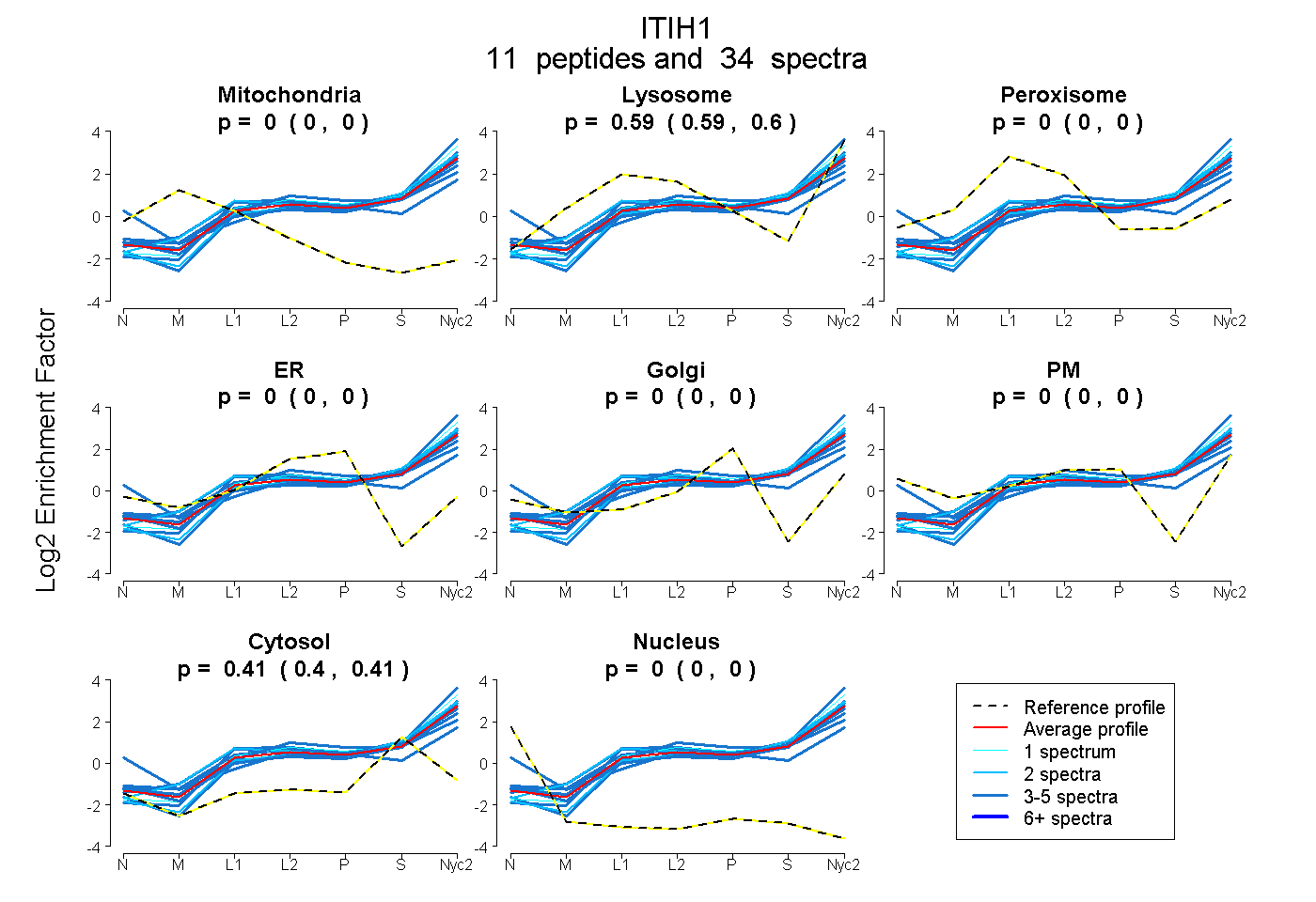
0.000 | 0.000
0.587 | 0.597
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.402 | 0.412
0.000 | 0.000
peptides
spectra
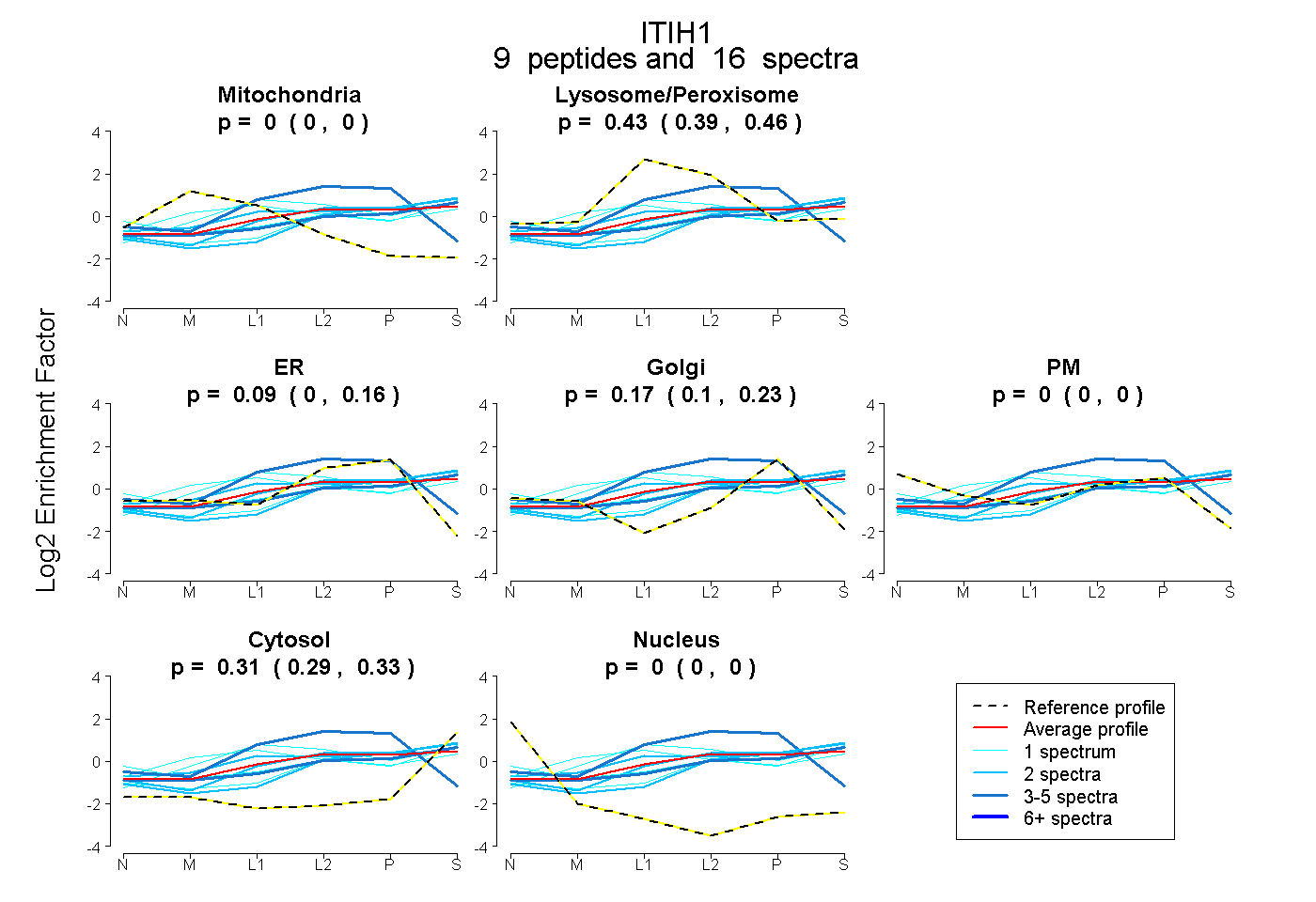
0.000 | 0.000
0.389 | 0.459
0.002 | 0.157
0.100 | 0.232
0.000 | 0.000
0.288 | 0.334
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
34 spectra |
 |
0.000 0.000 | 0.000 |
0.592 0.587 | 0.597 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.408 0.402 | 0.412 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
16 spectra |
 |
0.000 0.000 | 0.000 |
0.427 0.389 | 0.459 |
0.086 0.002 | 0.157 |
0.173 0.100 | 0.232 |
0.000 0.000 | 0.000 |
0.313 0.288 | 0.334 |
0.000 0.000 | 0.000 |
| 1 spectrum, GSLVPASHANLQAAQDFVR | 0.000 | 0.332 | 0.000 | 0.000 | 0.257 | 0.412 | 0.000 | |||
| 1 spectrum, FAHYVITSQVVNSANK | 0.000 | 0.617 | 0.000 | 0.099 | 0.000 | 0.284 | 0.000 | |||
| 3 spectra, QLTVTR | 0.000 | 0.402 | 0.598 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, EVAFDVEIPK | 0.000 | 0.500 | 0.000 | 0.241 | 0.000 | 0.259 | 0.000 | |||
| 1 spectrum, AAISGENAGLVR | 0.000 | 0.209 | 0.308 | 0.000 | 0.000 | 0.483 | 0.000 | |||
| 1 spectrum, LTQYDIVIK | 0.097 | 0.507 | 0.000 | 0.143 | 0.000 | 0.253 | 0.000 | |||
| 3 spectra, VTYDVNR | 0.000 | 0.353 | 0.063 | 0.182 | 0.000 | 0.403 | 0.000 | |||
| 2 spectra, QYYDGSEIVVAGR | 0.000 | 0.169 | 0.325 | 0.000 | 0.000 | 0.506 | 0.000 | |||
| 2 spectra, GIEILNR | 0.000 | 0.369 | 0.224 | 0.000 | 0.000 | 0.407 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
94 spectra |
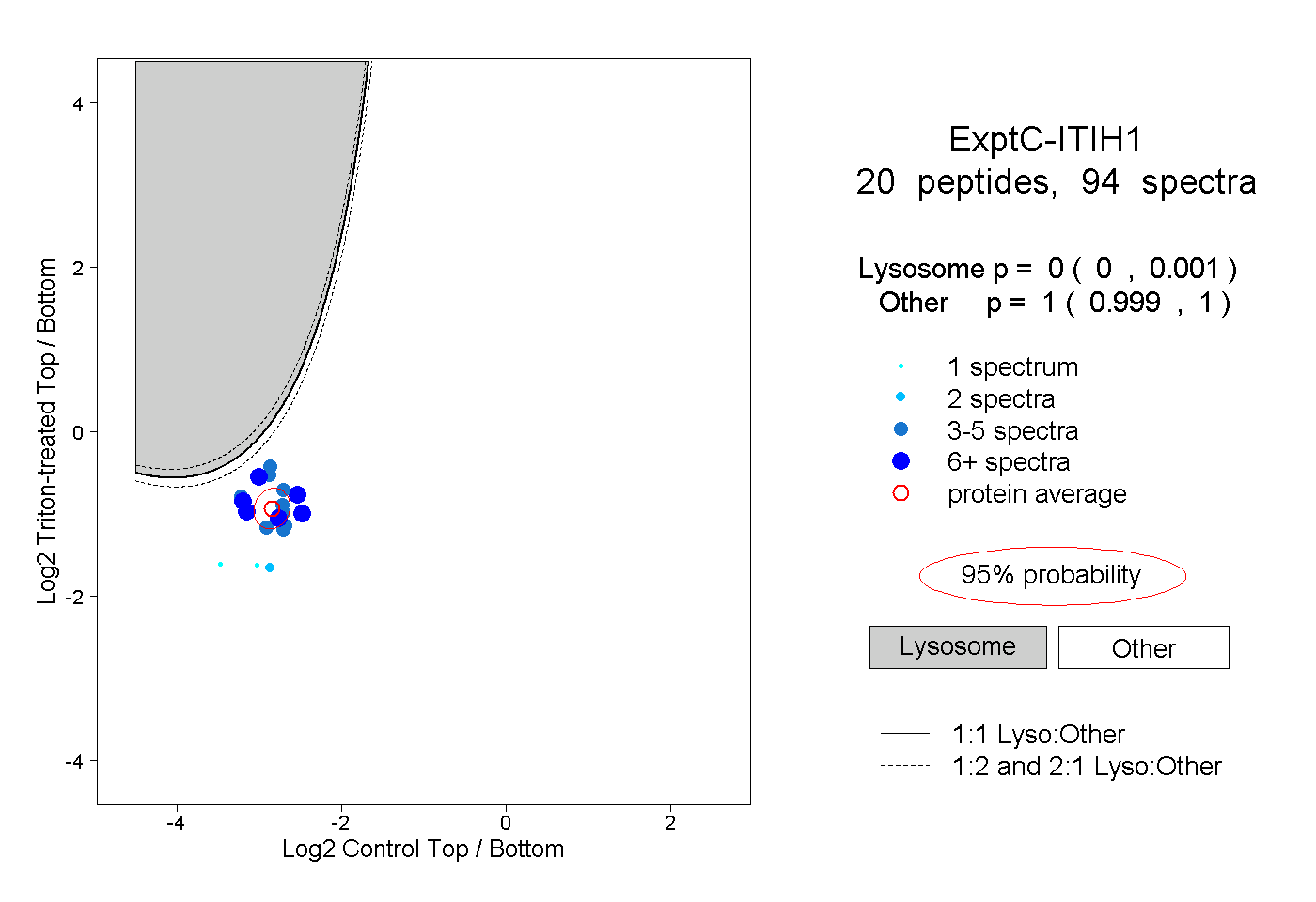 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
7 spectra |
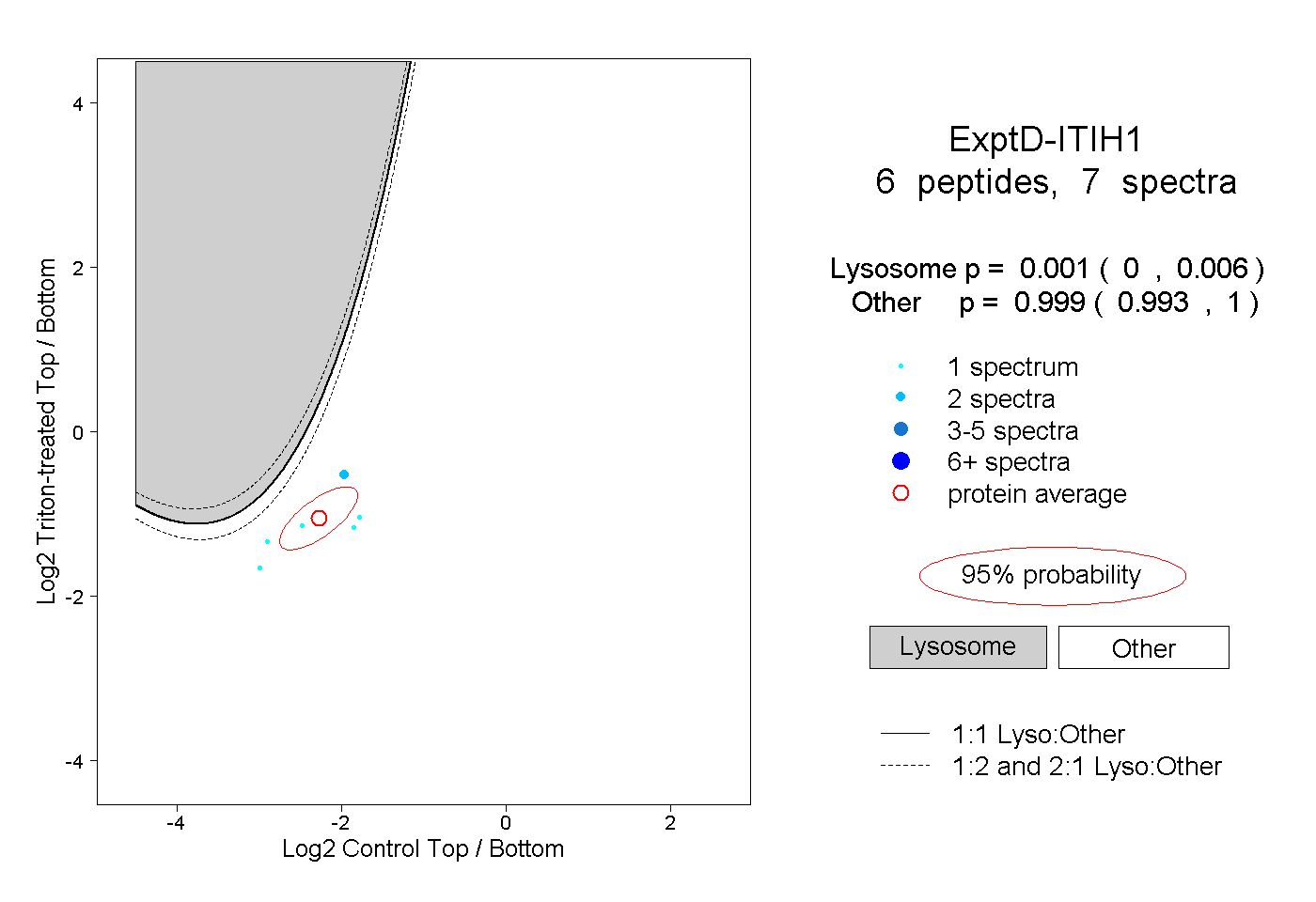 |
0.001 0.000 | 0.006 |
0.999 0.993 | 1.000 |