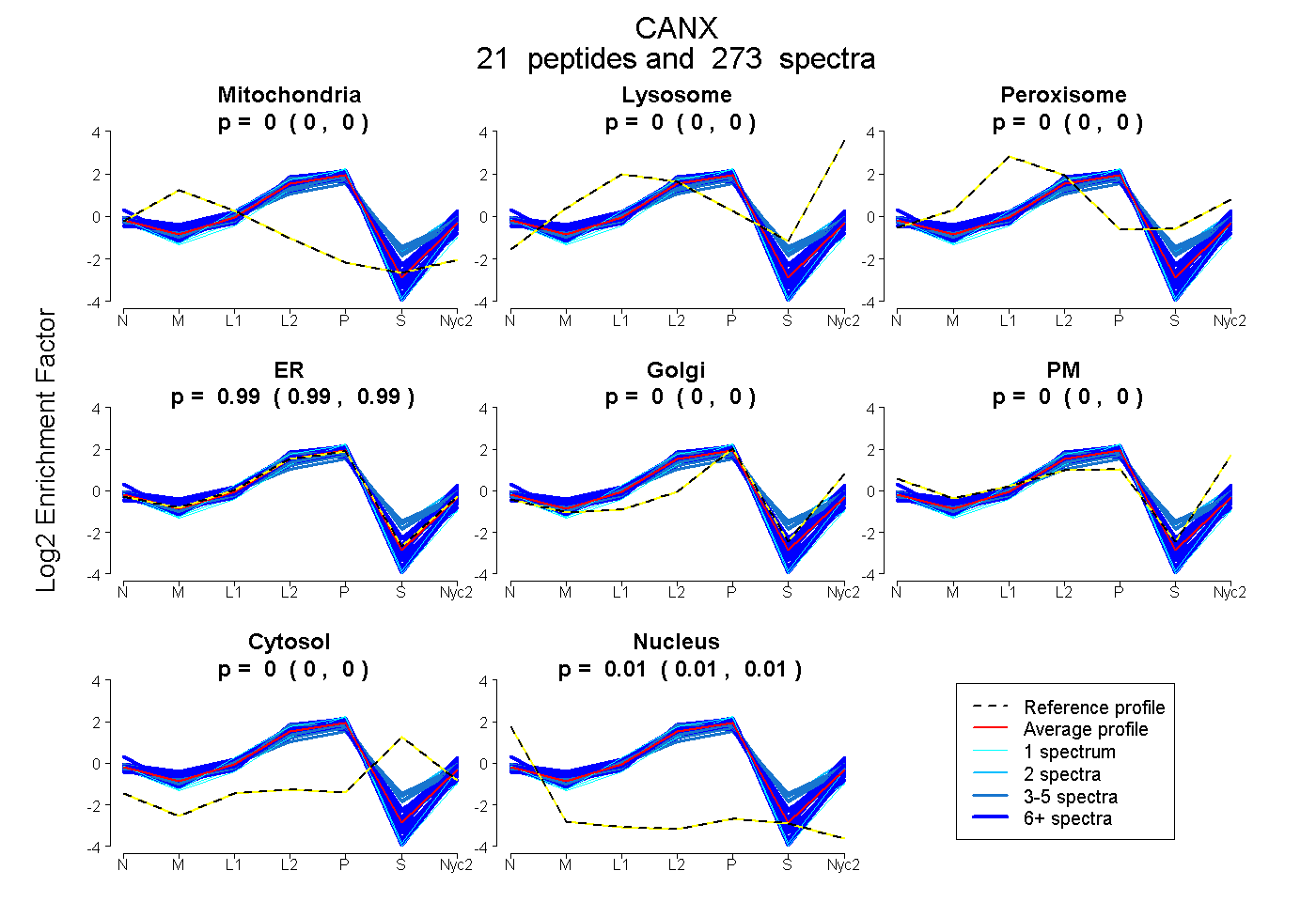
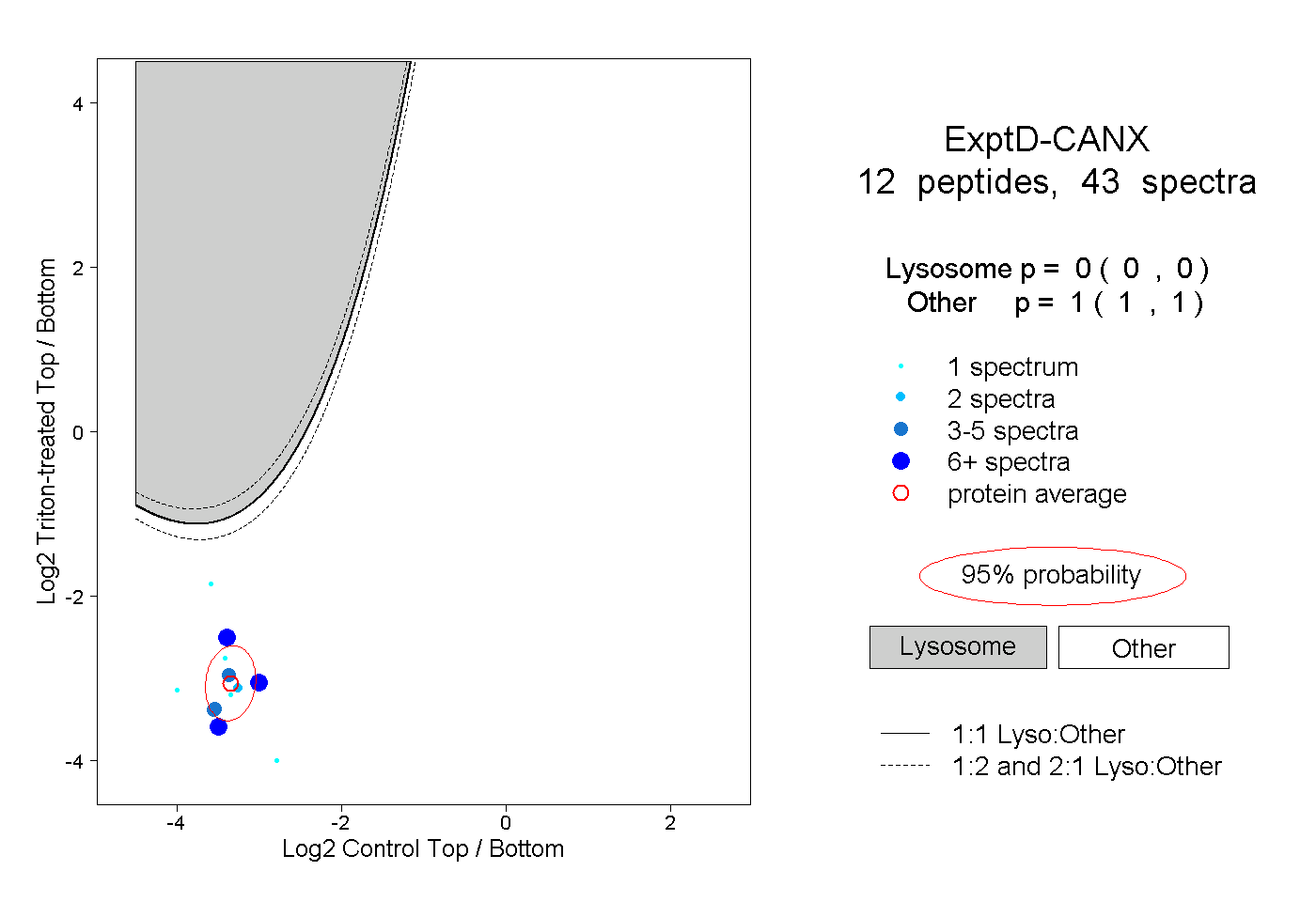
| 23 spectra, LHFIFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, KPEDWDERPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, IPNPDFFEDLEPFR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, WEVDEMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, TPYTIMFGPDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, QSNAMEYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 20 spectra, TSELNLDQFHDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 17 spectra, APVPTGEVYFADSFDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 25 spectra, GSLSGWILSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 51 spectra, TGVYEEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, EIEDPEDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, IADPDAVKPDDWDEDAPSK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, TDAPQPDVK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 27 spectra, CGEDYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 40 spectra, SDTSTPPSPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 31 spectra, GLVLMSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, CESAPGCGVWQRPMIDNPNYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, WKPPMIDNPNYQGIWKPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VVDDWANDGWGLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, DDTDDEIAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 41 spectra, RPDADLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 12 spectra, TYFTDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |