peptides
spectra
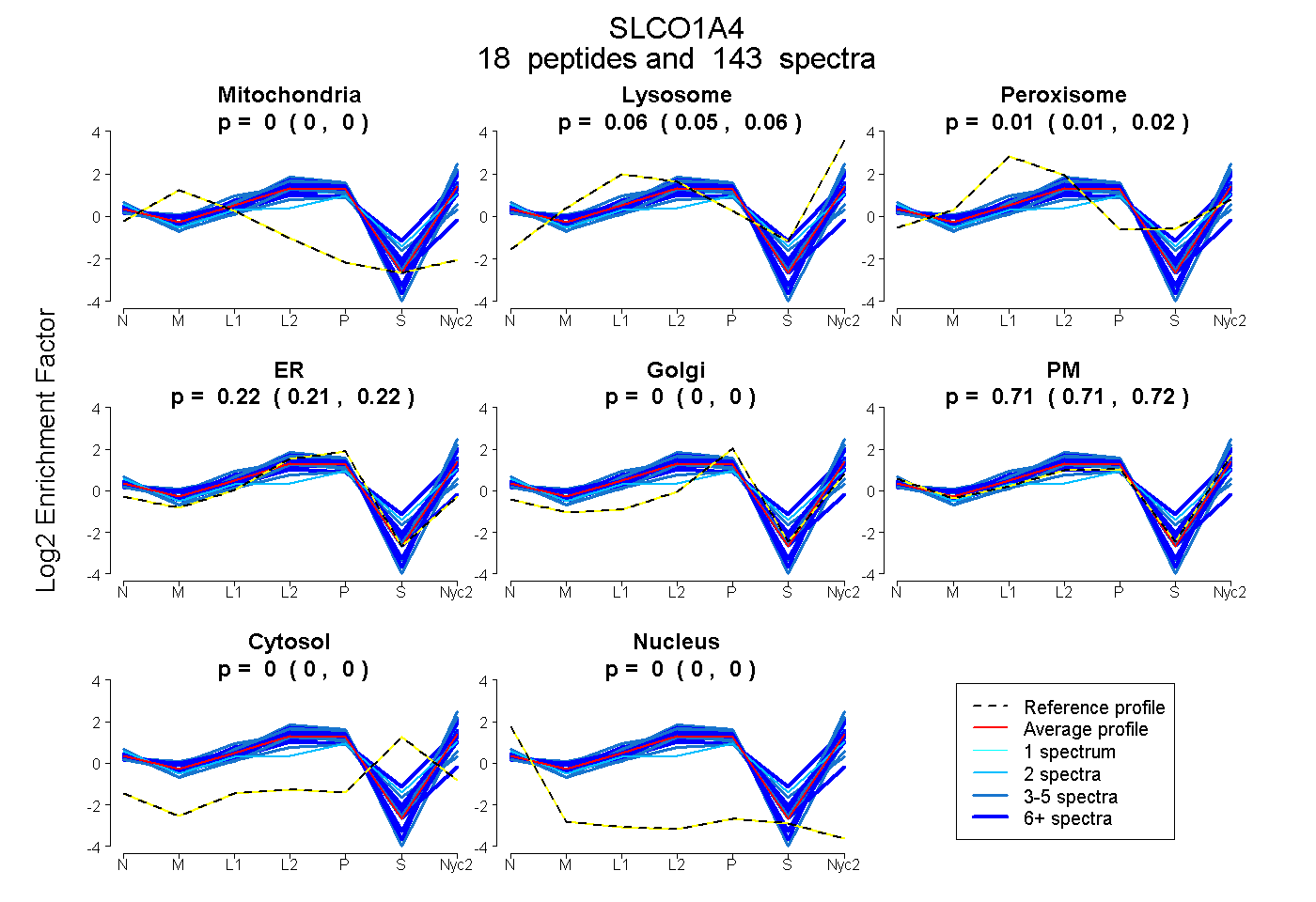
0.000 | 0.000
0.051 | 0.062
0.005 | 0.017
0.211 | 0.223
0.000 | 0.000
0.708 | 0.719
0.000 | 0.000
0.000 | 0.000
peptides
spectra
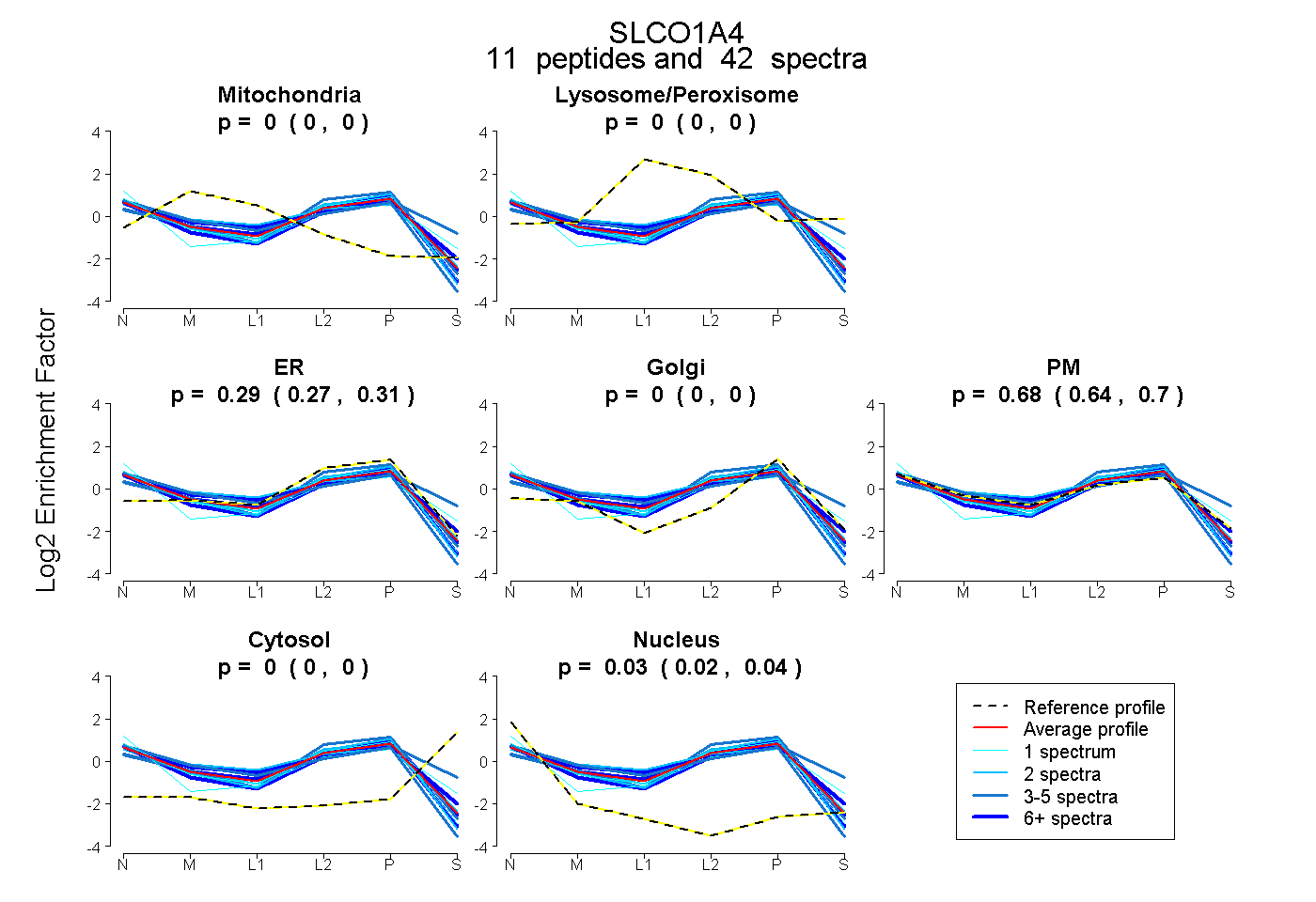
0.000 | 0.000
0.000 | 0.000
0.268 | 0.312
0.000 | 0.000
0.642 | 0.703
0.000 | 0.000
0.023 | 0.037
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
143 spectra |
 |
0.000 0.000 | 0.000 |
0.057 0.051 | 0.062 |
0.012 0.005 | 0.017 |
0.217 0.211 | 0.223 |
0.000 0.000 | 0.000 |
0.714 0.708 | 0.719 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
42 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.292 0.268 | 0.312 |
0.000 0.000 | 0.000 |
0.677 0.642 | 0.703 |
0.000 0.000 | 0.000 |
0.031 0.023 | 0.037 |
| 2 spectra, TCLHWGTLK | 0.039 | 0.008 | 0.100 | 0.000 | 0.853 | 0.000 | 0.000 | |||
| 6 spectra, ESECTEVLR | 0.000 | 0.000 | 0.357 | 0.107 | 0.462 | 0.000 | 0.074 | |||
| 3 spectra, MYDINSFR | 0.000 | 0.000 | 0.630 | 0.000 | 0.341 | 0.000 | 0.030 | |||
| 2 spectra, DFFVFMK | 0.000 | 0.000 | 0.341 | 0.004 | 0.642 | 0.000 | 0.013 | |||
| 1 spectrum, YLEQQYGK | 0.000 | 0.000 | 0.408 | 0.000 | 0.528 | 0.000 | 0.064 | |||
| 3 spectra, VLADCNTR | 0.021 | 0.000 | 0.324 | 0.000 | 0.587 | 0.000 | 0.067 | |||
| 2 spectra, TFQFPGDIESSK | 0.000 | 0.000 | 0.598 | 0.000 | 0.311 | 0.000 | 0.091 | |||
| 5 spectra, EGLQENVDGTENAK | 0.000 | 0.161 | 0.000 | 0.232 | 0.512 | 0.095 | 0.000 | |||
| 9 spectra, LYLGLPAALR | 0.000 | 0.000 | 0.413 | 0.000 | 0.537 | 0.000 | 0.049 | |||
| 8 spectra, SLGVGLHAFCIR | 0.000 | 0.037 | 0.078 | 0.000 | 0.886 | 0.000 | 0.000 | |||
| 1 spectrum, SQTLNPTQDPSECVK | 0.000 | 0.000 | 0.051 | 0.000 | 0.842 | 0.022 | 0.085 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
308 spectra |
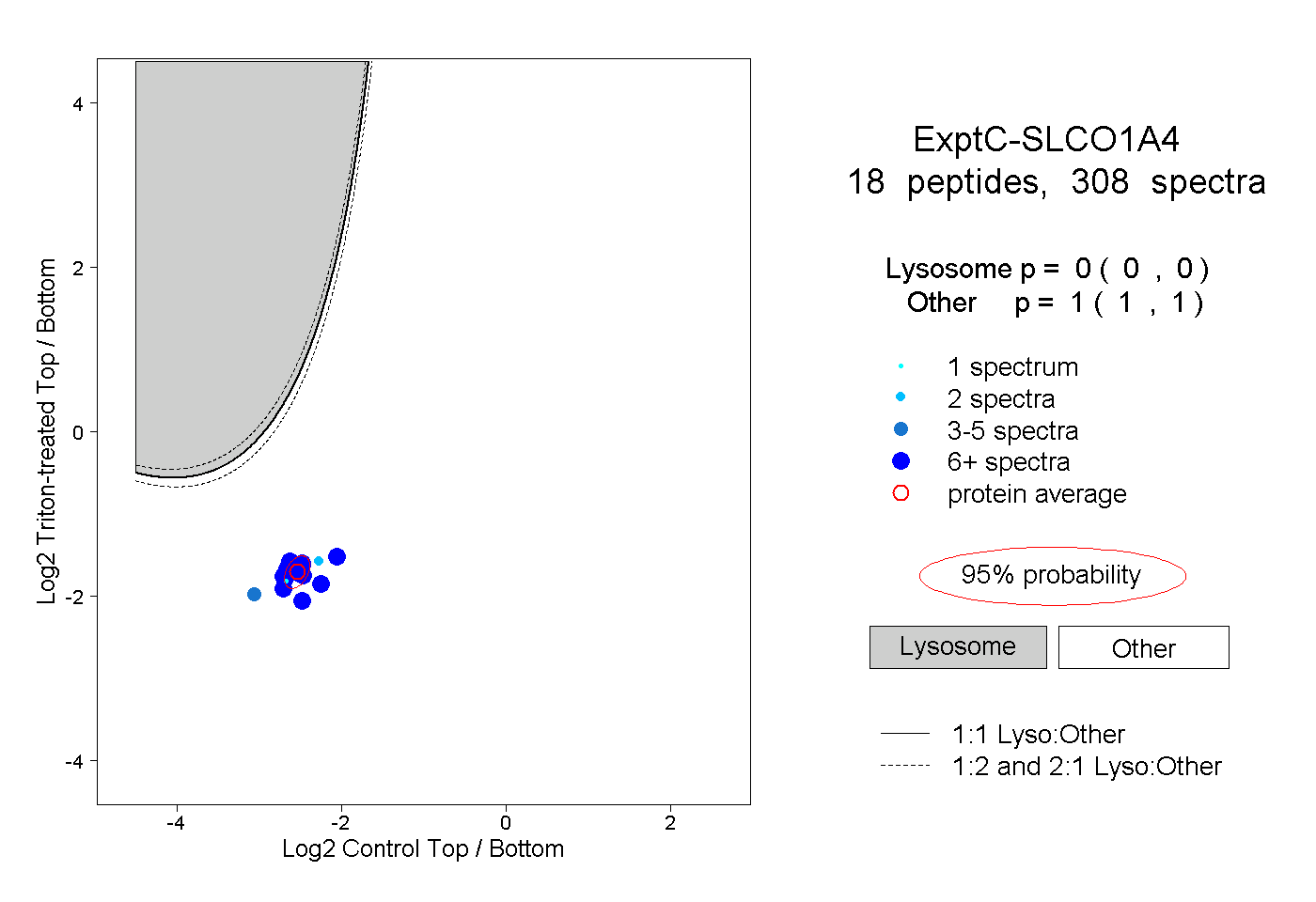 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
18 spectra |
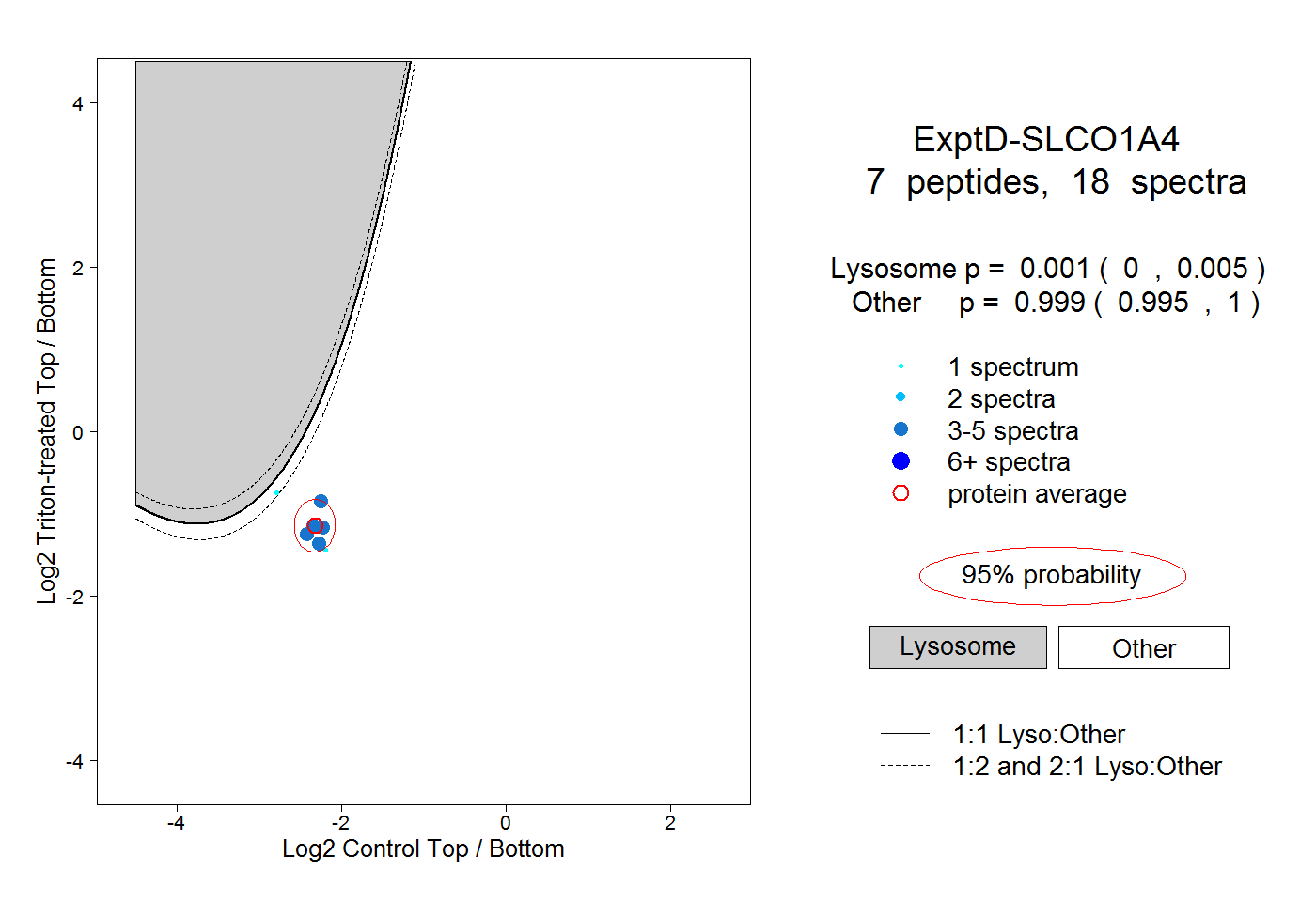 |
0.001 0.000 | 0.005 |
0.999 0.995 | 1.000 |