peptides
spectra
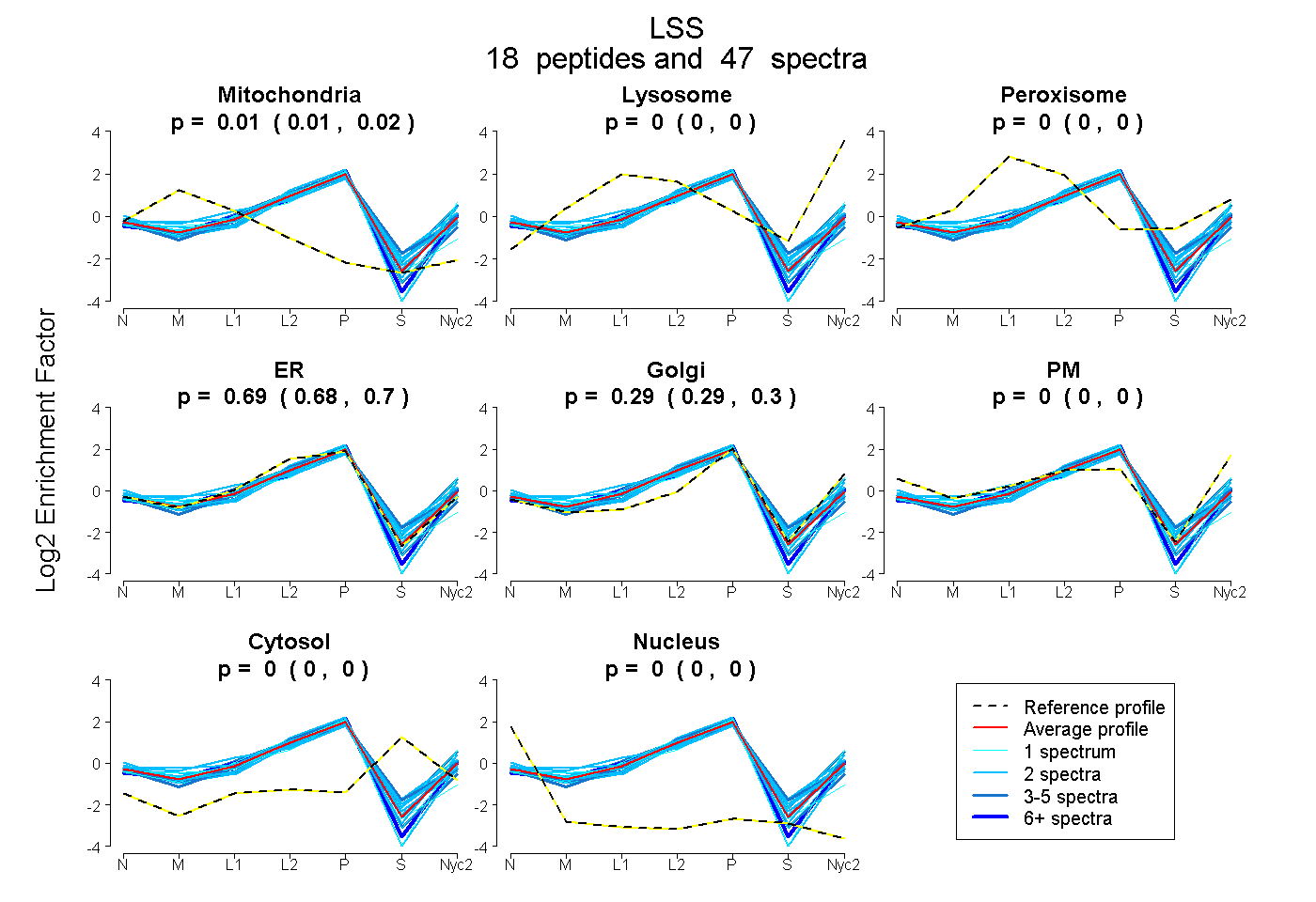
0.012 | 0.017
0.000 | 0.000
0.000 | 0.001
0.684 | 0.698
0.285 | 0.301
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
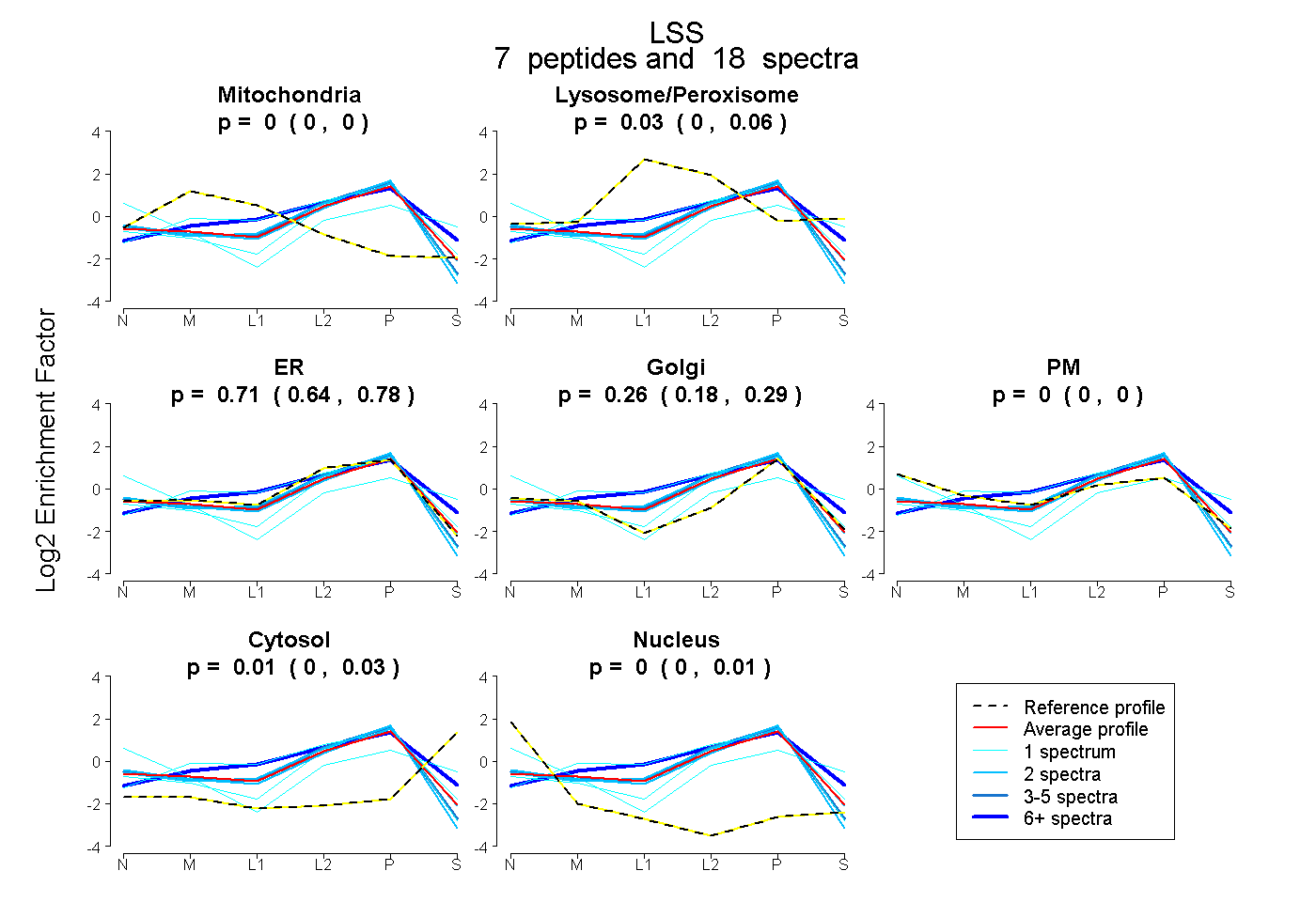
0.000 | 0.000
0.000 | 0.060
0.640 | 0.777
0.185 | 0.290
0.000 | 0.000
0.000 | 0.030
0.000 | 0.009
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
47 spectra |
 |
0.015 0.012 | 0.017 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.001 |
0.692 0.684 | 0.698 |
0.294 0.285 | 0.301 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
18 spectra |
 |
0.000 0.000 | 0.000 |
0.029 0.000 | 0.060 |
0.710 0.640 | 0.777 |
0.255 0.185 | 0.290 |
0.000 0.000 | 0.000 |
0.005 0.000 | 0.030 |
0.000 0.000 | 0.009 |
| 1 spectrum, HPDISAQER | 0.000 | 0.000 | 0.000 | 0.292 | 0.483 | 0.225 | 0.000 | |||
| 2 spectra, NIFPIWALGR | 0.000 | 0.000 | 0.917 | 0.071 | 0.000 | 0.000 | 0.012 | |||
| 1 spectrum, LHNELGR | 0.026 | 0.148 | 0.740 | 0.085 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LSASEDPLVQSLR | 0.000 | 0.000 | 0.610 | 0.390 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, TEPATDLTR | 0.000 | 0.003 | 0.695 | 0.302 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, AVLLLQER | 0.000 | 0.000 | 0.870 | 0.127 | 0.000 | 0.000 | 0.002 | |||
| 8 spectra, AHEFLR | 0.000 | 0.243 | 0.516 | 0.184 | 0.000 | 0.058 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
86 spectra |
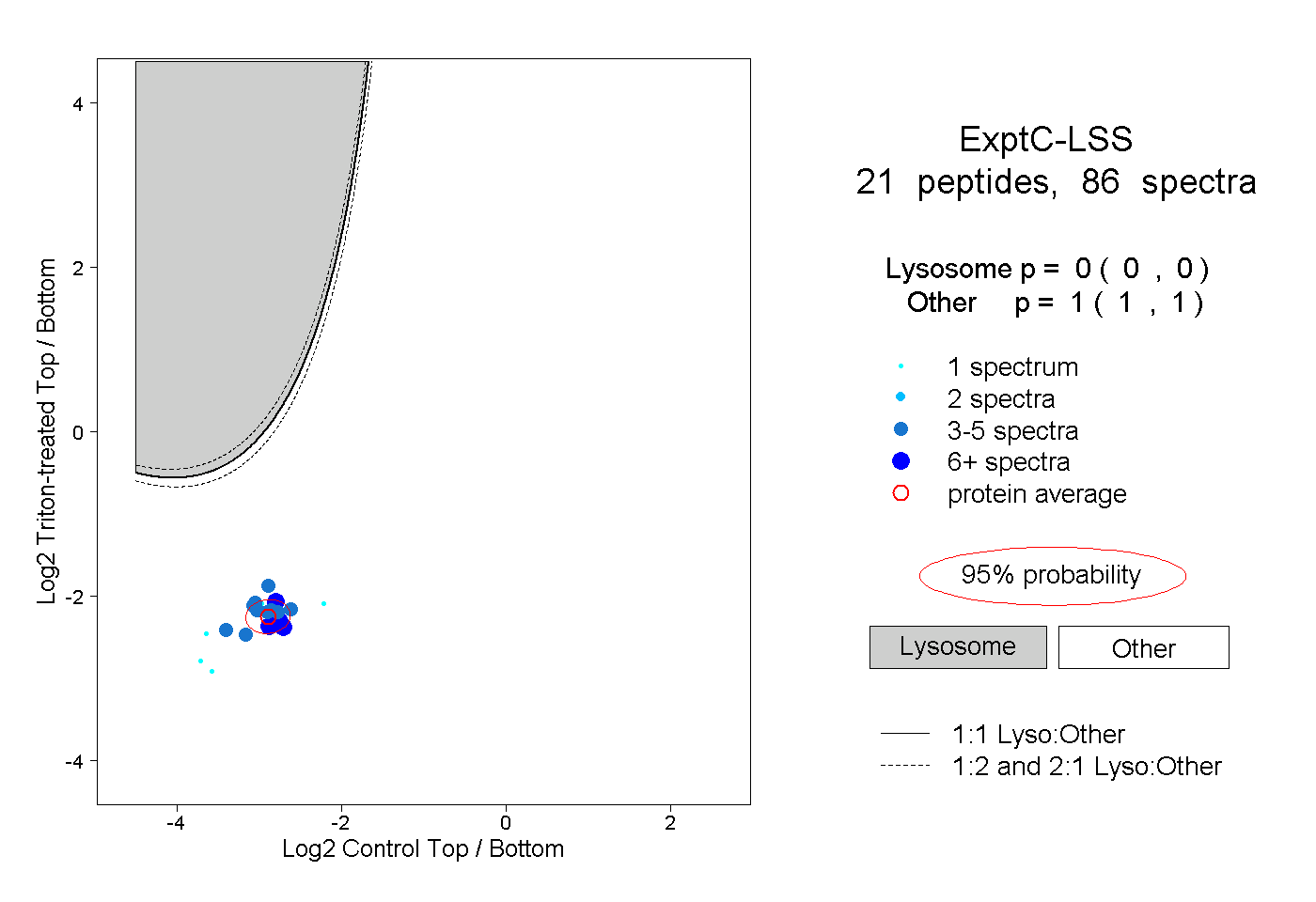 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
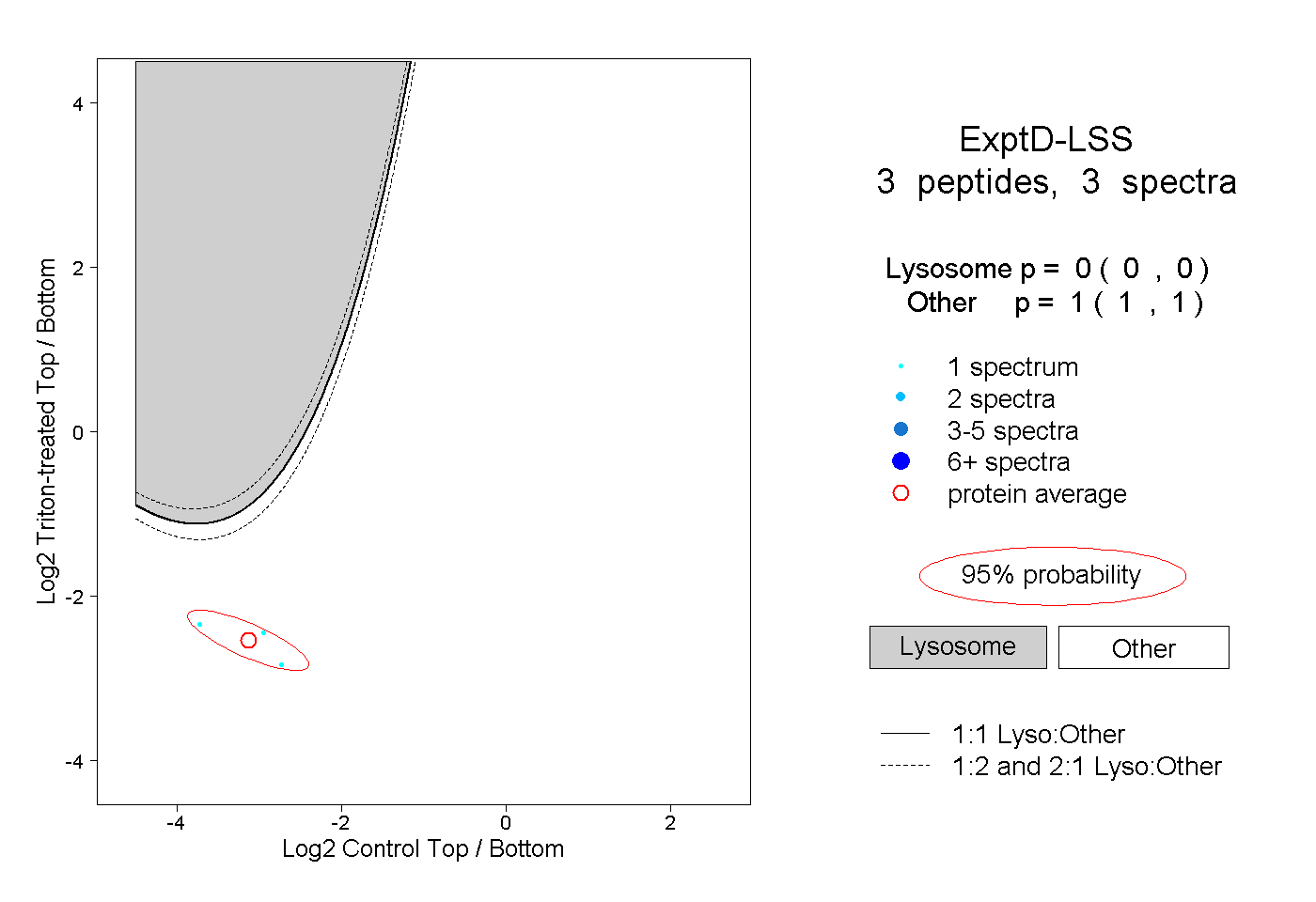 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |