peptides
spectra
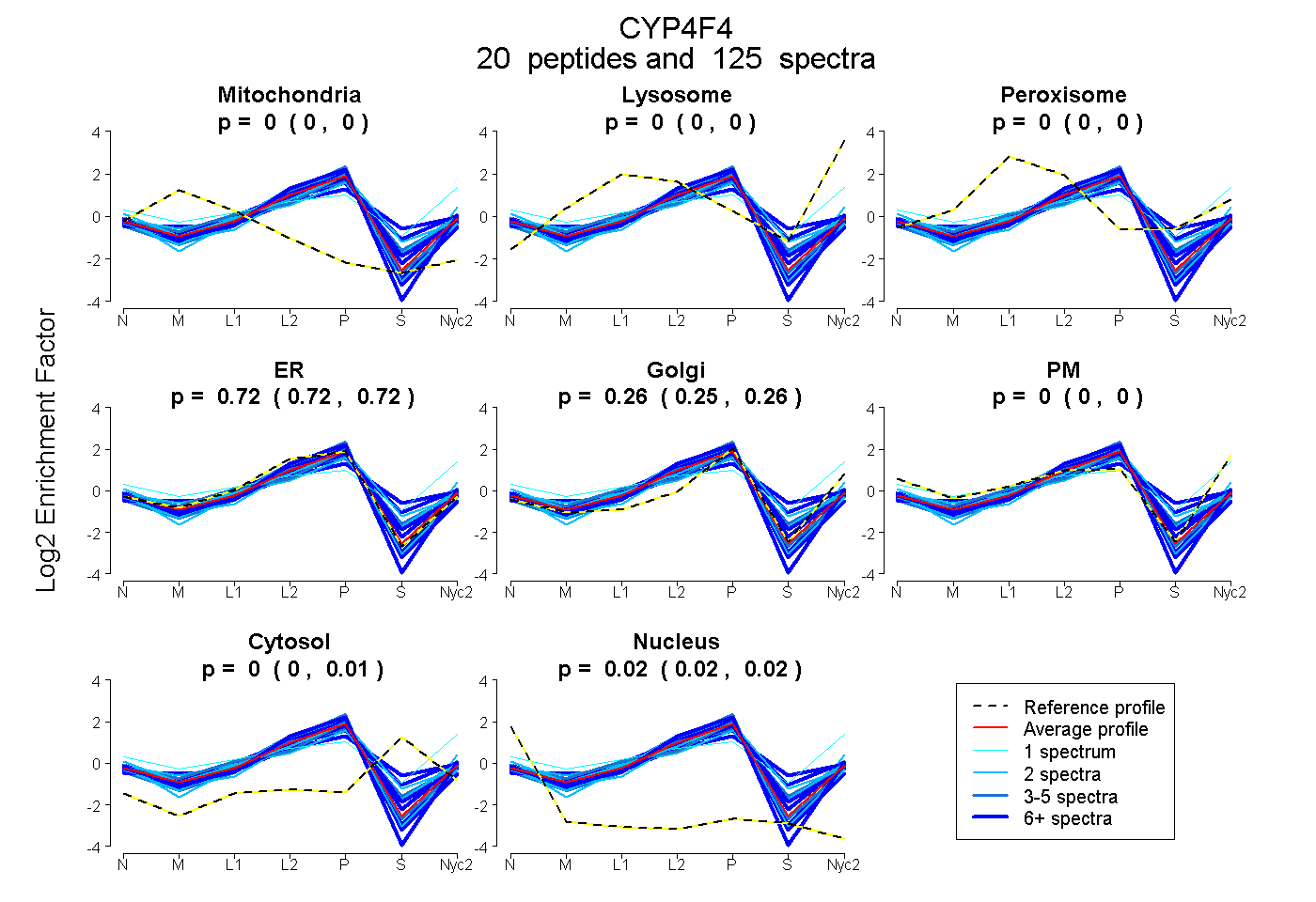
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.716 | 0.723
0.251 | 0.260
0.000 | 0.000
0.000 | 0.008
0.019 | 0.024
peptides
spectra

0.000 | 0.000
0.000 | 0.007
0.834 | 0.860
0.138 | 0.158
0.000 | 0.000
0.000 | 0.001
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
125 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.719 0.716 | 0.723 |
0.256 0.251 | 0.260 |
0.000 0.000 | 0.000 |
0.002 0.000 | 0.008 |
0.022 0.019 | 0.024 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
39 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.007 |
0.852 0.834 | 0.860 |
0.148 0.138 | 0.158 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.001 |
0.000 0.000 | 0.000 |
| 3 spectra, LVHNFTDAVIQGR | 0.071 | 0.000 | 0.929 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, AEGGLWLR | 0.000 | 0.000 | 0.854 | 0.137 | 0.000 | 0.000 | 0.009 | |||
| 8 spectra, TLDFIDVLLLTK | 0.000 | 0.000 | 0.847 | 0.153 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, SVLSASASVALK | 0.000 | 0.000 | 0.693 | 0.307 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, LHPPVTVISR | 0.000 | 0.000 | 0.809 | 0.191 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, IFNDSTNIMHAK | 0.000 | 0.125 | 0.649 | 0.083 | 0.000 | 0.143 | 0.000 | |||
| 1 spectrum, NISLMTLDSLQK | 0.000 | 0.263 | 0.546 | 0.191 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, FDPENIK | 0.000 | 0.057 | 0.597 | 0.227 | 0.000 | 0.119 | 0.000 | |||
| 1 spectrum, WQDLASGGSAR | 0.000 | 0.000 | 0.602 | 0.398 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, VAIALTLLR | 0.000 | 0.088 | 0.772 | 0.087 | 0.053 | 0.000 | 0.000 | |||
| 1 spectrum, PQLDLSWLGLR | 0.000 | 0.000 | 0.808 | 0.090 | 0.101 | 0.000 | 0.001 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
51 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |