peptides
spectra
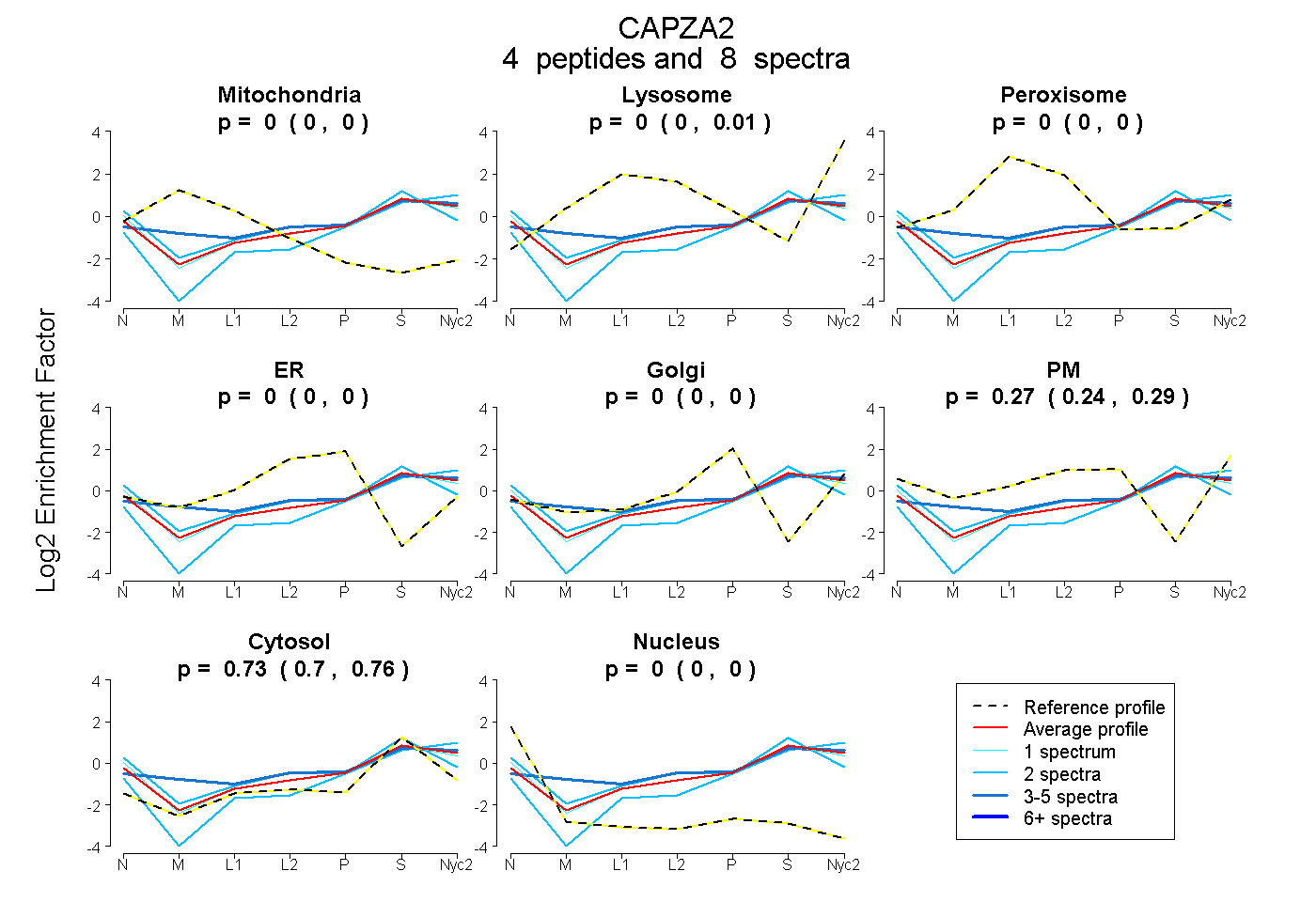
0.000 | 0.000
0.000 | 0.013
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.237 | 0.289
0.703 | 0.758
0.000 | 0.000
peptides
spectra
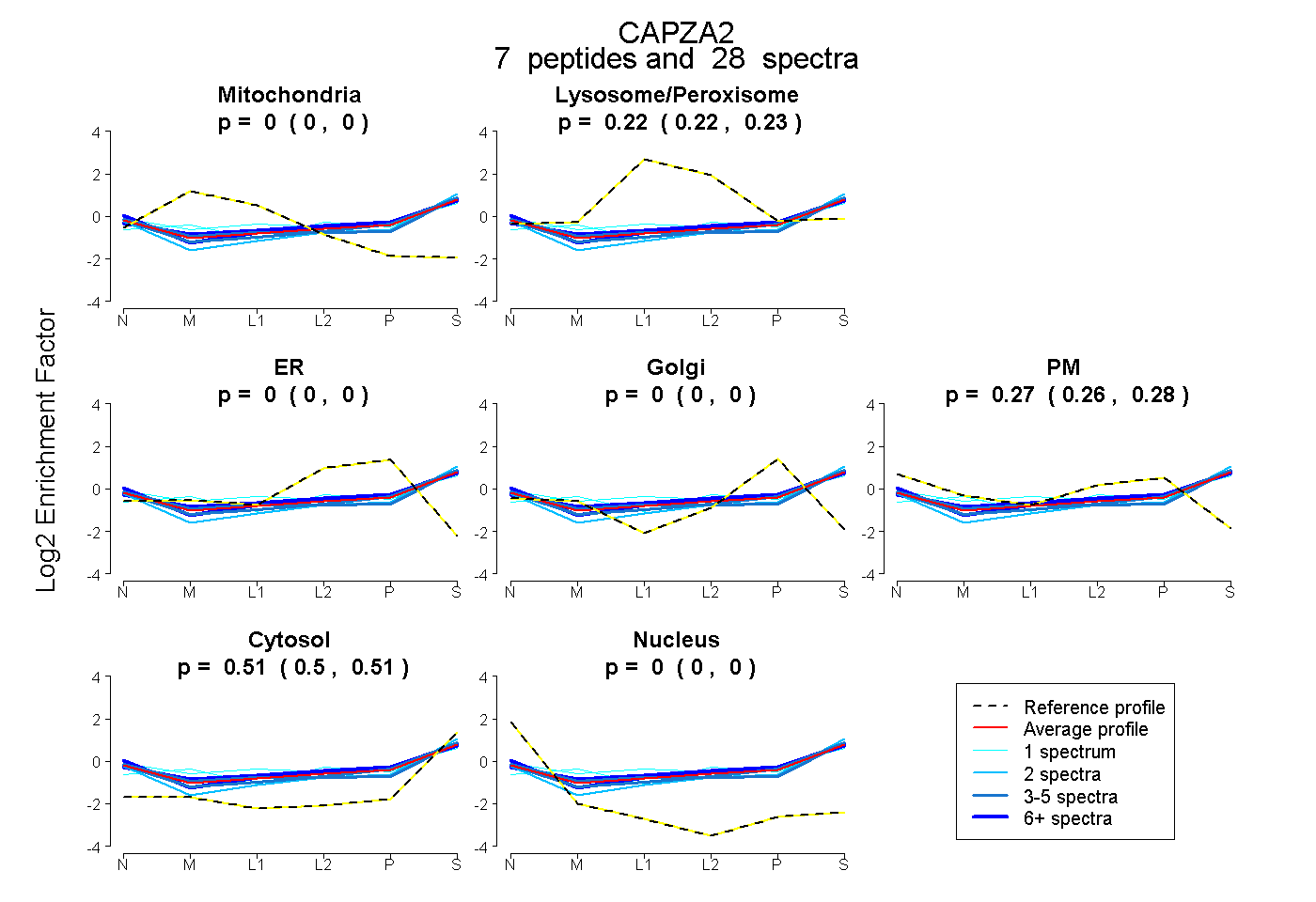
0.000 | 0.000
0.216 | 0.227
0.000 | 0.000
0.000 | 0.000
0.265 | 0.277
0.502 | 0.510
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
8 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.013 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.267 0.237 | 0.289 |
0.733 0.703 | 0.758 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
28 spectra |
 |
0.000 0.000 | 0.000 |
0.222 0.216 | 0.227 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.272 0.265 | 0.277 |
0.507 0.502 | 0.510 |
0.000 0.000 | 0.000 |
| 1 spectrum, EATDPRPYEAENAIESWR | 0.000 | 0.280 | 0.000 | 0.000 | 0.302 | 0.418 | 0.000 | |||
| 12 spectra, FIIHAPPGEFNEVFNDVR | 0.000 | 0.261 | 0.000 | 0.011 | 0.253 | 0.475 | 0.000 | |||
| 2 spectra, FTVTPSTTQVVGILK | 0.000 | 0.176 | 0.000 | 0.000 | 0.215 | 0.609 | 0.000 | |||
| 3 spectra, TSVETALR | 0.000 | 0.185 | 0.000 | 0.000 | 0.279 | 0.537 | 0.000 | |||
| 1 spectrum, EGAAHAFAQYNLDQFTPVK | 0.000 | 0.240 | 0.000 | 0.041 | 0.221 | 0.498 | 0.000 | |||
| 3 spectra, NFWNGR | 0.000 | 0.236 | 0.000 | 0.000 | 0.217 | 0.536 | 0.011 | |||
| 6 spectra, LLLNNDNLLR | 0.000 | 0.213 | 0.000 | 0.000 | 0.314 | 0.473 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
29 spectra |
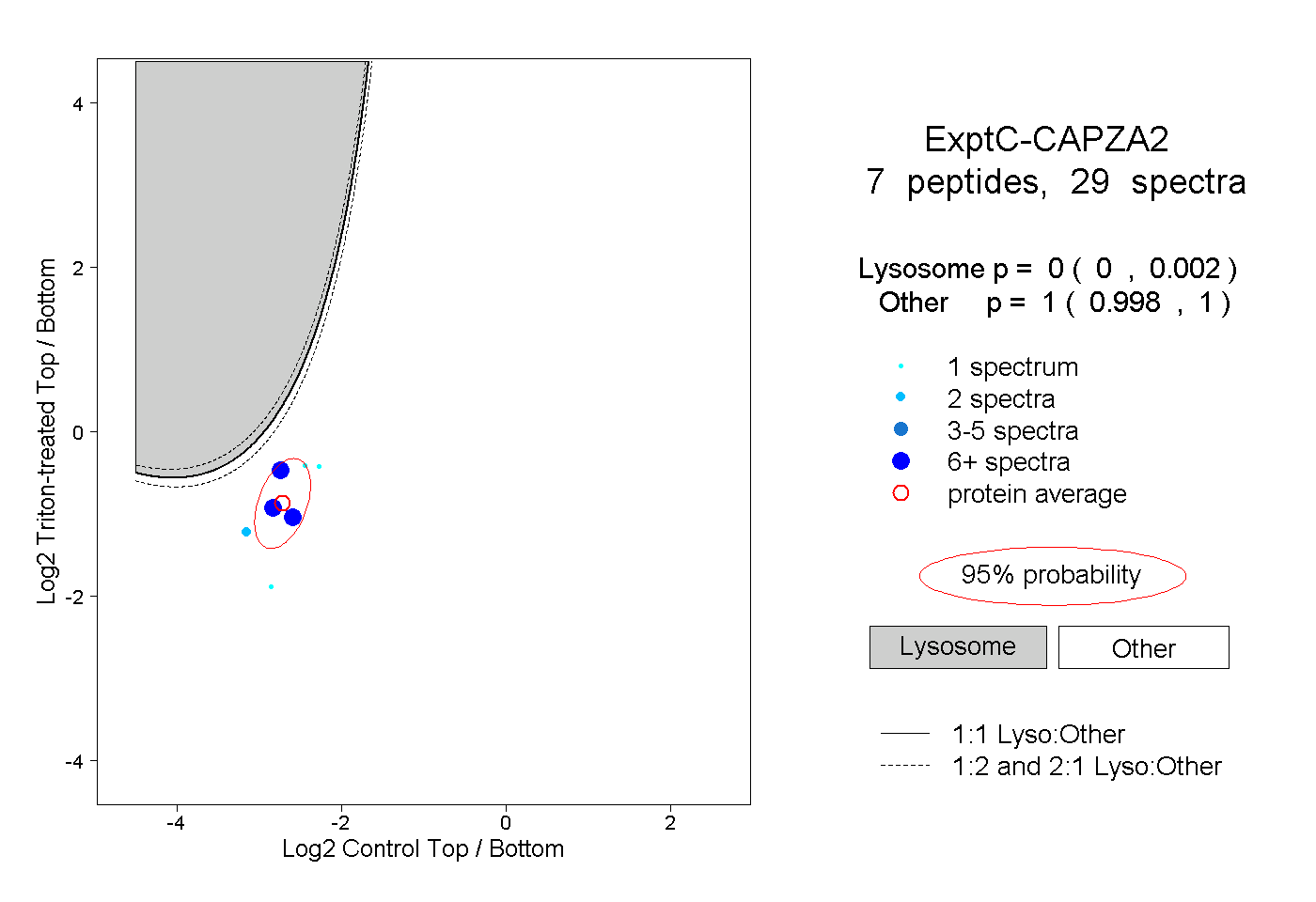 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
14 spectra |
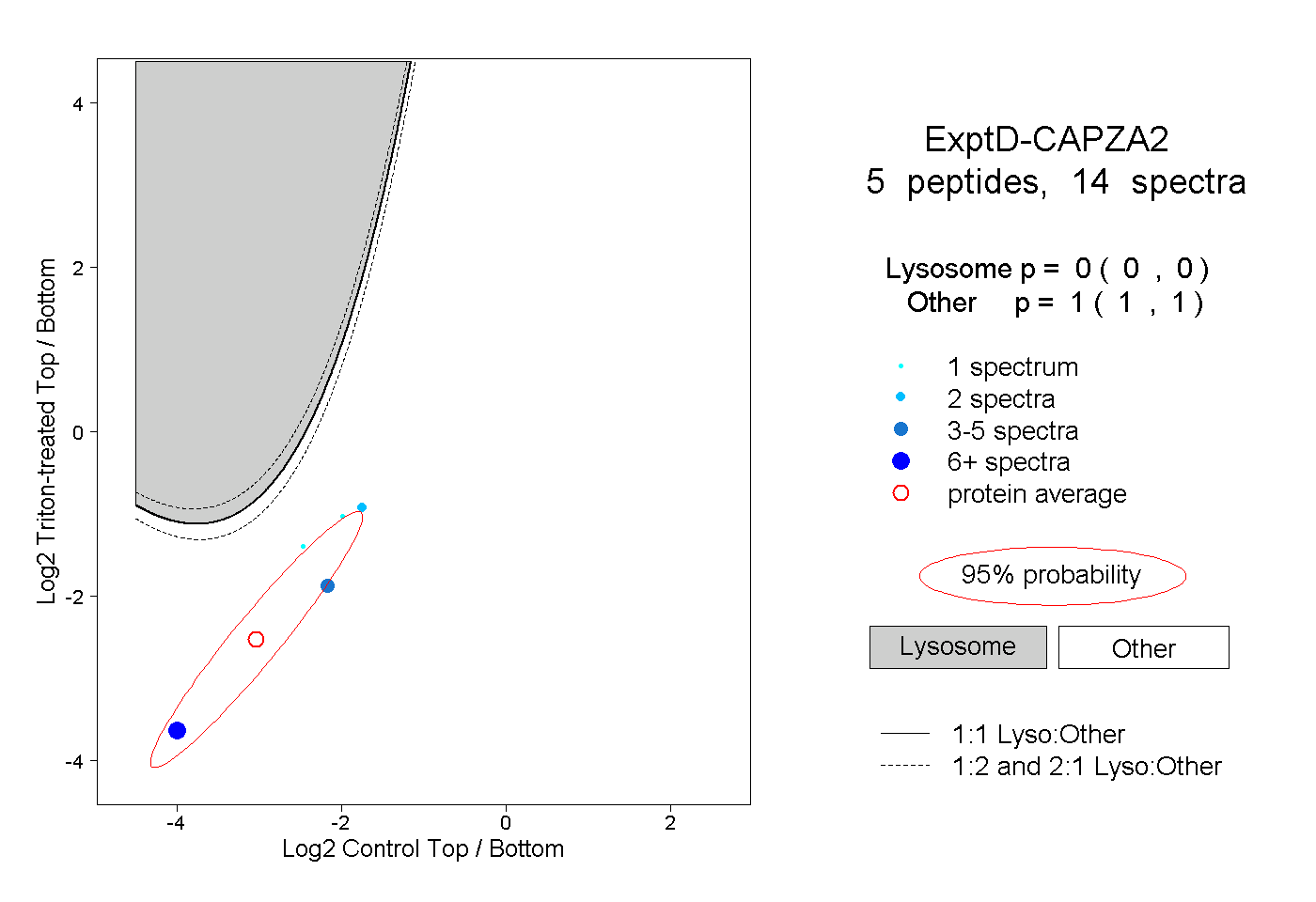 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |