peptides
spectra

0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.092 | 0.129
0.594 | 0.638
0.000 | 0.000
0.224 | 0.246
0.026 | 0.040
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
28 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.112 0.092 | 0.129 |
0.618 0.594 | 0.638 |
0.000 0.000 | 0.000 |
0.236 0.224 | 0.246 |
0.034 0.026 | 0.040 |
| 2 spectra, VNDVPEEFLYNPLTR | 0.000 | 0.000 | 0.000 | 0.015 | 0.634 | 0.000 | 0.351 | 0.000 | ||
| 1 spectrum, TYINPFVSFIDQR | 0.000 | 0.000 | 0.000 | 0.171 | 0.511 | 0.000 | 0.218 | 0.100 | ||
| 3 spectra, SFVTWLR | 0.000 | 0.000 | 0.000 | 0.210 | 0.657 | 0.000 | 0.125 | 0.007 | ||
| 2 spectra, SAPAGSPHPAAGAR | 0.000 | 0.000 | 0.000 | 0.133 | 0.562 | 0.000 | 0.275 | 0.030 | ||
| 1 spectrum, ETHSALGPALQAAFK | 0.000 | 0.016 | 0.000 | 0.000 | 0.603 | 0.098 | 0.284 | 0.000 | ||
| 1 spectrum, VVPQPPLQK | 0.077 | 0.000 | 0.144 | 0.030 | 0.559 | 0.000 | 0.190 | 0.000 | ||
| 1 spectrum, SQPLVHLMK | 0.022 | 0.000 | 0.128 | 0.000 | 0.703 | 0.000 | 0.147 | 0.000 | ||
| 1 spectrum, LTDEGAIHVNDR | 0.000 | 0.000 | 0.000 | 0.239 | 0.318 | 0.000 | 0.347 | 0.096 | ||
| 2 spectra, LNCSPDSFR | 0.000 | 0.000 | 0.000 | 0.247 | 0.515 | 0.000 | 0.153 | 0.084 | ||
| 2 spectra, MIHPNLYR | 0.000 | 0.000 | 0.000 | 0.163 | 0.382 | 0.000 | 0.451 | 0.003 | ||
| 4 spectra, TDFFQHLVEDR | 0.000 | 0.000 | 0.000 | 0.212 | 0.533 | 0.000 | 0.211 | 0.043 | ||
| 5 spectra, LMSPTGGR | 0.000 | 0.000 | 0.000 | 0.079 | 0.756 | 0.000 | 0.068 | 0.097 | ||
| 3 spectra, SVSSSLSDAR | 0.000 | 0.000 | 0.000 | 0.018 | 0.802 | 0.000 | 0.120 | 0.061 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
2 spectra |
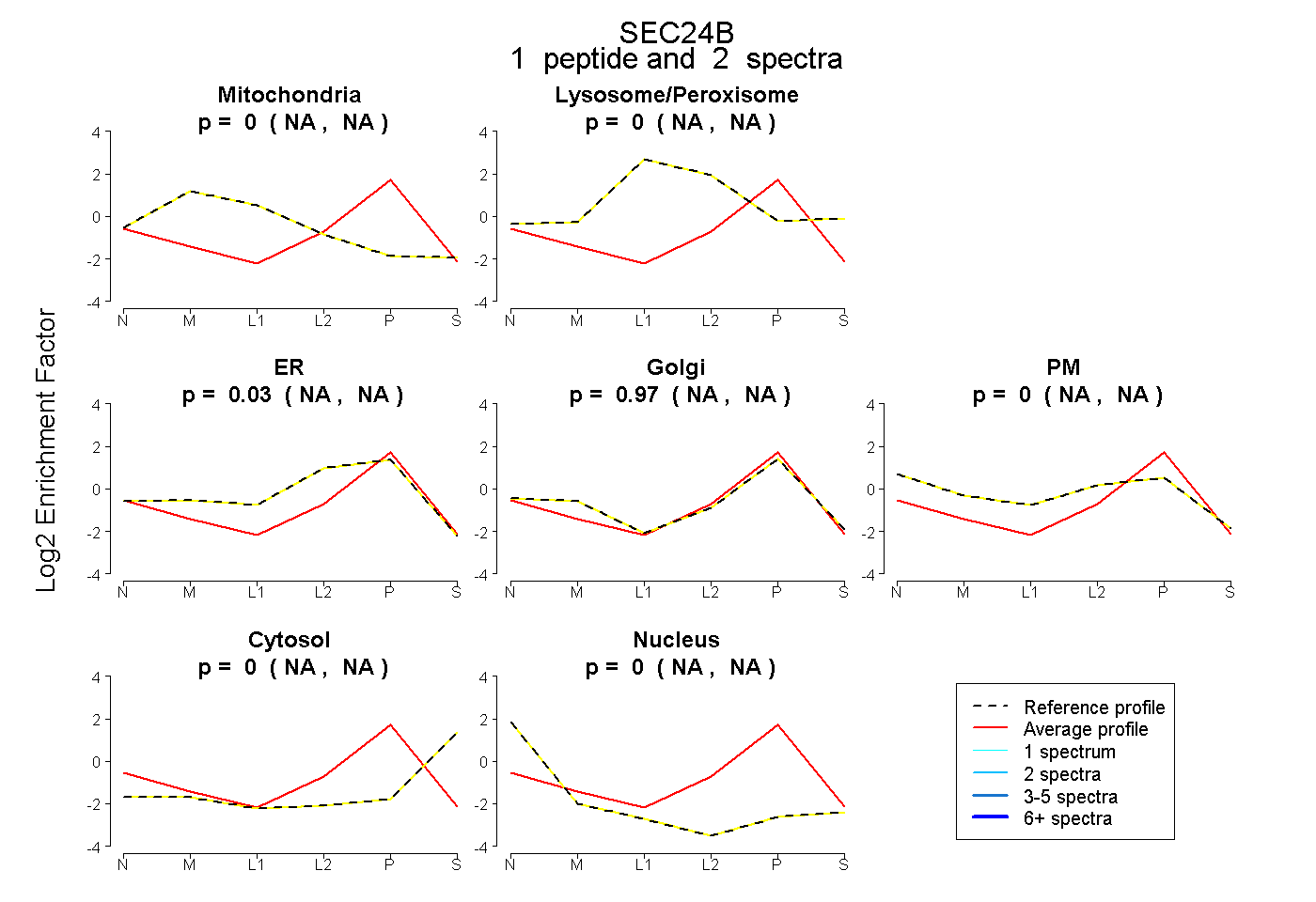 |
0.000 NA | NA |
0.000 NA | NA |
0.031 NA | NA |
0.969 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
19 spectra |
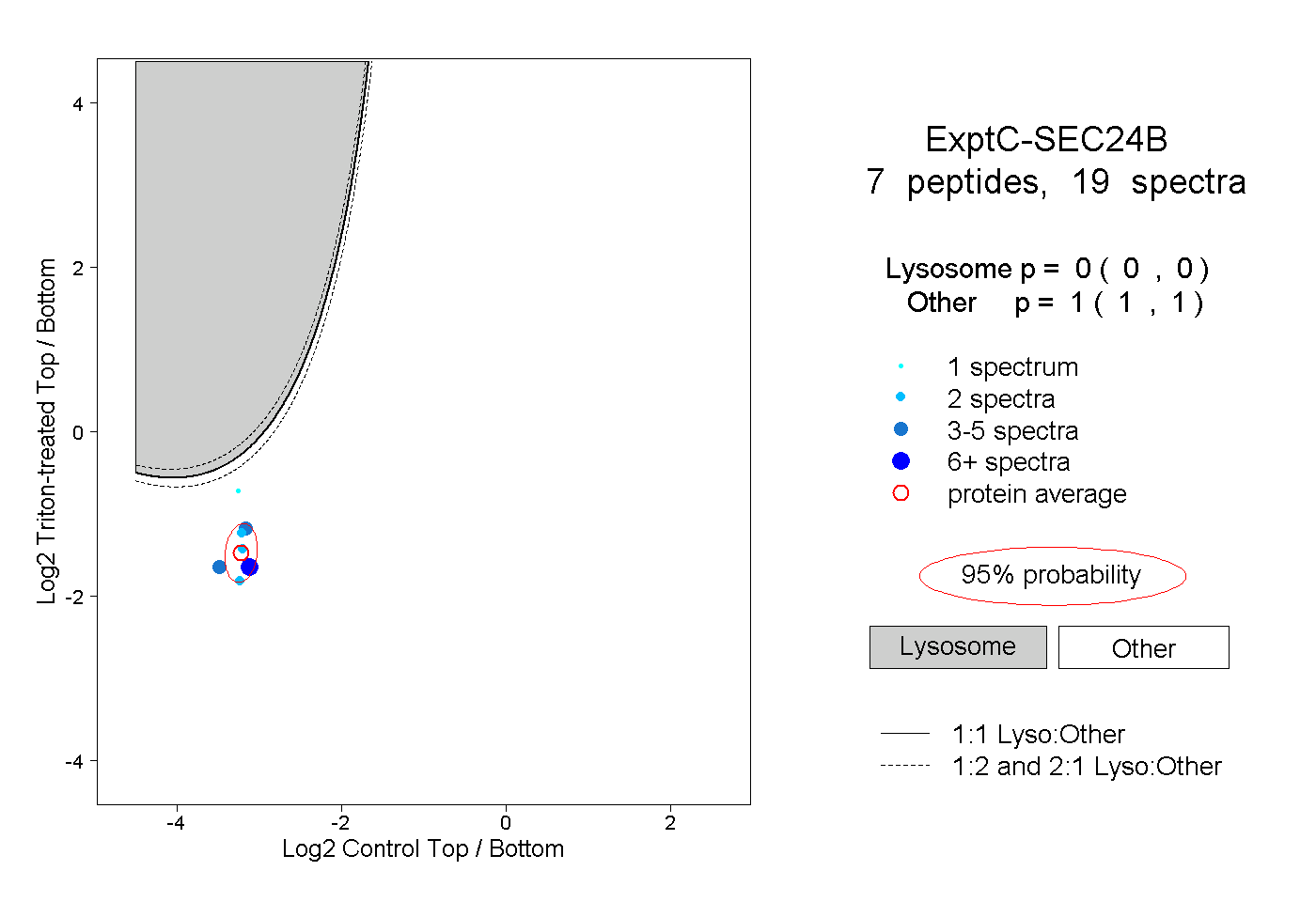 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
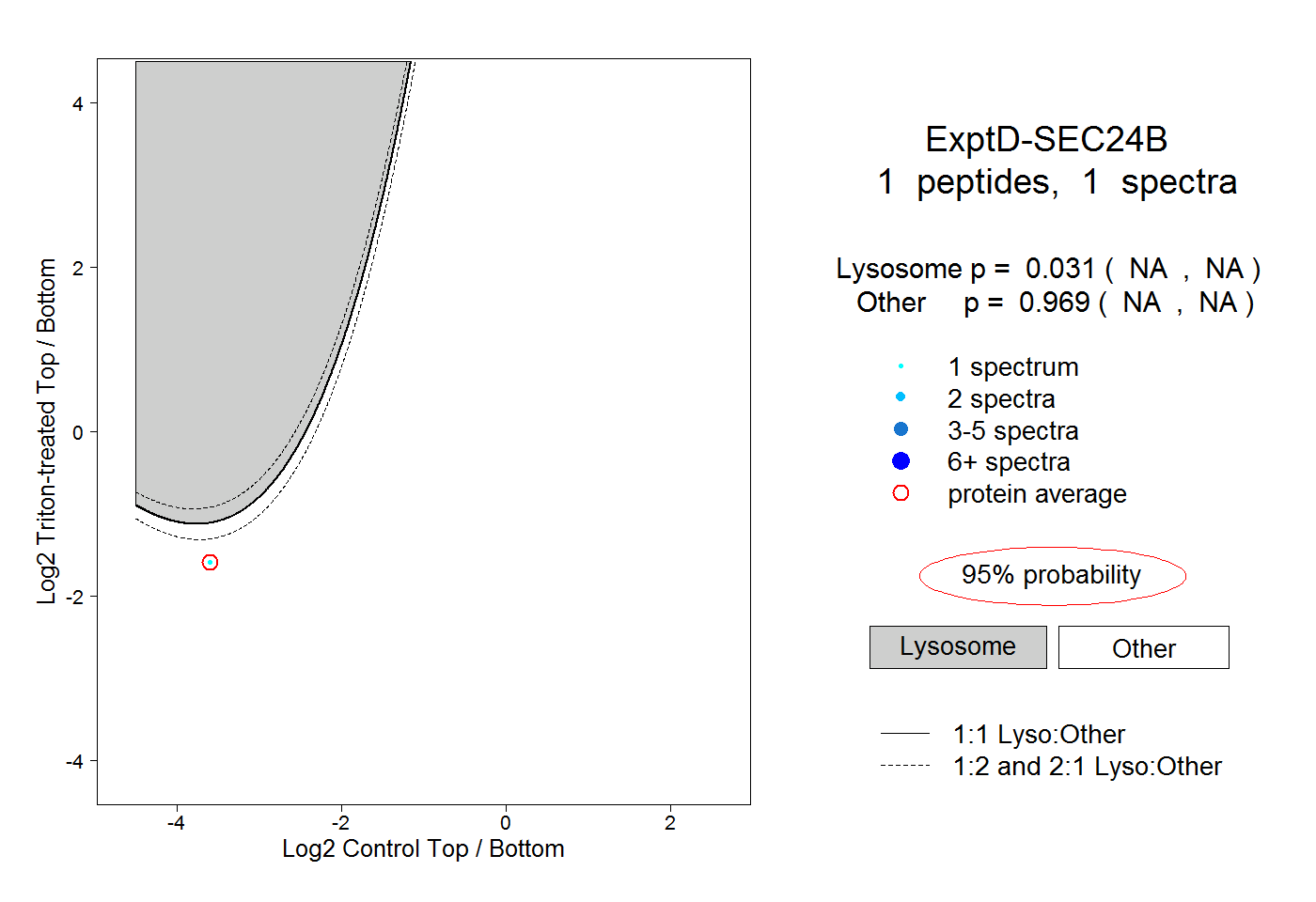 |
0.031 NA | NA |
0.969 NA | NA |