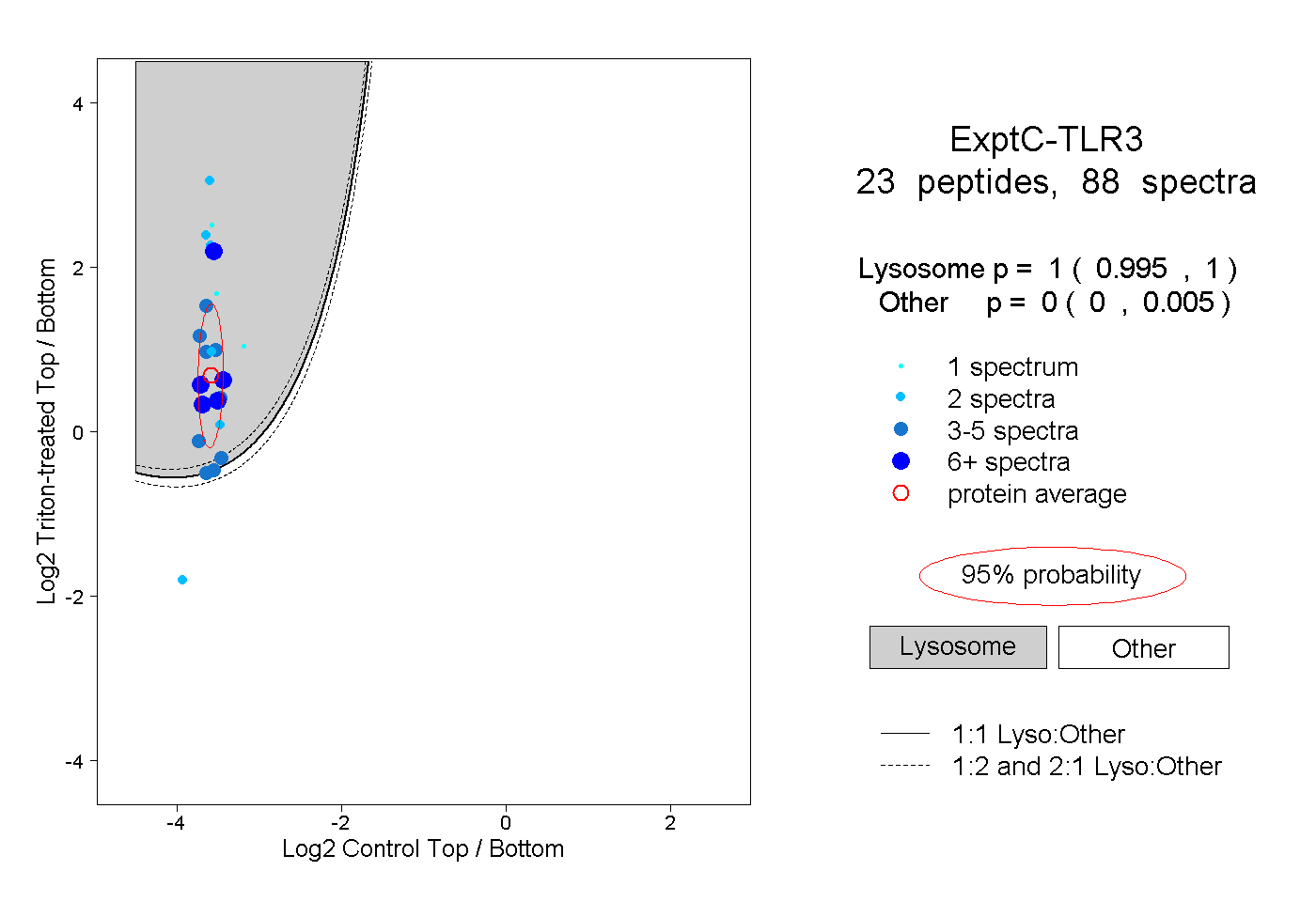
| 6 spectra, NLFELK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, CLEHLNMDDNTIPGIK |
|
0.505 |
|
|
|
|
|
|
|
0.495 |
| 10 spectra, YNVADCSHLK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 7 spectra, SFTLVPSLQR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, LDLSSNPLK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 1 spectrum, EIDAQGEQFEYTAYIIHAQK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 3 spectra, NLITSVEK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, FCLEER |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 3 spectra, INAFHHK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, YLSLSK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, SLNLQK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, YLQLTSK |
|
0.993 |
|
|
|
|
|
|
|
0.007 |
| 2 spectra, DPLCR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, SHCILNWPIQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 10 spectra, YHGLPVK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 1 spectrum, DFEAGVLGLEAIVNSIK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 4 spectra, HANPGGPVNFLK |
|
0.782 |
|
|
|
|
|
|
|
0.218 |
| 1 spectrum, YLSLK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, LFDTSSCK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 6 spectra, SNTFTGLVSLK |
|
1.000 |
|
|
|
|
|
|
|
0.000 |
| 2 spectra, EFSPGCFHAIGK |
|
0.996 |
|
|
|
|
|
|
|
0.004 |
| 4 spectra, LNHALCLR |
|
0.500 |
|
|
|
|
|
|
|
0.500 |
| 4 spectra, LQVALGSR |
|
1.000 |
|
|
|
|
|
|
|
0.000 |