peptides
spectra

0.000 | 0.000
0.981 | 1.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.017
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
29 spectra |
 |
0.000 0.000 | 0.000 |
0.992 0.981 | 1.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.008 0.000 | 0.017 |
0.000 0.000 | 0.000 |
| 1 spectrum, NLFELK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, YNVADCSHLK | 0.000 | 0.731 | 0.000 | 0.000 | 0.000 | 0.163 | 0.107 | 0.000 | ||
| 2 spectra, SFTLVPSLQR | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, LDLSSNPLK | 0.000 | 0.476 | 0.000 | 0.000 | 0.000 | 0.422 | 0.101 | 0.000 | ||
| 4 spectra, FCLEER | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 2 spectra, YLQLTSK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, SHCILNWPIQK | 0.000 | 0.423 | 0.000 | 0.000 | 0.000 | 0.577 | 0.000 | 0.000 | ||
| 2 spectra, HANPGGPVNFLK | 0.000 | 0.851 | 0.000 | 0.000 | 0.000 | 0.027 | 0.122 | 0.000 | ||
| 1 spectrum, LFDTSSCK | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | ||
| 1 spectrum, EFSPGCFHAIGK | 0.442 | 0.529 | 0.000 | 0.000 | 0.000 | 0.029 | 0.000 | 0.000 | ||
| 1 spectrum, SNTFTGLVSLK | 0.000 | 0.939 | 0.000 | 0.000 | 0.000 | 0.000 | 0.061 | 0.000 | ||
| 4 spectra, LQVALGSR | 0.000 | 0.912 | 0.000 | 0.000 | 0.000 | 0.000 | 0.088 | 0.000 | ||
| 6 spectra, LNHALCLR | 0.000 | 0.869 | 0.000 | 0.000 | 0.000 | 0.000 | 0.131 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
7 spectra |
 |
0.053 0.000 | 0.104 |
0.947 0.871 | 1.000 |
0.000 0.000 | 0.017 |
0.000 0.000 | 0.025 |
0.000 0.000 | 0.035 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.028 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
88 spectra |
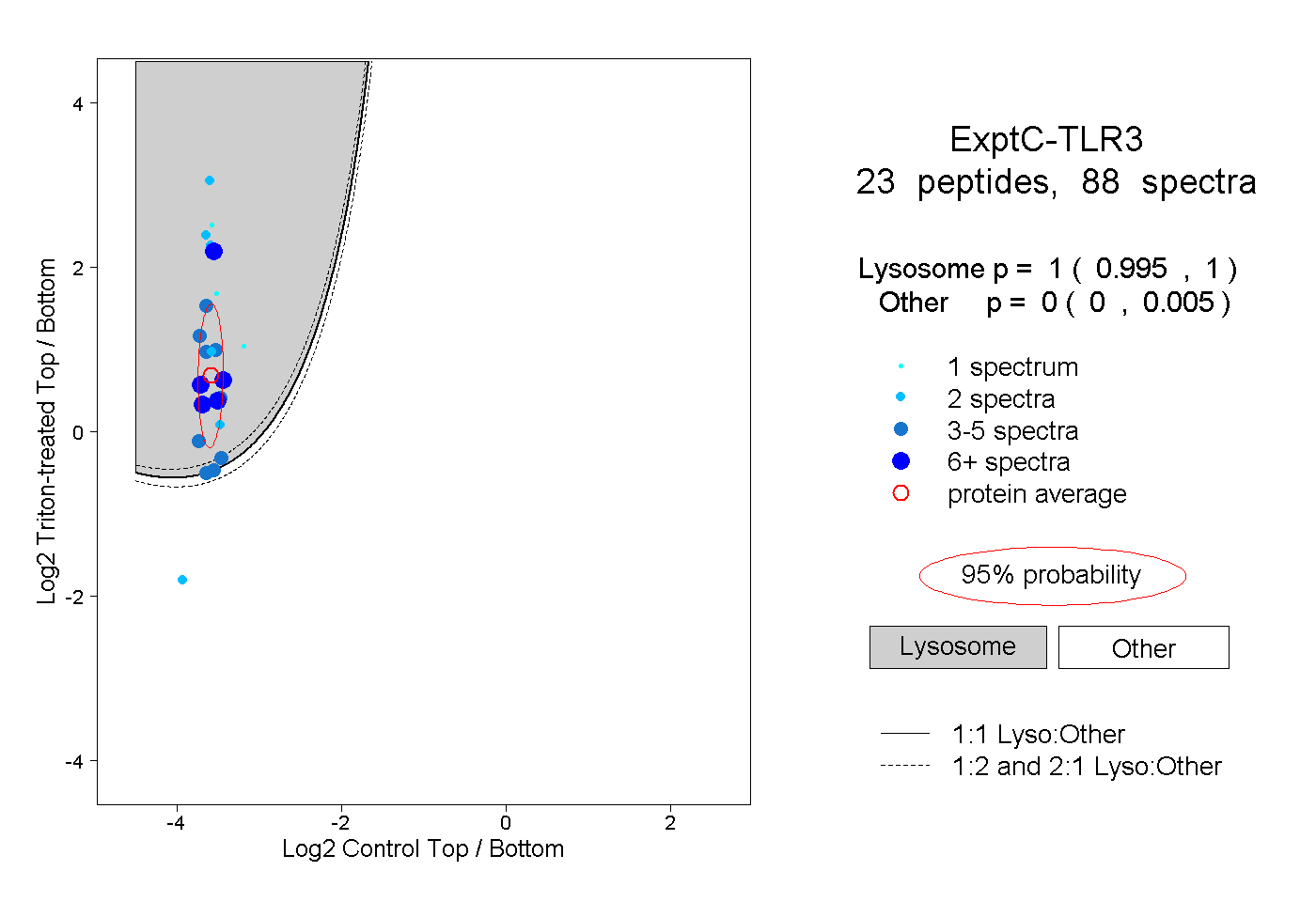 |
1.000 0.995 | 1.000 |
0.000 0.000 | 0.005 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
 |
0.805 0.003 | 1.000 |
0.195 0.000 | 0.997 |