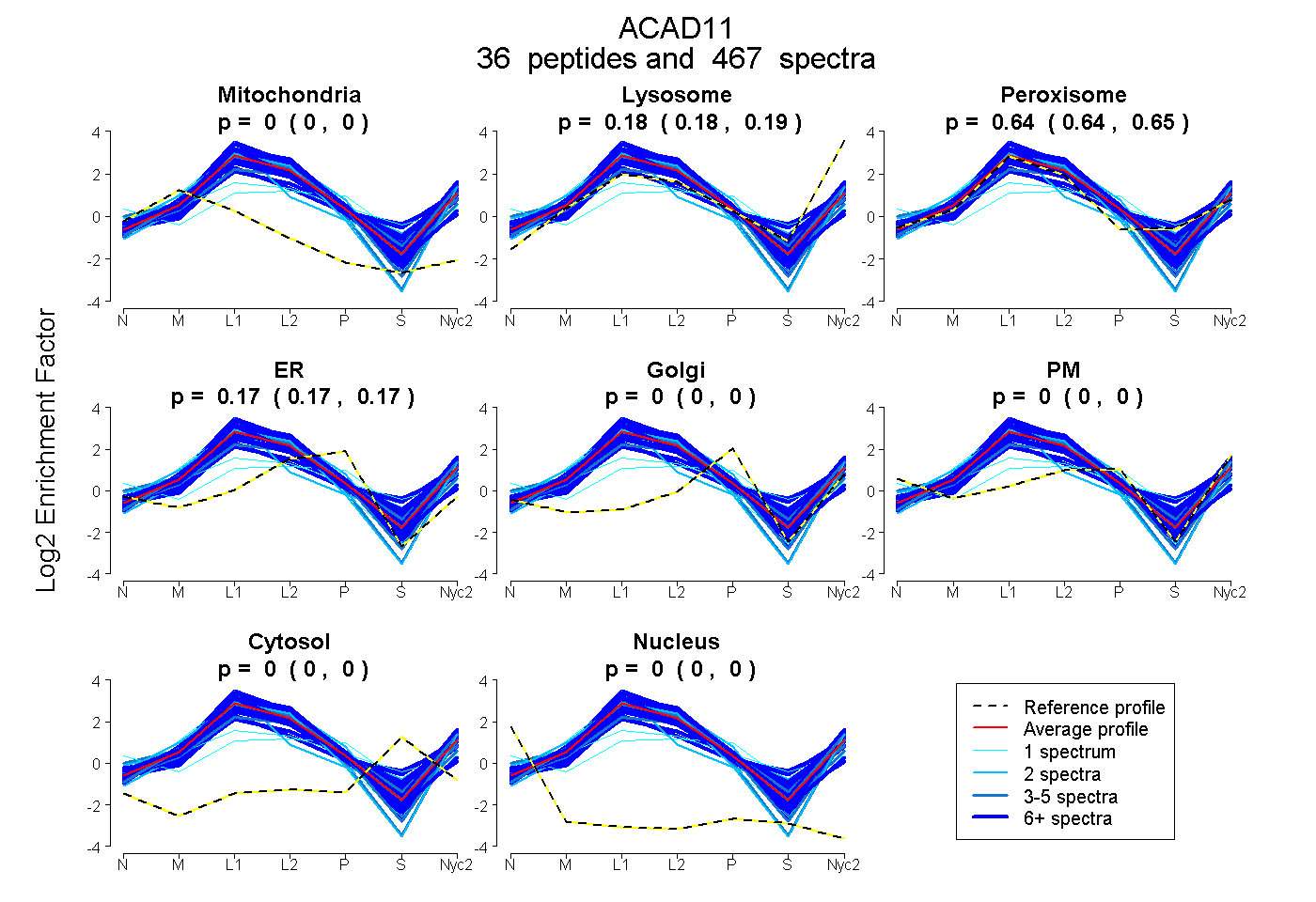
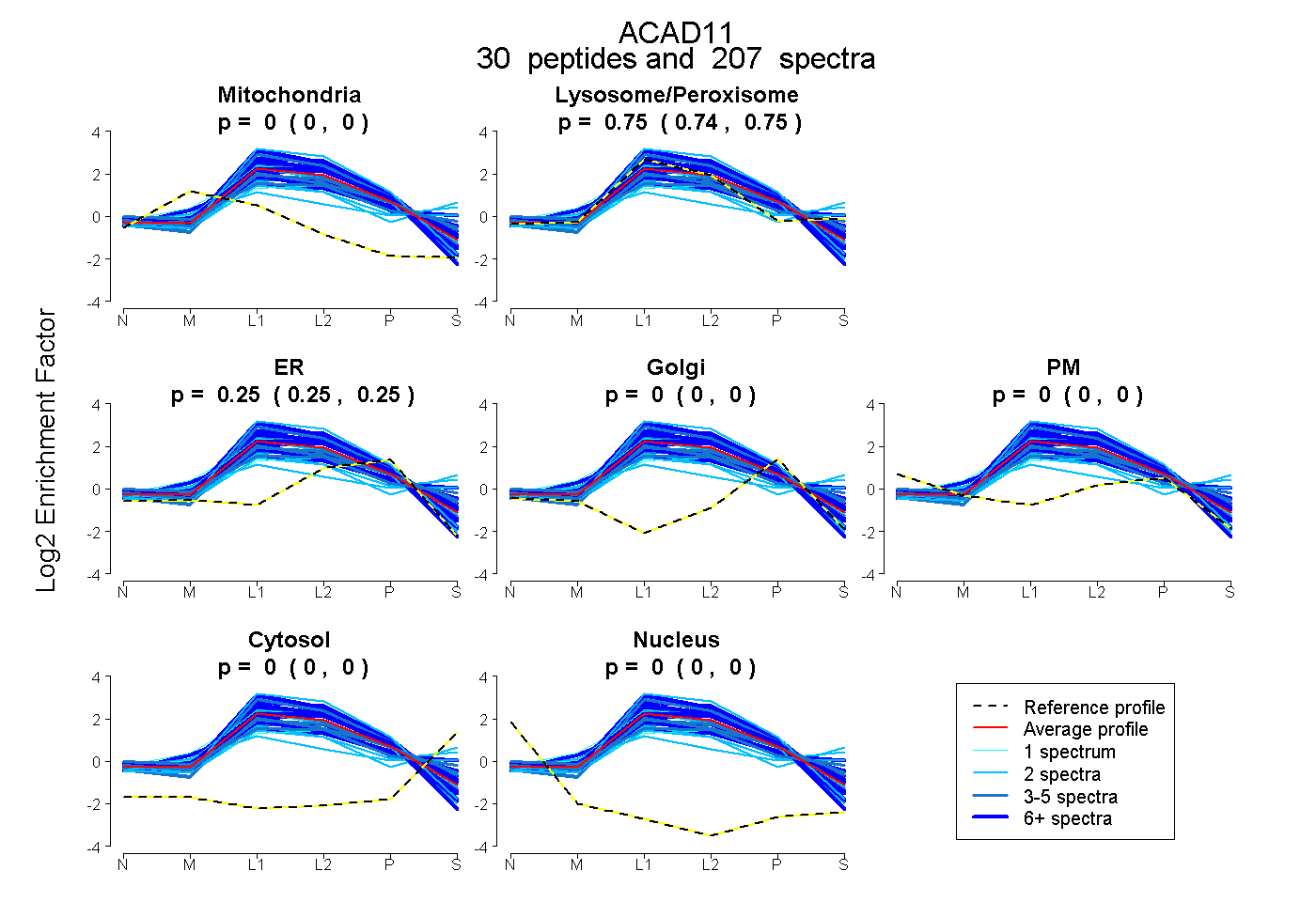
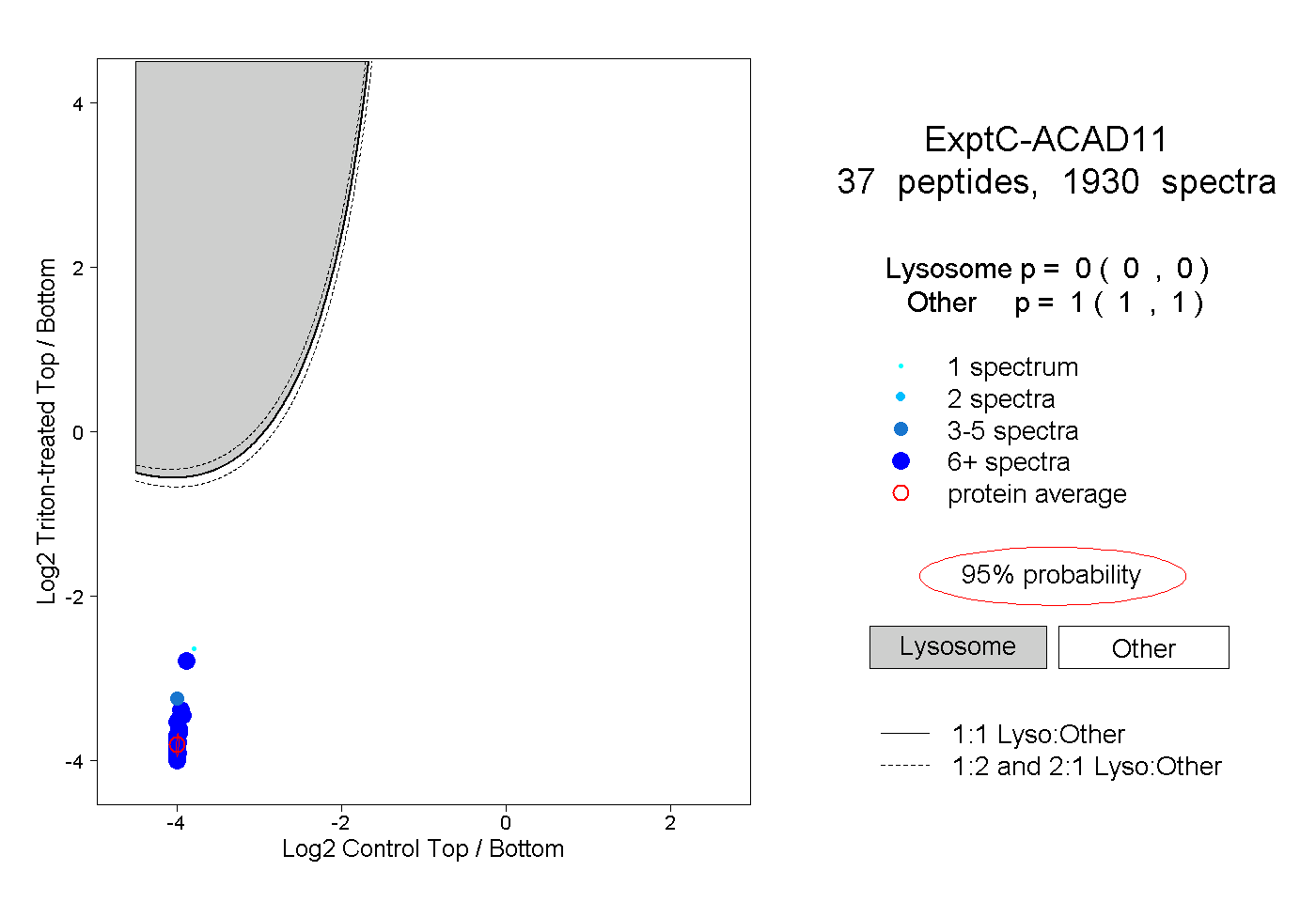
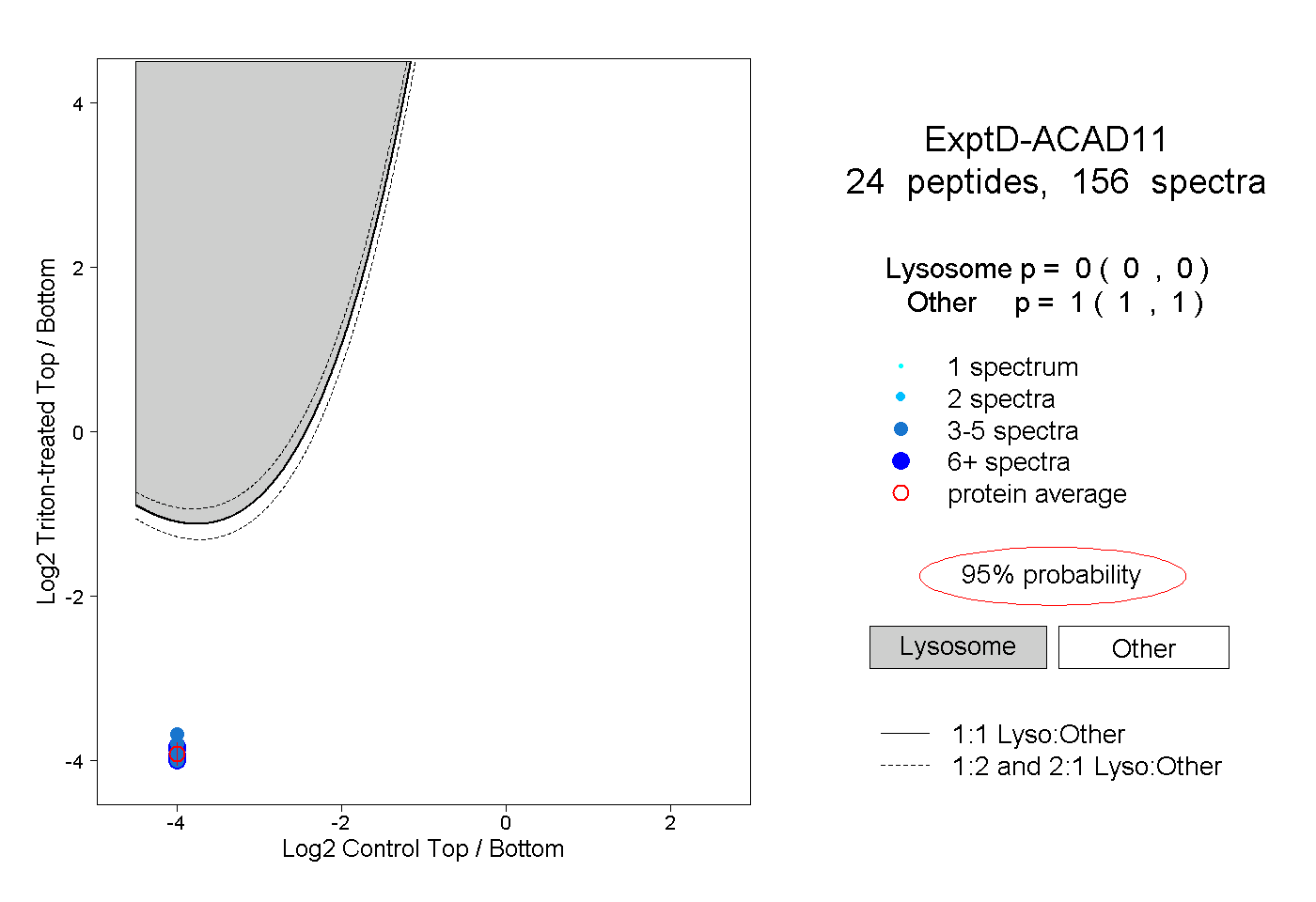
| 4 spectra, TLPMINR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, LALEELR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, AAHSIDTLGSAAAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LFAQSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, EAFGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, DFSIPGVSPAER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TLSTVPPQADAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, YGTGVGYCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 25 spectra, MELQDQAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SGQSNPTFFLQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, EIAMIK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, SVGLAER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, EMDVTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, LADGPDEVHLSAIAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, VPASNLILGEGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, GQEVLTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, QQWLEPLLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 19 spectra, GFEISQGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DTVEVLPQHK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, NLPDSDNEECLVHGDFK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LDNIVFHPK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, TESPSVSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, QVSTWTK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 21 spectra, GSQAYVLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |