peptides
spectra
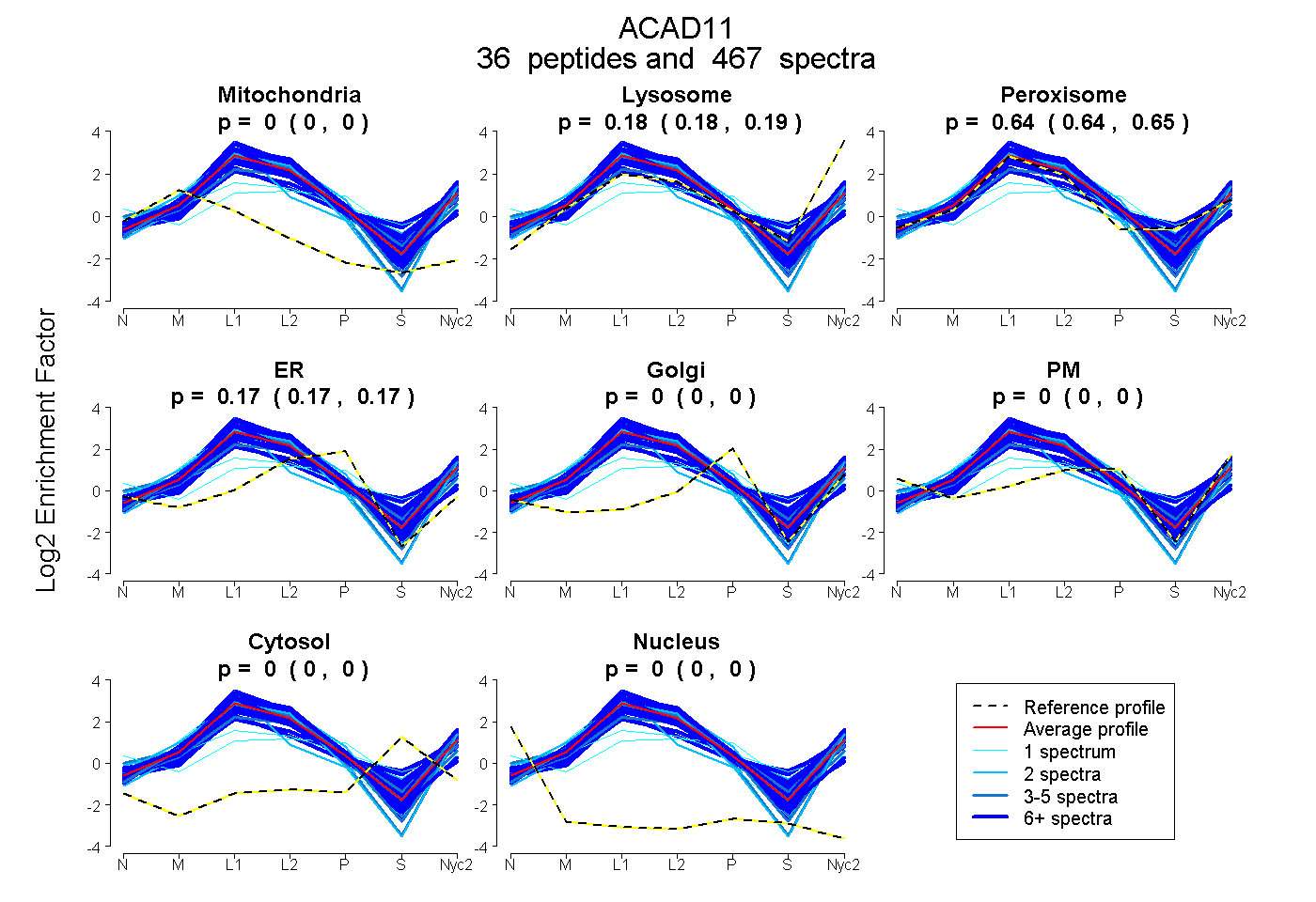
0.000 | 0.000
0.183 | 0.186
0.643 | 0.646
0.169 | 0.172
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
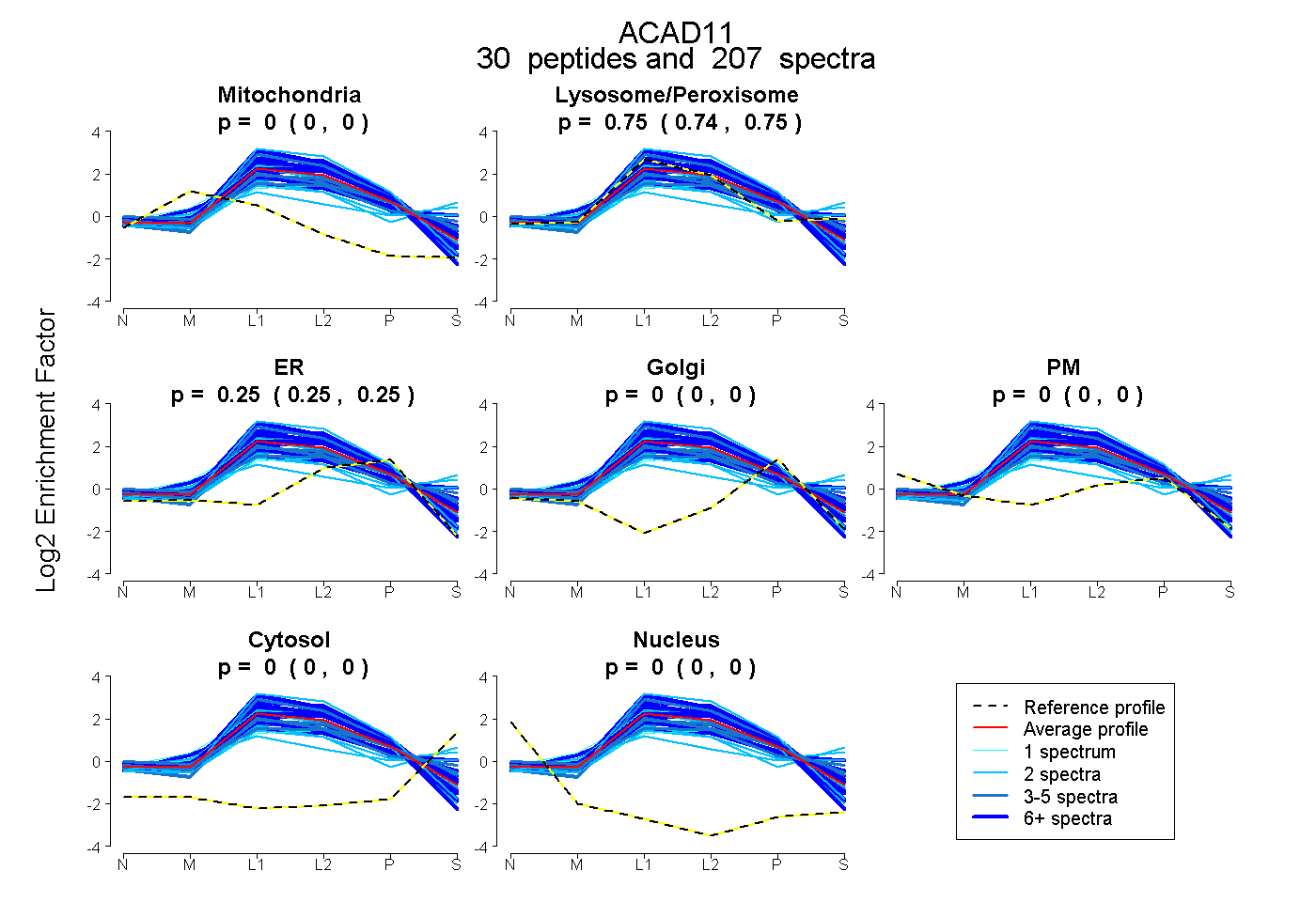
0.000 | 0.000
0.745 | 0.751
0.249 | 0.254
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
467 spectra |
 |
0.000 0.000 | 0.000 |
0.185 0.183 | 0.186 |
0.645 0.643 | 0.646 |
0.171 0.169 | 0.172 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
207 spectra |
 |
0.000 0.000 | 0.000 |
0.748 0.745 | 0.751 |
0.252 0.249 | 0.254 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 24 spectra, IAVVLGR | 0.000 | 0.822 | 0.178 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, LFAQSR | 0.000 | 0.778 | 0.222 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, EAFGK | 0.000 | 0.761 | 0.239 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, DGGSYIVHGK | 0.000 | 0.770 | 0.000 | 0.000 | 0.000 | 0.230 | 0.000 | |||
| 2 spectra, SGQSNPTFFLQK | 0.000 | 0.659 | 0.341 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, EIAMIK | 0.000 | 0.646 | 0.354 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, SVGLAER | 0.000 | 0.767 | 0.233 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 18 spectra, LAGIAQGVYSR | 0.000 | 0.668 | 0.332 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, QQWLEPLLR | 0.000 | 0.837 | 0.163 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, ILQIMCDR | 0.000 | 0.734 | 0.266 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, NLPDSDNEECLVHGDFK | 0.000 | 0.734 | 0.265 | 0.001 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, QVSTWTK | 0.000 | 0.787 | 0.000 | 0.064 | 0.000 | 0.149 | 0.000 | |||
| 1 spectrum, EVAEYYAQNGNSAEK | 0.000 | 0.517 | 0.483 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 13 spectra, LALEELR | 0.000 | 0.782 | 0.218 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, TLPMINR | 0.000 | 0.778 | 0.222 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, SLEAYLNQHLPGFGSDHR | 0.079 | 0.631 | 0.000 | 0.171 | 0.000 | 0.119 | 0.000 | |||
| 8 spectra, AAHSIDTLGSAAAR | 0.085 | 0.650 | 0.205 | 0.059 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, LYEHEVVAHWIAK | 0.000 | 0.855 | 0.017 | 0.122 | 0.000 | 0.005 | 0.000 | |||
| 5 spectra, QHVFPAEK | 0.000 | 0.781 | 0.219 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, AVLTVTQYR | 0.000 | 0.783 | 0.217 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, TLSTVPPQADAK | 0.000 | 0.834 | 0.166 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, AIQVHGGAGVSQDYPLANMYAIIR | 0.000 | 0.770 | 0.230 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, MELQDQAR | 0.000 | 0.801 | 0.199 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, GFEISQGR | 0.000 | 0.783 | 0.081 | 0.135 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, DTVEVLPQHK | 0.000 | 0.741 | 0.122 | 0.018 | 0.119 | 0.000 | 0.000 | |||
| 3 spectra, WWSSGAGNPK | 0.000 | 0.743 | 0.000 | 0.089 | 0.166 | 0.003 | 0.000 | |||
| 4 spectra, LDNIVFHPK | 0.000 | 0.821 | 0.179 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, WEHPLVIEK | 0.000 | 0.743 | 0.257 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, GSQAYVLR | 0.000 | 0.773 | 0.227 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 19 spectra, TESPSVSR | 0.000 | 0.627 | 0.373 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1930 spectra |
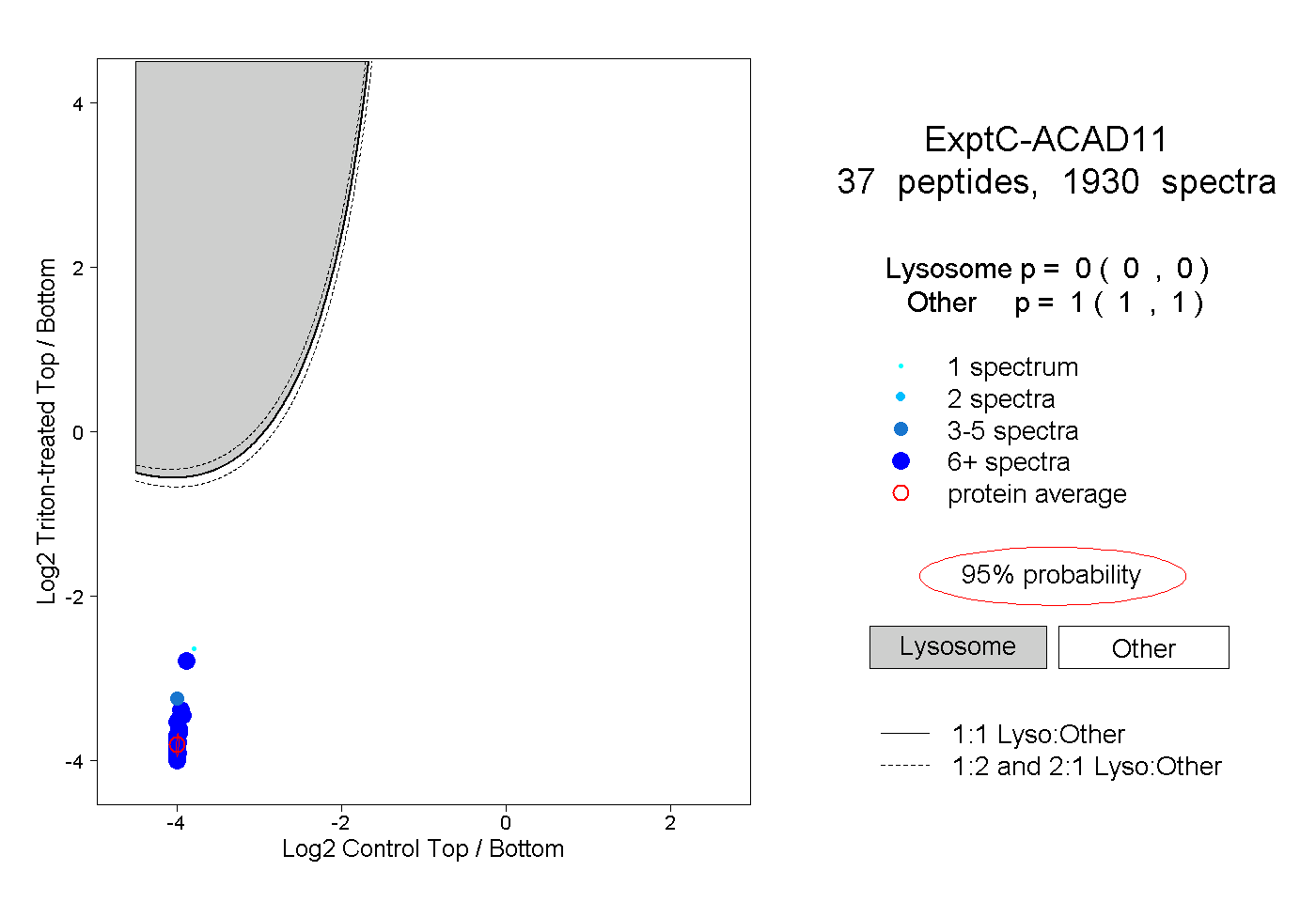 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
156 spectra |
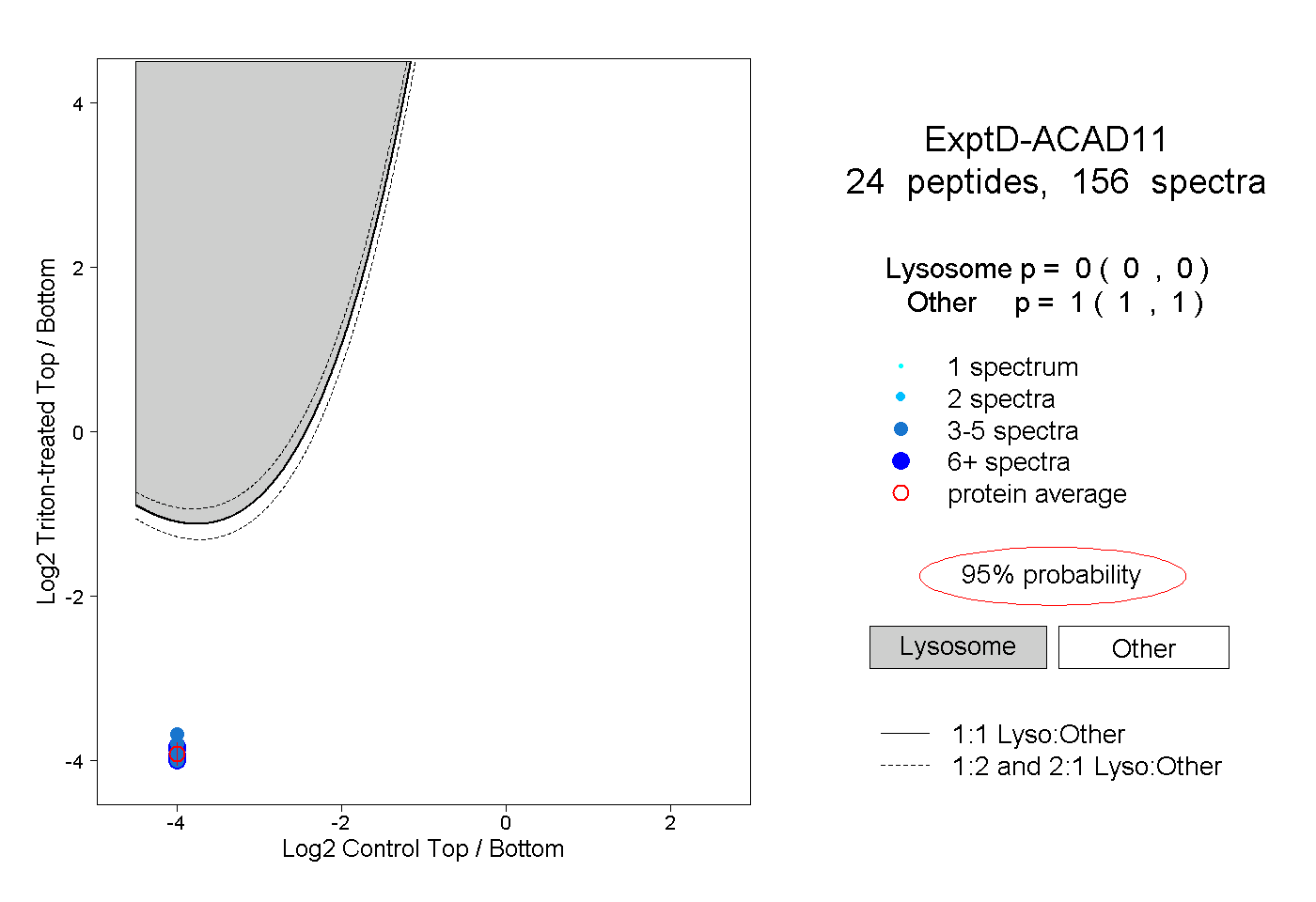 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |