peptides
spectra
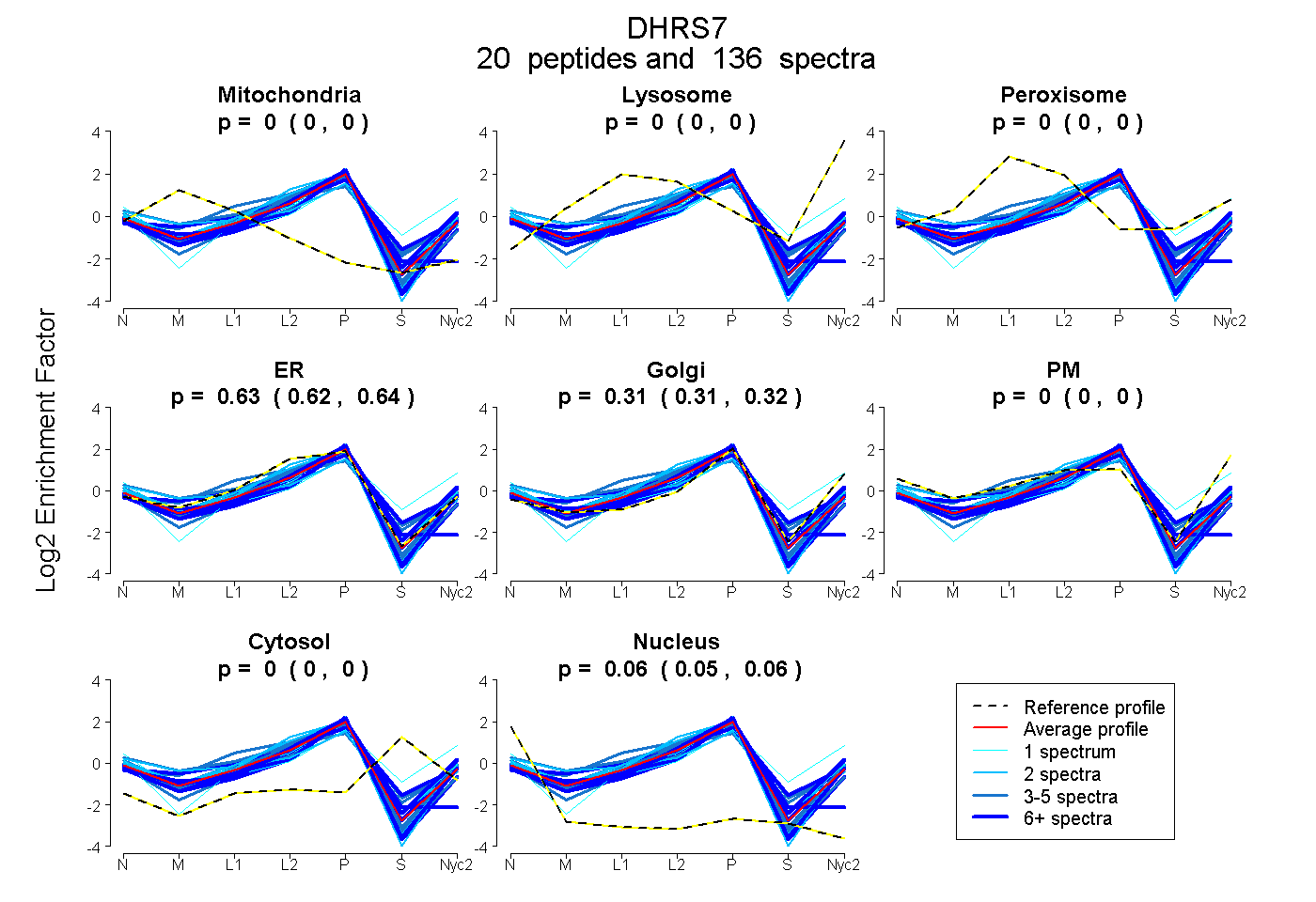
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.623 | 0.636
0.306 | 0.321
0.000 | 0.000
0.000 | 0.000
0.054 | 0.058
peptides
spectra

0.000 | 0.000
0.000 | 0.012
0.590 | 0.637
0.247 | 0.279
0.102 | 0.128
0.000 | 0.003
0.000 | 0.007
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
136 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.630 0.623 | 0.636 |
0.314 0.306 | 0.321 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.056 0.054 | 0.058 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
86 spectra |
 |
0.000 0.000 | 0.000 |
0.002 0.000 | 0.012 |
0.610 0.590 | 0.637 |
0.264 0.247 | 0.279 |
0.124 0.102 | 0.128 |
0.000 0.000 | 0.003 |
0.000 0.000 | 0.007 |
| 2 spectra, CVLPHMMER | 0.000 | 0.231 | 0.000 | 0.734 | 0.023 | 0.012 | 0.000 | |||
| 17 spectra, TVLQEFGR | 0.000 | 0.000 | 0.687 | 0.311 | 0.000 | 0.000 | 0.002 | |||
| 1 spectrum, IDILVNNGGR | 0.000 | 0.395 | 0.000 | 0.436 | 0.101 | 0.068 | 0.000 | |||
| 9 spectra, VLGITWYR | 0.000 | 0.000 | 0.730 | 0.202 | 0.053 | 0.000 | 0.015 | |||
| 28 spectra, GFFDVLR | 0.000 | 0.000 | 0.645 | 0.342 | 0.000 | 0.000 | 0.012 | |||
| 6 spectra, DWILQGR | 0.000 | 0.000 | 0.706 | 0.294 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, AAWMGQCPEQALADK | 0.000 | 0.000 | 0.704 | 0.296 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LGVCLVLSAR | 0.000 | 0.260 | 0.000 | 0.506 | 0.234 | 0.000 | 0.000 | |||
| 2 spectra, AVLQEFGK | 0.000 | 0.000 | 0.741 | 0.000 | 0.259 | 0.000 | 0.000 | |||
| 2 spectra, VLIEVNYLGTVSLTK | 0.000 | 0.257 | 0.195 | 0.367 | 0.000 | 0.182 | 0.000 | |||
| 4 spectra, DILVLPLDLADTSSHDIATK | 0.000 | 0.257 | 0.266 | 0.383 | 0.024 | 0.070 | 0.000 | |||
| 2 spectra, AYVWQYVPFR | 0.000 | 0.000 | 0.813 | 0.181 | 0.000 | 0.000 | 0.005 | |||
| 9 spectra, SLVGIVPRPLCSGYAASK | 0.000 | 0.000 | 0.834 | 0.114 | 0.000 | 0.000 | 0.052 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
136 spectra |
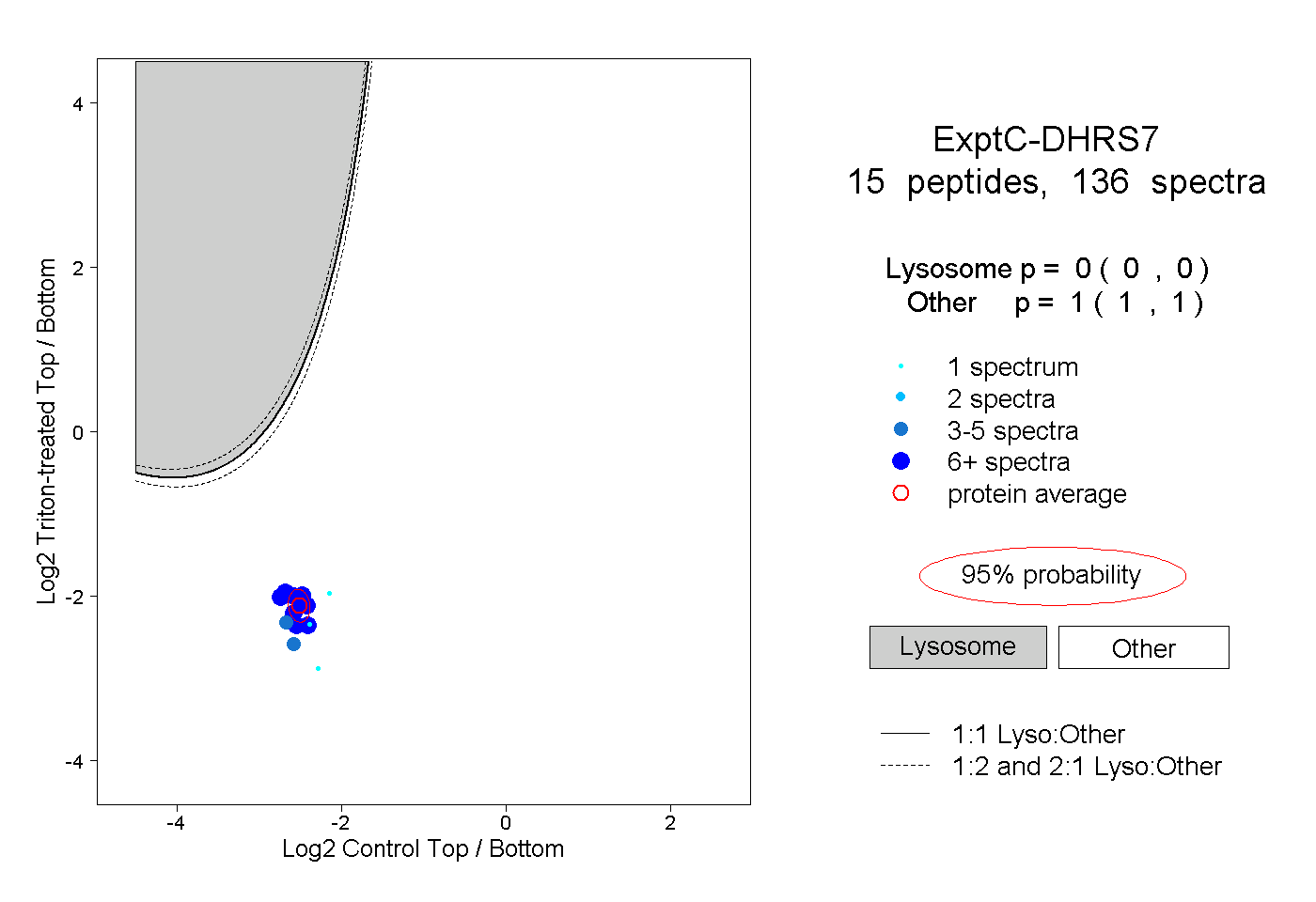 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
16 spectra |
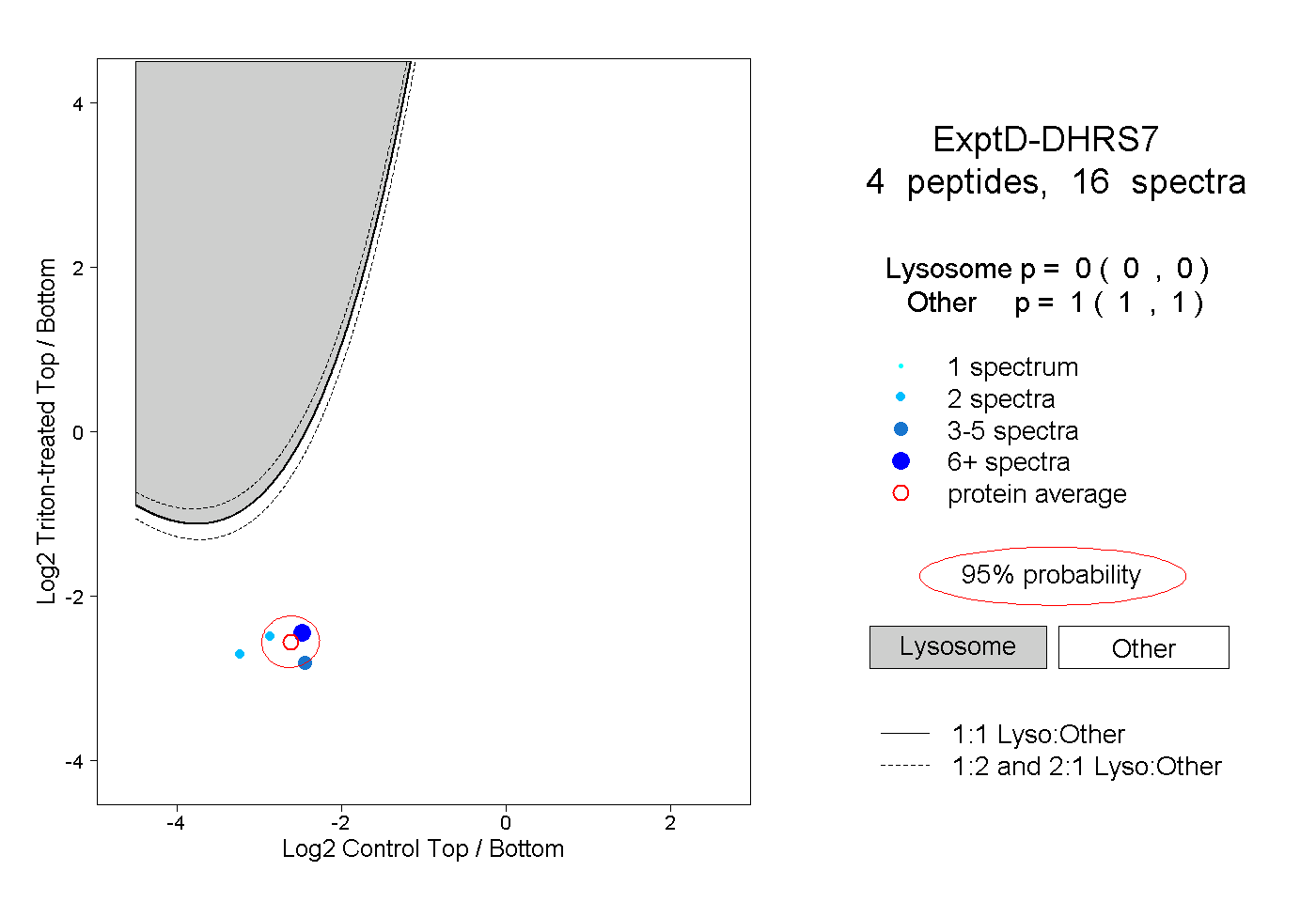 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |