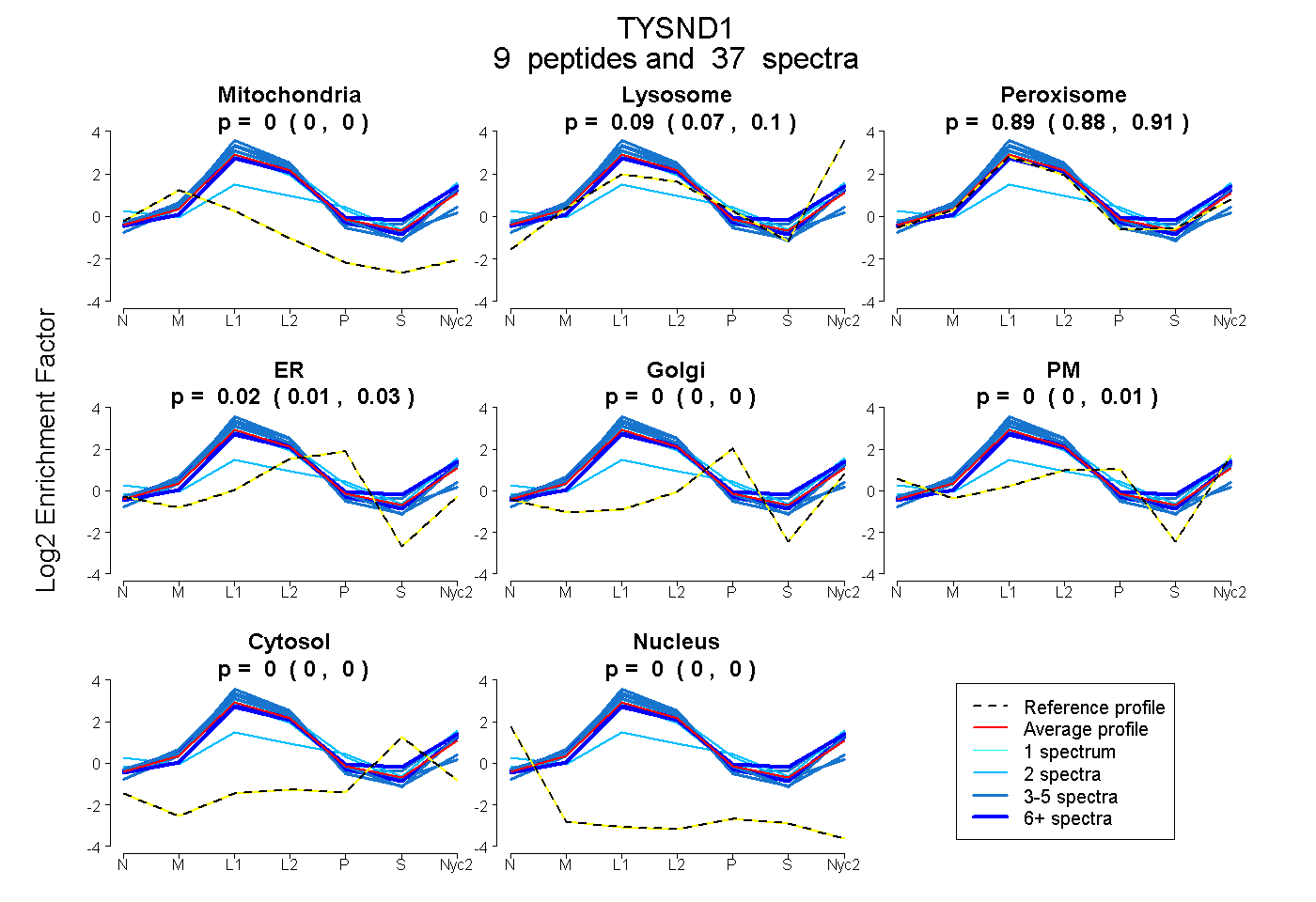
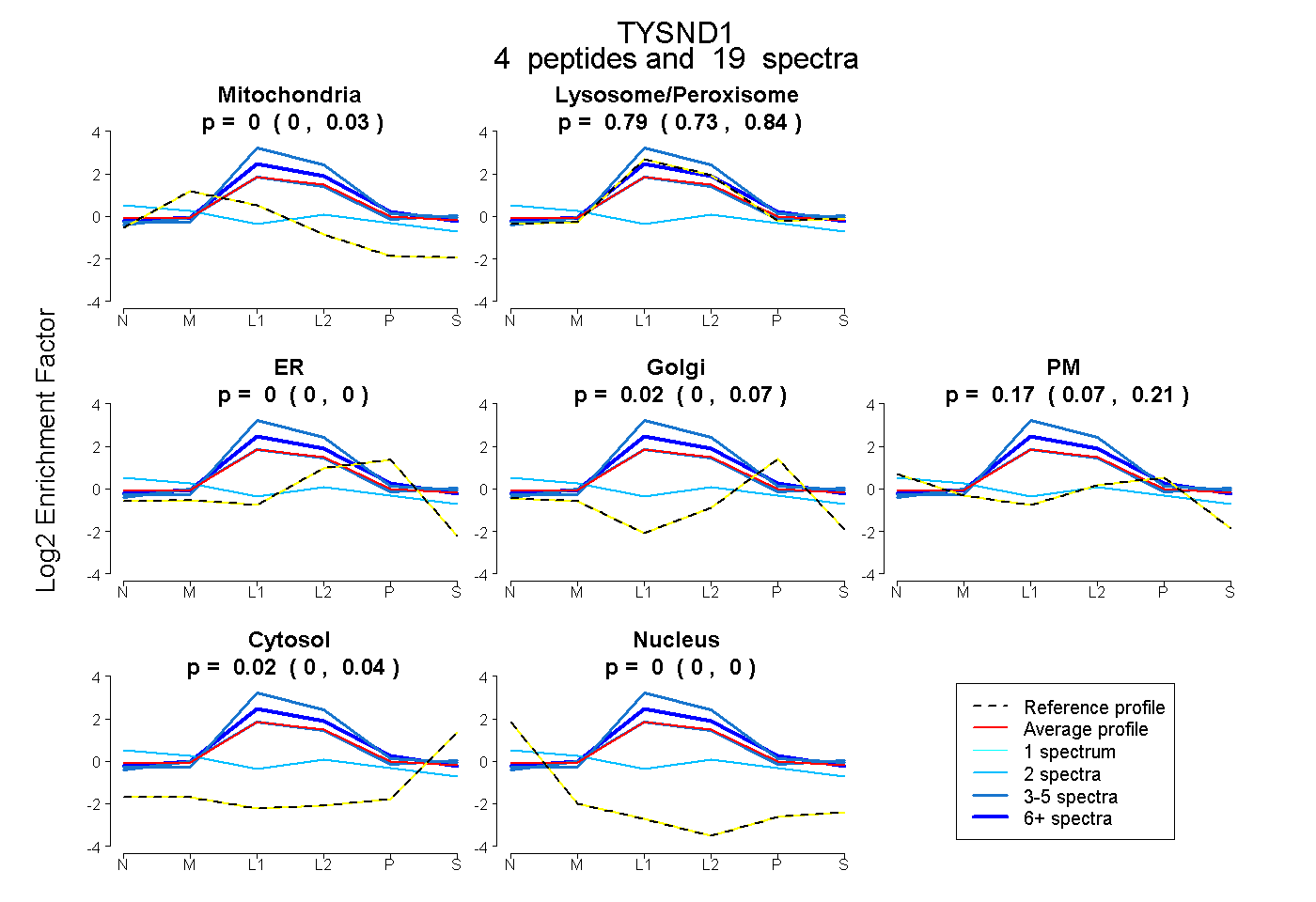
| 5 spectra, GVLSNAAGPLLLTDAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, NVAIWGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, QYSQTGDLCGLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, GPAVTVAPLGAVAK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, AGQPDAGSWSCSGVILSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, ELDHTTEPVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, QWGPSLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TGSAALTQTGAAFLPGDSCSDDLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 11 spectra, LVVTCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, VAEQAGCVVSASR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 9 spectra, ALGWFALLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, VLVHSATPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 14 spectra, LQRPLPEAPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 8 spectra, SPGLVLCHGGIFTPFLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LHVQWGPTAASPAGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SGDLLGIVASNTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |