peptides
spectra
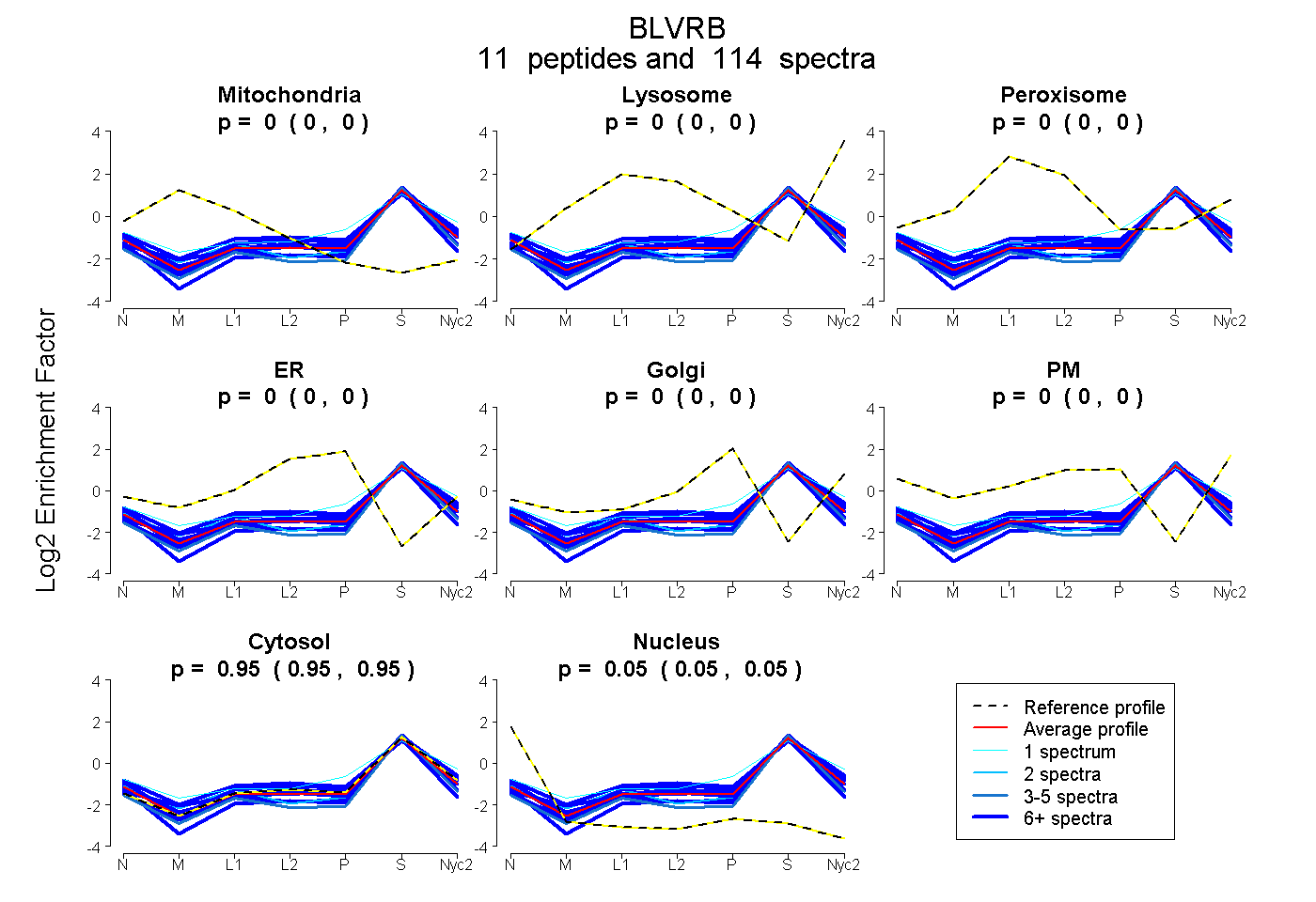
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.948 | 0.952
0.048 | 0.052
peptides
spectra
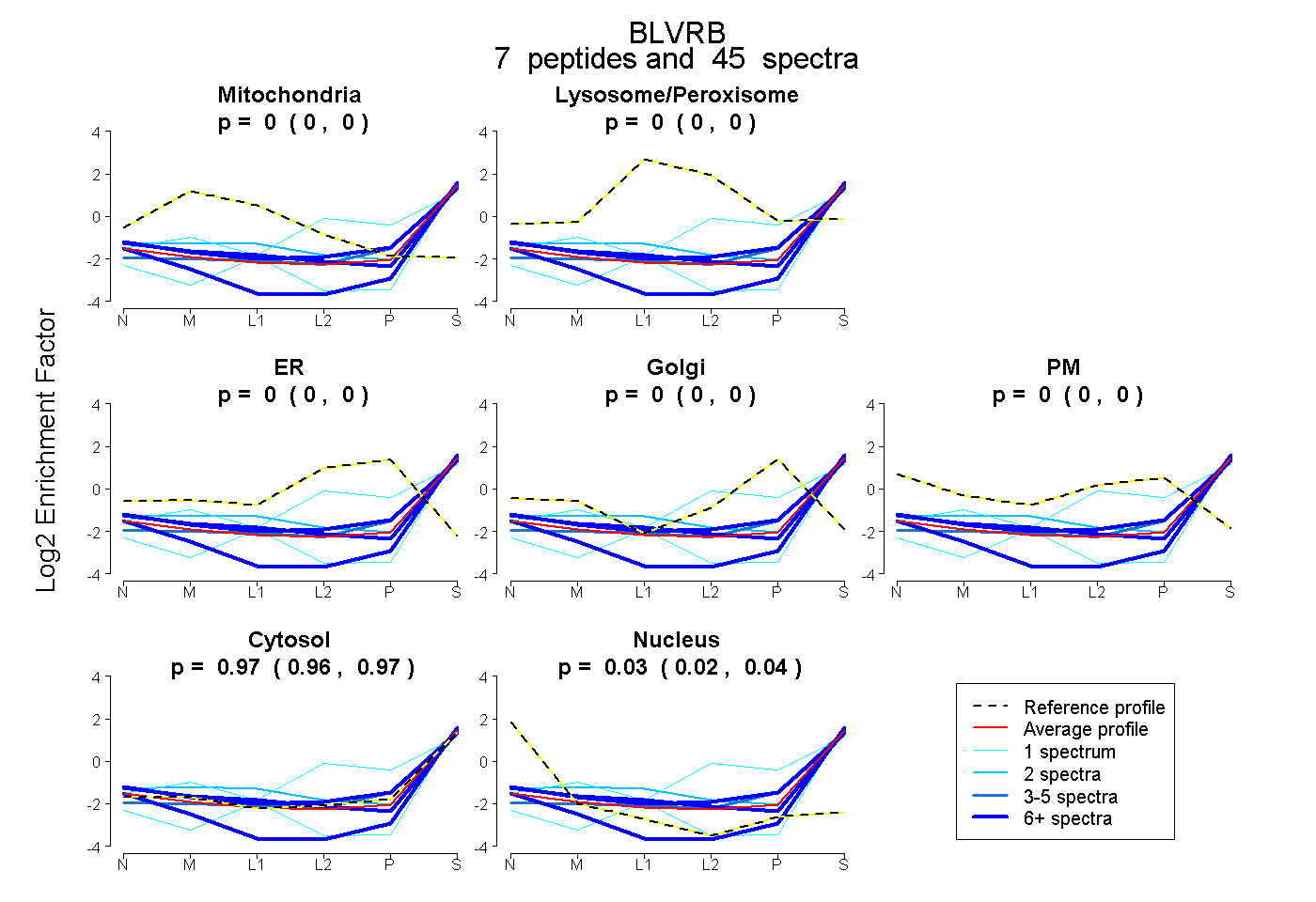
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.960 | 0.974
0.024 | 0.038
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
114 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.950 0.948 | 0.952 |
0.050 0.048 | 0.052 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
45 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.968 0.960 | 0.974 |
0.032 0.024 | 0.038 |
| 10 spectra, IAIFGATGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.862 | 0.138 | |||
| 2 spectra, CLTTHEYDGQK | 0.071 | 0.089 | 0.000 | 0.000 | 0.000 | 0.841 | 0.000 | |||
| 1 spectrum, AHGVDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.988 | 0.012 | |||
| 7 spectra, TYPSHQYD | 0.000 | 0.030 | 0.000 | 0.000 | 0.000 | 0.909 | 0.061 | |||
| 20 spectra, LQDVTDDHIR | 0.000 | 0.031 | 0.000 | 0.000 | 0.049 | 0.899 | 0.021 | |||
| 1 spectrum, LPSEGPQPAHVVVGDVLQAGDVDK | 0.000 | 0.117 | 0.243 | 0.000 | 0.000 | 0.640 | 0.000 | |||
| 4 spectra, HDLGHFMLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
110 spectra |
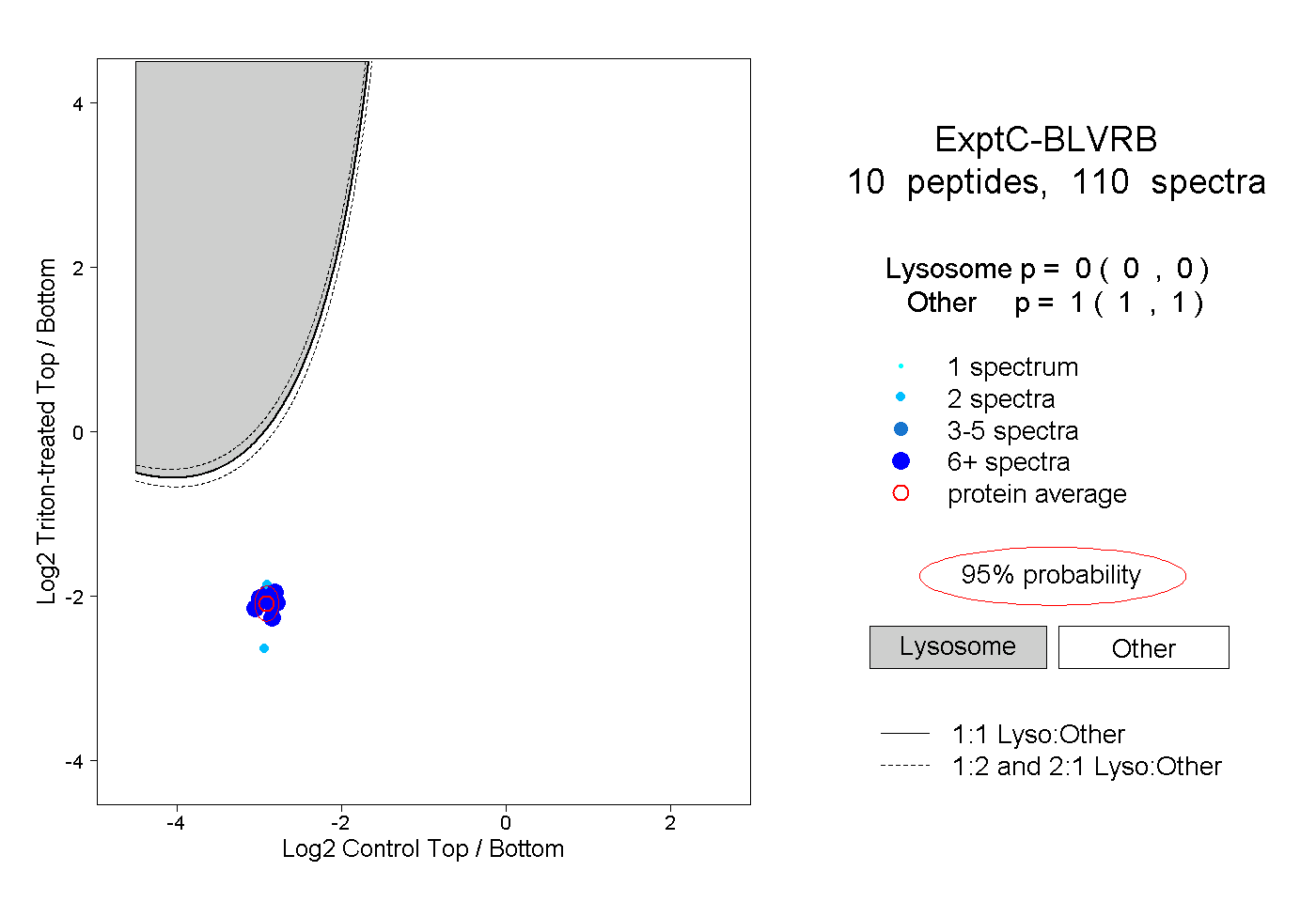 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
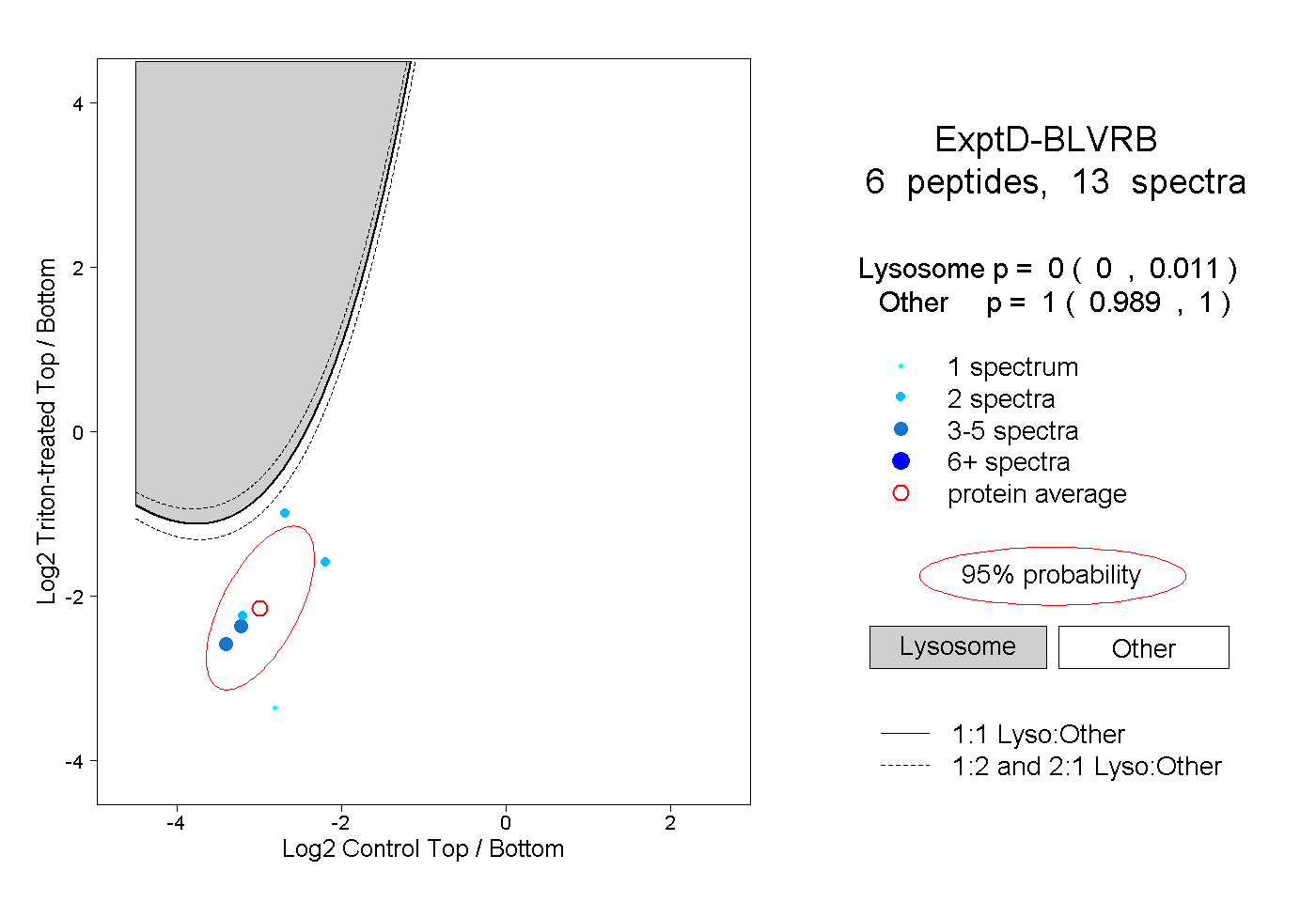 |
0.000 0.000 | 0.011 |
1.000 0.989 | 1.000 |