peptides
spectra
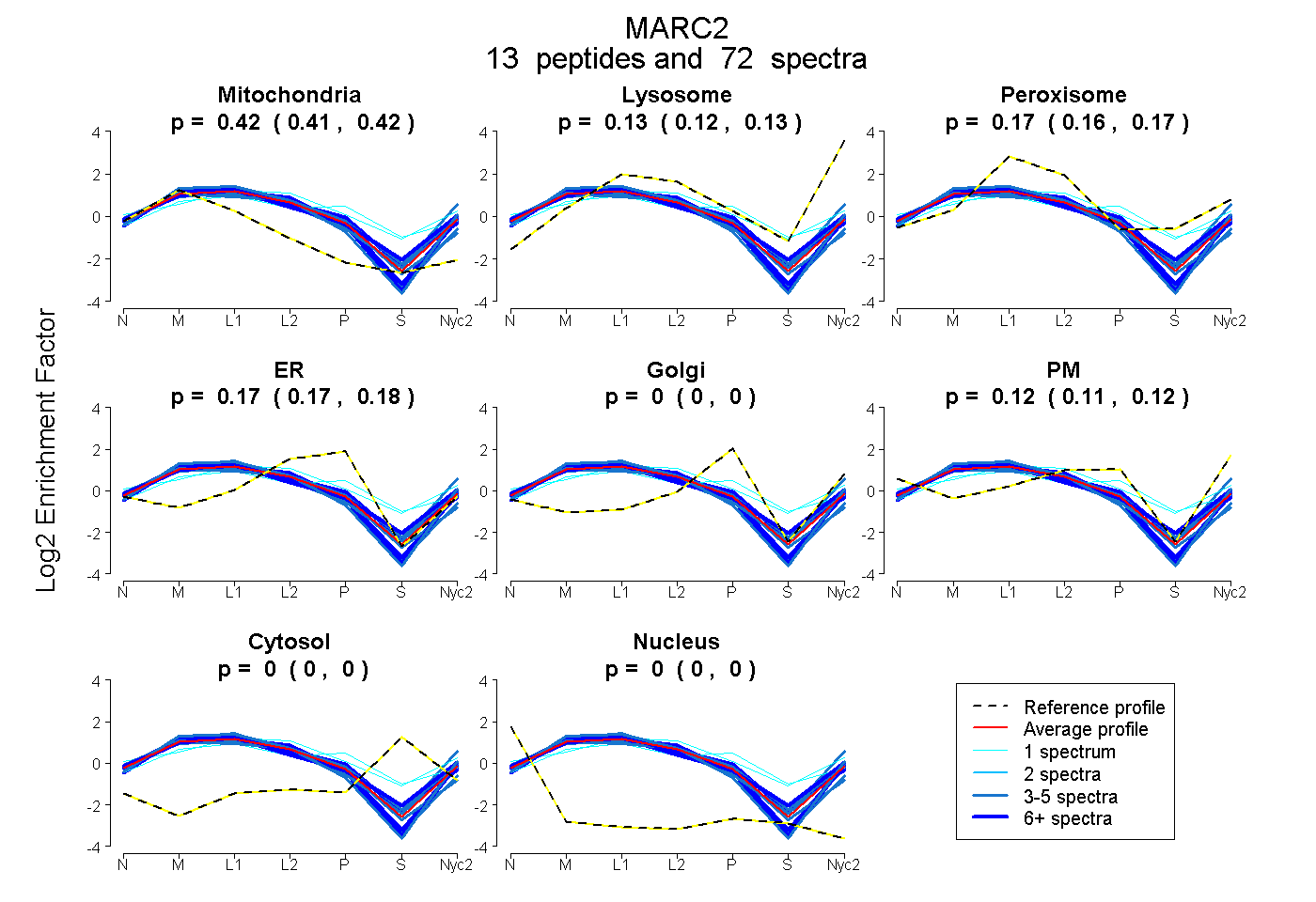
0.414 | 0.420
0.121 | 0.131
0.158 | 0.173
0.166 | 0.179
0.000 | 0.000
0.110 | 0.124
0.000 | 0.000
0.000 | 0.000
peptides
spectra

0.581 | 0.593
0.174 | 0.192
0.220 | 0.237
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
72 spectra |
 |
0.417 0.414 | 0.420 |
0.126 0.121 | 0.131 |
0.166 0.158 | 0.173 |
0.173 0.166 | 0.179 |
0.000 0.000 | 0.000 |
0.118 0.110 | 0.124 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
52 spectra |
 |
0.587 0.581 | 0.593 |
0.184 0.174 | 0.192 |
0.230 0.220 | 0.237 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 3 spectra, FWMVVK | 0.547 | 0.295 | 0.158 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, GSSSSTALAR | 0.364 | 0.200 | 0.076 | 0.126 | 0.234 | 0.000 | 0.000 | |||
| 2 spectra, WFTSYLK | 0.556 | 0.200 | 0.197 | 0.013 | 0.035 | 0.000 | 0.000 | |||
| 1 spectrum, QLQQVGTVSK | 0.697 | 0.111 | 0.191 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, DCGDEVAR | 0.652 | 0.192 | 0.156 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, VGDPVYR | 0.573 | 0.141 | 0.287 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, VWIYPIK | 0.233 | 0.457 | 0.000 | 0.310 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, EPLETLK | 0.510 | 0.142 | 0.348 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, IPSSGGK | 0.474 | 0.335 | 0.000 | 0.151 | 0.041 | 0.000 | 0.000 | |||
| 9 spectra, LFGLDIK | 0.709 | 0.182 | 0.108 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, LGLPGQPR | 0.665 | 0.142 | 0.193 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, SIYQSSPLFGMYFSVEK | 0.436 | 0.390 | 0.000 | 0.068 | 0.000 | 0.106 | 0.000 | |||
| 2 spectra, EDGHMITAR | 0.530 | 0.217 | 0.133 | 0.000 | 0.120 | 0.000 | 0.000 | |||
| 1 spectrum, VLSCPR | 0.808 | 0.016 | 0.176 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
550 spectra |
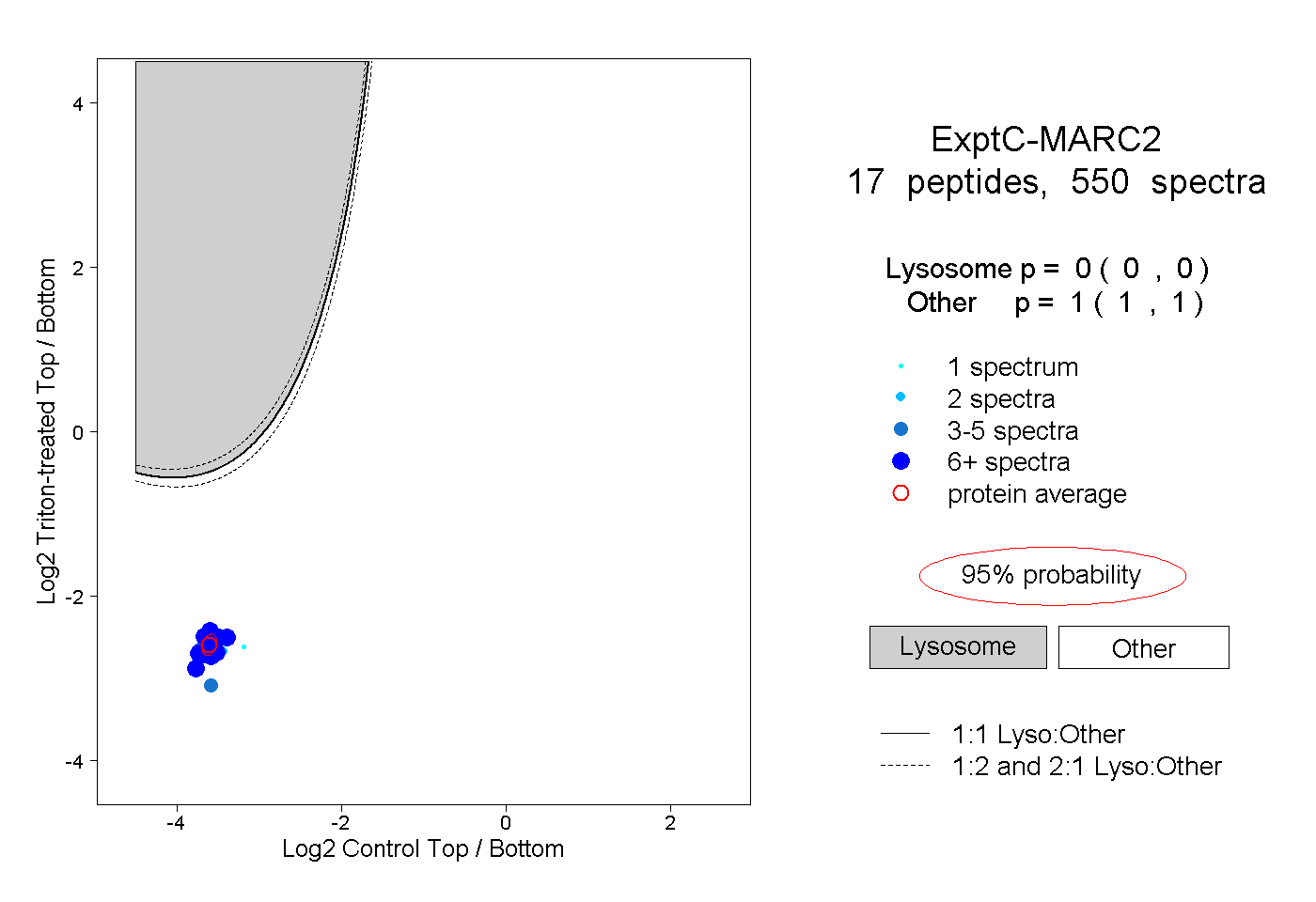 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
71 spectra |
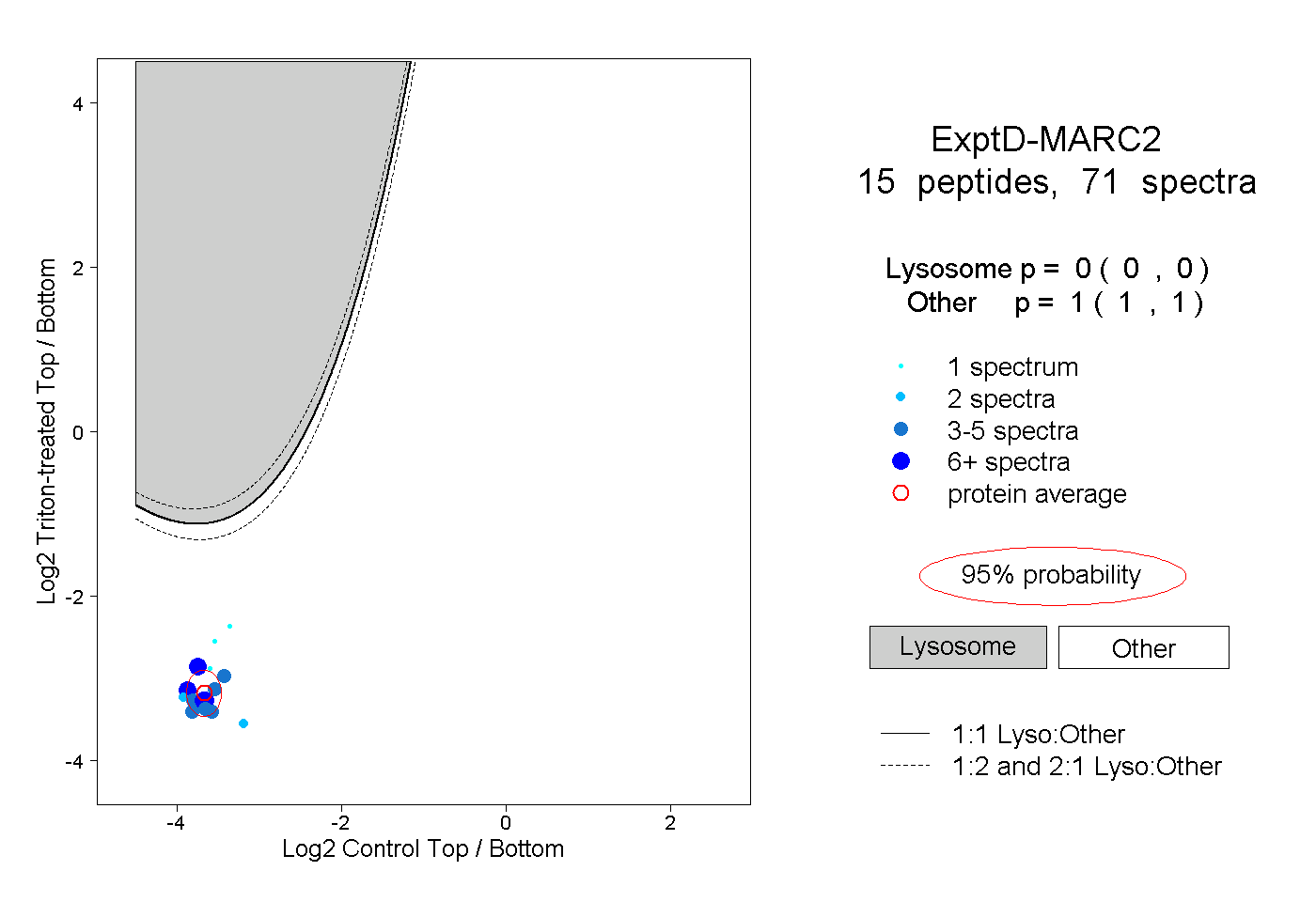 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |