peptides
spectra
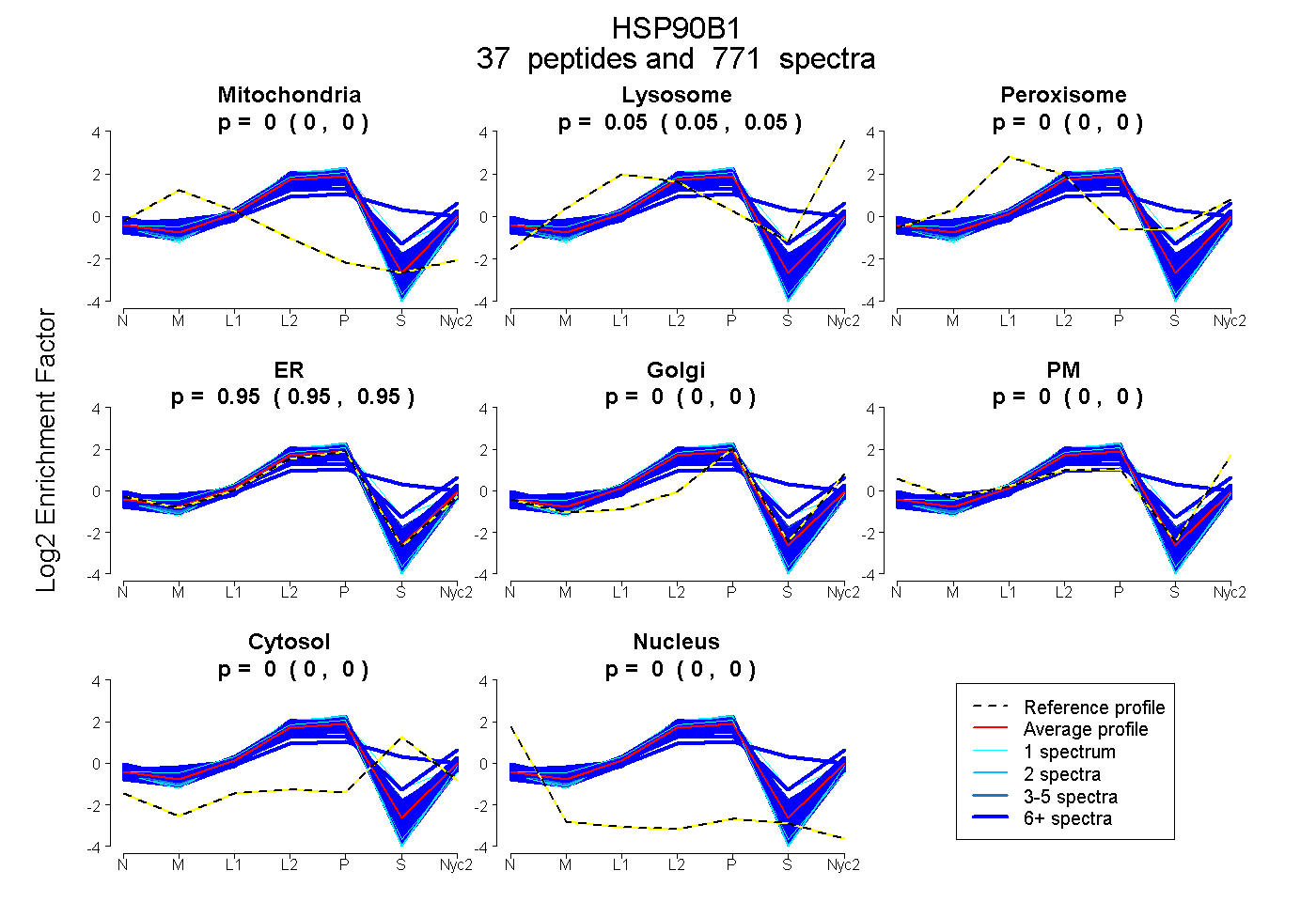
0.000 | 0.000
0.051 | 0.052
0.000 | 0.000
0.948 | 0.949
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
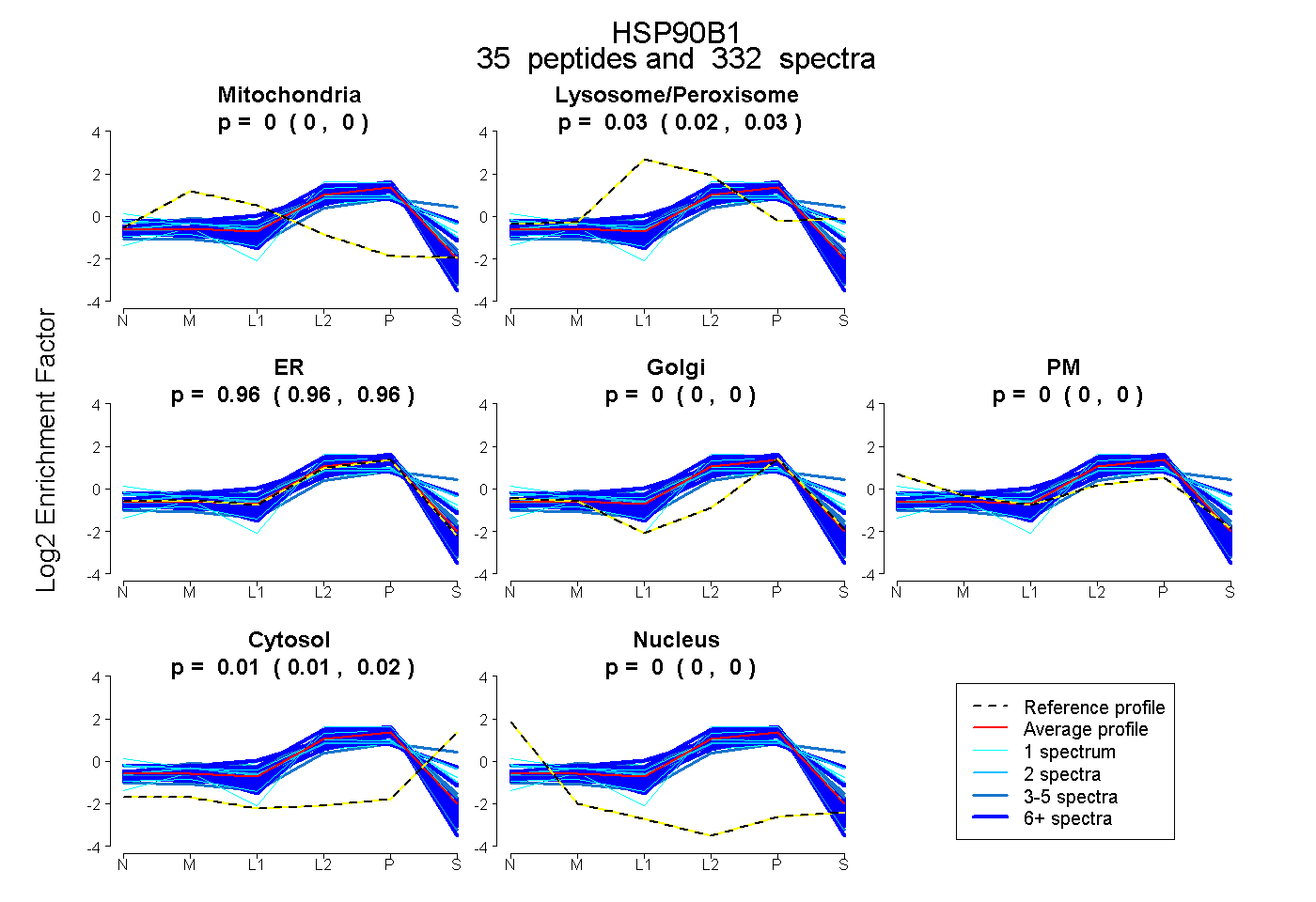
0.000 | 0.000
0.023 | 0.027
0.957 | 0.963
0.000 | 0.000
0.000 | 0.000
0.013 | 0.016
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
771 spectra |
 |
0.000 0.000 | 0.000 |
0.051 0.051 | 0.052 |
0.000 0.000 | 0.000 |
0.949 0.948 | 0.949 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
332 spectra |
 |
0.000 0.000 | 0.000 |
0.025 0.023 | 0.027 |
0.960 0.957 | 0.963 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.015 0.013 | 0.016 |
0.000 0.000 | 0.000 |
| 1 spectrum, YNDTFWK | 0.000 | 0.283 | 0.385 | 0.178 | 0.092 | 0.062 | 0.000 | |||
| 2 spectra, YSQFINFPIYVWSSK | 0.000 | 0.251 | 0.462 | 0.113 | 0.000 | 0.173 | 0.000 | |||
| 7 spectra, EFEPLLNWMK | 0.000 | 0.000 | 0.988 | 0.000 | 0.000 | 0.012 | 0.000 | |||
| 23 spectra, ETLQQHK | 0.000 | 0.001 | 0.999 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TLDMIK | 0.000 | 0.000 | 0.870 | 0.000 | 0.000 | 0.130 | 0.000 | |||
| 5 spectra, GTTITLVLK | 0.000 | 0.019 | 0.862 | 0.000 | 0.000 | 0.119 | 0.000 | |||
| 6 spectra, AQAYQTGK | 0.000 | 0.386 | 0.139 | 0.359 | 0.115 | 0.000 | 0.000 | |||
| 8 spectra, SGYLLPDTK | 0.000 | 0.157 | 0.487 | 0.287 | 0.000 | 0.070 | 0.000 | |||
| 9 spectra, NLLHVTDTGVGMTR | 0.000 | 0.432 | 0.269 | 0.191 | 0.000 | 0.108 | 0.000 | |||
| 1 spectrum, VFITDDFHDMMPK | 0.000 | 0.000 | 0.911 | 0.078 | 0.000 | 0.010 | 0.000 | |||
| 2 spectra, EEASDYLELDTIK | 0.000 | 0.082 | 0.844 | 0.028 | 0.000 | 0.045 | 0.000 | |||
| 1 spectrum, FDESEK | 0.000 | 0.207 | 0.760 | 0.000 | 0.033 | 0.000 | 0.000 | |||
| 23 spectra, EAESSPFVER | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, NLGTIAK | 0.000 | 0.303 | 0.352 | 0.271 | 0.058 | 0.016 | 0.000 | |||
| 8 spectra, TDDEVVQR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LTESPCALVASQYGWSGNMER | 0.000 | 0.230 | 0.108 | 0.236 | 0.359 | 0.067 | 0.000 | |||
| 5 spectra, SILFVPTSAPR | 0.000 | 0.123 | 0.817 | 0.050 | 0.000 | 0.010 | 0.000 | |||
| 12 spectra, FAFQAEVNR | 0.000 | 0.030 | 0.970 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 19 spectra, LIINSLYK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, LISLTDENALAGNEELTVK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, FQNVAK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 12 spectra, VIVTSK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, GNTLGR | 0.000 | 0.085 | 0.778 | 0.137 | 0.000 | 0.000 | 0.000 | |||
| 13 spectra, EVEEDEYK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, ELISNASDALDK | 0.000 | 0.094 | 0.507 | 0.000 | 0.000 | 0.399 | 0.000 | |||
| 26 spectra, AVVSQR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, DISTNYYASQK | 0.000 | 0.000 | 0.934 | 0.011 | 0.000 | 0.055 | 0.000 | |||
| 28 spectra, LGVIEDHSNR | 0.016 | 0.177 | 0.639 | 0.169 | 0.000 | 0.000 | 0.000 | |||
| 36 spectra, IYFMAGSSR | 0.000 | 0.000 | 0.936 | 0.064 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, YLNFVK | 0.000 | 0.022 | 0.978 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, GVVDSDDLPLNVSR | 0.000 | 0.000 | 0.935 | 0.044 | 0.000 | 0.021 | 0.000 | |||
| 4 spectra, EFGTNIK | 0.053 | 0.045 | 0.901 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 10 spectra, GLFDEYGSK | 0.000 | 0.000 | 0.978 | 0.022 | 0.000 | 0.000 | 0.000 | |||
| 19 spectra, TFEINPR | 0.067 | 0.026 | 0.907 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, SGTSEFLNK | 0.000 | 0.000 | 0.900 | 0.100 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
1466 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
188 spectra |
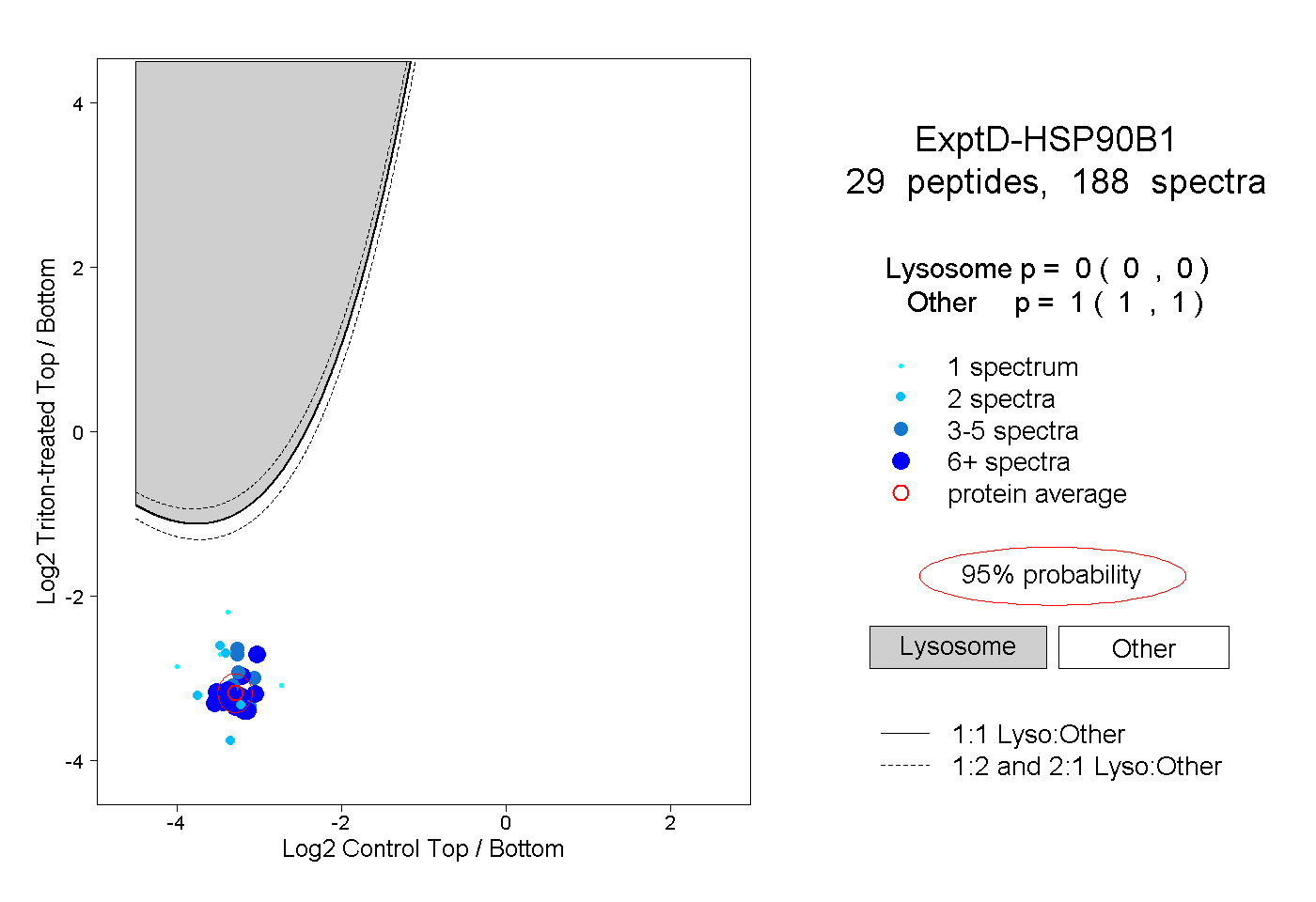 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |