peptides
spectra
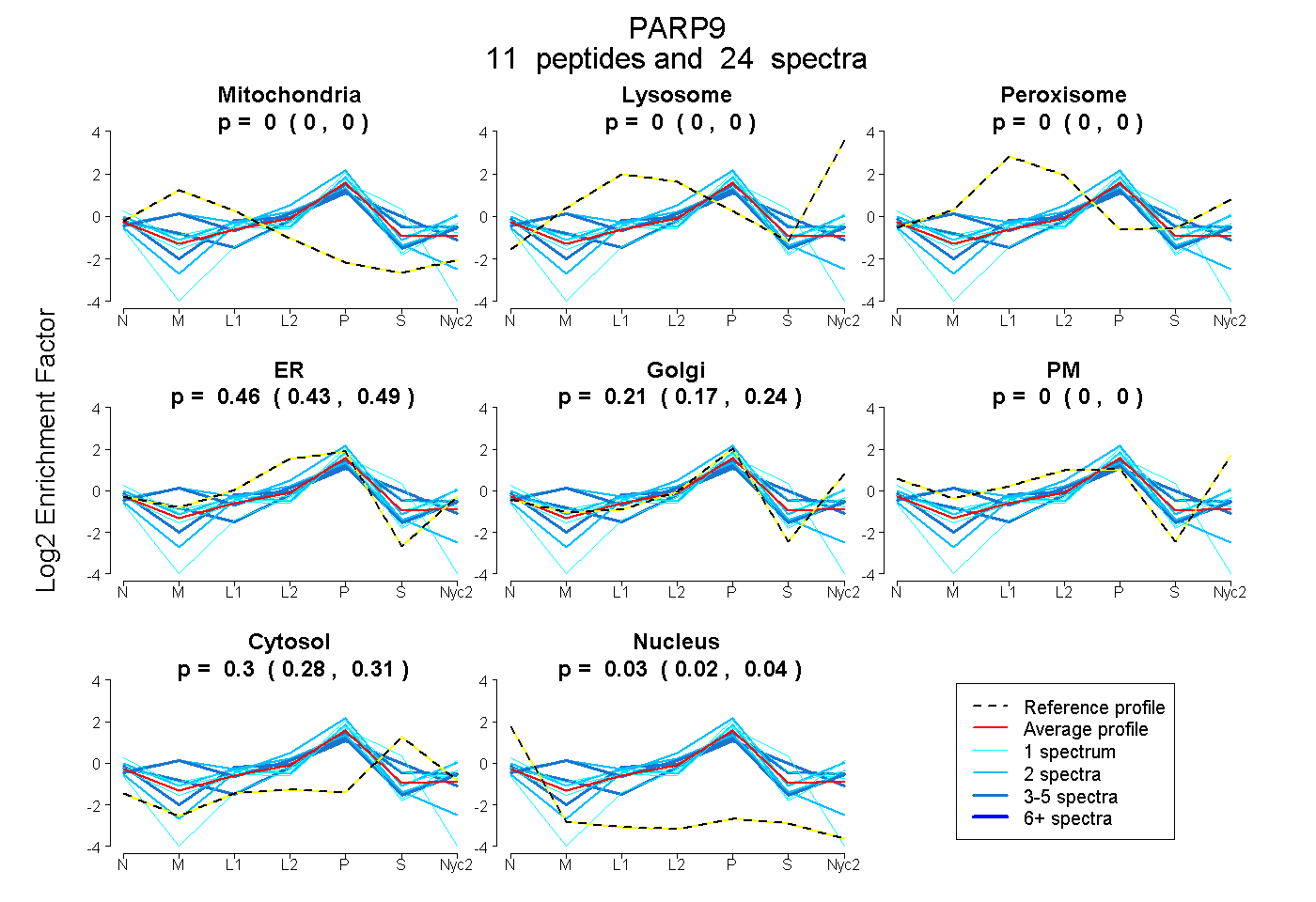
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.427 | 0.490
0.167 | 0.243
0.000 | 0.000
0.284 | 0.315
0.018 | 0.040
peptides
spectra
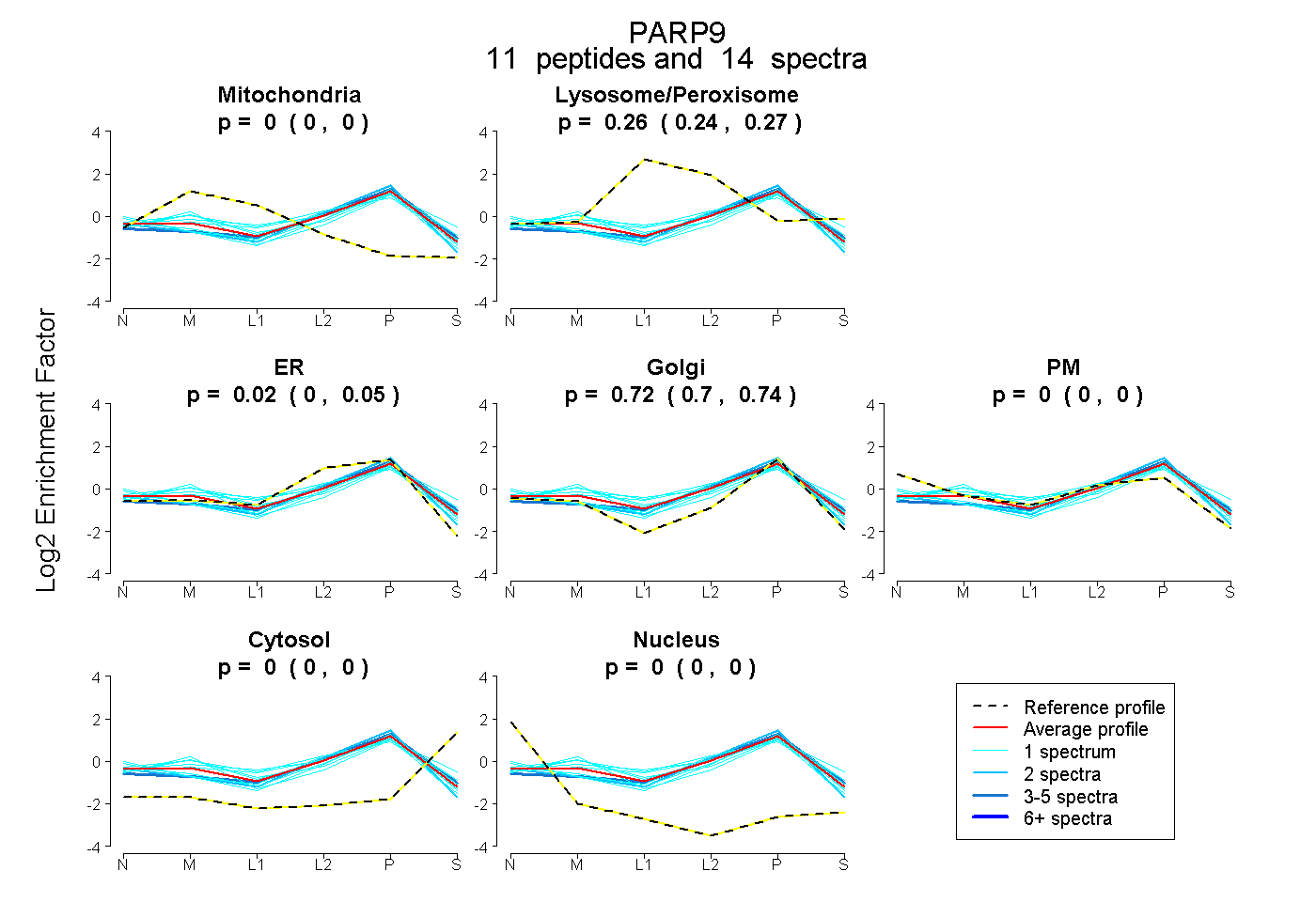
0.000 | 0.000
0.241 | 0.268
0.000 | 0.051
0.699 | 0.735
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
24 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.462 0.427 | 0.490 |
0.208 0.167 | 0.243 |
0.000 0.000 | 0.000 |
0.301 0.284 | 0.315 |
0.030 0.018 | 0.040 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
14 spectra |
 |
0.000 0.000 | 0.000 |
0.257 0.241 | 0.268 |
0.022 0.000 | 0.051 |
0.721 0.699 | 0.735 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, SNESQLYEVLQK | 0.000 | 0.327 | 0.003 | 0.670 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LSSDYQVVQVTK | 0.000 | 0.232 | 0.000 | 0.717 | 0.000 | 0.052 | 0.000 | |||
| 1 spectrum, WIATHGK | 0.073 | 0.238 | 0.000 | 0.690 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TATLEVK | 0.131 | 0.099 | 0.051 | 0.719 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, IVIFPVDVETYK | 0.011 | 0.335 | 0.000 | 0.572 | 0.082 | 0.000 | 0.000 | |||
| 2 spectra, IPVGGFAVTR | 0.000 | 0.087 | 0.389 | 0.523 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, IMFEEIVAFAK | 0.000 | 0.353 | 0.000 | 0.631 | 0.000 | 0.016 | 0.000 | |||
| 3 spectra, HNIFEILK | 0.000 | 0.194 | 0.191 | 0.551 | 0.000 | 0.064 | 0.000 | |||
| 1 spectrum, YLWTCTQDR | 0.097 | 0.125 | 0.287 | 0.491 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, YPTPAGSSSPAQK | 0.000 | 0.217 | 0.112 | 0.444 | 0.109 | 0.118 | 0.000 | |||
| 1 spectrum, QTVSNLR | 0.000 | 0.111 | 0.033 | 0.650 | 0.199 | 0.008 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
35 spectra |
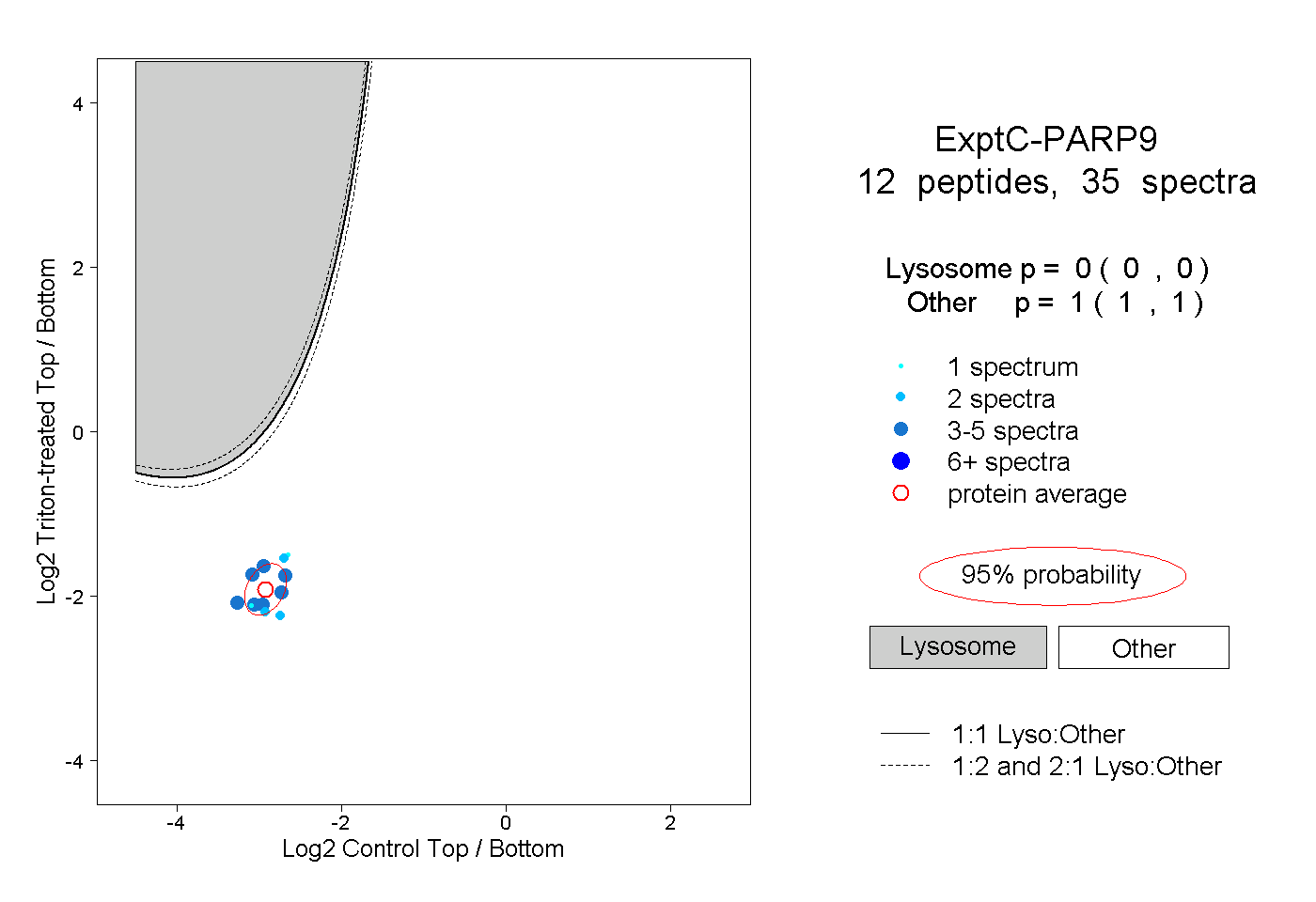 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
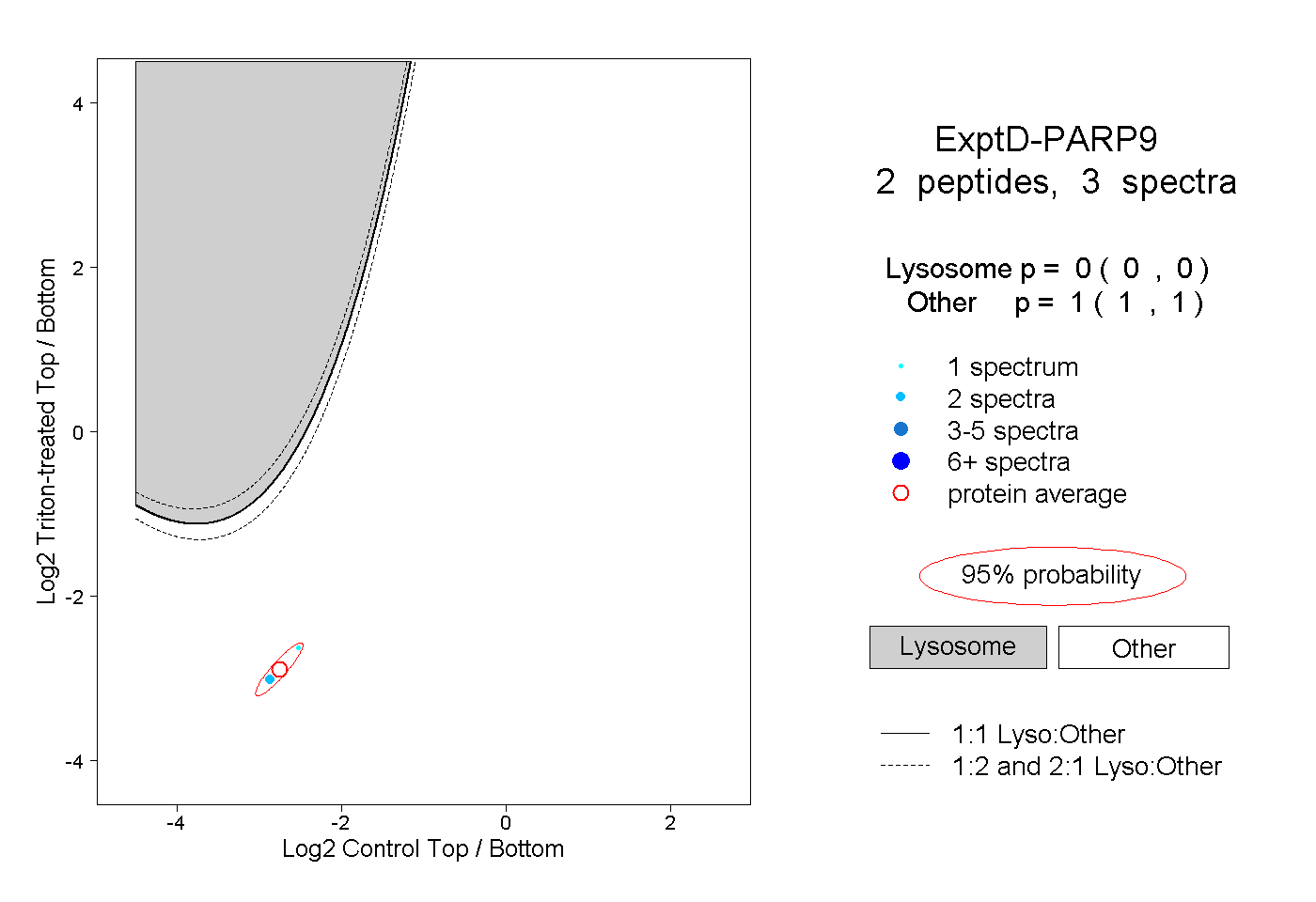 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |