peptides
spectra
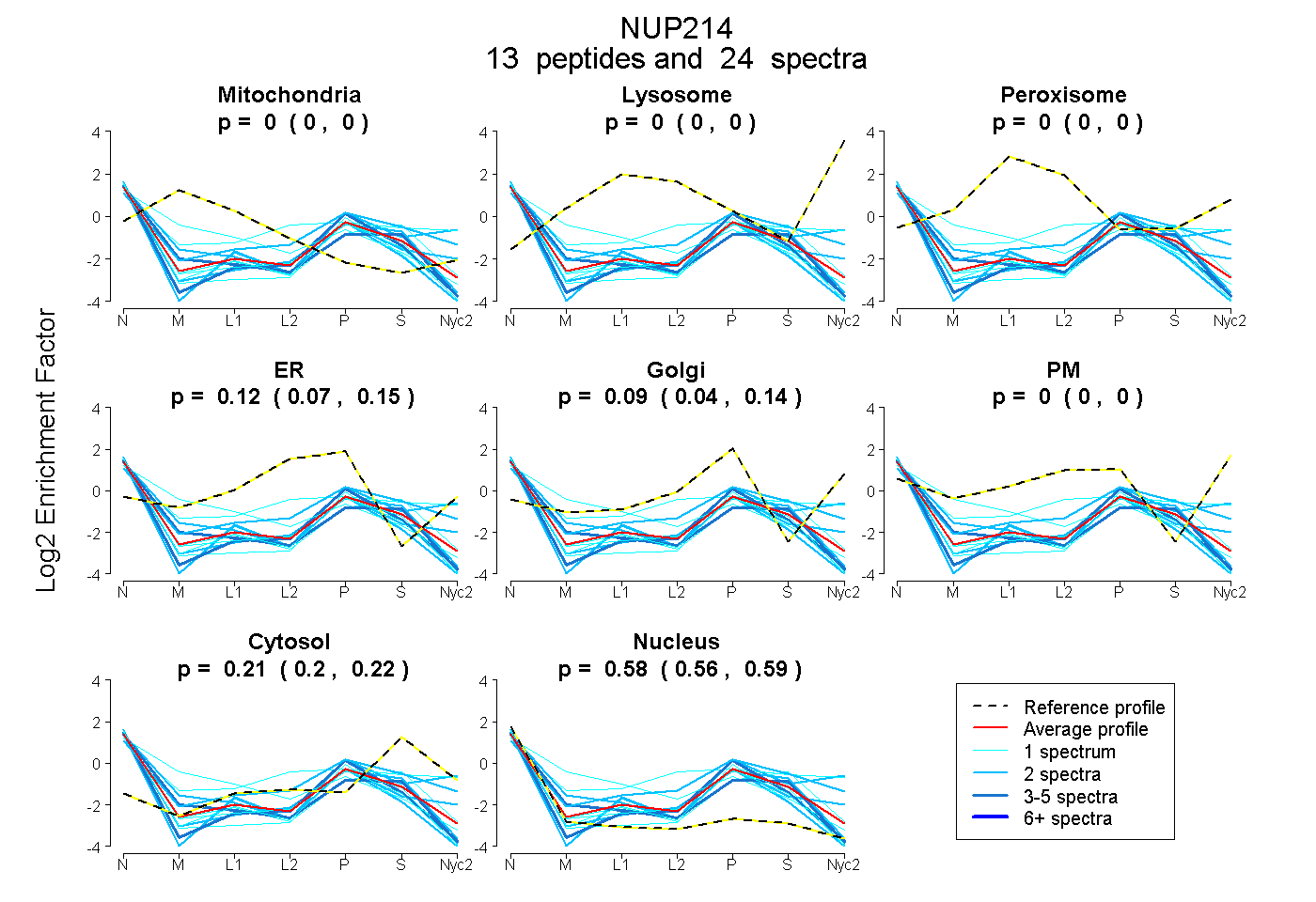
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.068 | 0.152
0.042 | 0.140
0.000 | 0.000
0.201 | 0.223
0.564 | 0.589
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
24 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.115 0.068 | 0.152 |
0.093 0.042 | 0.140 |
0.000 0.000 | 0.000 |
0.214 0.201 | 0.223 |
0.578 0.564 | 0.589 |
| 1 spectrum, ESDPVMAGIGEEIAHFQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.157 | 0.000 | 0.053 | 0.790 | ||
| 2 spectra, SAFLSQR | 0.020 | 0.000 | 0.000 | 0.000 | 0.334 | 0.000 | 0.103 | 0.543 | ||
| 4 spectra, TLELISAEGER | 0.000 | 0.000 | 0.000 | 0.090 | 0.000 | 0.000 | 0.249 | 0.661 | ||
| 1 spectrum, TESDDLHTFLFEIR | 0.359 | 0.000 | 0.000 | 0.200 | 0.000 | 0.000 | 0.037 | 0.405 | ||
| 2 spectra, SEAQLQEIR | 0.000 | 0.000 | 0.000 | 0.105 | 0.000 | 0.000 | 0.280 | 0.615 | ||
| 2 spectra, SAQTAPSSAPSTGQK | 0.000 | 0.000 | 0.000 | 0.154 | 0.000 | 0.000 | 0.090 | 0.756 | ||
| 1 spectrum, TTLLEGFAGVEEAR | 0.000 | 0.000 | 0.000 | 0.148 | 0.000 | 0.000 | 0.166 | 0.686 | ||
| 2 spectra, VIPQGADTTMLATK | 0.000 | 0.000 | 0.000 | 0.062 | 0.245 | 0.061 | 0.334 | 0.298 | ||
| 1 spectrum, TTIESHTKPSPR | 0.000 | 0.000 | 0.000 | 0.139 | 0.000 | 0.000 | 0.141 | 0.720 | ||
| 1 spectrum, QSDQTNWESWVLEDSSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.060 | 0.000 | 0.379 | 0.561 | ||
| 4 spectra, STAPASLSR | 0.000 | 0.000 | 0.000 | 0.166 | 0.000 | 0.000 | 0.156 | 0.678 | ||
| 2 spectra, APHAVLTPVAASQAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.315 | 0.000 | 0.284 | 0.401 | ||
| 1 spectrum, LNHLVDSLQQLR | 0.000 | 0.000 | 0.021 | 0.001 | 0.000 | 0.424 | 0.328 | 0.225 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
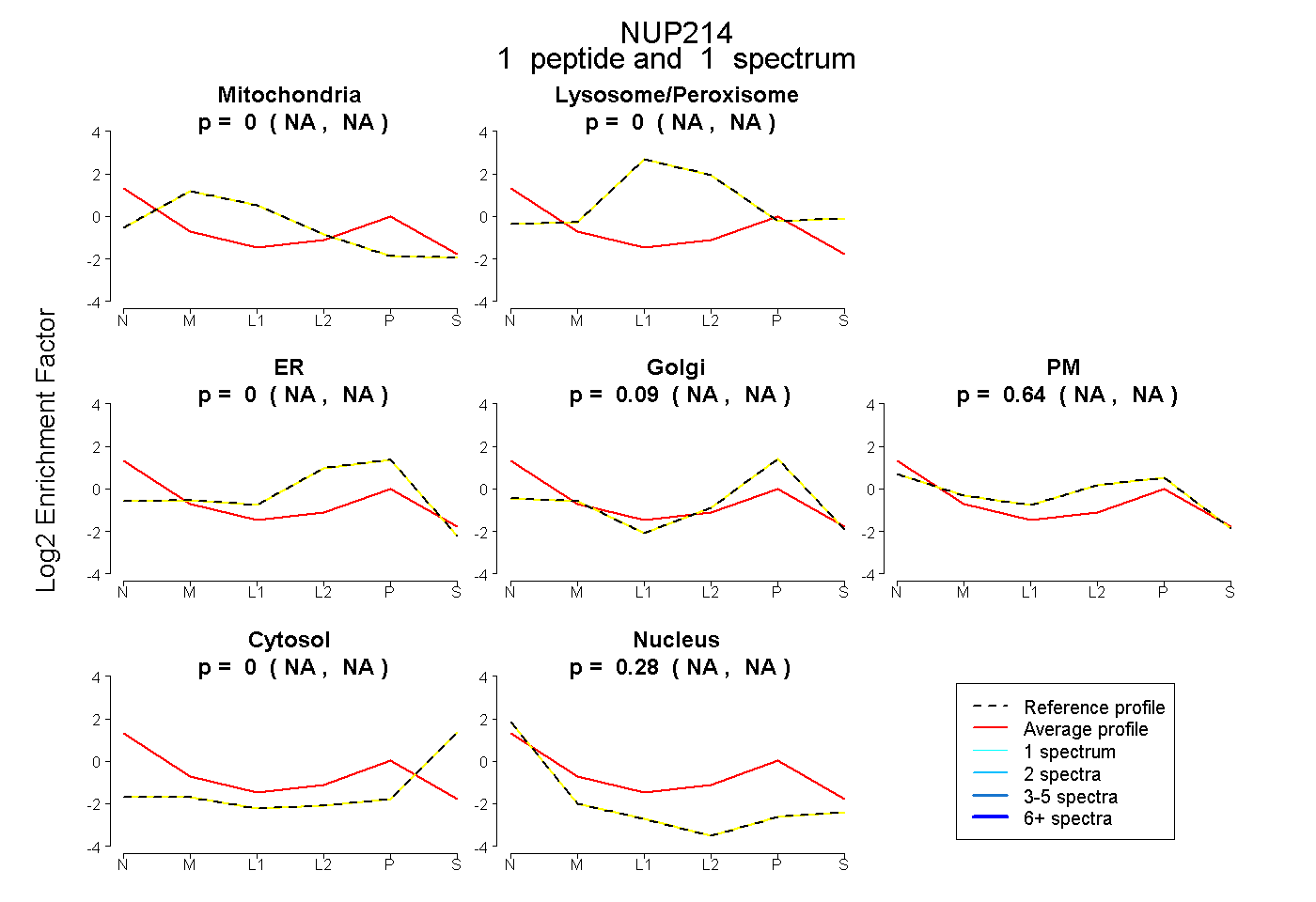 |
0.000 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.085 NA | NA |
0.636 NA | NA |
0.000 NA | NA |
0.279 NA | NA |