peptides
spectra
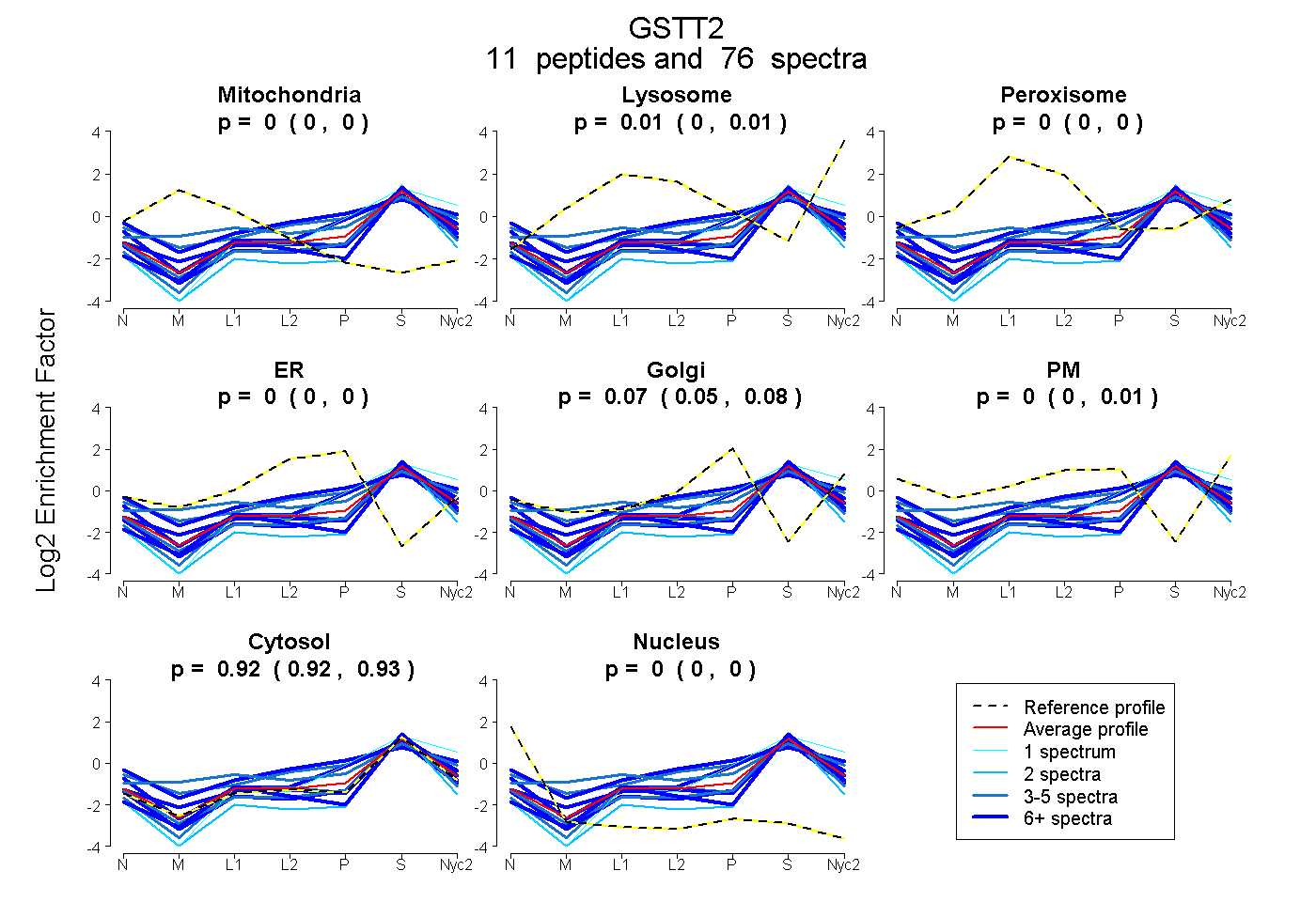
0.000 | 0.000
0.000 | 0.013
0.000 | 0.000
0.000 | 0.000
0.055 | 0.077
0.000 | 0.008
0.916 | 0.930
0.000 | 0.000
peptides
spectra
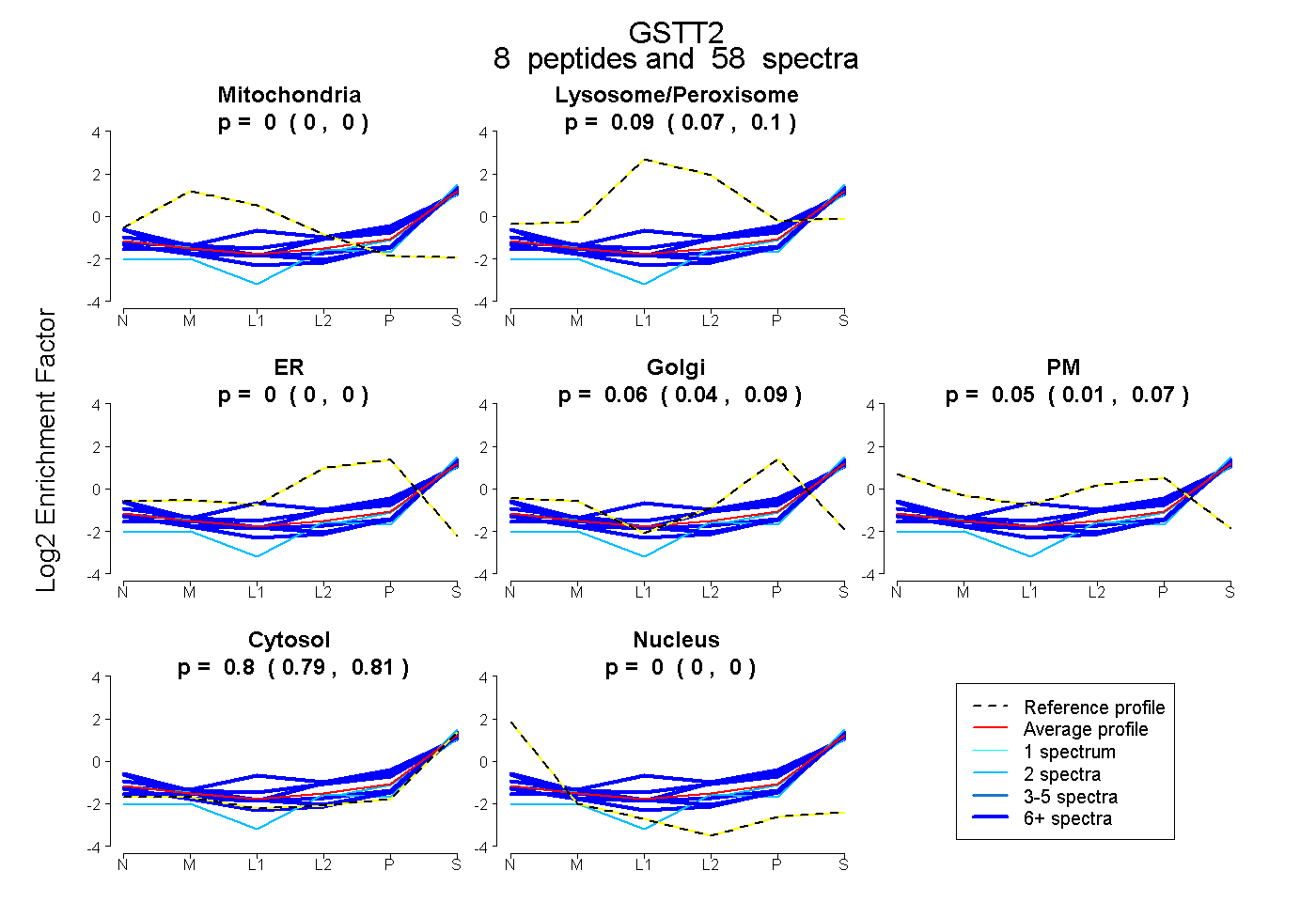
0.000 | 0.000
0.072 | 0.100
0.000 | 0.000
0.035 | 0.087
0.012 | 0.074
0.792 | 0.808
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
76 spectra |
 |
0.000 0.000 | 0.000 |
0.007 0.000 | 0.013 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.069 0.055 | 0.077 |
0.000 0.000 | 0.008 |
0.924 0.916 | 0.930 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
58 spectra |
 |
0.000 0.000 | 0.000 |
0.087 0.072 | 0.100 |
0.000 0.000 | 0.000 |
0.065 0.035 | 0.087 |
0.047 0.012 | 0.074 |
0.800 0.792 | 0.808 |
0.000 0.000 | 0.000 |
| 12 spectra, AVYIFAK | 0.000 | 0.113 | 0.000 | 0.000 | 0.205 | 0.682 | 0.000 | |||
| 8 spectra, NSMVLALQR | 0.000 | 0.075 | 0.000 | 0.032 | 0.000 | 0.893 | 0.000 | |||
| 7 spectra, GTFGVLLWTK | 0.000 | 0.000 | 0.000 | 0.043 | 0.000 | 0.930 | 0.027 | |||
| 6 spectra, YQVADHWYPADLQAR | 0.000 | 0.064 | 0.000 | 0.000 | 0.038 | 0.836 | 0.062 | |||
| 2 spectra, VLGPLIGVQVPEEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | |||
| 6 spectra, NGIPFQLR | 0.000 | 0.058 | 0.000 | 0.022 | 0.213 | 0.707 | 0.000 | |||
| 15 spectra, AQVHEYLGWHADNIR | 0.000 | 0.283 | 0.000 | 0.100 | 0.000 | 0.617 | 0.000 | |||
| 2 spectra, GLELYLDLLSQPSR | 0.000 | 0.034 | 0.000 | 0.047 | 0.109 | 0.811 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
89 spectra |
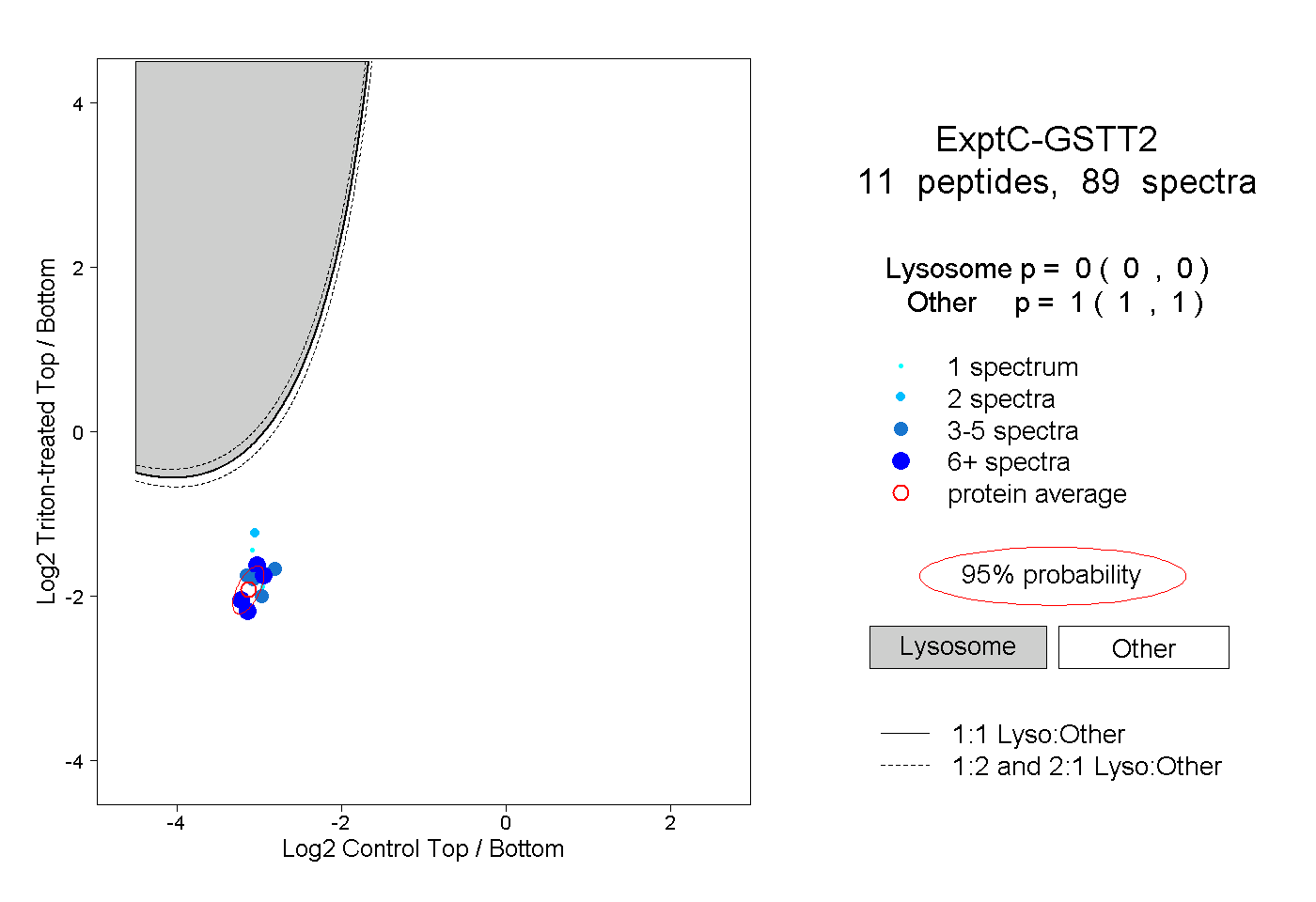 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
2 spectra |
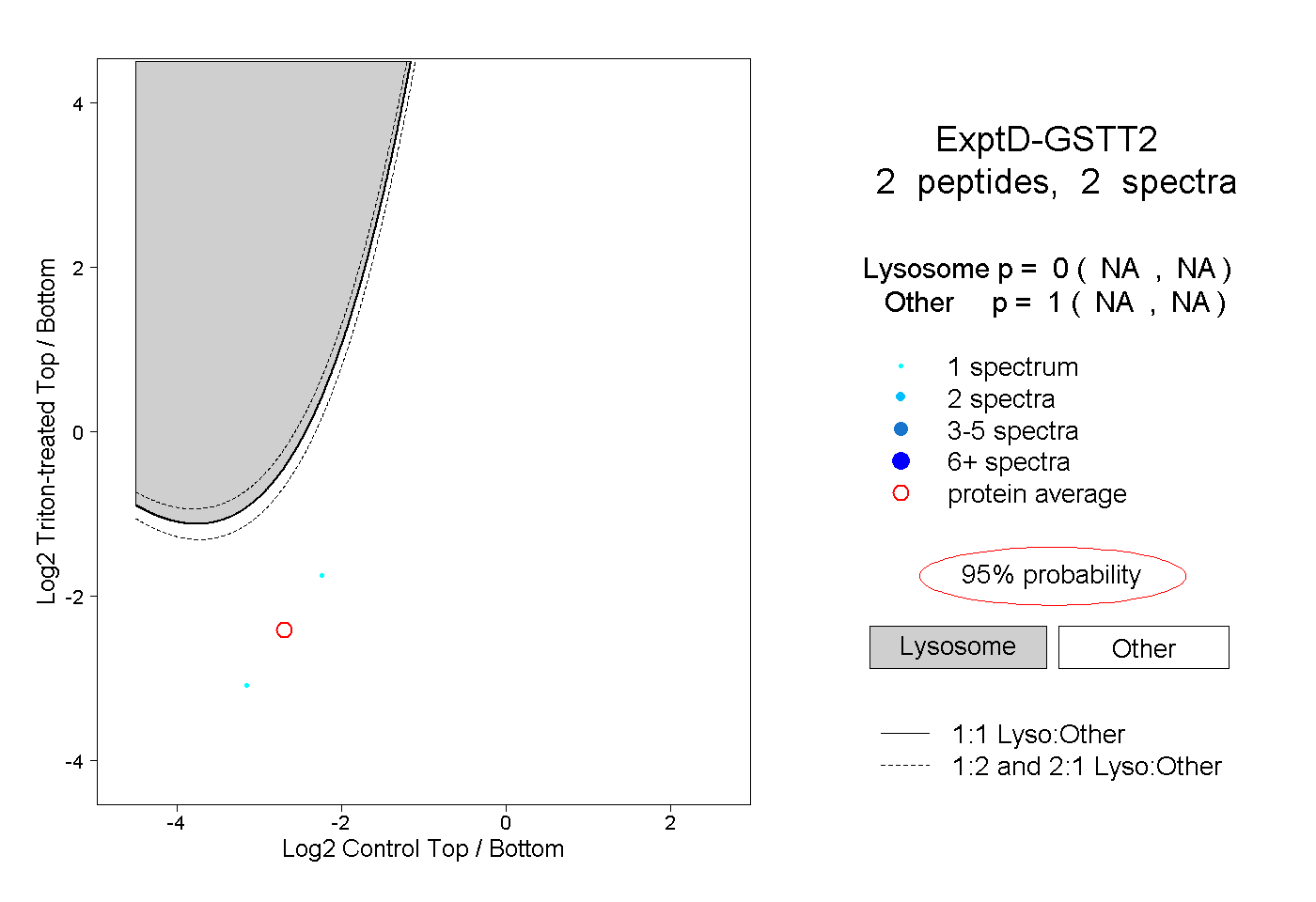 |
0.000 NA | NA |
1.000 NA | NA |