peptides
spectra

0.000 | 0.043
0.000 | 0.000
0.000 | 0.000
0.083 | 0.243
0.000 | 0.110
0.341 | 0.491
0.199 | 0.248
0.082 | 0.121
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
17 spectra |
 |
0.022 0.000 | 0.043 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.168 0.083 | 0.243 |
0.056 0.000 | 0.110 |
0.424 0.341 | 0.491 |
0.224 0.199 | 0.248 |
0.105 0.082 | 0.121 |
| 2 spectra, QMYDMVVK | 0.000 | 0.012 | 0.031 | 0.061 | 0.849 | 0.000 | 0.047 | 0.000 | ||
| 3 spectra, LAQIAGDHECGR | 0.108 | 0.000 | 0.000 | 0.179 | 0.000 | 0.473 | 0.101 | 0.139 | ||
| 2 spectra, TGLANSQGSS | 0.000 | 0.218 | 0.000 | 0.000 | 0.000 | 0.460 | 0.322 | 0.000 | ||
| 1 spectrum, DLQPYMPIPHVR | 0.000 | 0.000 | 0.000 | 0.600 | 0.083 | 0.000 | 0.316 | 0.000 | ||
| 2 spectra, AVDFLAANESR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.609 | 0.092 | 0.299 | ||
| 1 spectrum, APPAPPVAGEATSGNSAER | 0.000 | 0.189 | 0.218 | 0.000 | 0.000 | 0.224 | 0.369 | 0.000 | ||
| 2 spectra, GTGVPEDGR | 0.039 | 0.000 | 0.023 | 0.533 | 0.000 | 0.019 | 0.000 | 0.386 | ||
| 3 spectra, VWQGQAFHLDR | 0.000 | 0.000 | 0.039 | 0.552 | 0.000 | 0.108 | 0.121 | 0.181 | ||
| 1 spectrum, LCEPEEELLQQFK | 0.138 | 0.000 | 0.121 | 0.366 | 0.000 | 0.000 | 0.187 | 0.187 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
2 spectra |
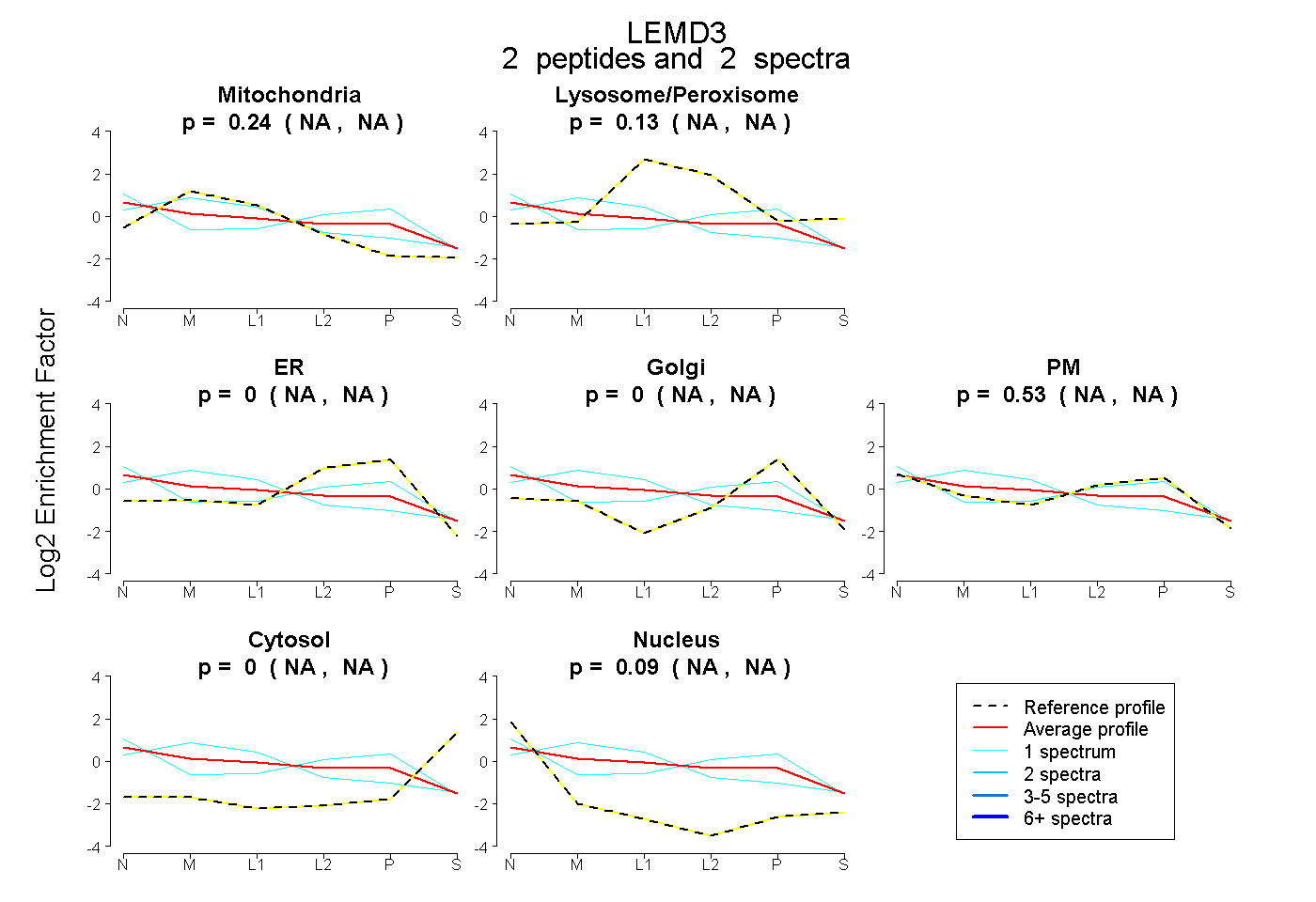 |
0.244 NA | NA |
0.132 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.535 NA | NA |
0.000 NA | NA |
0.089 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
1 spectrum |
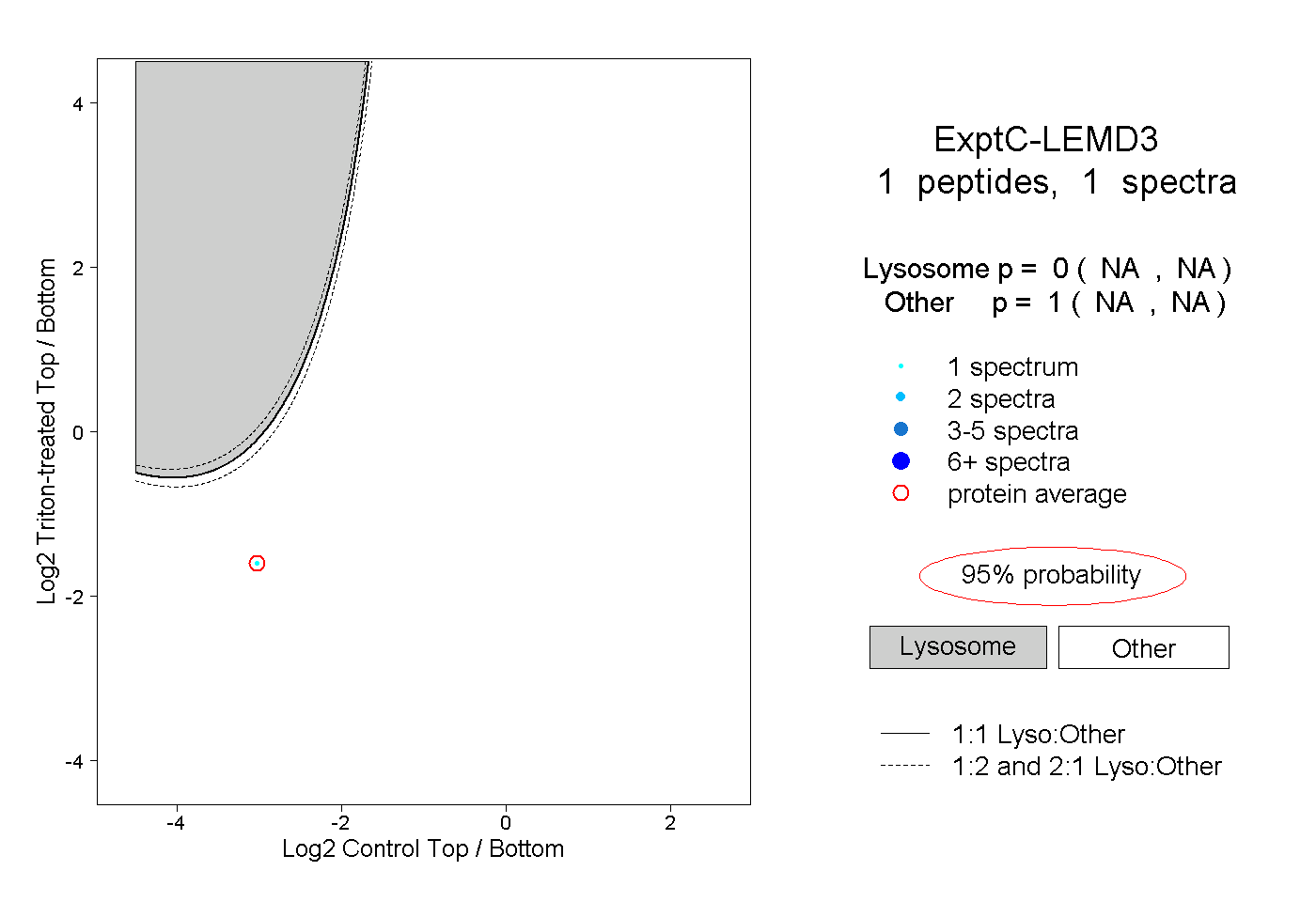 |
0.000 NA | NA |
1.000 NA | NA |