peptides
spectra
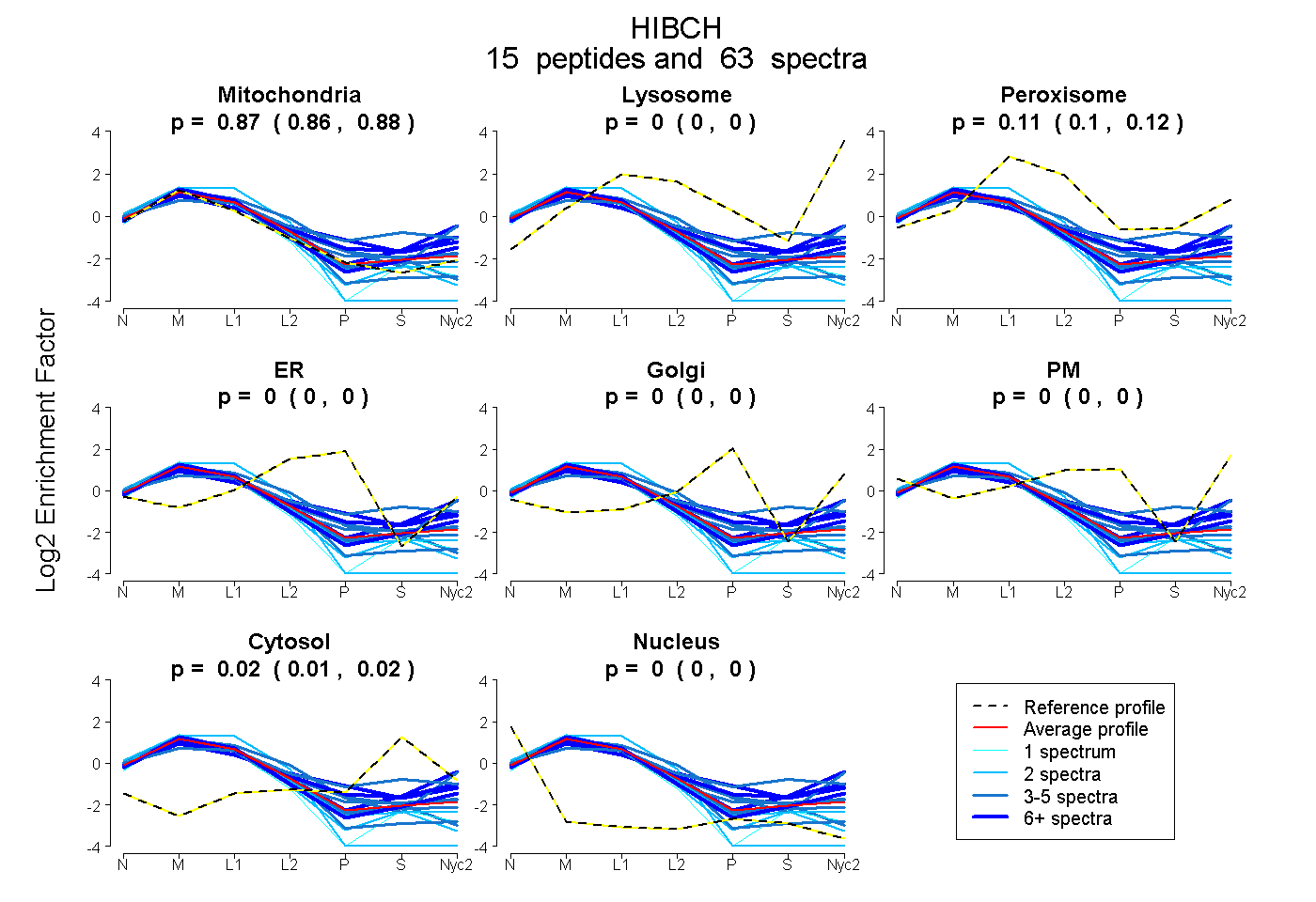
0.863 | 0.879
0.000 | 0.000
0.103 | 0.116
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.014 | 0.022
0.000 | 0.000
peptides
spectra
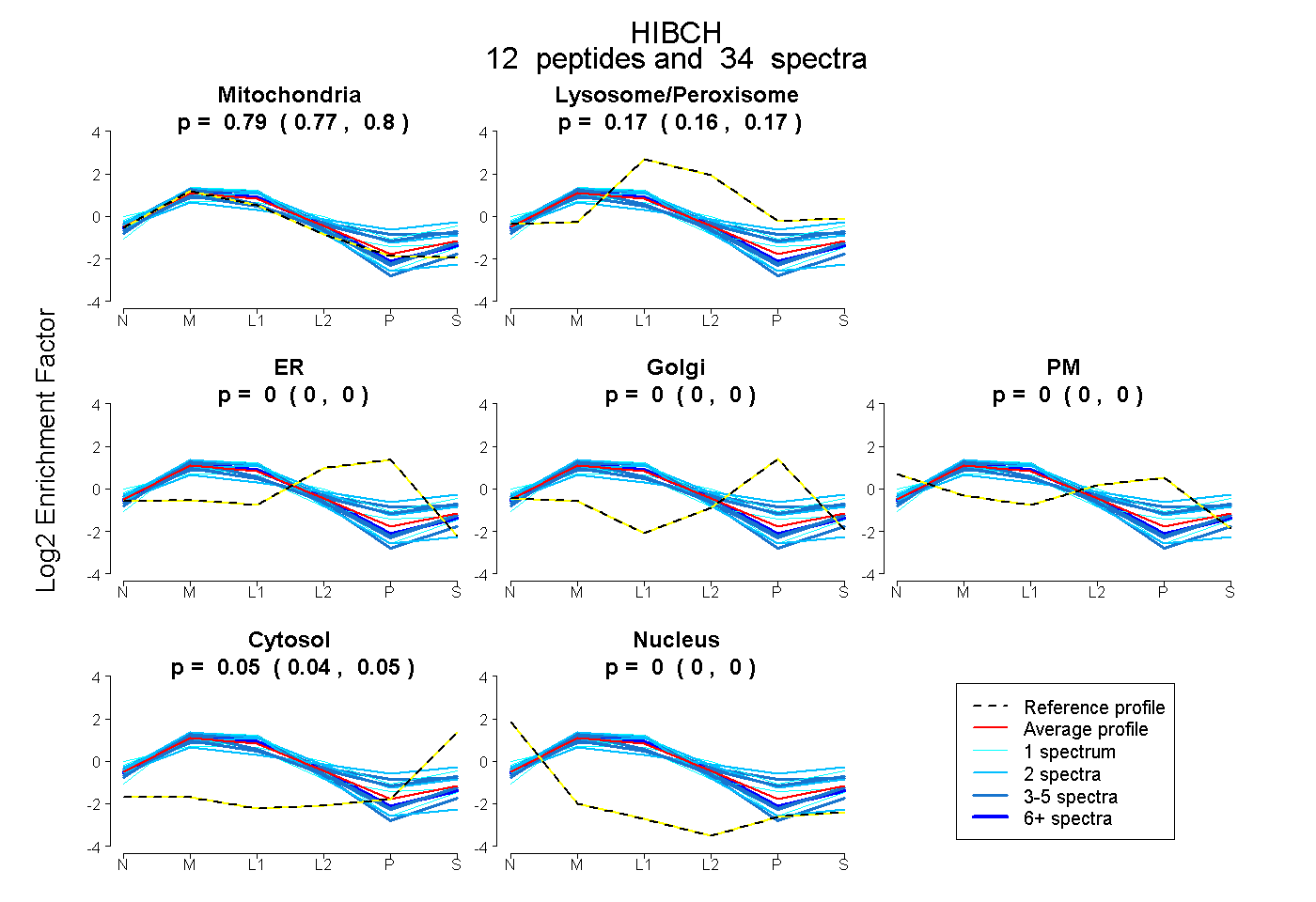
0.774 | 0.797
0.158 | 0.174
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.040 | 0.052
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
63 spectra |
 |
0.872 0.863 | 0.879 |
0.000 0.000 | 0.000 |
0.110 0.103 | 0.116 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.018 0.014 | 0.022 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
34 spectra |
 |
0.786 0.774 | 0.797 |
0.167 0.158 | 0.174 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.047 0.040 | 0.052 |
0.000 0.000 | 0.000 |
| 2 spectra, HTETAEVLLER | 0.645 | 0.309 | 0.000 | 0.000 | 0.000 | 0.045 | 0.000 | |||
| 3 spectra, GCAGVITLNRPK | 0.857 | 0.143 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, AFCAGGDIK | 0.564 | 0.303 | 0.000 | 0.077 | 0.000 | 0.056 | 0.000 | |||
| 4 spectra, LTQACMEGHDFHEGVR | 0.608 | 0.226 | 0.000 | 0.030 | 0.000 | 0.137 | 0.000 | |||
| 4 spectra, TLQEVLTMEYR | 0.889 | 0.048 | 0.000 | 0.000 | 0.000 | 0.063 | 0.000 | |||
| 2 spectra, QDGSPFAMEQIK | 0.365 | 0.332 | 0.000 | 0.139 | 0.000 | 0.165 | 0.000 | |||
| 1 spectrum, AGIATHFVDSEK | 0.452 | 0.319 | 0.000 | 0.000 | 0.109 | 0.120 | 0.000 | |||
| 1 spectrum, DVTDEDLNSYFK | 0.802 | 0.084 | 0.000 | 0.000 | 0.061 | 0.053 | 0.000 | |||
| 3 spectra, DPDTFLIIIK | 0.970 | 0.030 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, AGQTLSQDLFR | 0.880 | 0.115 | 0.000 | 0.000 | 0.000 | 0.005 | 0.000 | |||
| 2 spectra, QIYPQLK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LHVLEEELLALK | 0.913 | 0.087 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
260 spectra |
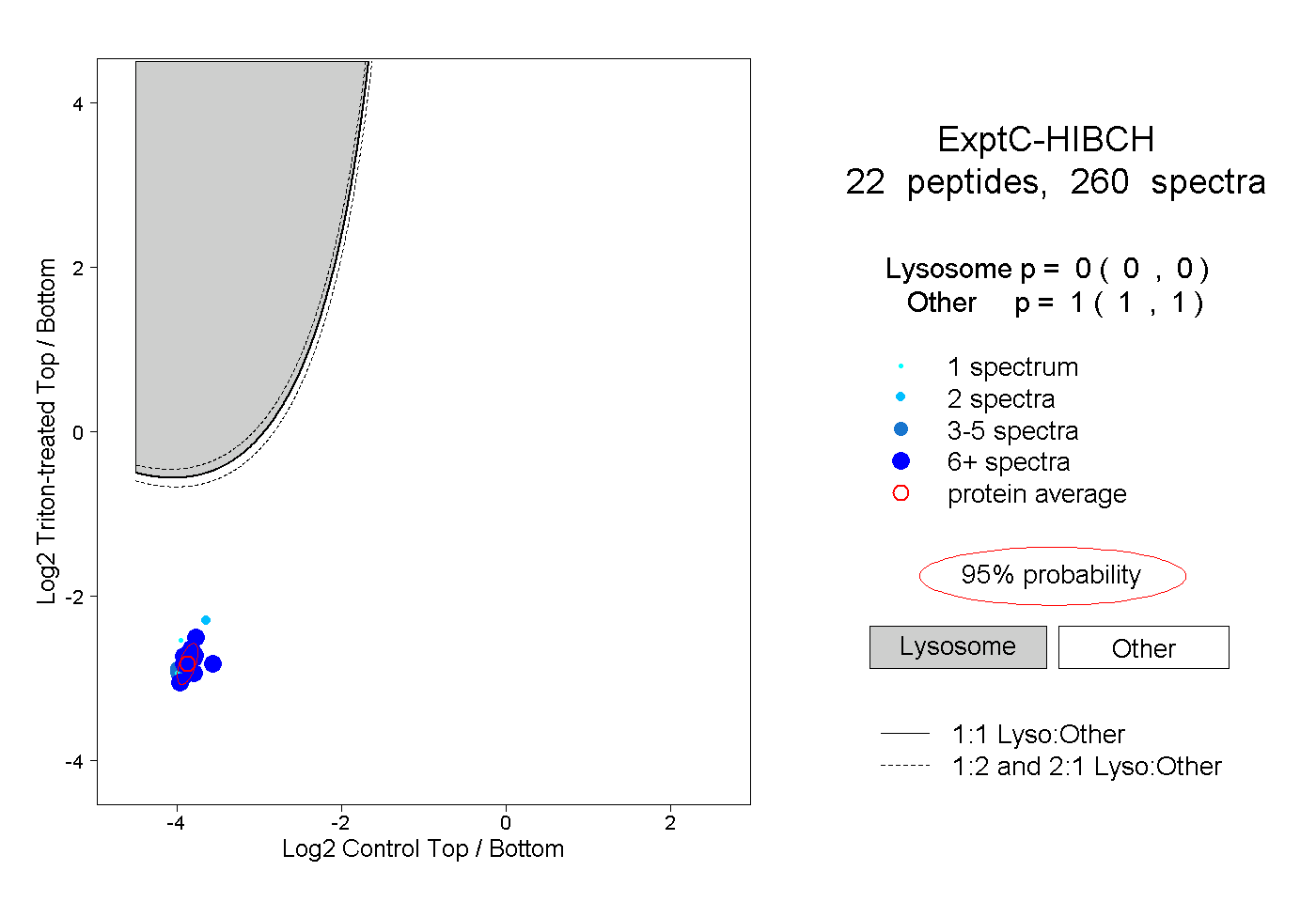 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
27 spectra |
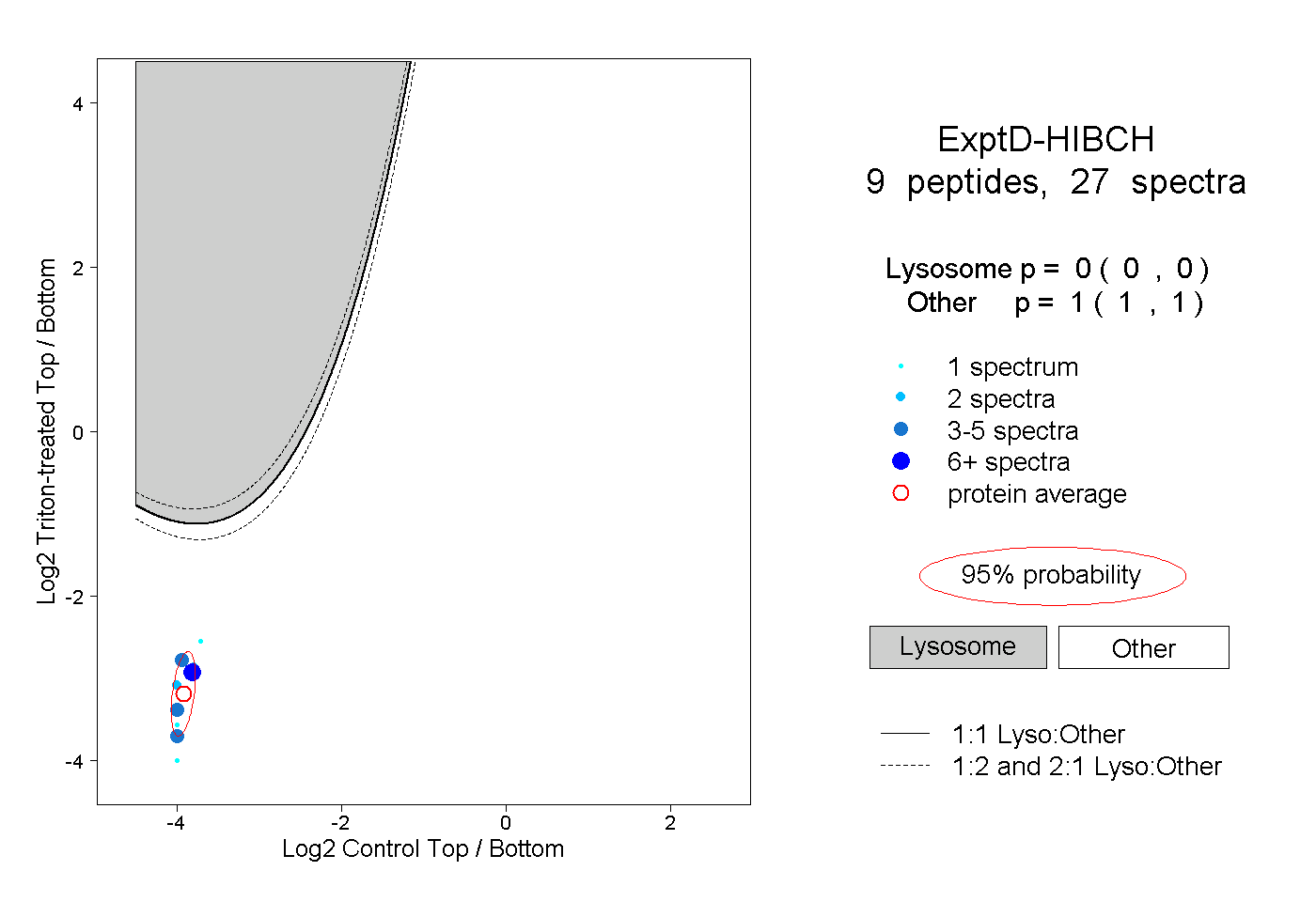 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |