peptides
spectra
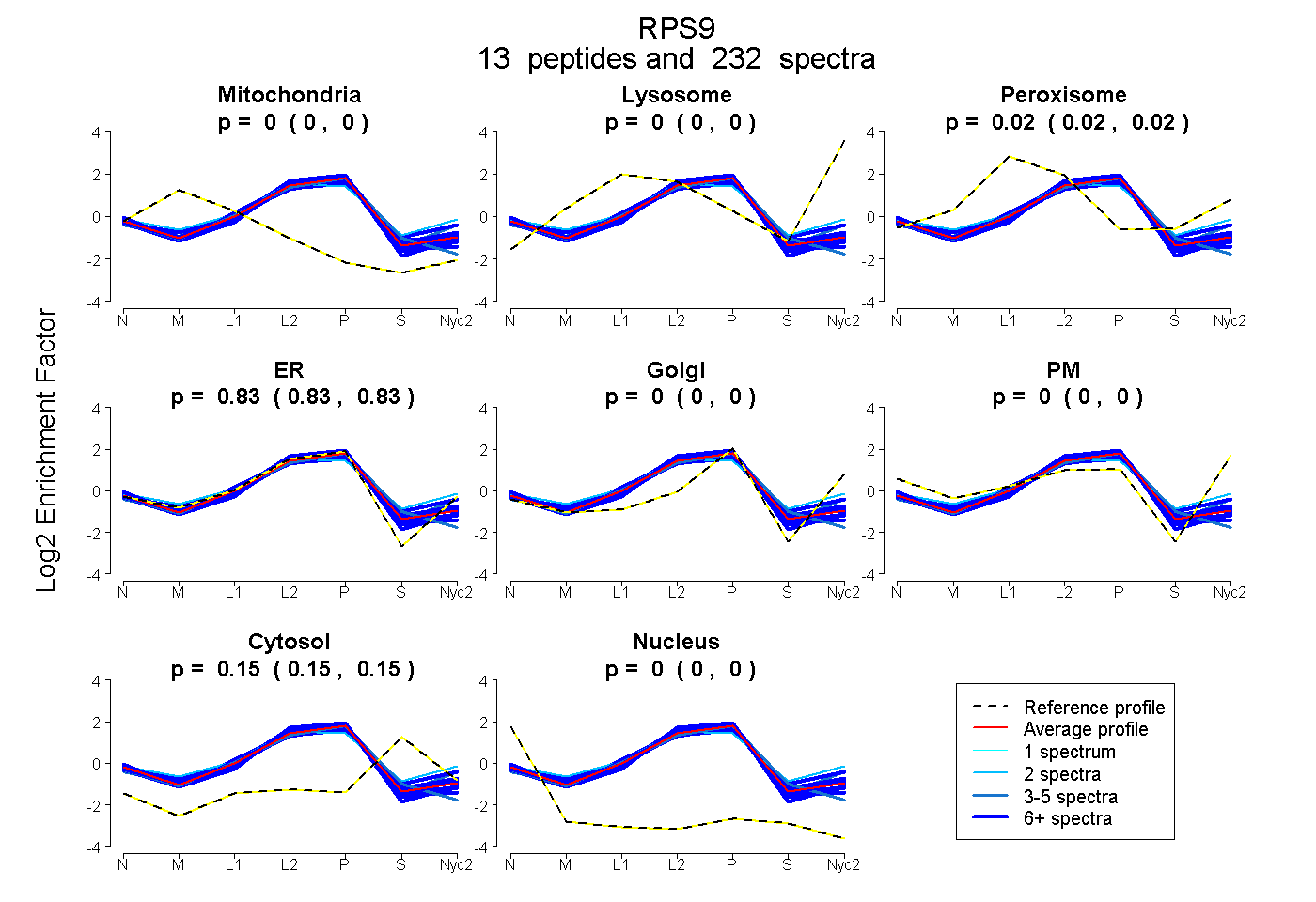
0.000 | 0.000
0.000 | 0.000
0.018 | 0.020
0.828 | 0.831
0.000 | 0.000
0.000 | 0.000
0.150 | 0.152
0.000 | 0.000
peptides
spectra
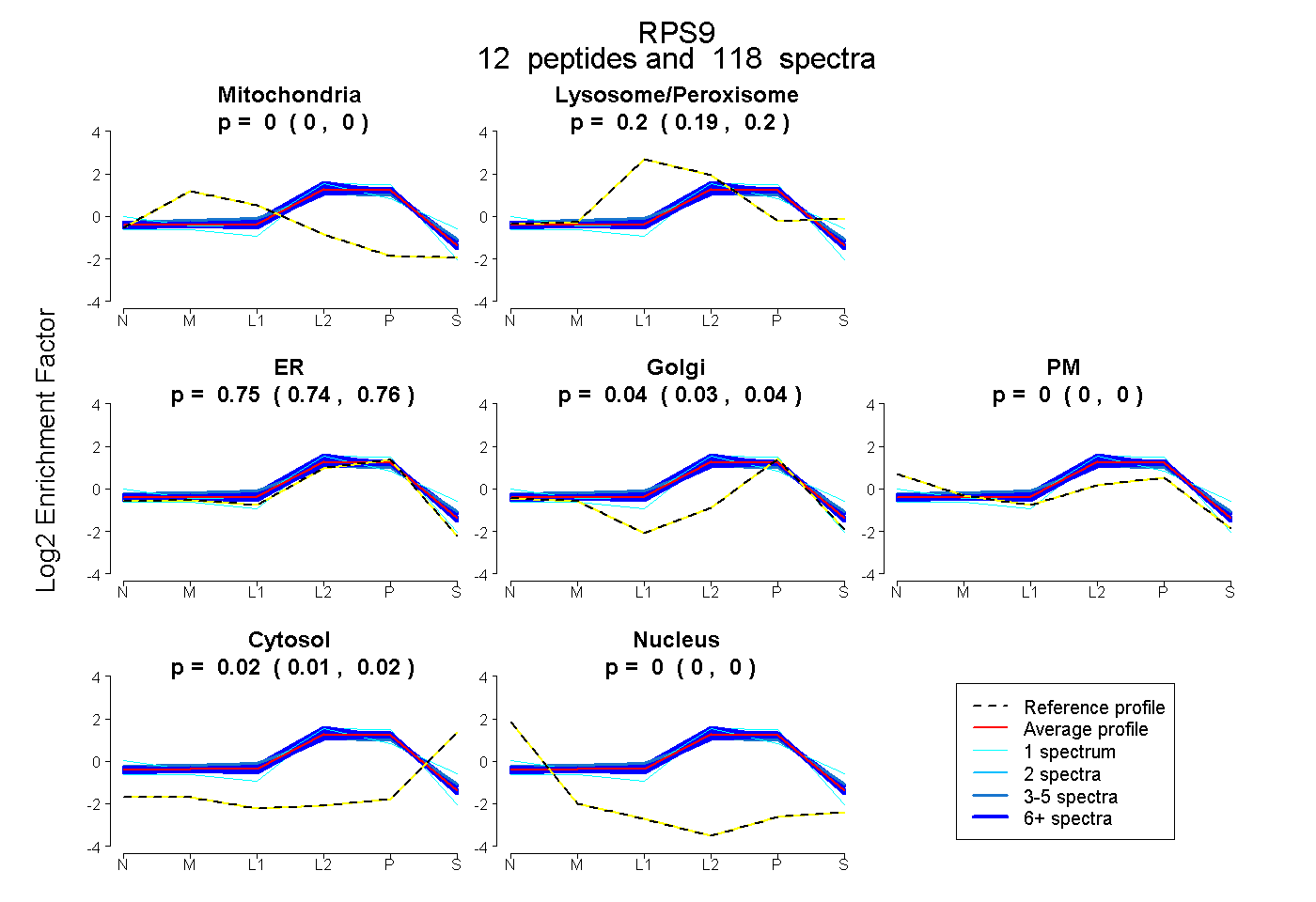
0.000 | 0.000
0.193 | 0.199
0.743 | 0.759
0.028 | 0.042
0.000 | 0.003
0.014 | 0.017
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
232 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.019 0.018 | 0.020 |
0.829 0.828 | 0.831 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.152 0.150 | 0.152 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
118 spectra |
 |
0.000 0.000 | 0.000 |
0.197 0.193 | 0.199 |
0.751 0.743 | 0.759 |
0.036 0.028 | 0.042 |
0.000 0.000 | 0.003 |
0.016 0.014 | 0.017 |
0.000 0.000 | 0.000 |
| 6 spectra, LQTQVFK | 0.000 | 0.177 | 0.782 | 0.000 | 0.017 | 0.024 | 0.000 | |||
| 9 spectra, IGVLDEGK | 0.000 | 0.256 | 0.638 | 0.086 | 0.000 | 0.020 | 0.000 | |||
| 11 spectra, LIGEYGLR | 0.000 | 0.123 | 0.844 | 0.000 | 0.000 | 0.033 | 0.000 | |||
| 3 spectra, SIHHAR | 0.000 | 0.337 | 0.371 | 0.218 | 0.074 | 0.000 | 0.000 | |||
| 15 spectra, HIDFSLR | 0.000 | 0.206 | 0.729 | 0.055 | 0.000 | 0.010 | 0.000 | |||
| 1 spectrum, GQGGAGAGDDEEED | 0.000 | 0.003 | 0.997 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, TYVTPR | 0.000 | 0.201 | 0.696 | 0.103 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, LDYILGLK | 0.000 | 0.259 | 0.733 | 0.000 | 0.000 | 0.008 | 0.000 | |||
| 22 spectra, LFEGNALLR | 0.000 | 0.173 | 0.786 | 0.011 | 0.000 | 0.030 | 0.000 | |||
| 19 spectra, SPYGGGRPGR | 0.000 | 0.207 | 0.593 | 0.130 | 0.070 | 0.000 | 0.000 | |||
| 1 spectrum, SWVCR | 0.000 | 0.283 | 0.468 | 0.000 | 0.177 | 0.072 | 0.000 | |||
| 16 spectra, IEDFLER | 0.000 | 0.173 | 0.822 | 0.000 | 0.000 | 0.005 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
296 spectra |
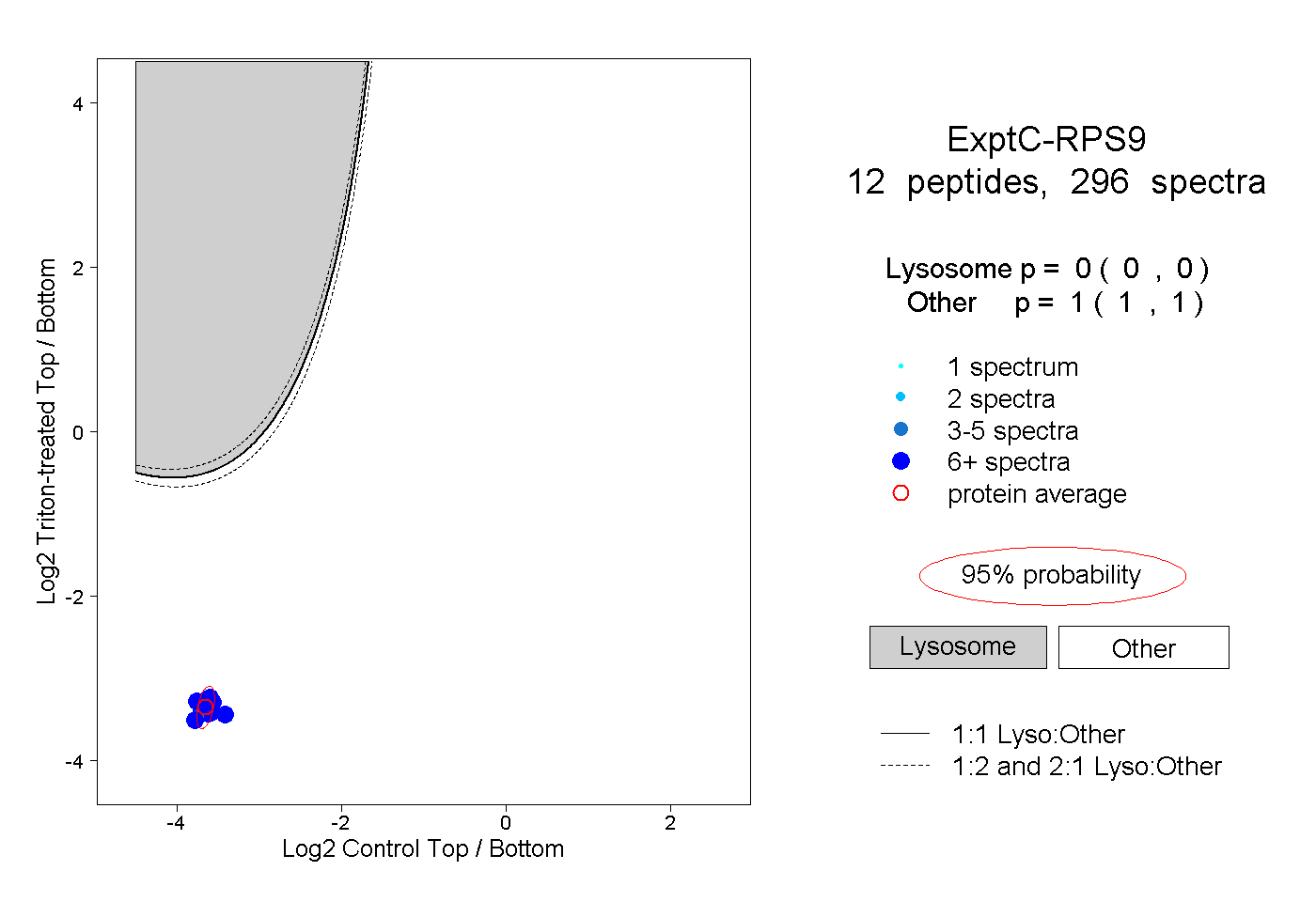 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
48 spectra |
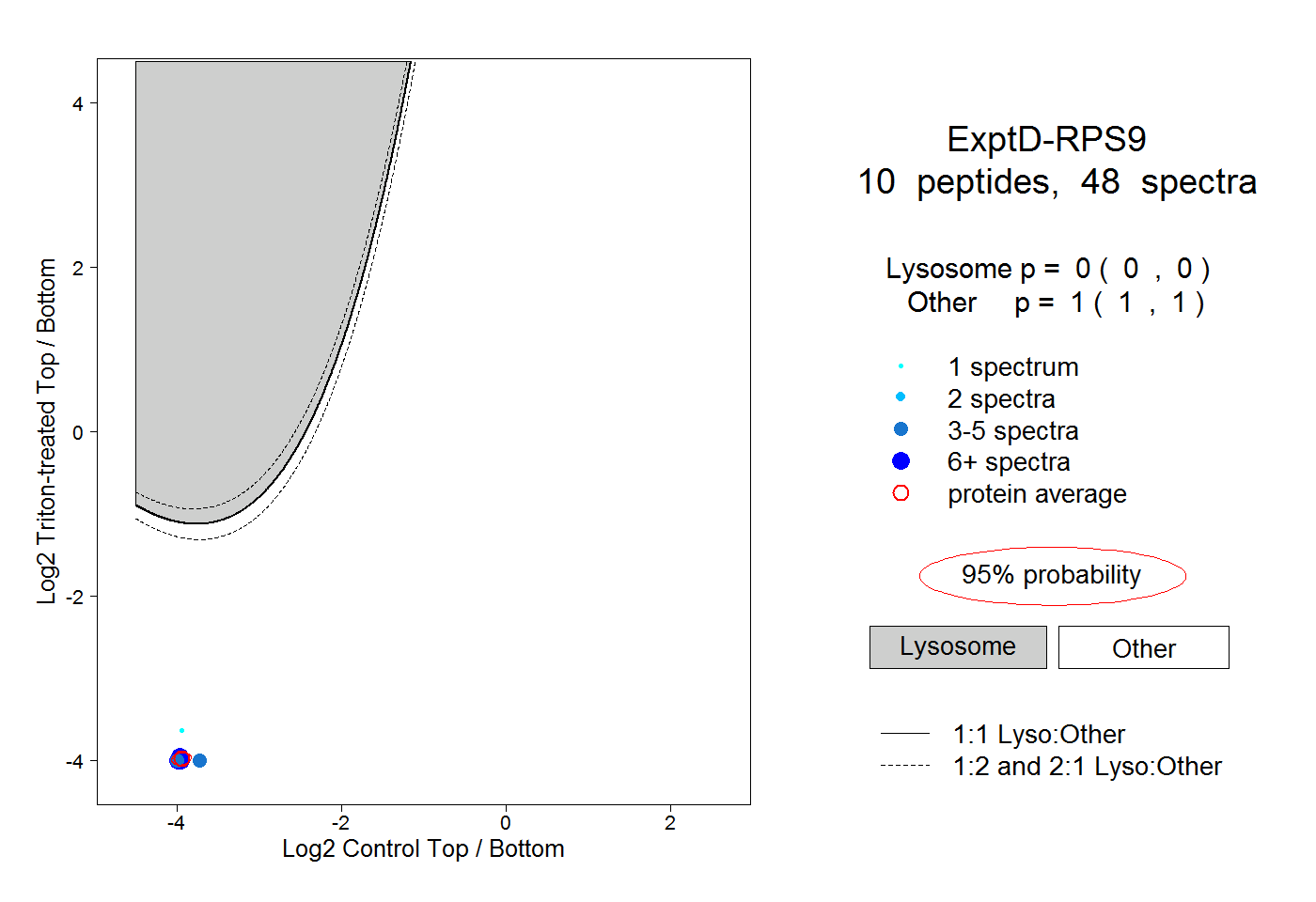 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |