peptides
spectra

0.000 | 0.000
0.003 | 0.006
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.994 | 0.996
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
265 spectra |
 |
0.000 0.000 | 0.000 |
0.005 0.003 | 0.006 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.995 0.994 | 0.996 |
0.000 0.000 | 0.000 |
| 2 spectra, LTPIGYVPK | 0.004 | 0.000 | 0.021 | 0.000 | 0.000 | 0.000 | 0.975 | 0.000 | ||
| 2 spectra, IFHVNWFR | 0.100 | 0.172 | 0.000 | 0.000 | 0.116 | 0.000 | 0.612 | 0.000 | ||
| 8 spectra, EDALNLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, VLEWMFGR | 0.000 | 0.016 | 0.000 | 0.000 | 0.000 | 0.000 | 0.984 | 0.000 | ||
| 4 spectra, EEGWLAEHMLILGITNPEGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.984 | 0.016 | ||
| 4 spectra, VIMHDPFAMRPFFGYNFGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, EIISFGSGYGGNSLLGK | 0.000 | 0.335 | 0.000 | 0.000 | 0.000 | 0.048 | 0.617 | 0.000 | ||
| 52 spectra, WMSEEDFEK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 6 spectra, IEGEDSAK | 0.027 | 0.000 | 0.007 | 0.000 | 0.000 | 0.054 | 0.912 | 0.000 | ||
| 4 spectra, EVEEIDK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.916 | 0.084 | ||
| 4 spectra, YDNCWLALTDPR | 0.078 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.922 | 0.000 | ||
| 4 spectra, EWRPQDEEPCAHPNSR | 0.000 | 0.000 | 0.098 | 0.135 | 0.000 | 0.087 | 0.680 | 0.000 | ||
| 8 spectra, MGTSVLEALGDGEFIK | 0.022 | 0.199 | 0.000 | 0.000 | 0.000 | 0.000 | 0.779 | 0.000 | ||
| 18 spectra, FLWPGFGENSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 21 spectra, LLAHMQEEGVIR | 0.009 | 0.072 | 0.000 | 0.000 | 0.000 | 0.052 | 0.867 | 0.000 | ||
| 15 spectra, SEATAAAEHK | 0.000 | 0.000 | 0.000 | 0.005 | 0.000 | 0.000 | 0.994 | 0.001 | ||
| 10 spectra, VECVGDDIAWMK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.953 | 0.047 | ||
| 1 spectrum, YLEDQVNADLPYEIER | 0.065 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.907 | 0.028 | ||
| 3 spectra, AINPENGFFGVAPGTSVK | 0.037 | 0.036 | 0.000 | 0.000 | 0.000 | 0.000 | 0.926 | 0.000 | ||
| 4 spectra, TNLAMMNPTLPGWK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 10 spectra, TNPNAIK | 0.000 | 0.000 | 0.000 | 0.069 | 0.000 | 0.000 | 0.931 | 0.000 | ||
| 7 spectra, IGIELTDSPYVVASMR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 16 spectra, FDAQGNLR | 0.023 | 0.047 | 0.000 | 0.000 | 0.006 | 0.000 | 0.924 | 0.000 | ||
| 1 spectrum, KPLVNNWACNPELTLIAHLPDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 6 spectra, DTVPIPK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.968 | 0.032 | ||
| 15 spectra, SGQSQLGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 4 spectra, VIQGSLDSLPQEVR | 0.049 | 0.008 | 0.000 | 0.000 | 0.000 | 0.000 | 0.943 | 0.000 | ||
| 10 spectra, CLHSVGCPLPLK | 0.078 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.922 | 0.000 | ||
| 2 spectra, PPQLHNGLDFSAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.976 | 0.024 | ||
| 4 spectra, YLAAAFPSACGK | 0.071 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.929 | 0.000 | ||
| 15 spectra, TVIITQEQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, GLGDVNVEELFGISK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.968 | 0.032 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
38 spectra |
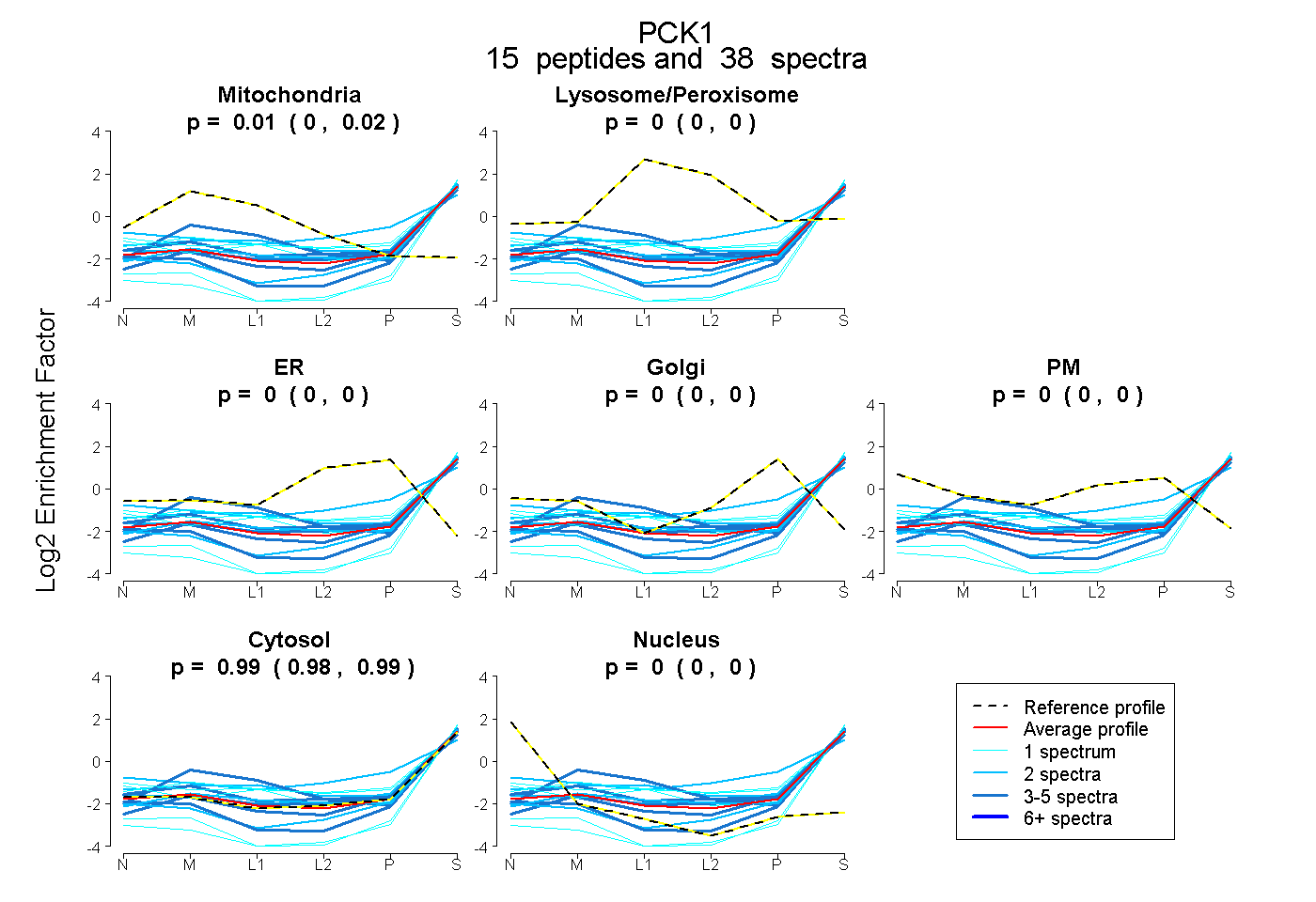 |
0.015 0.005 | 0.023 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.985 0.975 | 0.993 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
252 spectra |
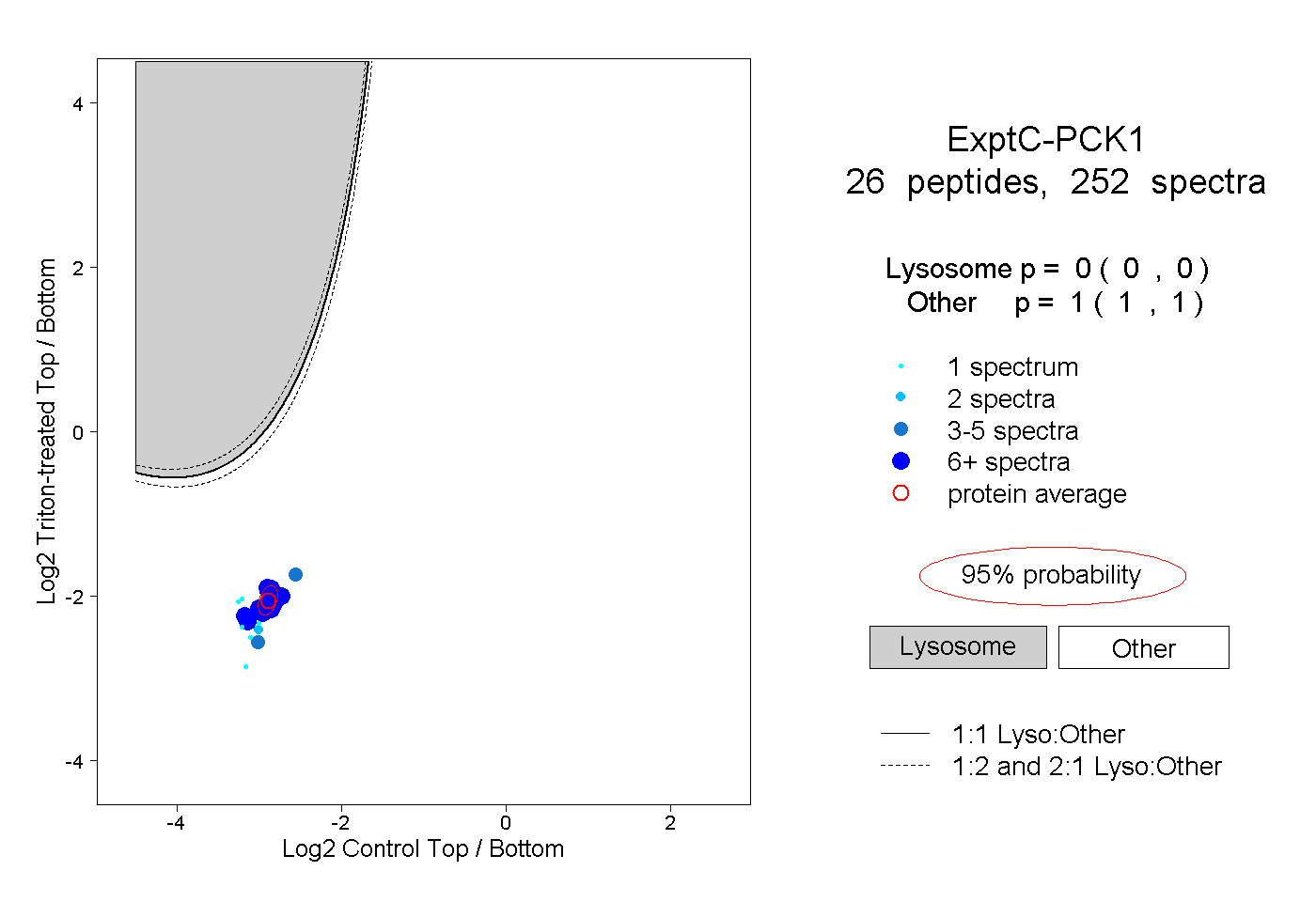 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
9 spectra |
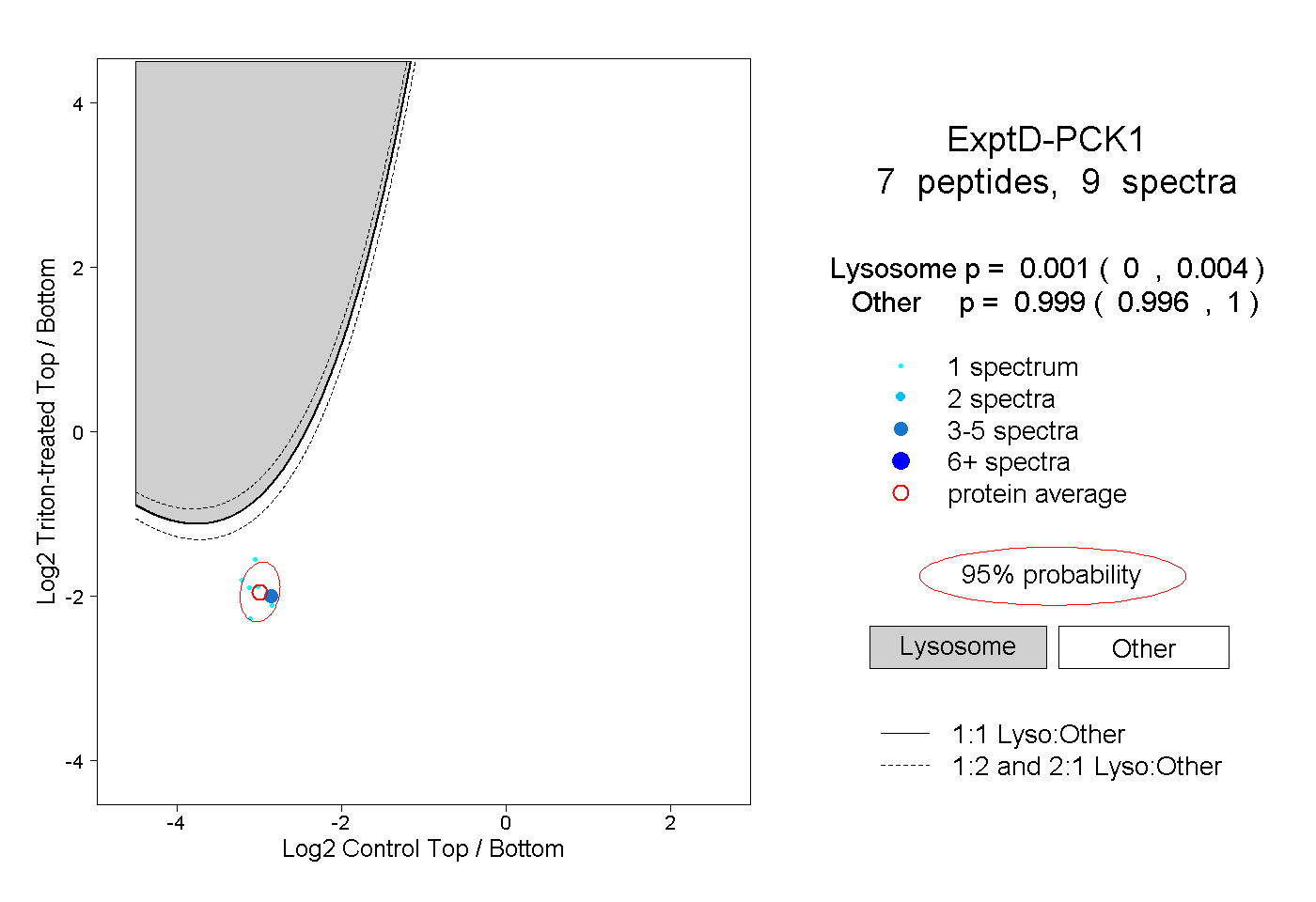 |
0.001 0.000 | 0.004 |
0.999 0.996 | 1.000 |