peptides
spectra
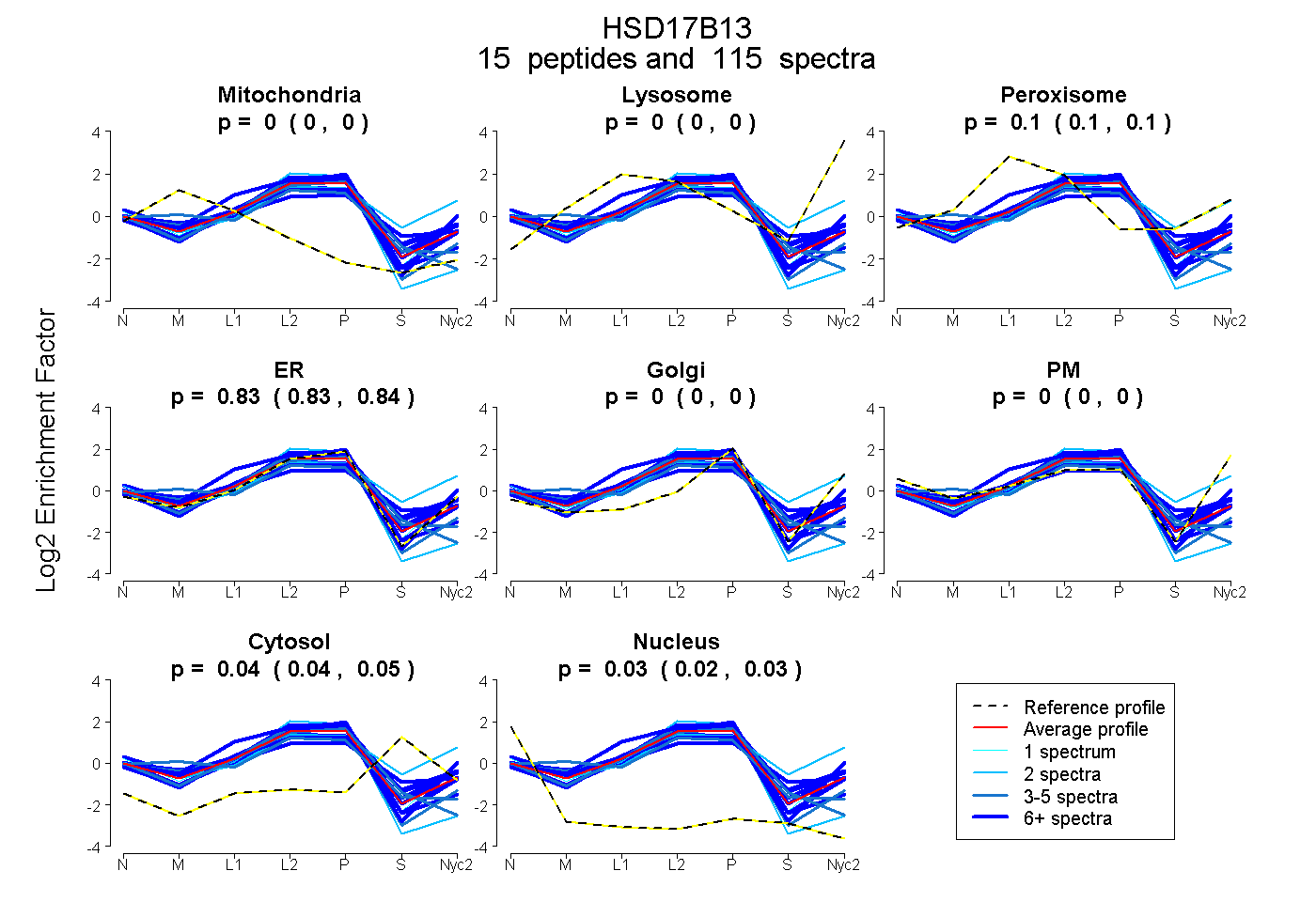
0.000 | 0.000
0.000 | 0.000
0.097 | 0.104
0.826 | 0.835
0.000 | 0.000
0.000 | 0.000
0.036 | 0.047
0.023 | 0.029
peptides
spectra
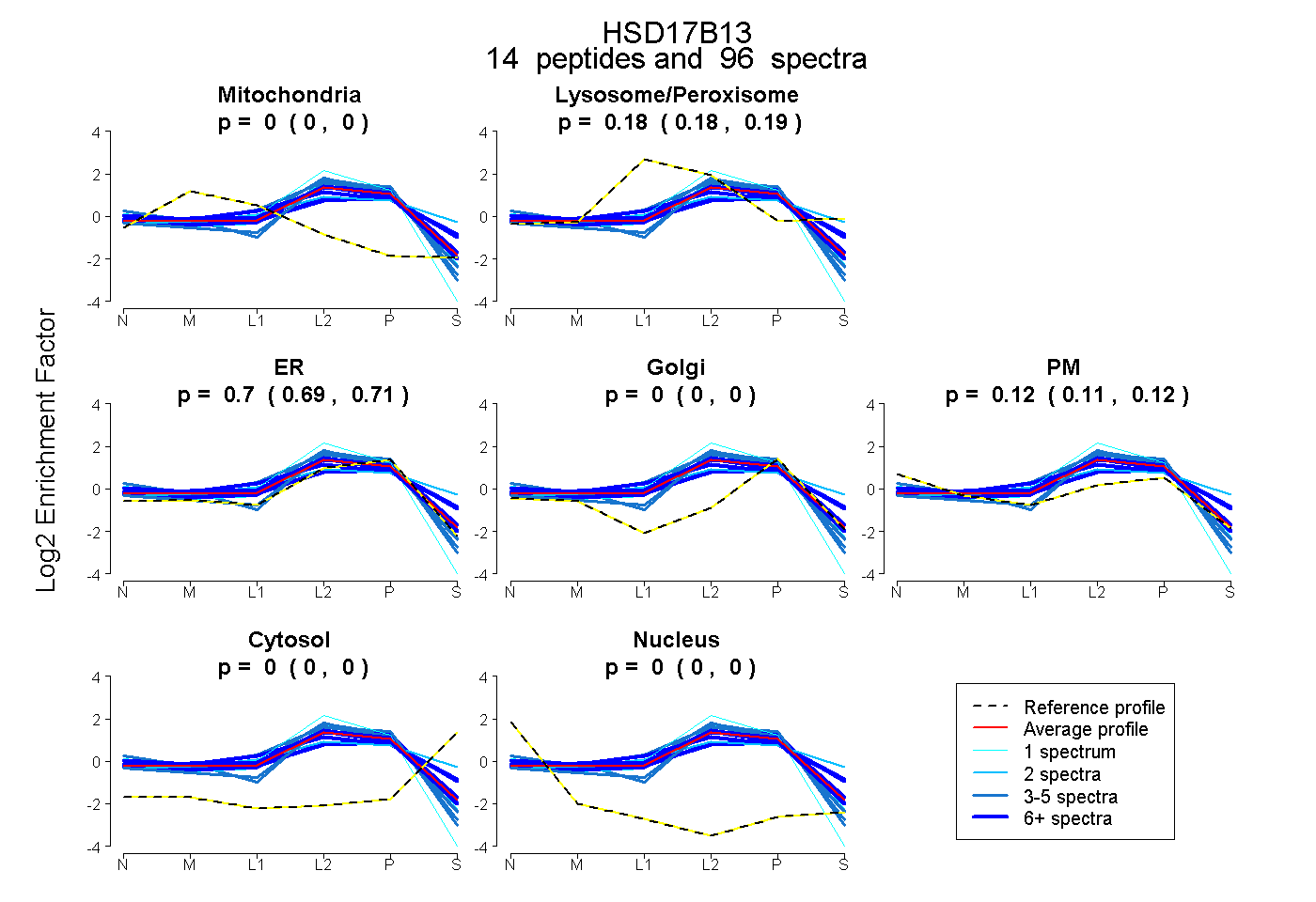
0.000 | 0.000
0.179 | 0.190
0.688 | 0.707
0.000 | 0.000
0.109 | 0.123
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
115 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.101 0.097 | 0.104 |
0.831 0.826 | 0.835 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.042 0.036 | 0.047 |
0.026 0.023 | 0.029 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
96 spectra |
 |
0.000 0.000 | 0.000 |
0.185 0.179 | 0.190 |
0.698 0.688 | 0.707 |
0.000 0.000 | 0.000 |
0.117 0.109 | 0.123 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 1 spectrum, TSCLCPVFVNTGFTK | 0.000 | 0.033 | 0.967 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 11 spectra, LTAYEFAK | 0.000 | 0.380 | 0.170 | 0.394 | 0.055 | 0.001 | 0.000 | |||
| 2 spectra, LWPVLEPDEVAR | 0.000 | 0.484 | 0.120 | 0.328 | 0.000 | 0.068 | 0.000 | |||
| 9 spectra, VIPYLIPYCSSK | 0.000 | 0.202 | 0.588 | 0.000 | 0.209 | 0.000 | 0.000 | |||
| 12 spectra, SVAGQTVLITGAGHGIGR | 0.000 | 0.203 | 0.705 | 0.000 | 0.091 | 0.000 | 0.000 | |||
| 9 spectra, IQNIQFEAIVGHR | 0.000 | 0.435 | 0.269 | 0.214 | 0.082 | 0.000 | 0.000 | |||
| 4 spectra, ALLPSMLR | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 19 spectra, FAAVGFHR | 0.000 | 0.165 | 0.824 | 0.000 | 0.011 | 0.000 | 0.000 | |||
| 1 spectrum, DEEITK | 0.000 | 0.110 | 0.890 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 9 spectra, LVLWDISK | 0.000 | 0.181 | 0.699 | 0.000 | 0.121 | 0.000 | 0.000 | |||
| 3 spectra, FFIPQR | 0.000 | 0.156 | 0.712 | 0.000 | 0.132 | 0.000 | 0.000 | |||
| 5 spectra, SLIDGILTNK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, ALTAELDTLGK | 0.000 | 0.340 | 0.234 | 0.270 | 0.116 | 0.040 | 0.000 | |||
| 3 spectra, HGVEETAAK | 0.000 | 0.227 | 0.773 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
155 spectra |
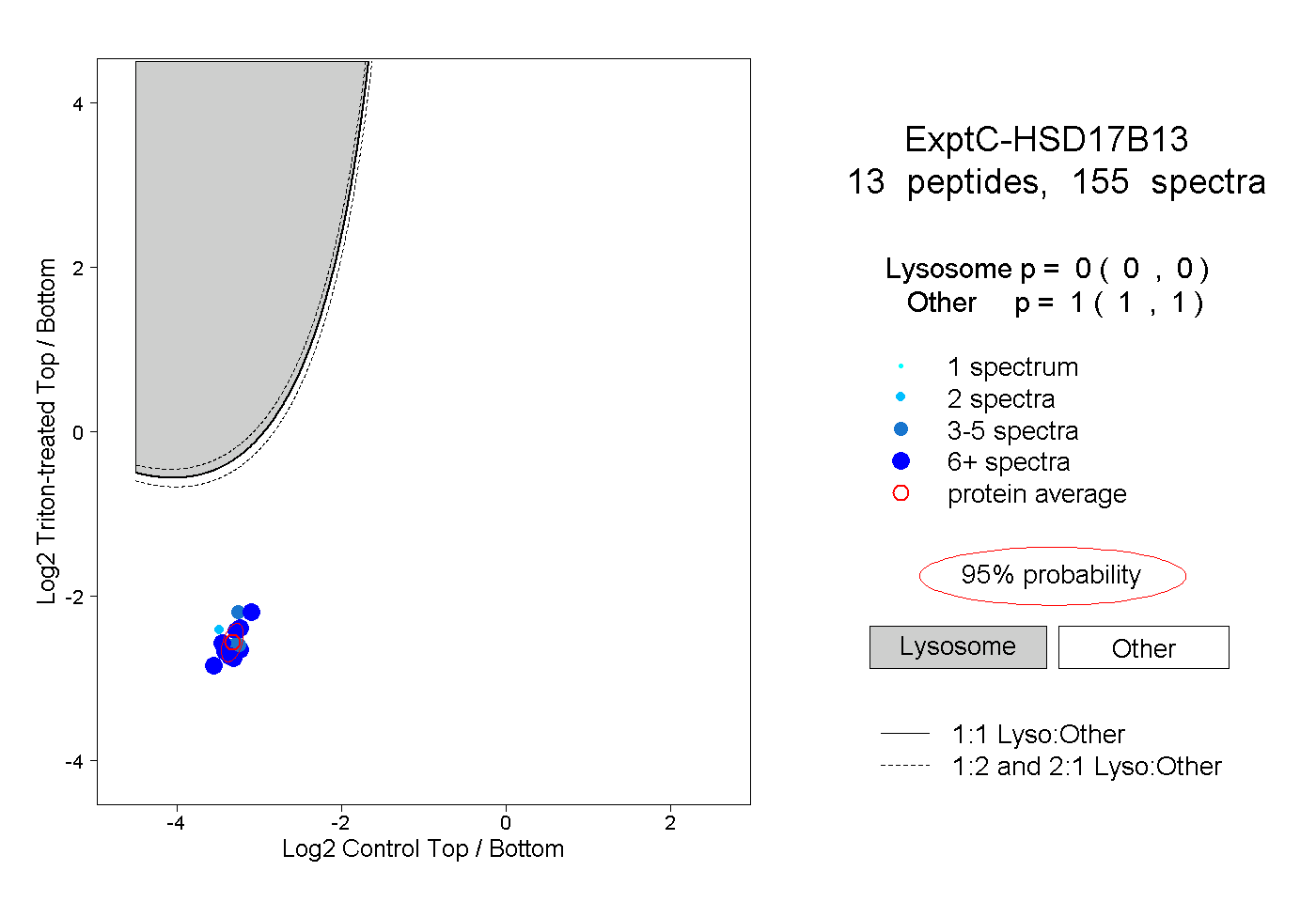 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
36 spectra |
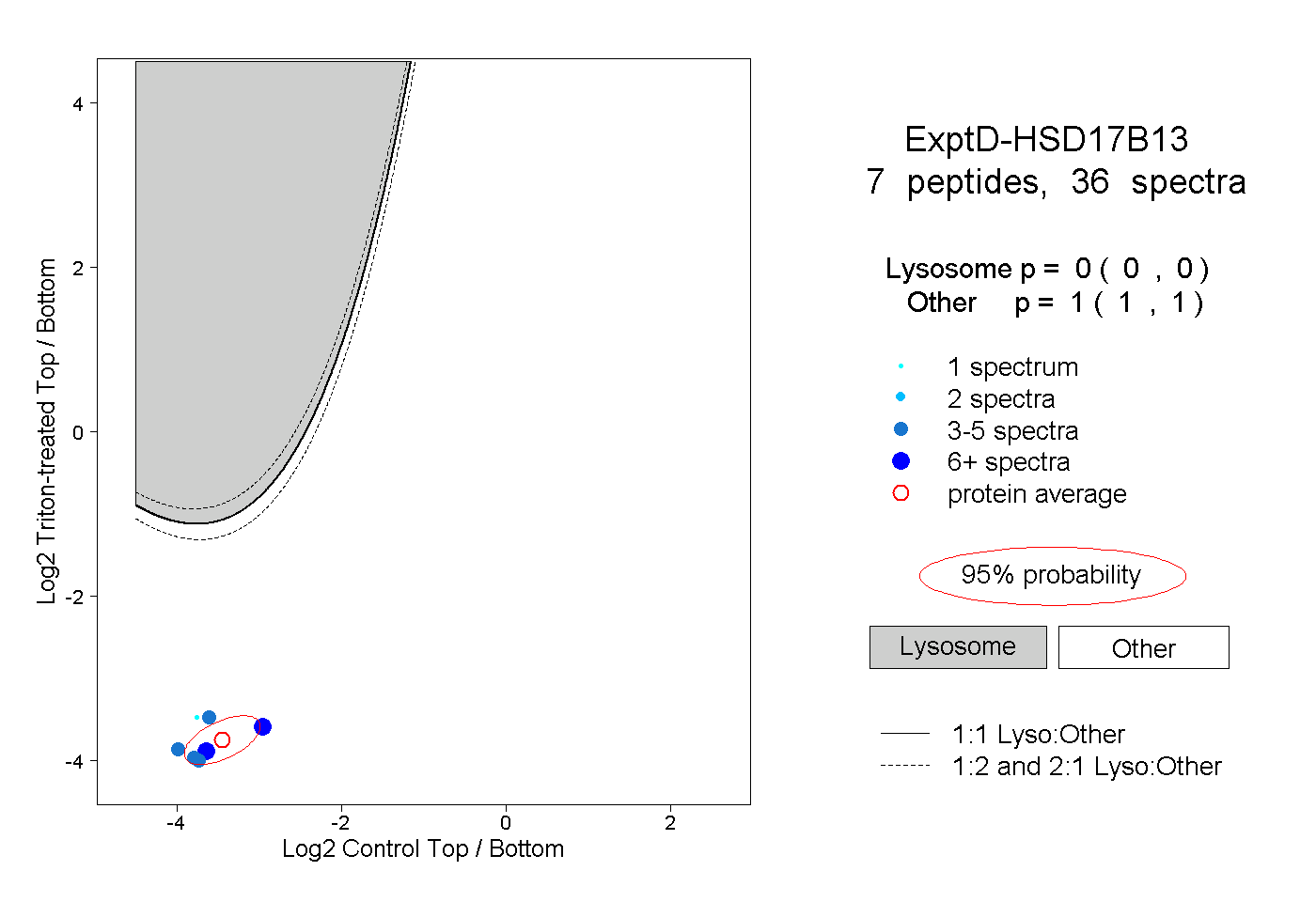 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |