peptides
spectra
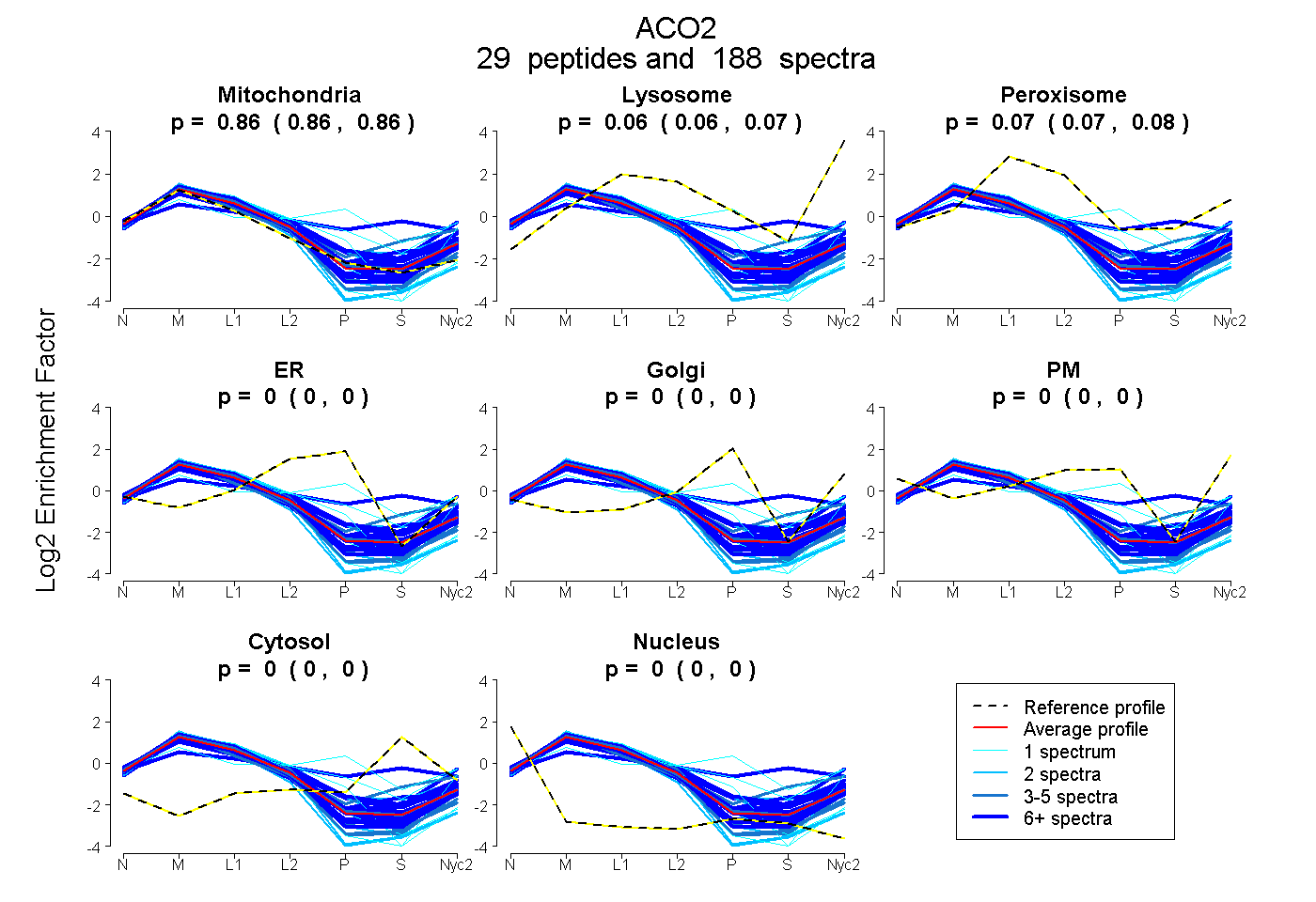
0.860 | 0.864
0.060 | 0.068
0.069 | 0.078
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
peptides
spectra
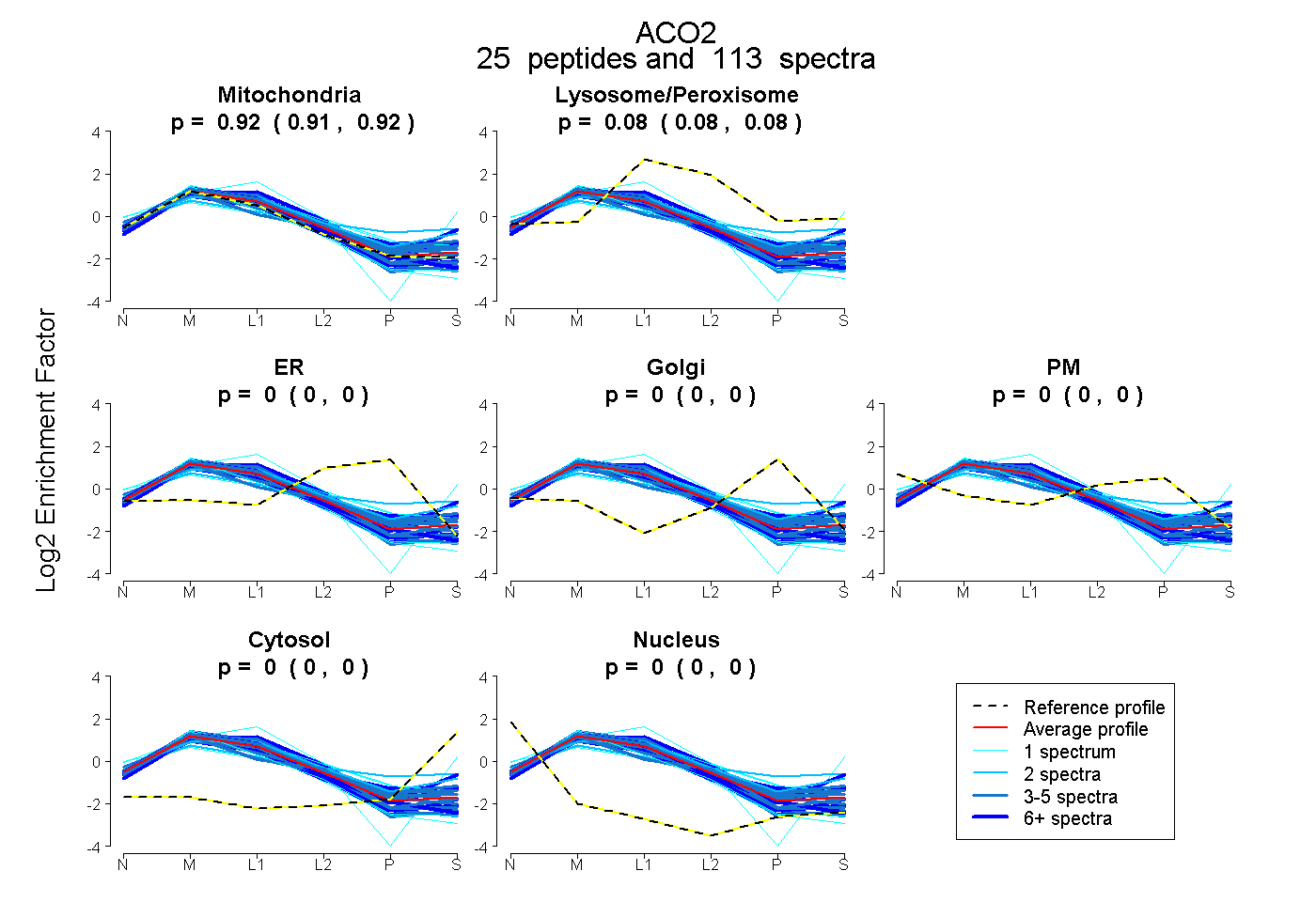
0.913 | 0.921
0.078 | 0.083
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.004
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
188 spectra |
 |
0.862 0.860 | 0.864 |
0.064 0.060 | 0.068 |
0.074 0.069 | 0.078 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
113 spectra |
 |
0.918 0.913 | 0.921 |
0.081 0.078 | 0.083 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.001 0.000 | 0.004 |
0.000 0.000 | 0.000 |
| 2 spectra, LTGTLSGWTSPK | 0.451 | 0.242 | 0.000 | 0.101 | 0.066 | 0.139 | 0.000 | |||
| 2 spectra, VAVPSTIHCDHLIEAQLGGEK | 0.646 | 0.266 | 0.000 | 0.000 | 0.000 | 0.087 | 0.000 | |||
| 4 spectra, SDFDPGQDTYQHPPK | 0.853 | 0.050 | 0.053 | 0.000 | 0.044 | 0.000 | 0.000 | |||
| 9 spectra, DGYAQILR | 0.990 | 0.010 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, EGWPLDIR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, IHPVDK | 0.944 | 0.056 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, YDLLEK | 0.930 | 0.070 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 14 spectra, IVYGHLDDPANQEIER | 0.756 | 0.142 | 0.000 | 0.056 | 0.000 | 0.047 | 0.000 | |||
| 1 spectrum, NAVTQEFGPVPDTAR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, NINIVR | 0.723 | 0.108 | 0.000 | 0.000 | 0.000 | 0.169 | 0.000 | |||
| 3 spectra, VGLIGSCTNSSYEDMGR | 0.947 | 0.000 | 0.007 | 0.000 | 0.000 | 0.045 | 0.000 | |||
| 3 spectra, LEAPDADELPR | 0.834 | 0.113 | 0.000 | 0.000 | 0.000 | 0.053 | 0.000 | |||
| 1 spectrum, LQLLEPFDK | 0.709 | 0.218 | 0.000 | 0.006 | 0.066 | 0.000 | 0.000 | |||
| 1 spectrum, DVGGIVLANACGPCIGQWDR | 0.653 | 0.067 | 0.000 | 0.000 | 0.000 | 0.281 | 0.000 | |||
| 3 spectra, QGLLPLTFADPSDYNK | 0.747 | 0.171 | 0.000 | 0.000 | 0.063 | 0.019 | 0.000 | |||
| 5 spectra, AGSALNR | 0.867 | 0.087 | 0.000 | 0.000 | 0.000 | 0.046 | 0.000 | |||
| 5 spectra, VAMSHFEPSEYIR | 0.756 | 0.091 | 0.001 | 0.051 | 0.000 | 0.101 | 0.000 | |||
| 11 spectra, VDVSPTSQR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 7 spectra, EHAALEPR | 0.765 | 0.217 | 0.000 | 0.000 | 0.000 | 0.018 | 0.000 | |||
| 3 spectra, LNRPLTLSEK | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, WVVIGDENYGEGSSR | 0.975 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.025 | |||
| 1 spectrum, IHETNLK | 0.719 | 0.275 | 0.000 | 0.000 | 0.005 | 0.000 | 0.000 | |||
| 3 spectra, VAGILTVK | 0.989 | 0.011 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, NTIVTSYNR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, QALAHGLK | 0.851 | 0.149 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
999 spectra |
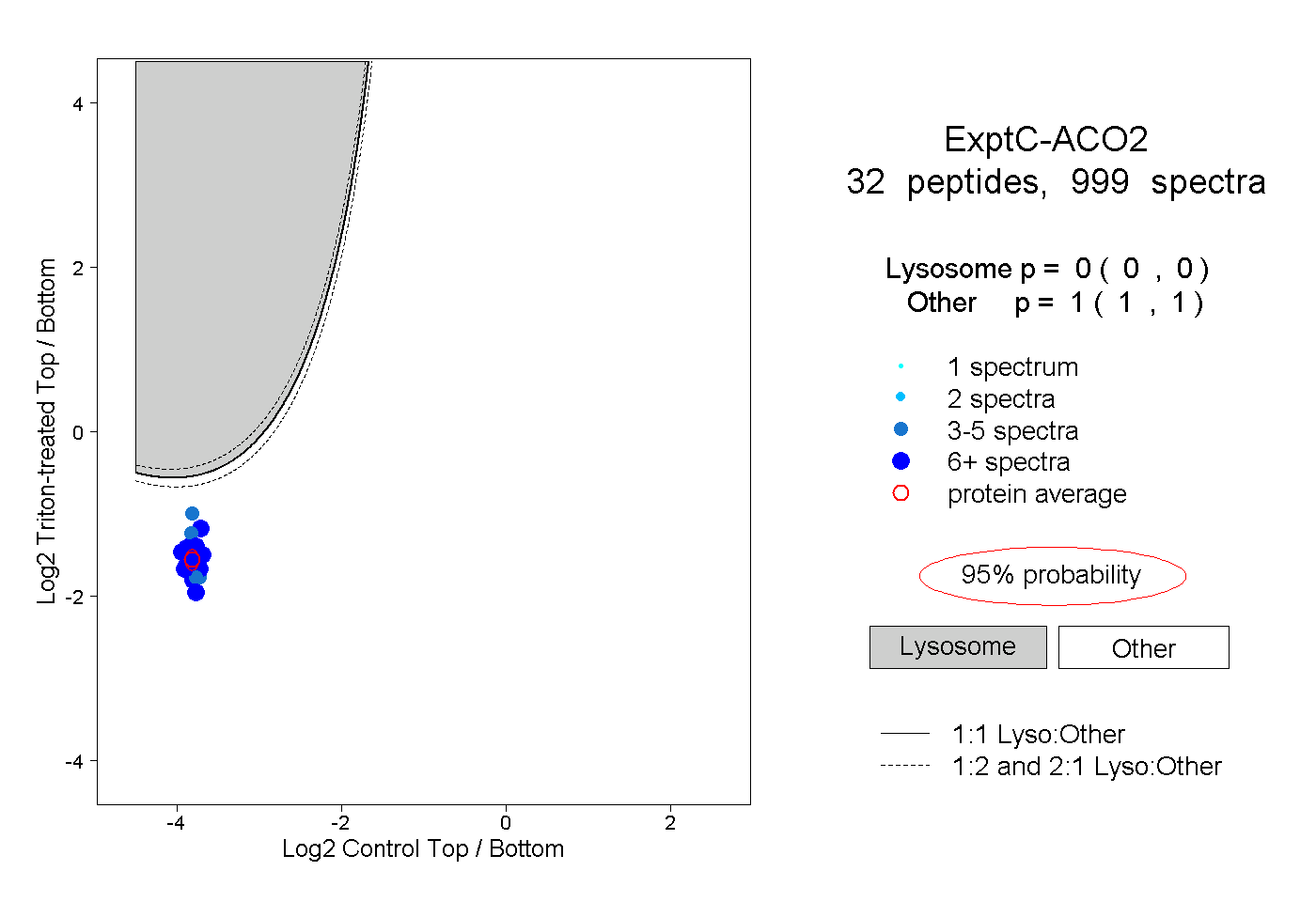 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
84 spectra |
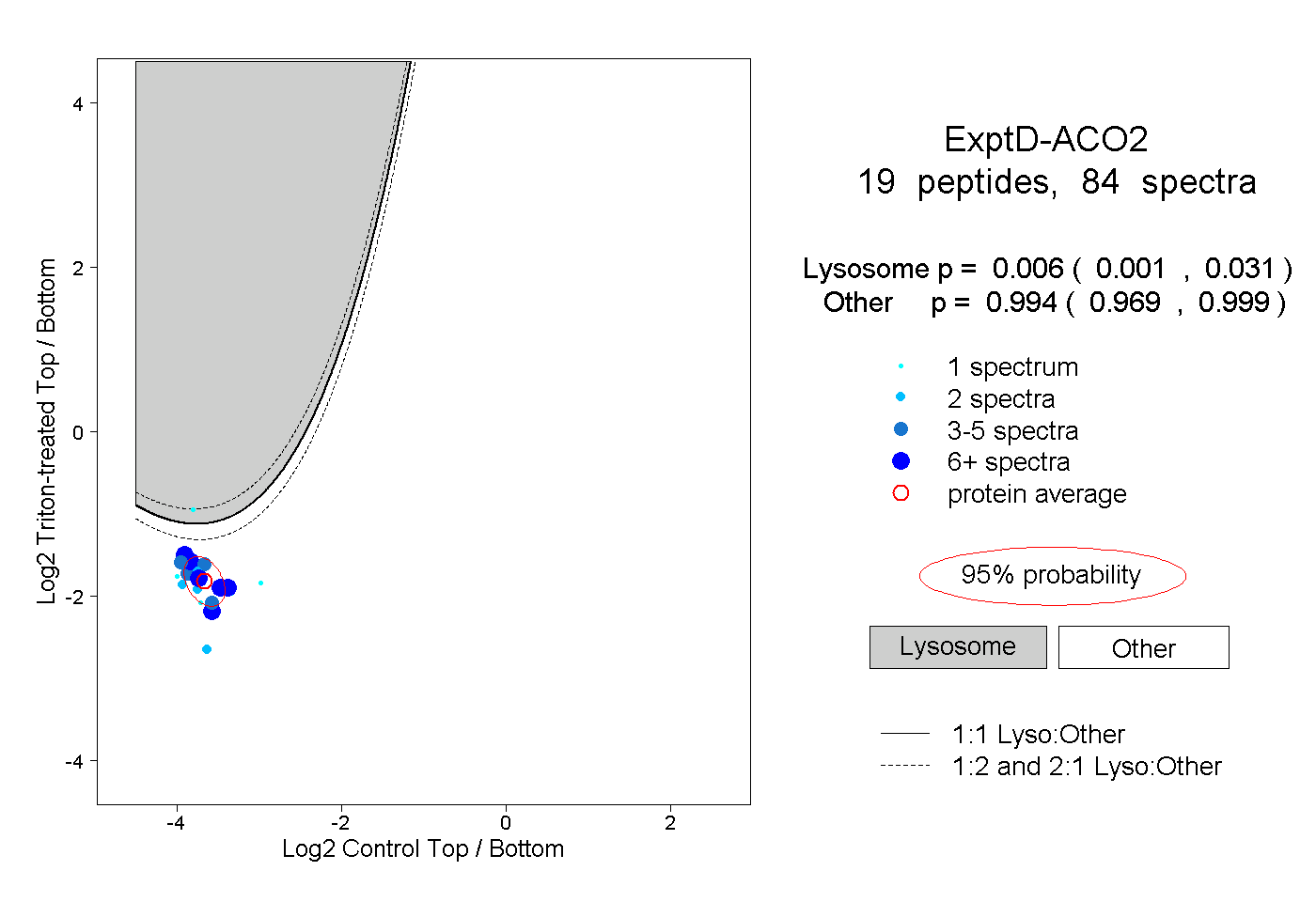 |
0.006 0.001 | 0.031 |
0.994 0.969 | 0.999 |