peptides
spectra
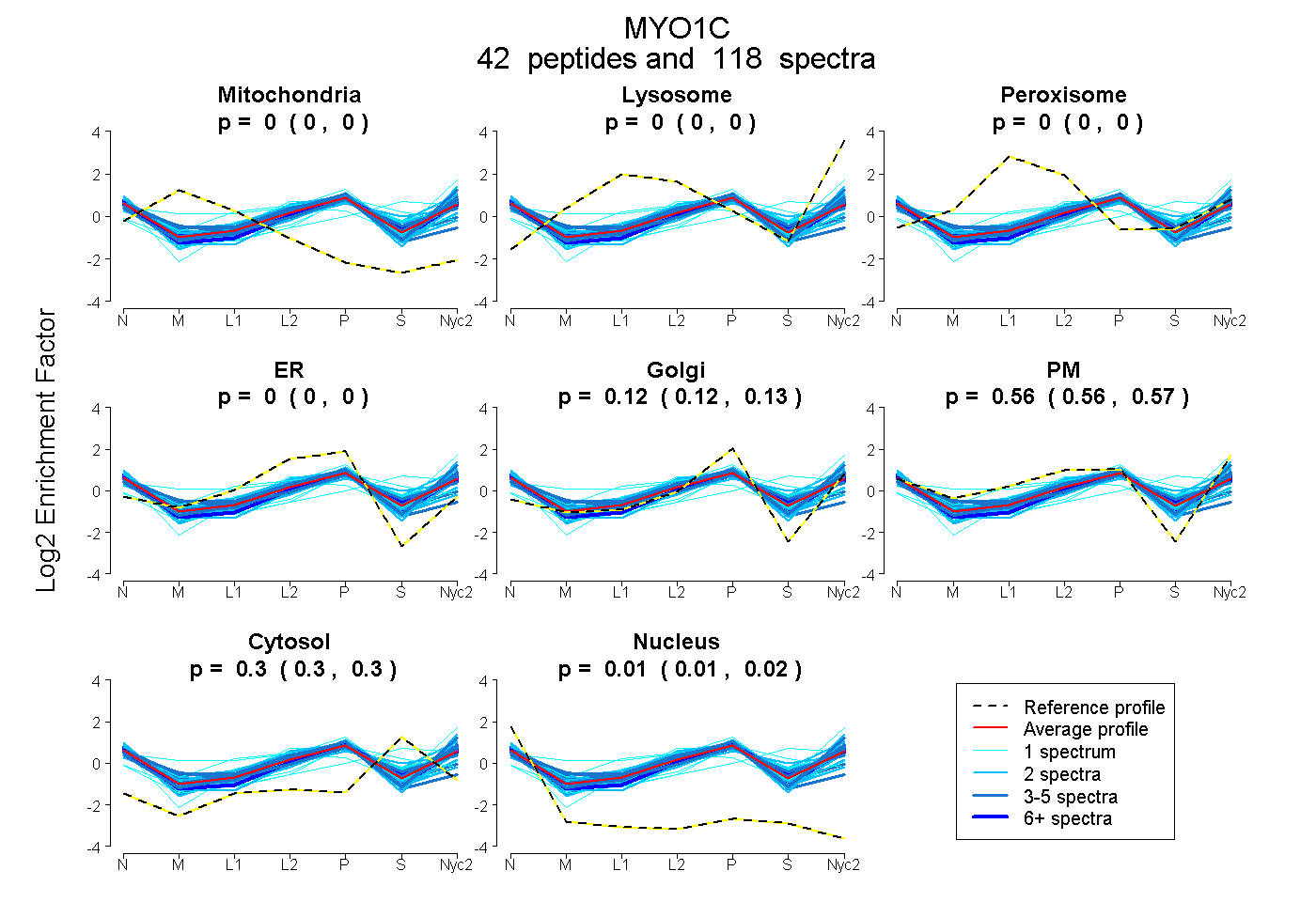
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.120 | 0.125
0.561 | 0.566
0.297 | 0.300
0.013 | 0.015
peptides
spectra
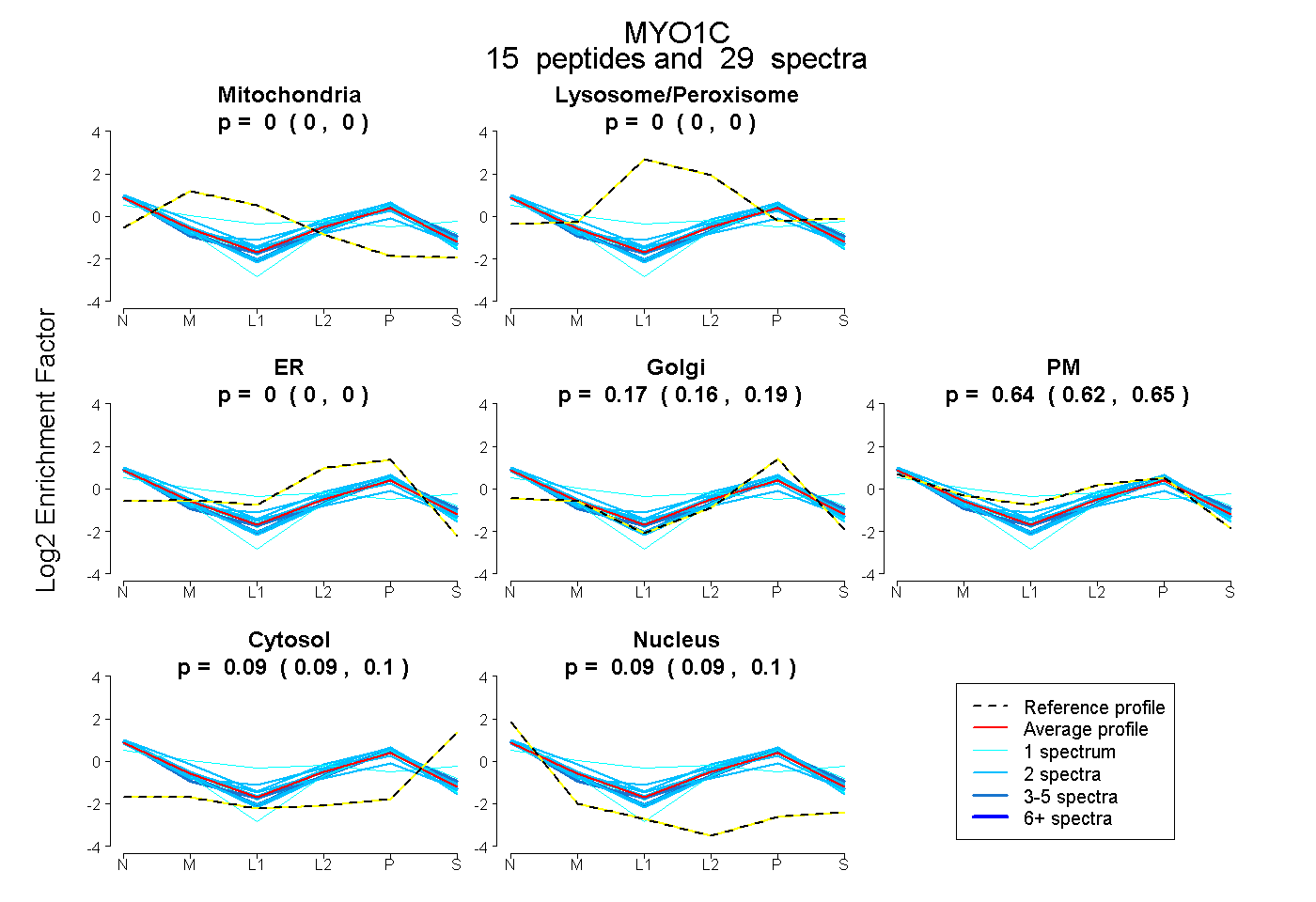
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.156 | 0.187
0.624 | 0.653
0.086 | 0.096
0.090 | 0.099
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
118 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.123 0.120 | 0.125 |
0.564 0.561 | 0.566 |
0.299 0.297 | 0.300 |
0.014 0.013 | 0.015 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
29 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.174 0.156 | 0.187 |
0.640 0.624 | 0.653 |
0.092 0.086 | 0.096 |
0.095 0.090 | 0.099 |
| 2 spectra, NPQSYLYLVK | 0.000 | 0.000 | 0.000 | 0.086 | 0.795 | 0.098 | 0.021 | |||
| 1 spectrum, MSLLQLVEILR | 0.000 | 0.000 | 0.000 | 0.553 | 0.241 | 0.000 | 0.206 | |||
| 2 spectra, TFTWLVR | 0.000 | 0.000 | 0.000 | 0.093 | 0.728 | 0.062 | 0.118 | |||
| 2 spectra, LLGVEGTTLR | 0.000 | 0.000 | 0.000 | 0.421 | 0.404 | 0.000 | 0.176 | |||
| 2 spectra, VVHQNHGER | 0.007 | 0.000 | 0.000 | 0.000 | 0.742 | 0.095 | 0.157 | |||
| 1 spectrum, DNYPQSVPR | 0.000 | 0.000 | 0.000 | 0.146 | 0.618 | 0.164 | 0.072 | |||
| 2 spectra, IQAAWR | 0.000 | 0.000 | 0.000 | 0.104 | 0.704 | 0.108 | 0.084 | |||
| 1 spectrum, AVASEIFK | 0.000 | 0.000 | 0.000 | 0.138 | 0.762 | 0.041 | 0.059 | |||
| 2 spectra, FDEVLIR | 0.000 | 0.000 | 0.000 | 0.276 | 0.535 | 0.116 | 0.073 | |||
| 2 spectra, TSFLLNLR | 0.000 | 0.000 | 0.000 | 0.133 | 0.764 | 0.071 | 0.032 | |||
| 4 spectra, IICDLVEEK | 0.000 | 0.000 | 0.000 | 0.205 | 0.561 | 0.130 | 0.105 | |||
| 1 spectrum, VNNININQGSITFAGGPGR | 0.088 | 0.229 | 0.000 | 0.000 | 0.435 | 0.211 | 0.037 | |||
| 1 spectrum, DLQIYTR | 0.000 | 0.000 | 0.000 | 0.288 | 0.585 | 0.025 | 0.102 | |||
| 4 spectra, LFLSTR | 0.000 | 0.000 | 0.000 | 0.350 | 0.467 | 0.054 | 0.129 | |||
| 2 spectra, LGTEEISPR | 0.000 | 0.000 | 0.000 | 0.366 | 0.444 | 0.056 | 0.134 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
152 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
3 spectra |
 |
0.000 0.000 | 0.002 |
1.000 0.998 | 1.000 |