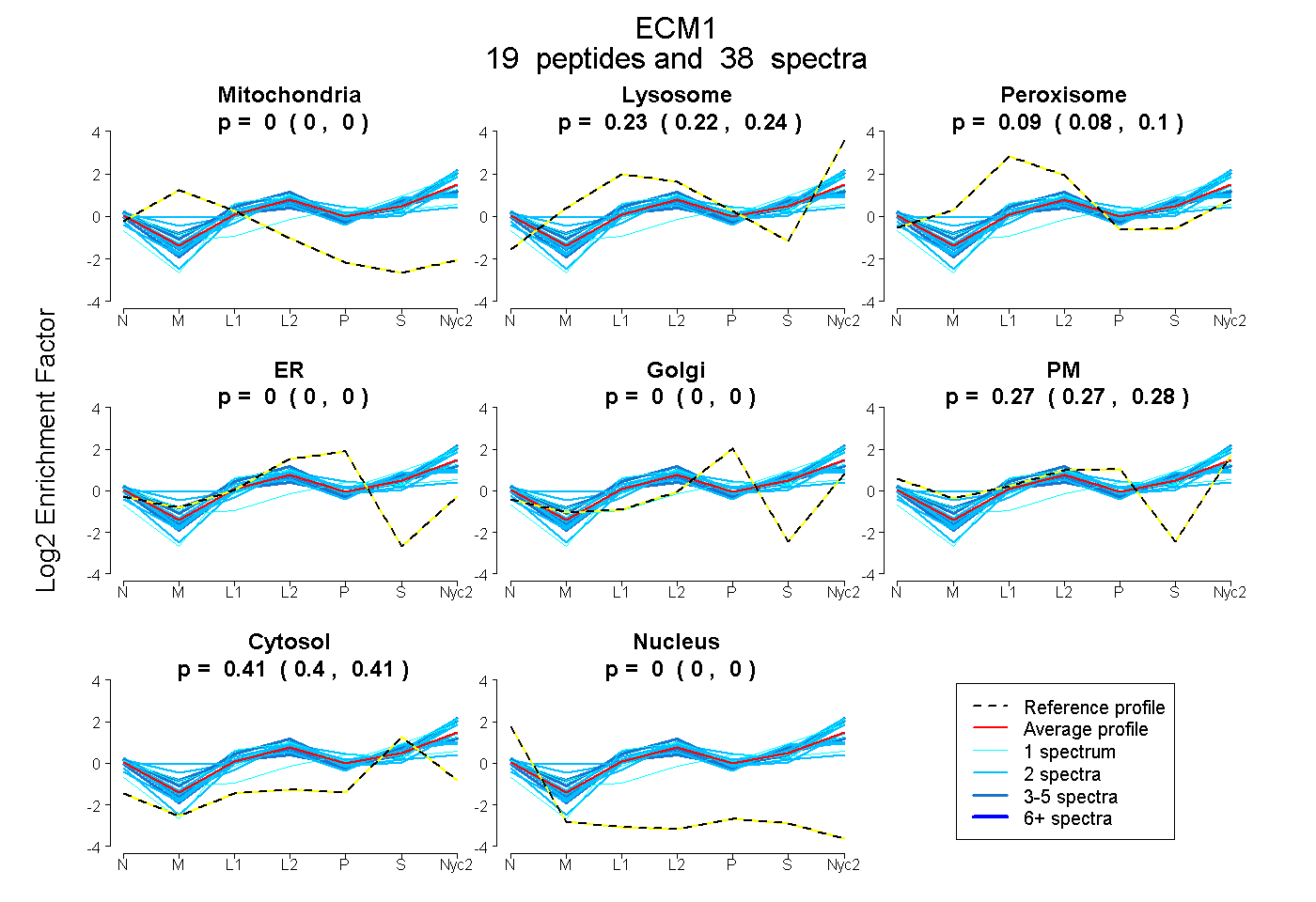
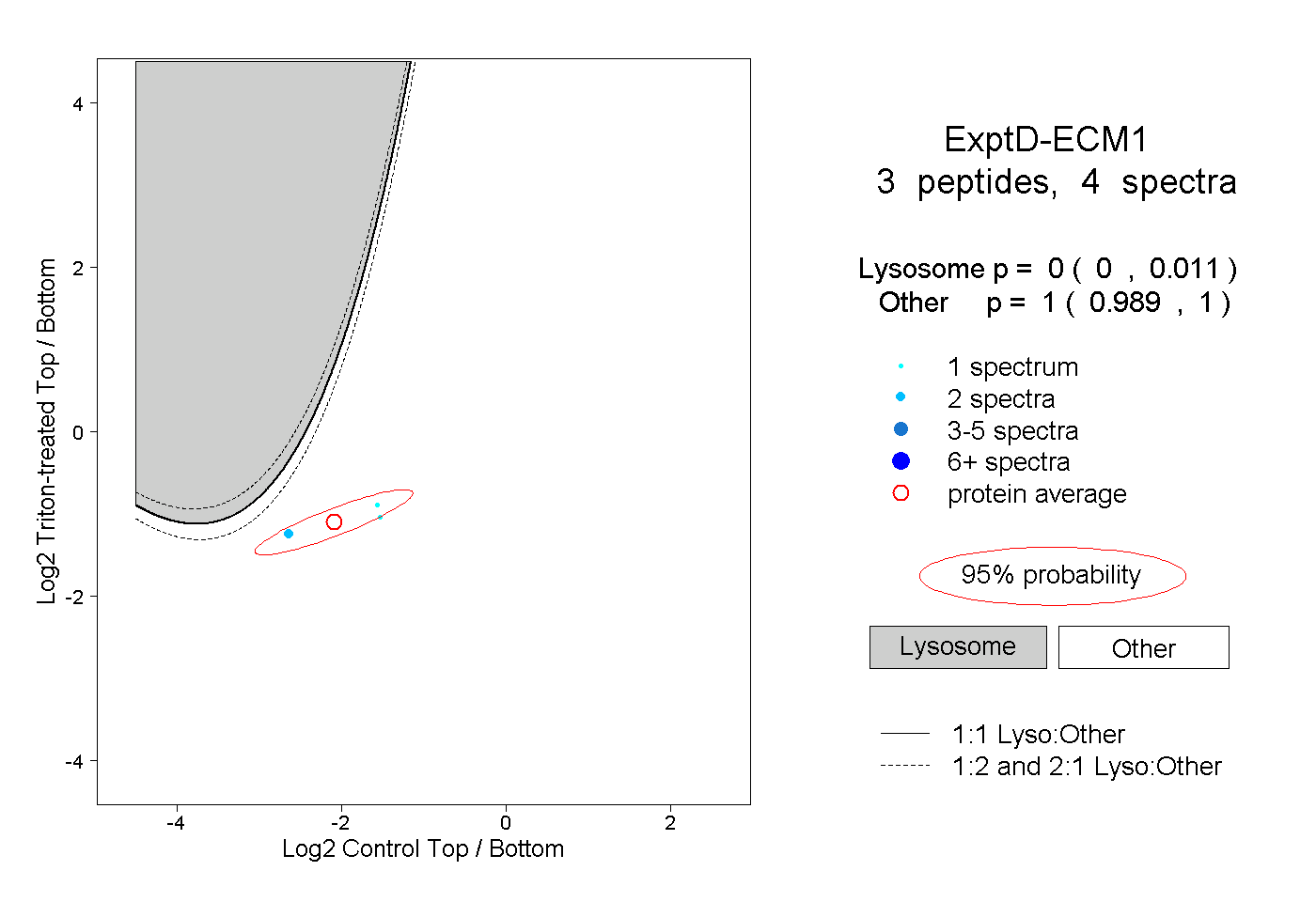
| 3 spectra, LETEFQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LDGFPPGRPSPDNLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, IPIEQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, DLLTVDLSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, NICLLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QLQALTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, NLPATDAIQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, EIDPPVQHQEEIVQSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LAFIEDLCGPR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, AWEDTLDGYCDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, TWNPAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QGEALNLLETGYSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QANCFNTNYLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, TRPHLCCK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, DPALCCTLSPGDK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, QICLPER |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, FSCFQK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GIWGHR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |