peptides
spectra
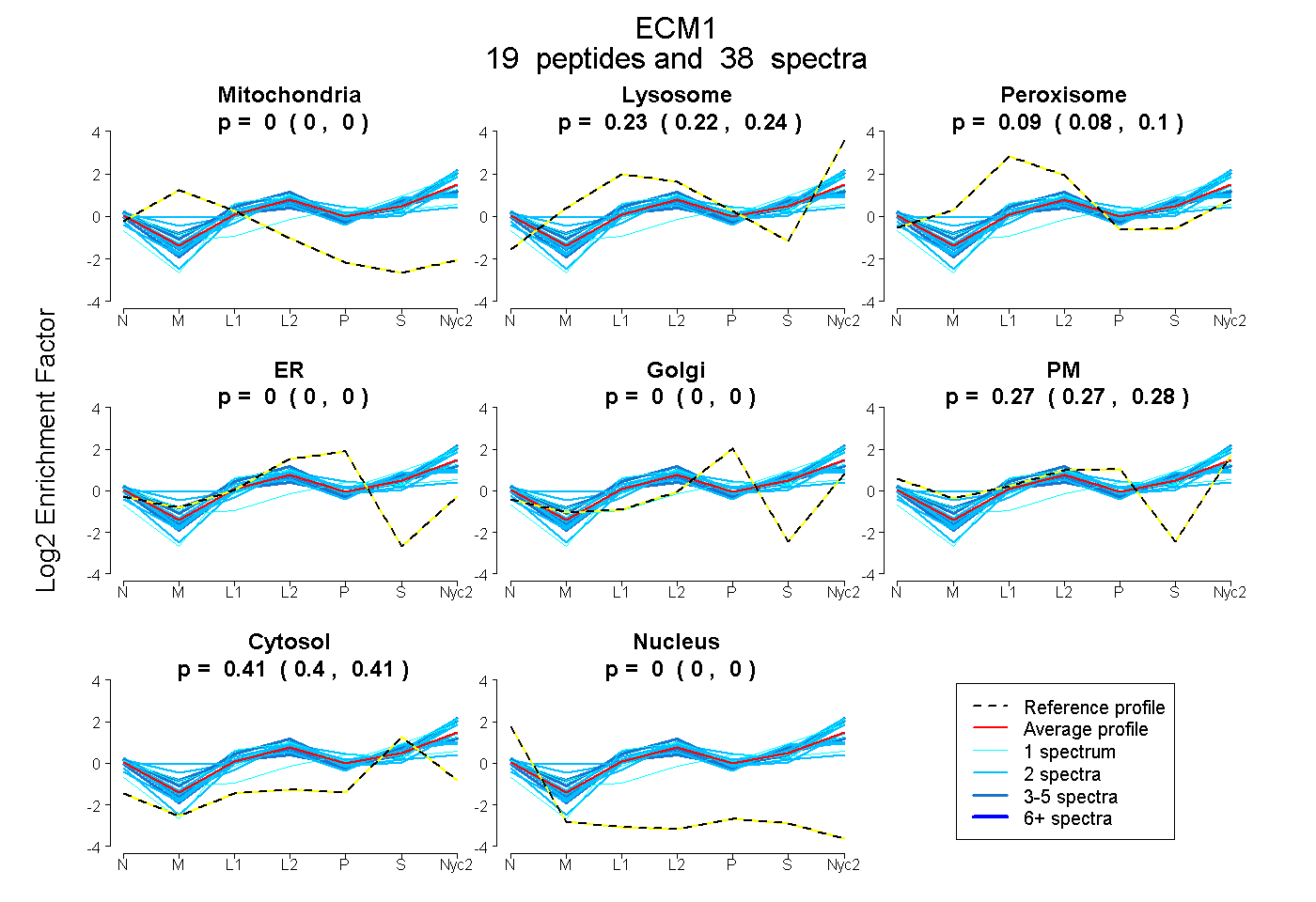
0.000 | 0.000
0.222 | 0.244
0.079 | 0.098
0.000 | 0.000
0.000 | 0.000
0.265 | 0.276
0.401 | 0.409
0.000 | 0.000
peptides
spectra

0.000 | 0.000
0.203 | 0.268
0.000 | 0.000
0.000 | 0.000
0.306 | 0.360
0.409 | 0.434
0.000 | 0.008
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
38 spectra |
 |
0.000 0.000 | 0.000 |
0.234 0.222 | 0.244 |
0.089 0.079 | 0.098 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.271 0.265 | 0.276 |
0.406 0.401 | 0.409 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
8 spectra |
 |
0.000 0.000 | 0.000 |
0.235 0.203 | 0.268 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.341 0.306 | 0.360 |
0.424 0.409 | 0.434 |
0.000 0.000 | 0.008 |
| 2 spectra, LETEFQR | 0.000 | 0.172 | 0.000 | 0.000 | 0.367 | 0.461 | 0.000 | |||
| 1 spectrum, QICLPER | 0.000 | 0.389 | 0.000 | 0.000 | 0.262 | 0.327 | 0.022 | |||
| 2 spectra, NICLLR | 0.000 | 0.145 | 0.000 | 0.000 | 0.366 | 0.489 | 0.000 | |||
| 2 spectra, QLQALTR | 0.000 | 0.149 | 0.000 | 0.000 | 0.418 | 0.432 | 0.000 | |||
| 1 spectrum, NLPATDAIQR | 0.000 | 0.354 | 0.000 | 0.000 | 0.242 | 0.380 | 0.023 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
52 spectra |
 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
4 spectra |
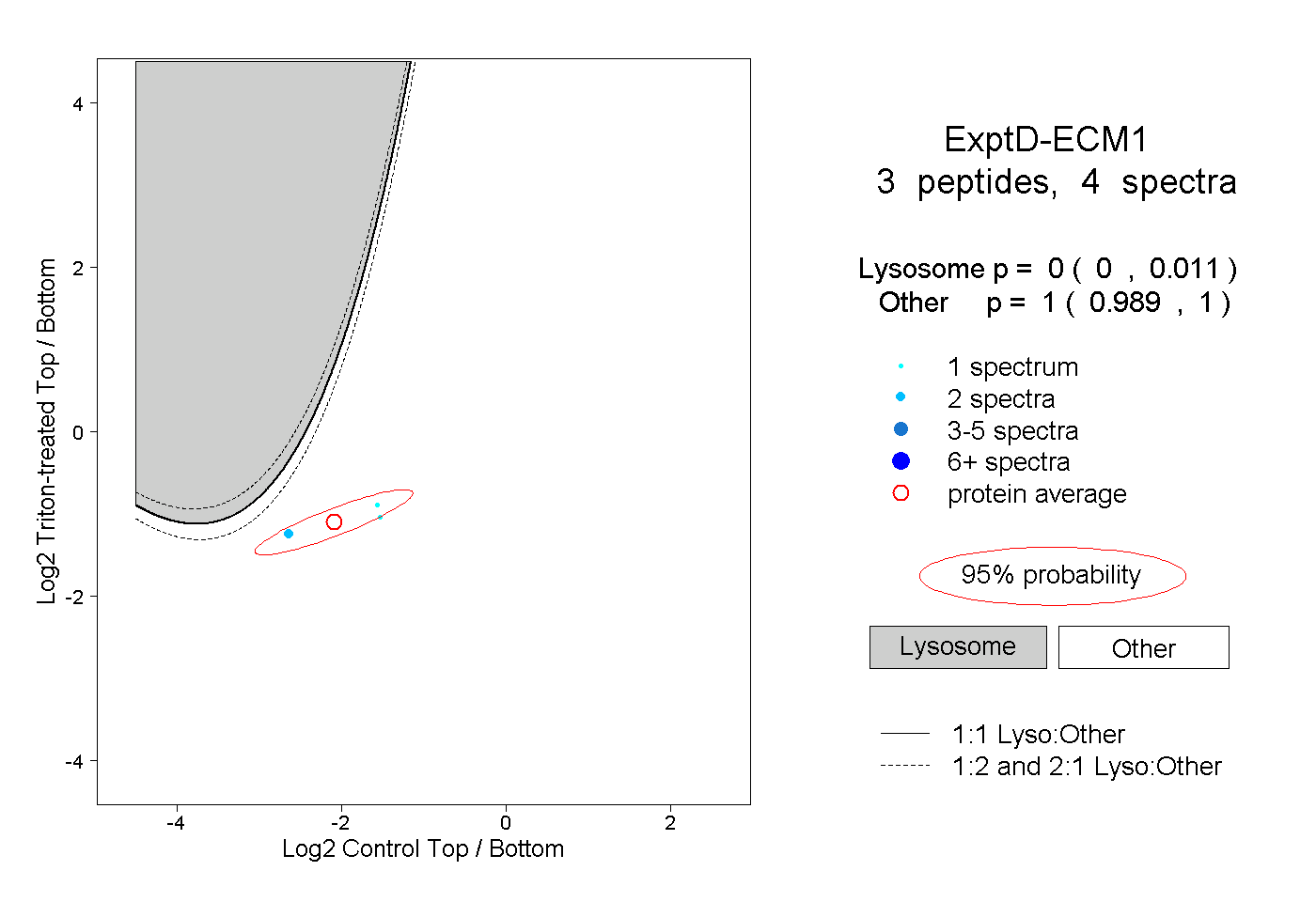 |
0.000 0.000 | 0.011 |
1.000 0.989 | 1.000 |