peptides
spectra
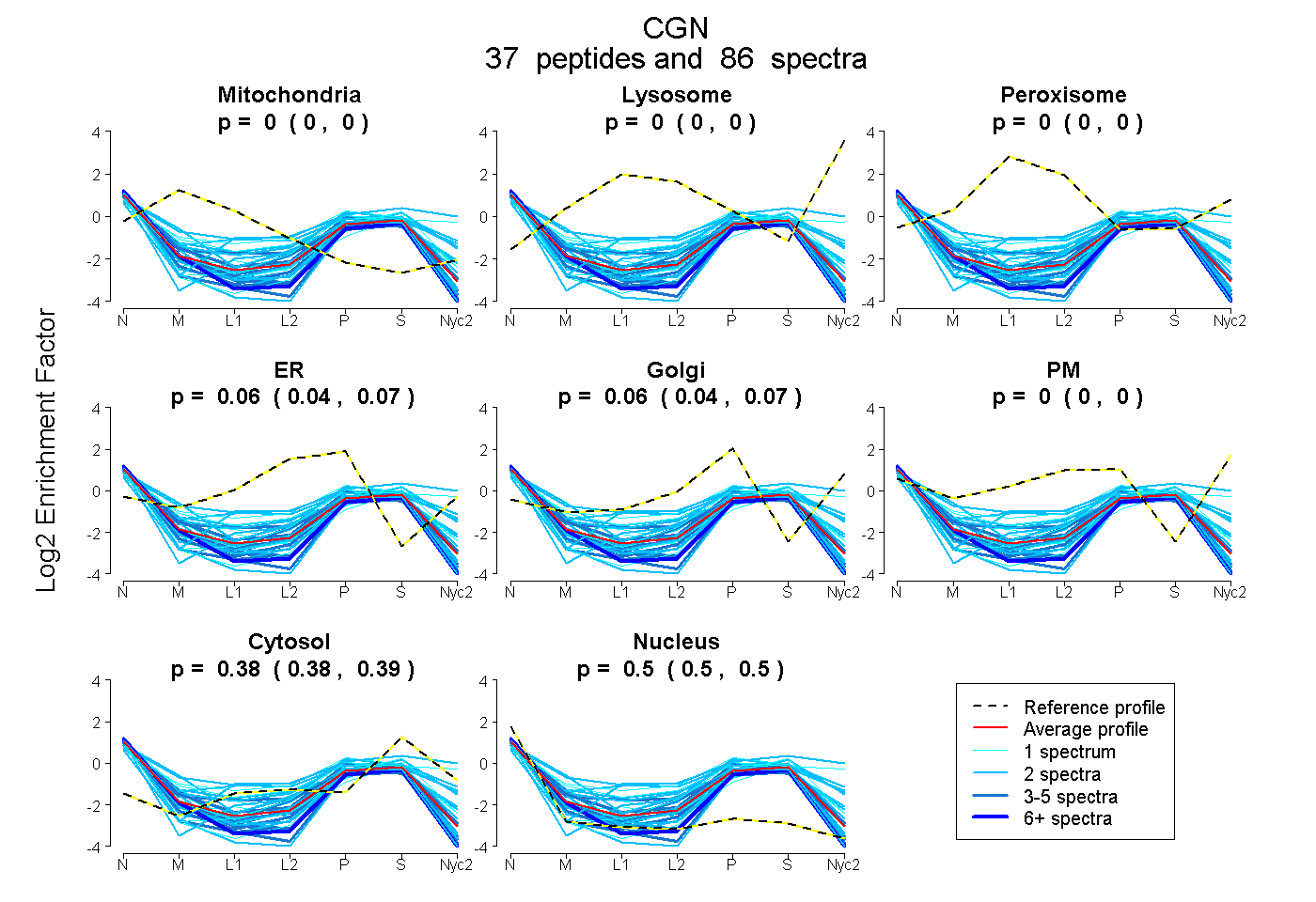
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.041 | 0.067
0.045 | 0.075
0.000 | 0.000
0.383 | 0.386
0.496 | 0.502
peptides
spectra
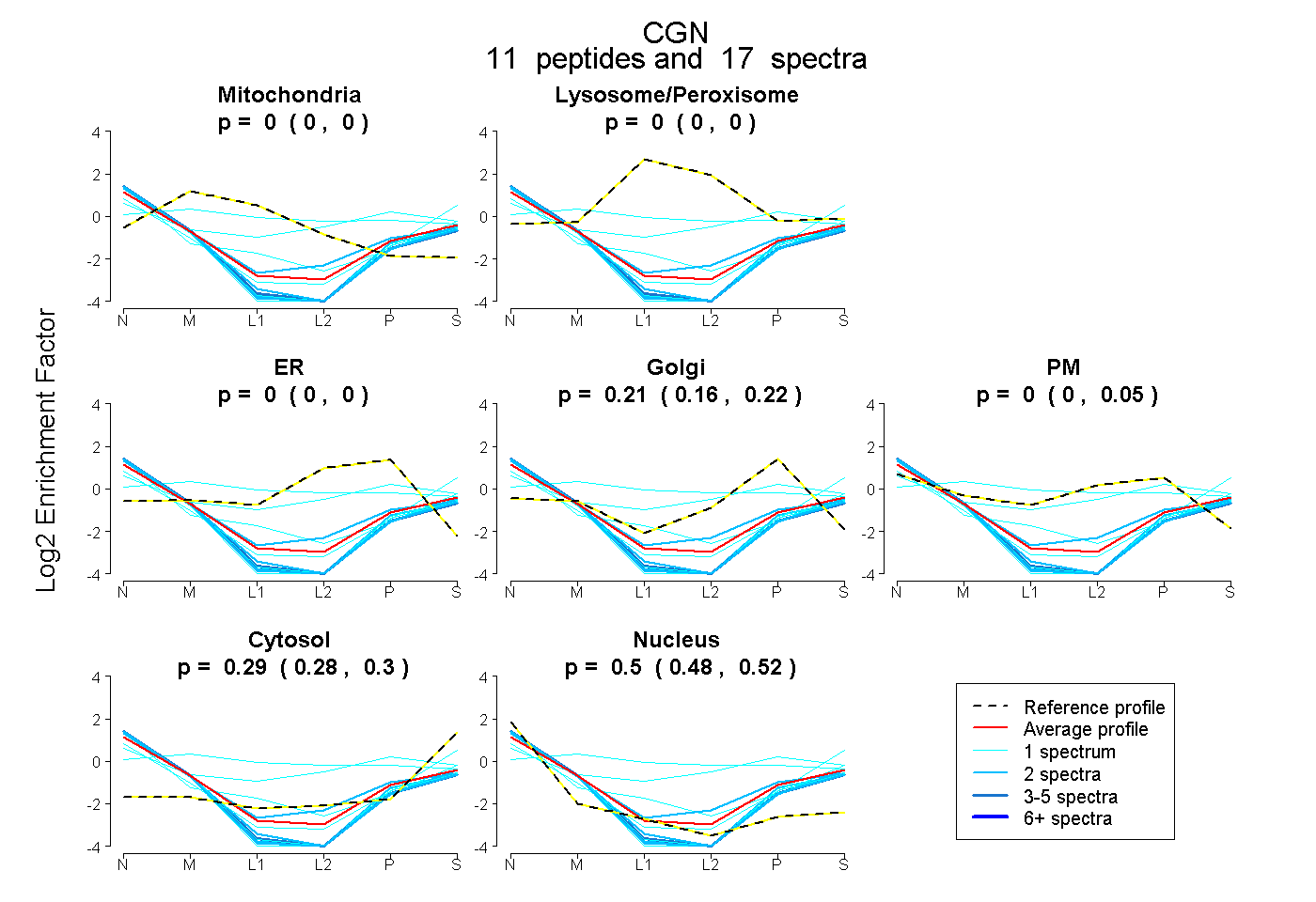
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.158 | 0.221
0.000 | 0.046
0.279 | 0.302
0.476 | 0.520
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
86 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.055 0.041 | 0.067 |
0.061 0.045 | 0.075 |
0.000 0.000 | 0.000 |
0.384 0.383 | 0.386 |
0.499 0.496 | 0.502 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
17 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.208 0.158 | 0.221 |
0.000 0.000 | 0.046 |
0.290 0.279 | 0.302 |
0.502 0.476 | 0.520 |
| 2 spectra, LGQEQQALNR | 0.000 | 0.000 | 0.000 | 0.112 | 0.198 | 0.240 | 0.450 | |||
| 3 spectra, ELLEELLEGK | 0.000 | 0.000 | 0.000 | 0.062 | 0.000 | 0.240 | 0.698 | |||
| 2 spectra, ALVGQAELTR | 0.000 | 0.000 | 0.000 | 0.098 | 0.000 | 0.230 | 0.672 | |||
| 1 spectrum, QATVETTLR | 0.000 | 0.000 | 0.000 | 0.038 | 0.000 | 0.516 | 0.445 | |||
| 2 spectra, TVLQSTNR | 0.000 | 0.000 | 0.000 | 0.050 | 0.000 | 0.247 | 0.702 | |||
| 1 spectrum, QALQTSQAER | 0.000 | 0.000 | 0.000 | 0.081 | 0.000 | 0.242 | 0.678 | |||
| 1 spectrum, SMQDATQDHAAVEAER | 0.000 | 0.062 | 0.000 | 0.000 | 0.661 | 0.277 | 0.000 | |||
| 1 spectrum, EGSADSEASVR | 0.000 | 0.000 | 0.000 | 0.078 | 0.000 | 0.250 | 0.672 | |||
| 1 spectrum, GPVDHGVQIR | 0.180 | 0.231 | 0.000 | 0.000 | 0.405 | 0.184 | 0.000 | |||
| 2 spectra, LLLGQEEGLR | 0.000 | 0.000 | 0.000 | 0.031 | 0.000 | 0.293 | 0.675 | |||
| 1 spectrum, ASTYGVAVR | 0.000 | 0.114 | 0.000 | 0.000 | 0.065 | 0.280 | 0.541 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
27 spectra |
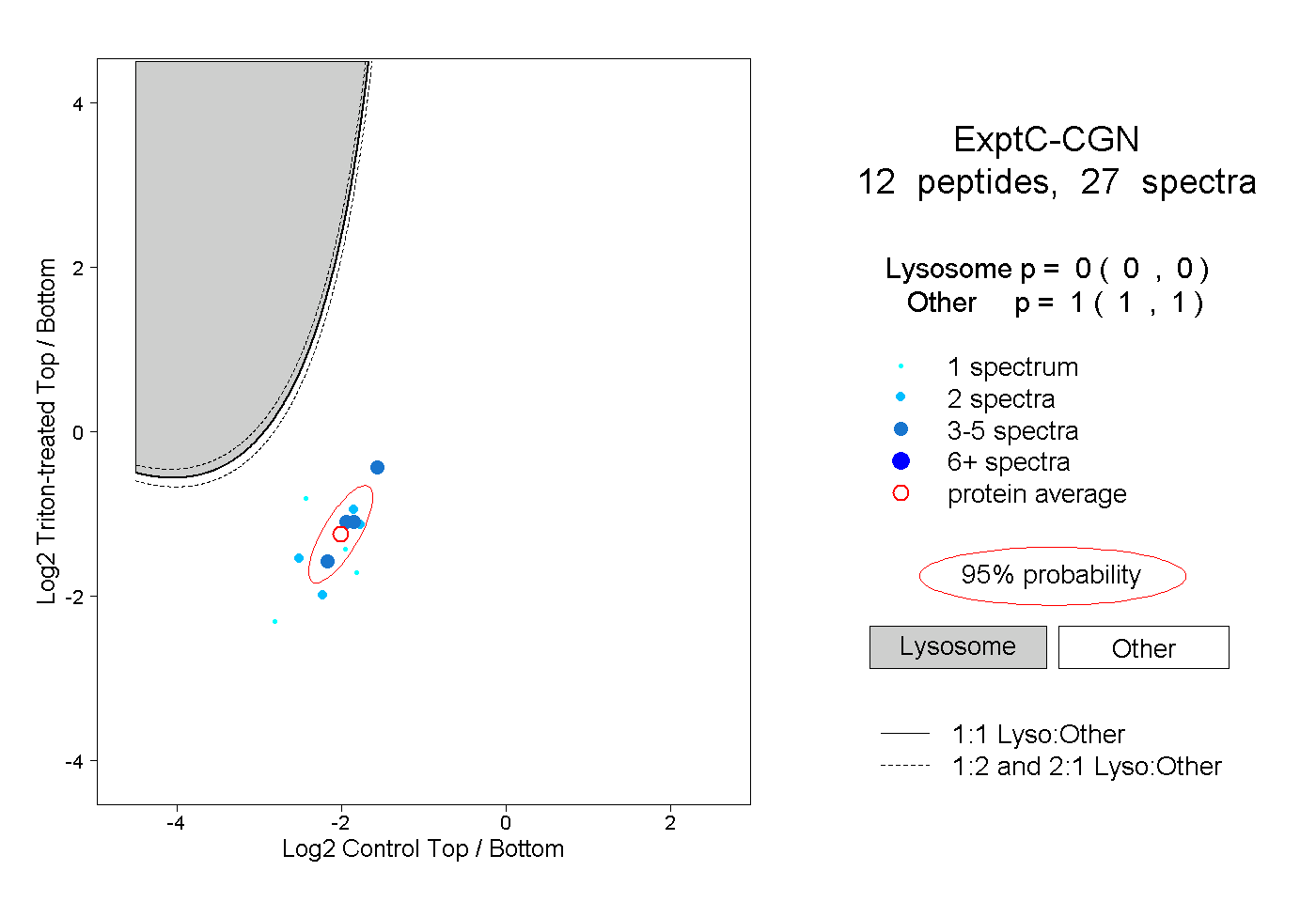 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
 |
0.000 NA | NA |
1.000 NA | NA |