peptides
spectra
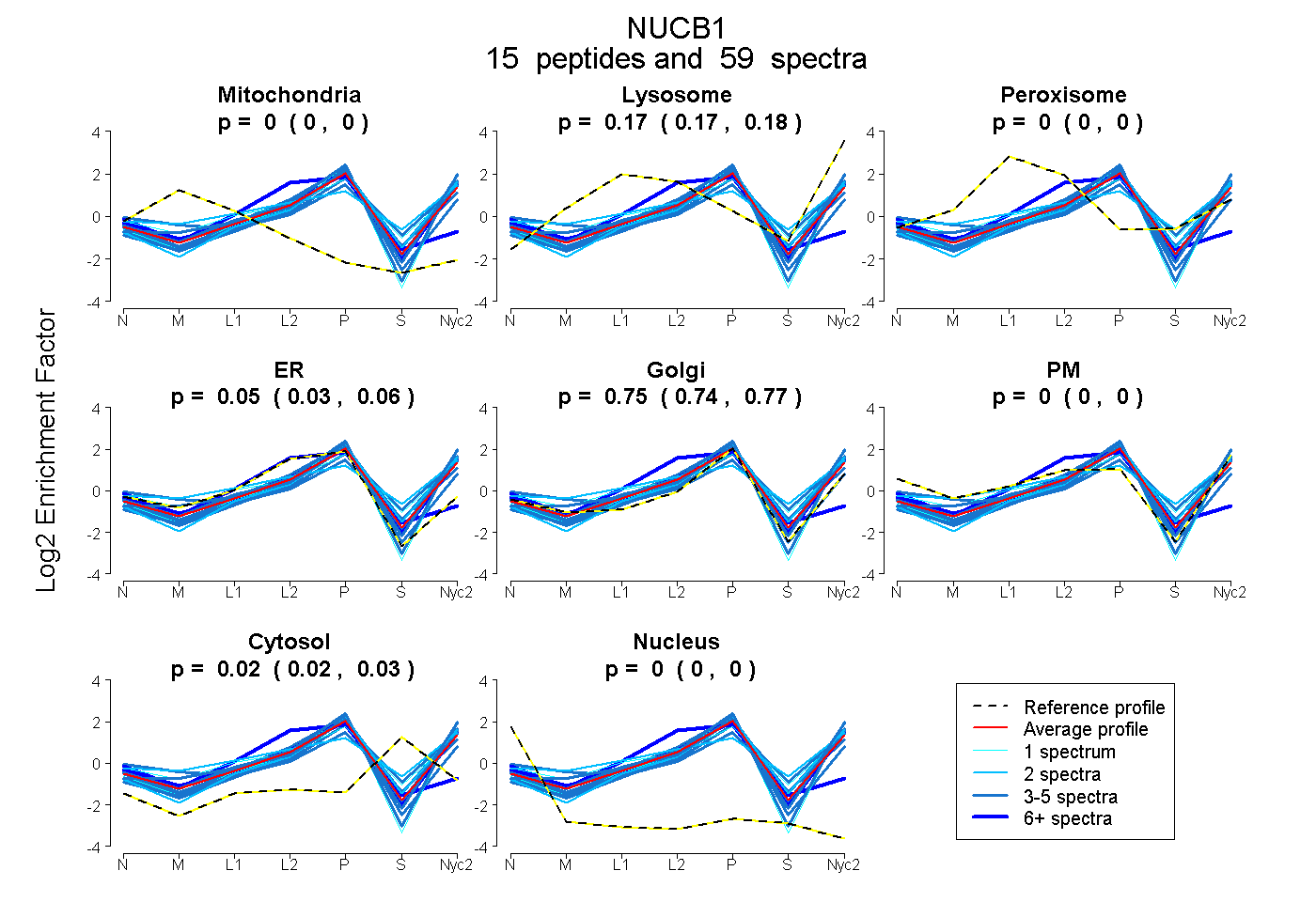
0.000 | 0.000
0.166 | 0.178
0.000 | 0.000
0.033 | 0.063
0.739 | 0.768
0.000 | 0.000
0.018 | 0.029
0.000 | 0.000
peptides
spectra
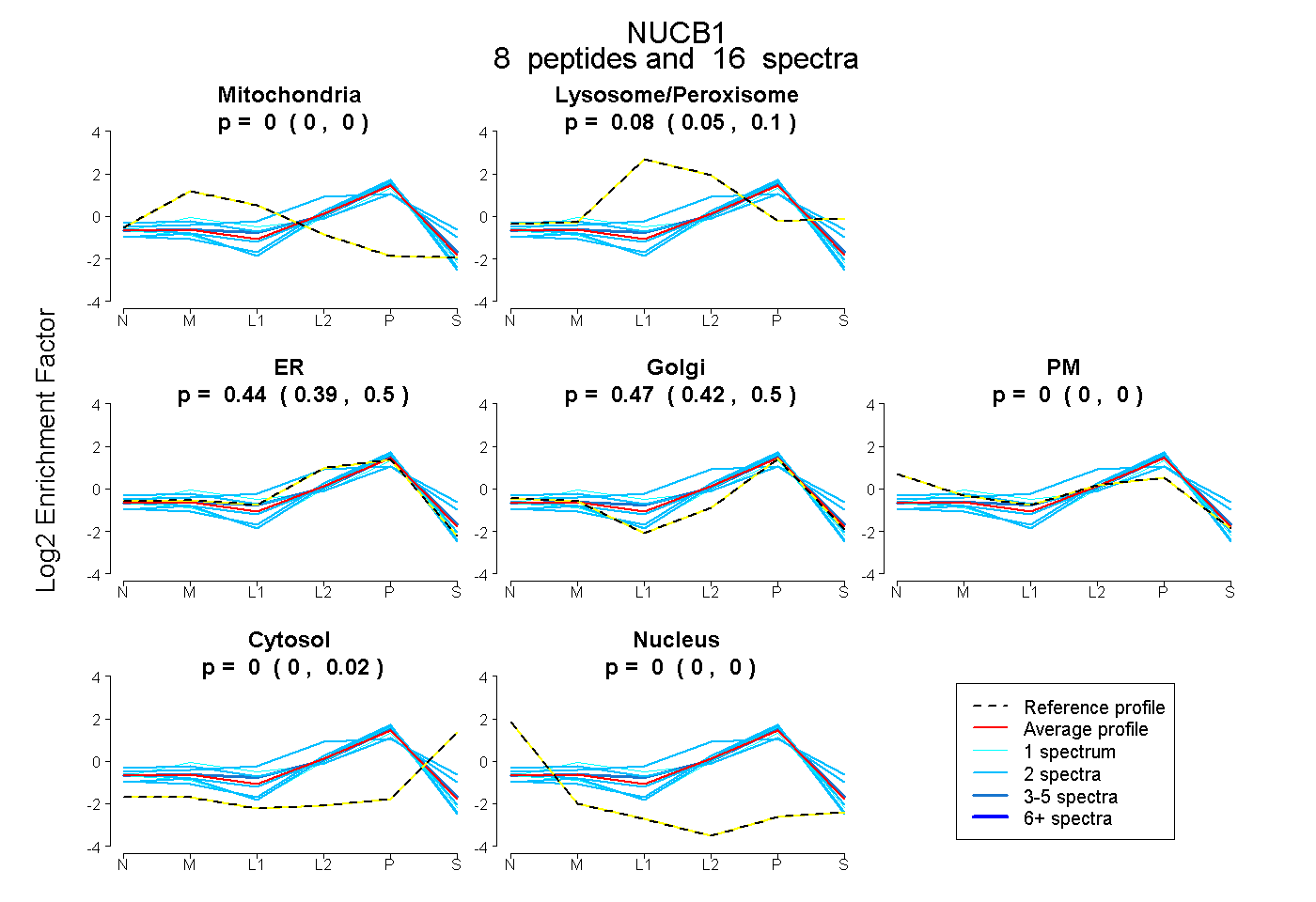
0.000 | 0.000
0.050 | 0.103
0.385 | 0.502
0.418 | 0.503
0.000 | 0.000
0.000 | 0.018
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
59 spectra |
 |
0.000 0.000 | 0.000 |
0.172 0.166 | 0.178 |
0.000 0.000 | 0.000 |
0.049 0.033 | 0.063 |
0.755 0.739 | 0.768 |
0.000 0.000 | 0.000 |
0.024 0.018 | 0.029 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
16 spectra |
 |
0.000 0.000 | 0.000 |
0.082 0.050 | 0.103 |
0.442 0.385 | 0.502 |
0.474 0.418 | 0.503 |
0.000 0.000 | 0.000 |
0.001 0.000 | 0.018 |
0.000 0.000 | 0.000 |
| 2 spectra, YLQEVINVLETDGHFR | 0.000 | 0.000 | 0.425 | 0.575 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LQEEER | 0.000 | 0.342 | 0.346 | 0.243 | 0.000 | 0.068 | 0.000 | |||
| 4 spectra, LSQELDFVSHNVR | 0.000 | 0.149 | 0.323 | 0.528 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, FEEELAAR | 0.000 | 0.000 | 0.527 | 0.473 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LQAANAEDIK | 0.118 | 0.074 | 0.436 | 0.372 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, EAELNAR | 0.000 | 0.000 | 0.588 | 0.412 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LSQETEALGR | 0.000 | 0.000 | 0.377 | 0.623 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, QFEHLDPQNQHTFEAR | 0.000 | 0.295 | 0.000 | 0.687 | 0.000 | 0.018 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
91 spectra |
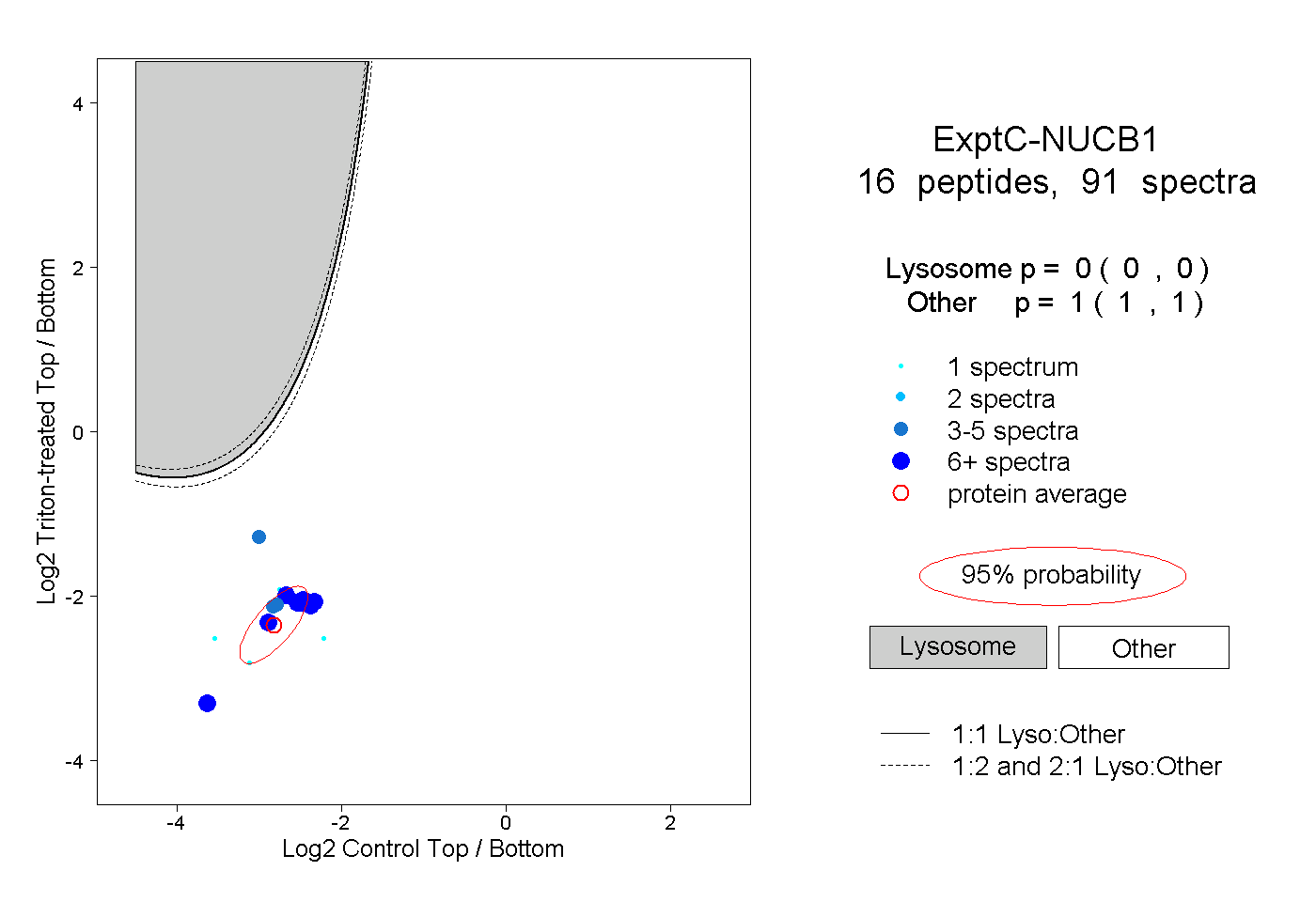 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
13 spectra |
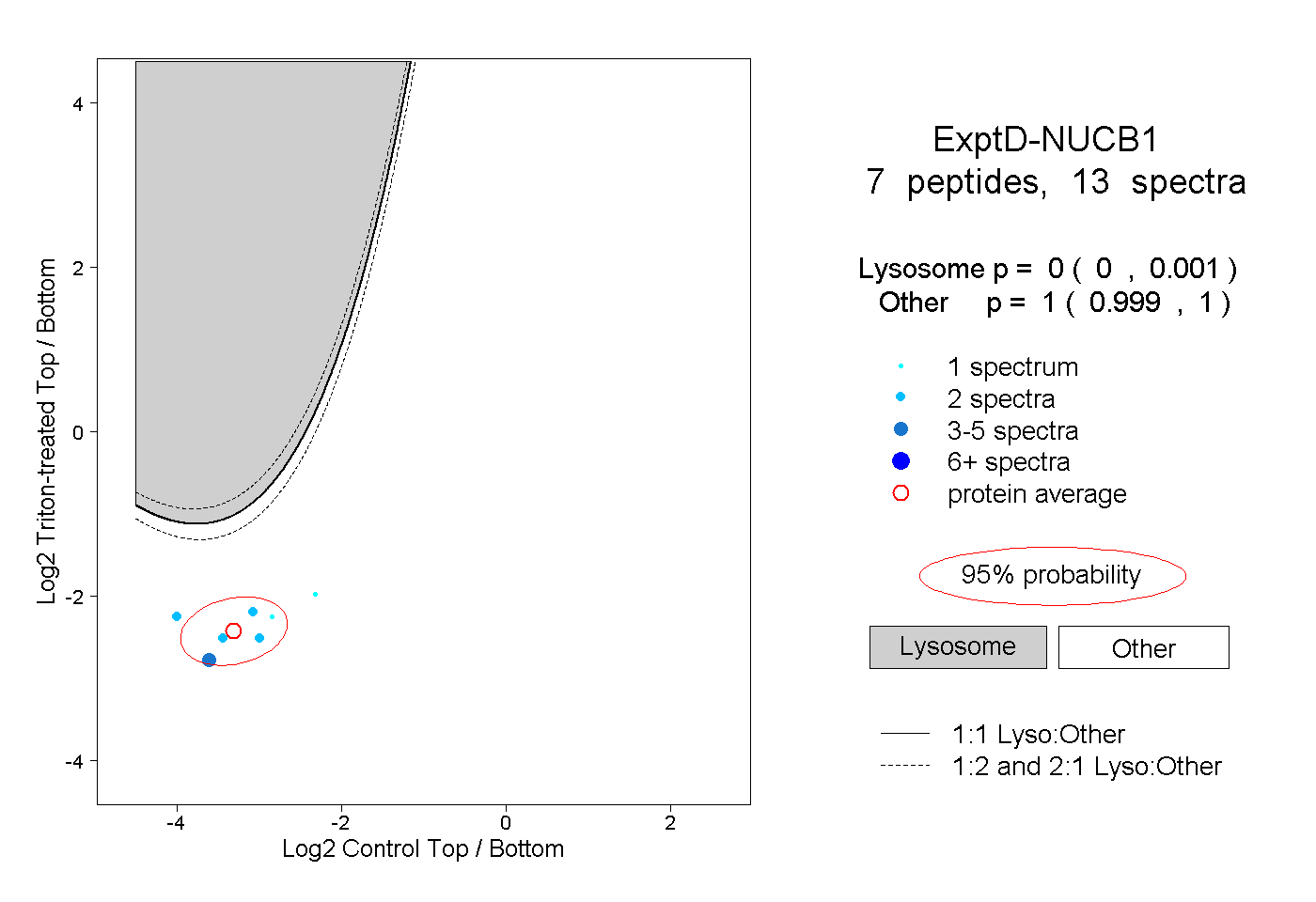 |
0.000 0.000 | 0.001 |
1.000 0.999 | 1.000 |