peptides
spectra
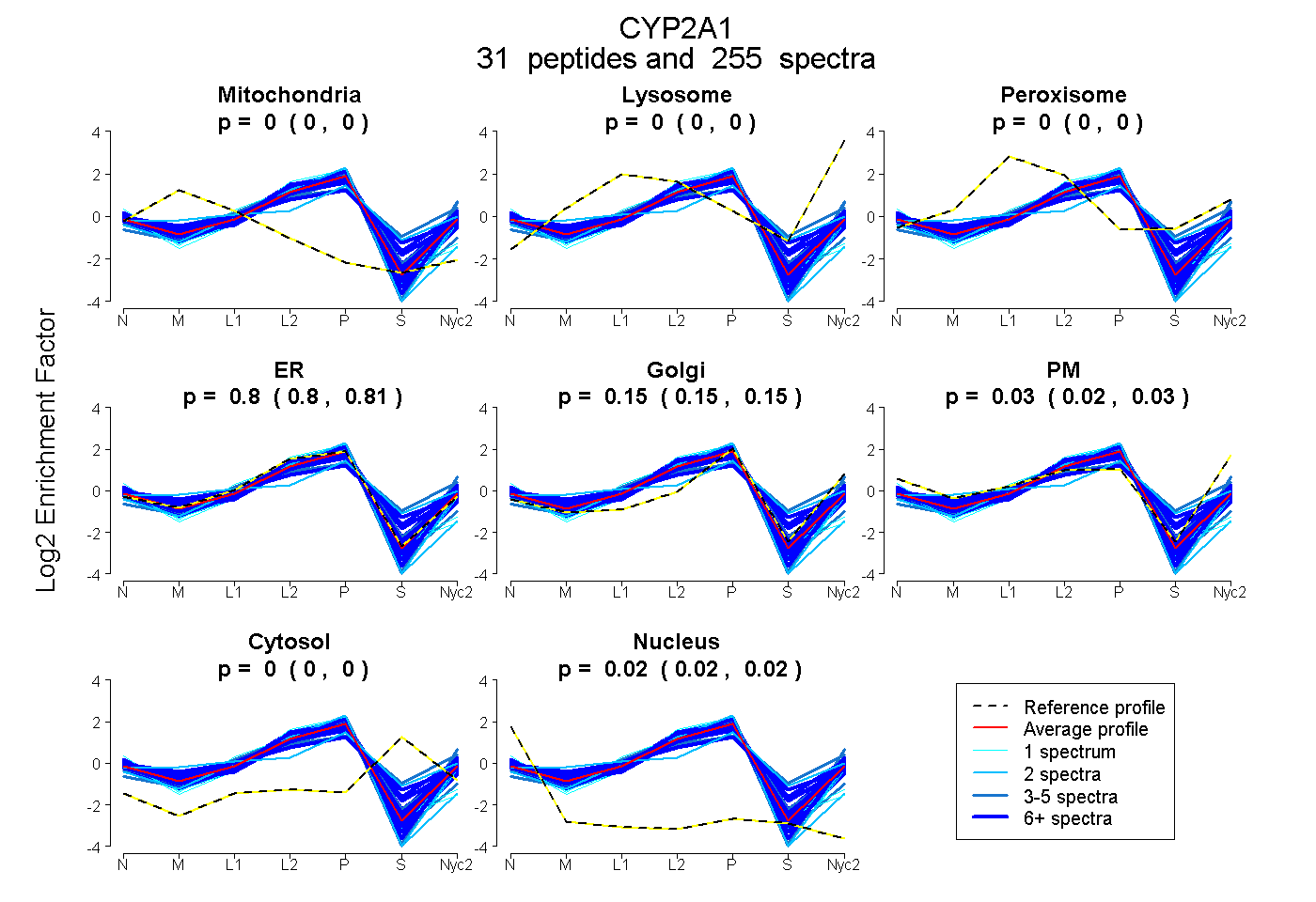
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.798 | 0.805
0.145 | 0.151
0.024 | 0.030
0.000 | 0.000
0.021 | 0.023
peptides
spectra
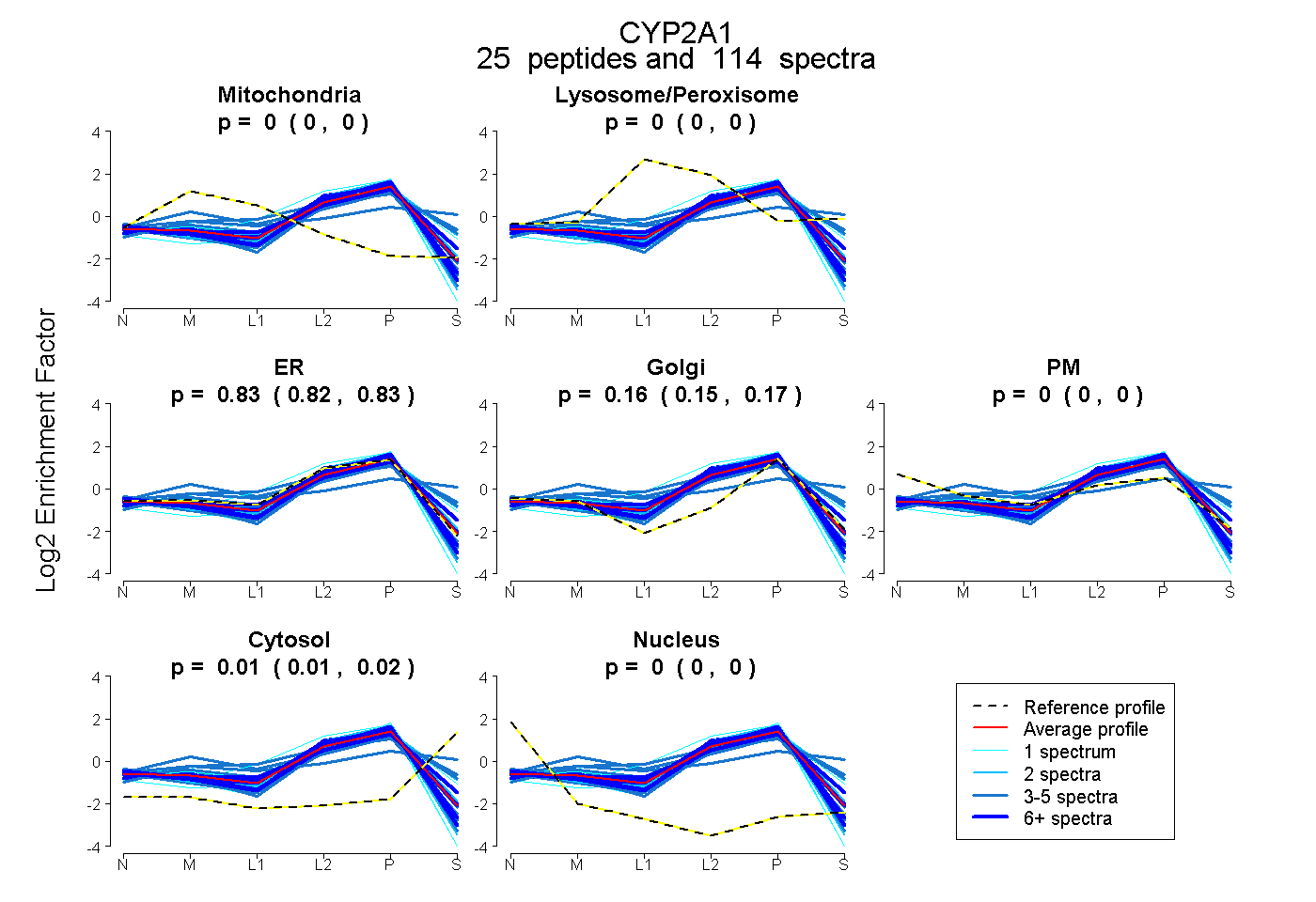
0.000 | 0.000
0.000 | 0.000
0.823 | 0.833
0.151 | 0.166
0.000 | 0.000
0.007 | 0.016
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
255 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.802 0.798 | 0.805 |
0.149 0.145 | 0.151 |
0.028 0.024 | 0.030 |
0.000 0.000 | 0.000 |
0.022 0.021 | 0.023 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
114 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.828 0.823 | 0.833 |
0.160 0.151 | 0.166 |
0.000 0.000 | 0.000 |
0.012 0.007 | 0.016 |
0.000 0.000 | 0.000 |
| 6 spectra, YLPGPQQQIIK | 0.000 | 0.000 | 0.799 | 0.201 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, QNHSTLDPNSPR | 0.000 | 0.376 | 0.000 | 0.399 | 0.000 | 0.225 | 0.000 | |||
| 6 spectra, YGFLLLMK | 0.000 | 0.000 | 0.904 | 0.092 | 0.000 | 0.005 | 0.000 | |||
| 4 spectra, VHEEIEQVIGR | 0.000 | 0.348 | 0.275 | 0.293 | 0.000 | 0.084 | 0.000 | |||
| 4 spectra, MPYTQAVINEIQR | 0.000 | 0.176 | 0.549 | 0.149 | 0.000 | 0.126 | 0.000 | |||
| 2 spectra, NAAFLPFSTGK | 0.000 | 0.000 | 0.968 | 0.016 | 0.000 | 0.000 | 0.016 | |||
| 5 spectra, LSIATLR | 0.000 | 0.000 | 0.658 | 0.342 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, FCLGDGLAK | 0.000 | 0.052 | 0.753 | 0.046 | 0.000 | 0.149 | 0.000 | |||
| 2 spectra, QPQYEDHMK | 0.000 | 0.000 | 0.883 | 0.086 | 0.000 | 0.030 | 0.000 | |||
| 14 spectra, YGPVFTIHLGPR | 0.000 | 0.128 | 0.561 | 0.262 | 0.000 | 0.049 | 0.000 | |||
| 4 spectra, HPDVEAK | 0.000 | 0.000 | 0.906 | 0.072 | 0.000 | 0.000 | 0.021 | |||
| 1 spectrum, DFIDSFLIR | 0.000 | 0.000 | 0.851 | 0.149 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GEQATYNTLFK | 0.000 | 0.000 | 0.687 | 0.313 | 0.000 | 0.000 | 0.000 | |||
| 22 spectra, NFIDSFLIR | 0.000 | 0.000 | 0.746 | 0.254 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, GYGVAFSSGER | 0.000 | 0.000 | 0.681 | 0.319 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, FSNLAPLGIPR | 0.000 | 0.000 | 0.815 | 0.115 | 0.000 | 0.070 | 0.000 | |||
| 6 spectra, LEDFMIEK | 0.000 | 0.000 | 0.839 | 0.151 | 0.000 | 0.010 | 0.000 | |||
| 4 spectra, EALVDQAEEFSGR | 0.196 | 0.000 | 0.772 | 0.032 | 0.000 | 0.000 | 0.000 | |||
| 3 spectra, DVYSSITQLSER | 0.040 | 0.000 | 0.641 | 0.315 | 0.000 | 0.003 | 0.000 | |||
| 1 spectrum, GTDVFPILGSLMTDPK | 0.000 | 0.000 | 0.768 | 0.232 | 0.000 | 0.000 | 0.000 | |||
| 15 spectra, ILEEAGYLIK | 0.000 | 0.030 | 0.777 | 0.194 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, TVSNVISSIVFGER | 0.000 | 0.124 | 0.676 | 0.105 | 0.000 | 0.094 | 0.000 | |||
| 1 spectrum, DFDPQNFLDDK | 0.000 | 0.000 | 0.896 | 0.104 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, GFFLPK | 0.000 | 0.000 | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 2 spectra, LEDINESPKPLGFTR | 0.000 | 0.024 | 0.798 | 0.156 | 0.022 | 0.000 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
303 spectra |
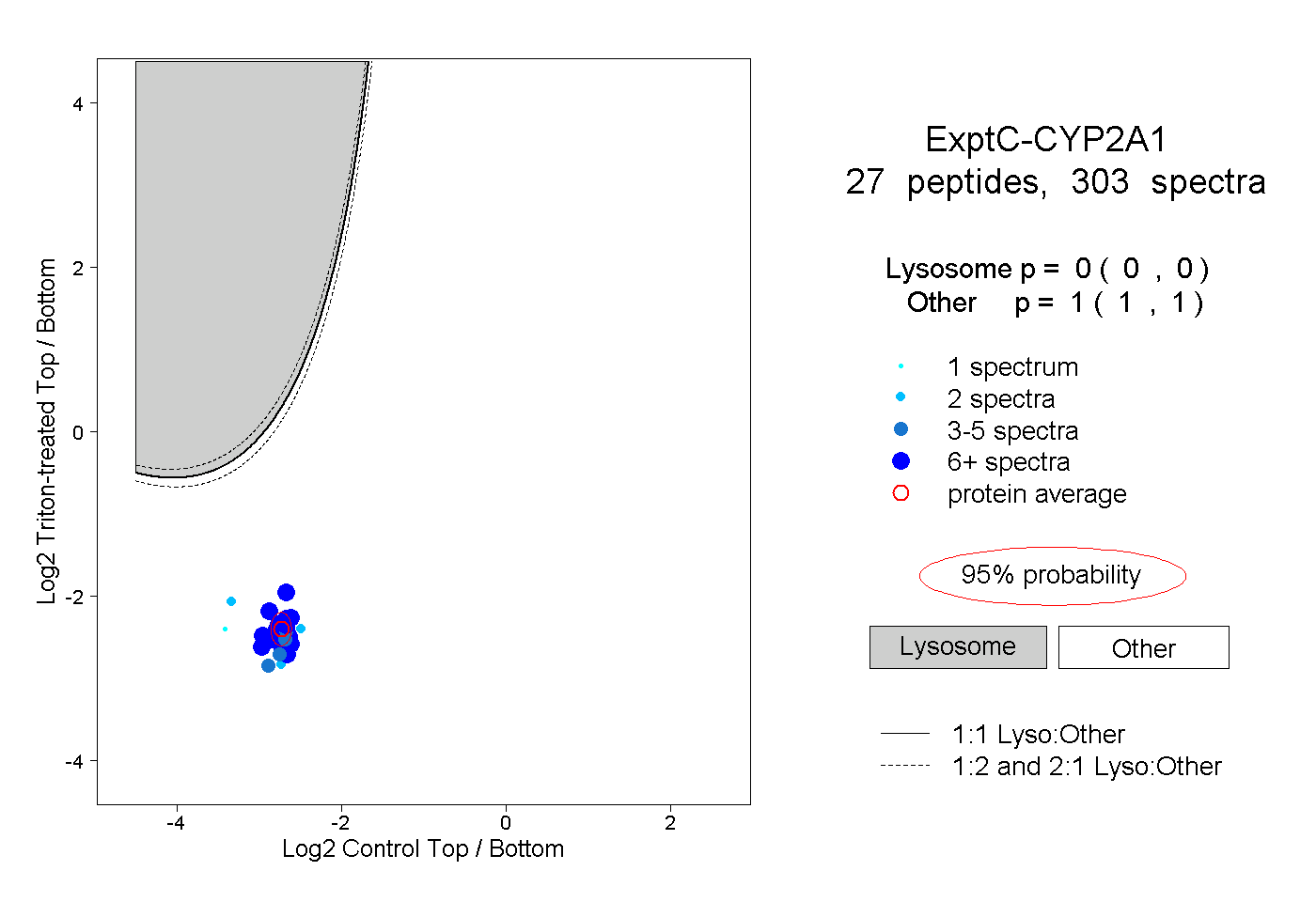 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
37 spectra |
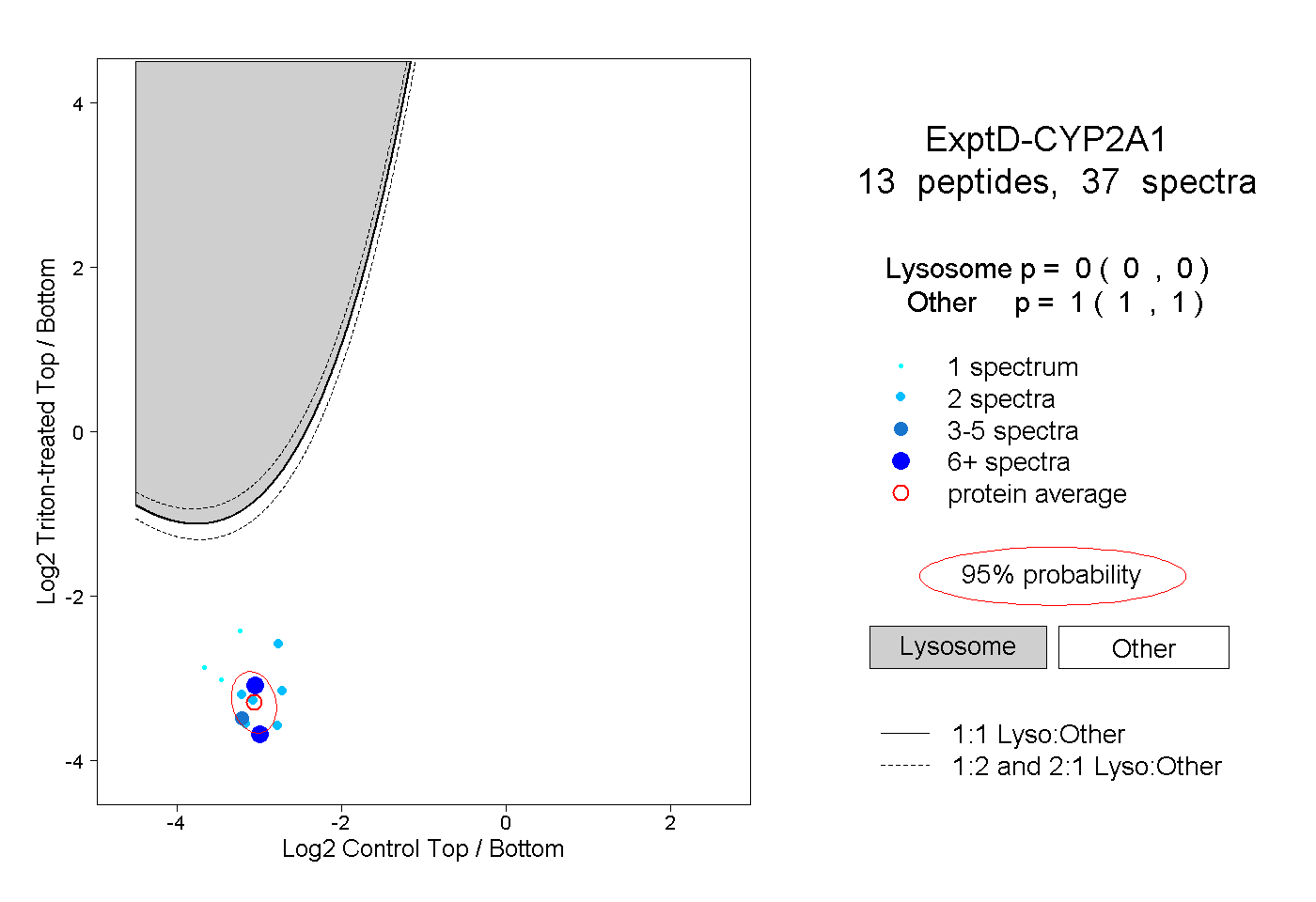 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |