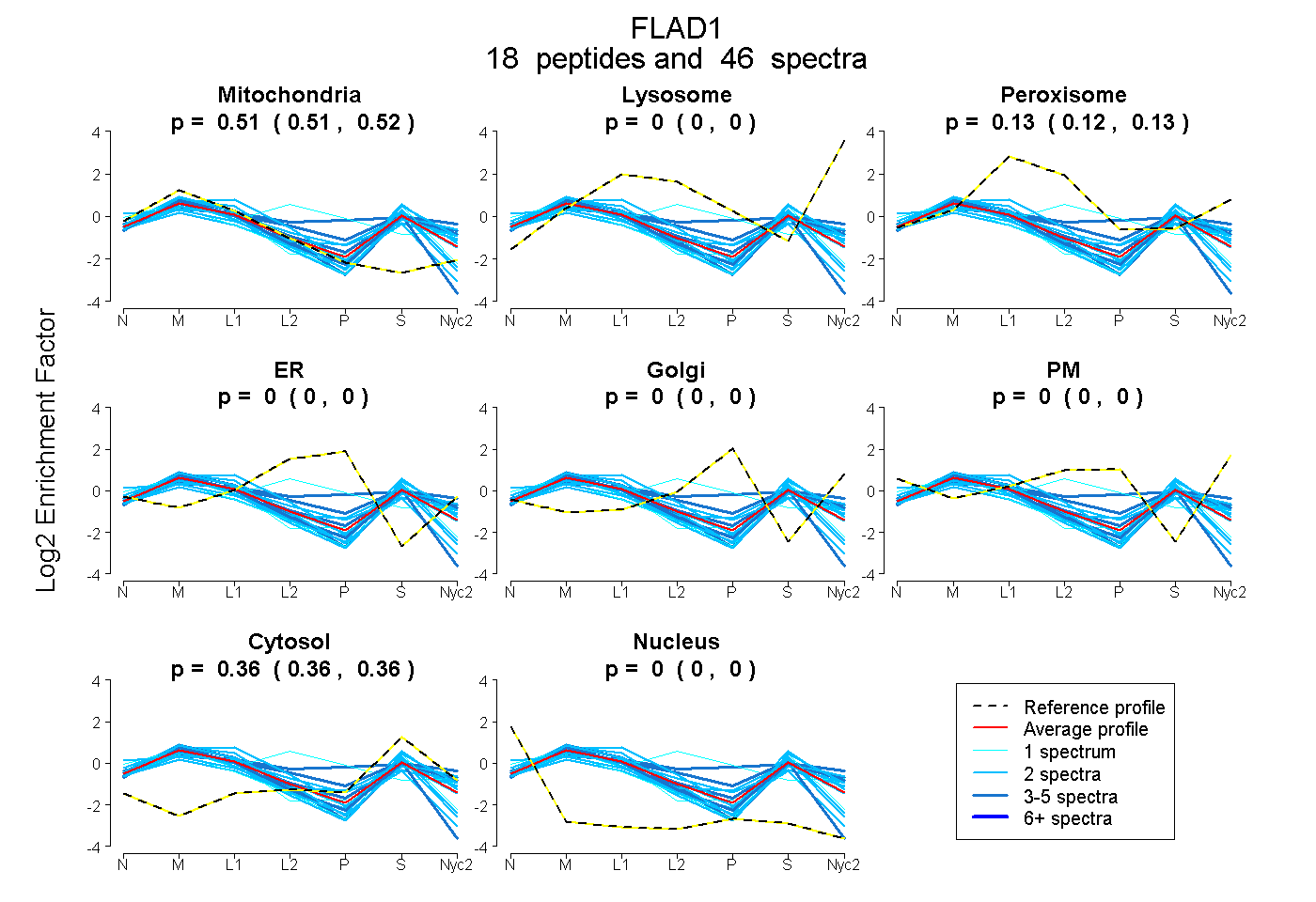
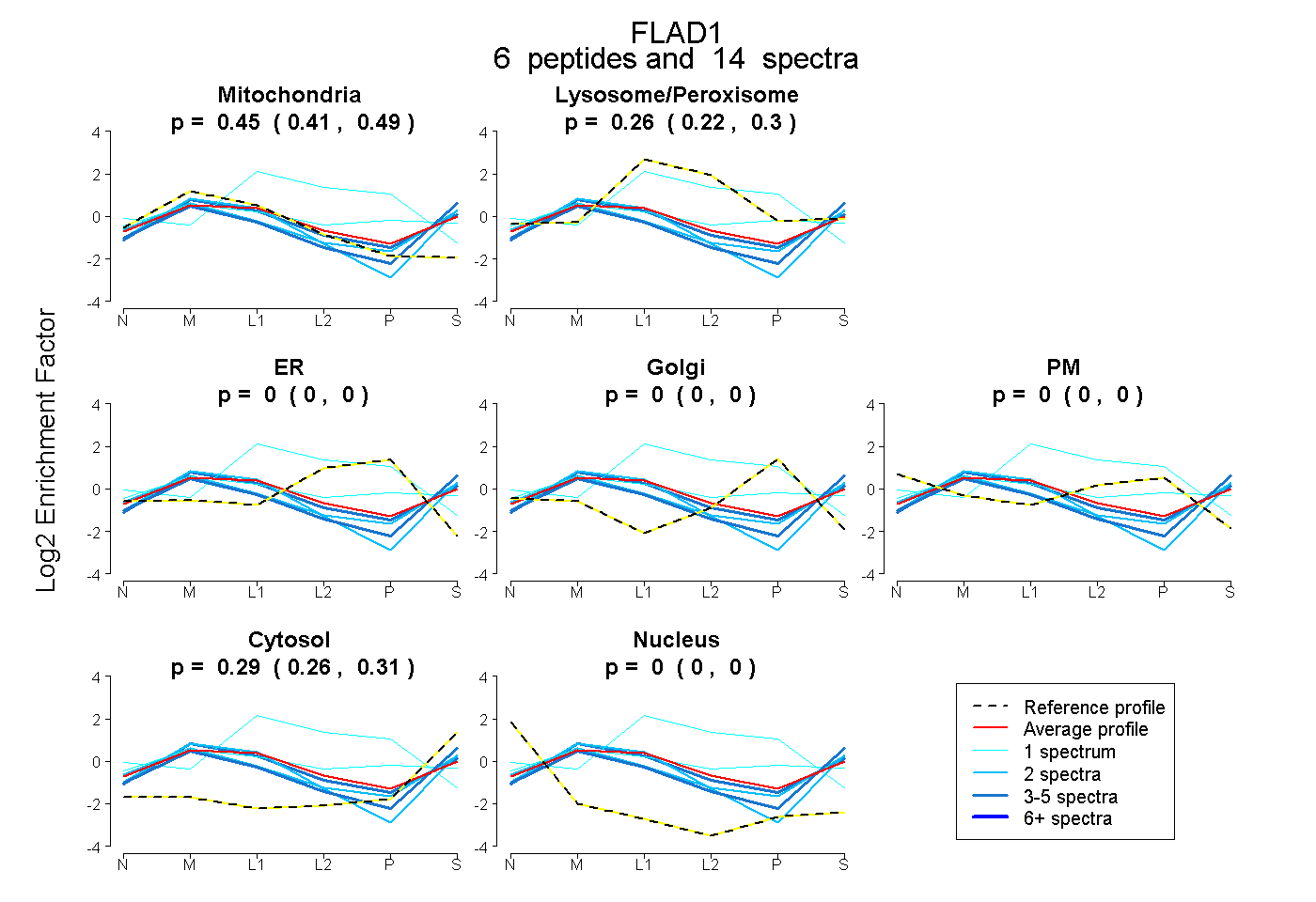
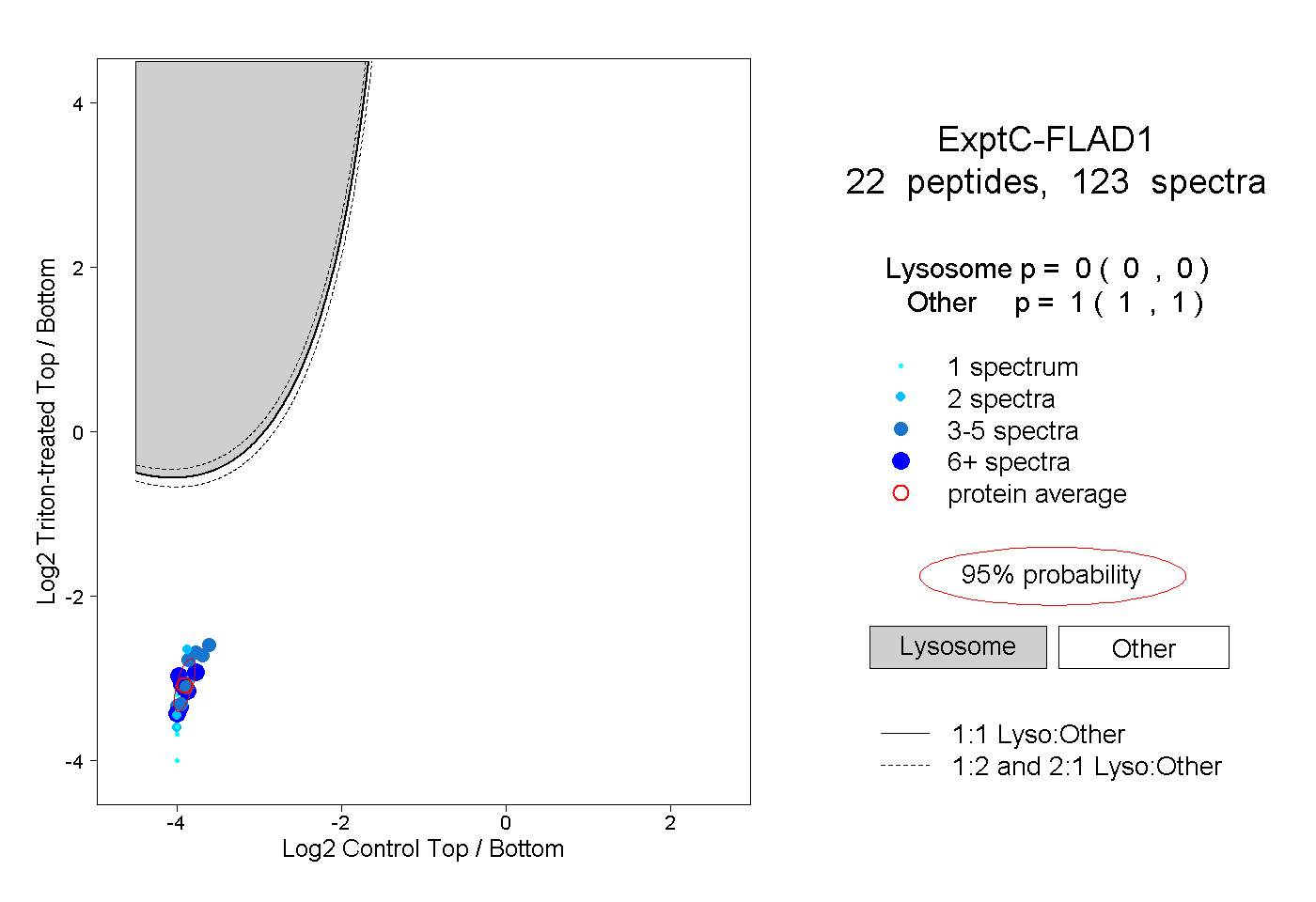
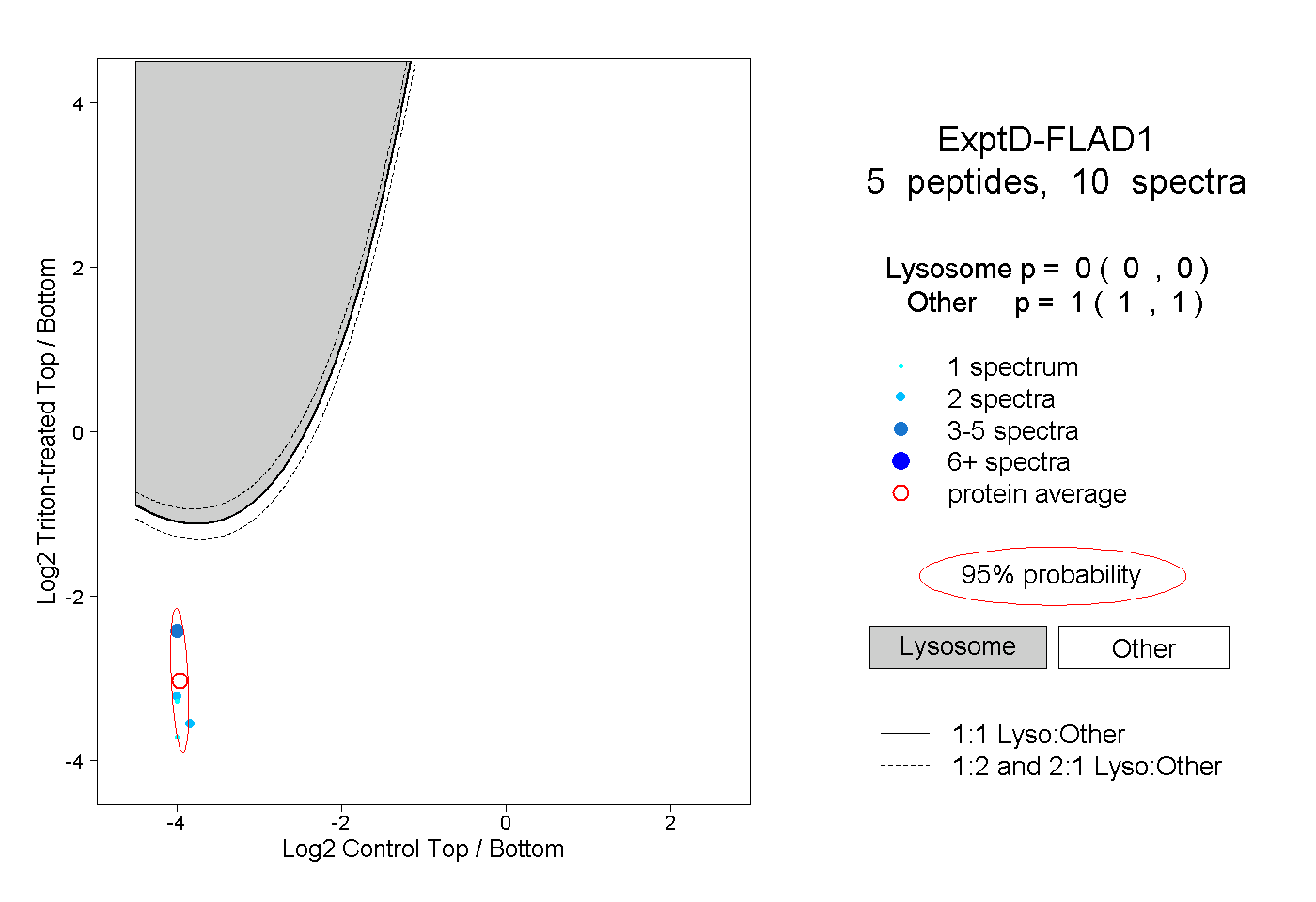
| 14 spectra, FPLVSVR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, DCTALLHLFHAAVQR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, INPLLDWTYR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, LAESGSCLGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, VSVVPDEVATIASEVTSFSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, TLGGEGWEK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, SVTAGIIIVGDEILK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, QALGELQGK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 1 spectrum, FPDVPKPLQILYIR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 29 spectra, ASELPPGR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, NIWEFLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, YNLQMLEAEGNMK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, SLGVQVCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, NVYLFPGIPELLR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, GHTQDTNTYFLCR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 7 spectra, LSMVPSSAR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 5 spectra, HPQLEAVLMGTR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 13 spectra, GYTSLGSR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 3 spectra, QNPALK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 4 spectra, QLFVPYCILYDR |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 2 spectra, GLFQNTAVQFHLK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |
| 6 spectra, ASEAVYK |
|
0.000 |
|
|
|
|
|
|
|
1.000 |