peptides
spectra
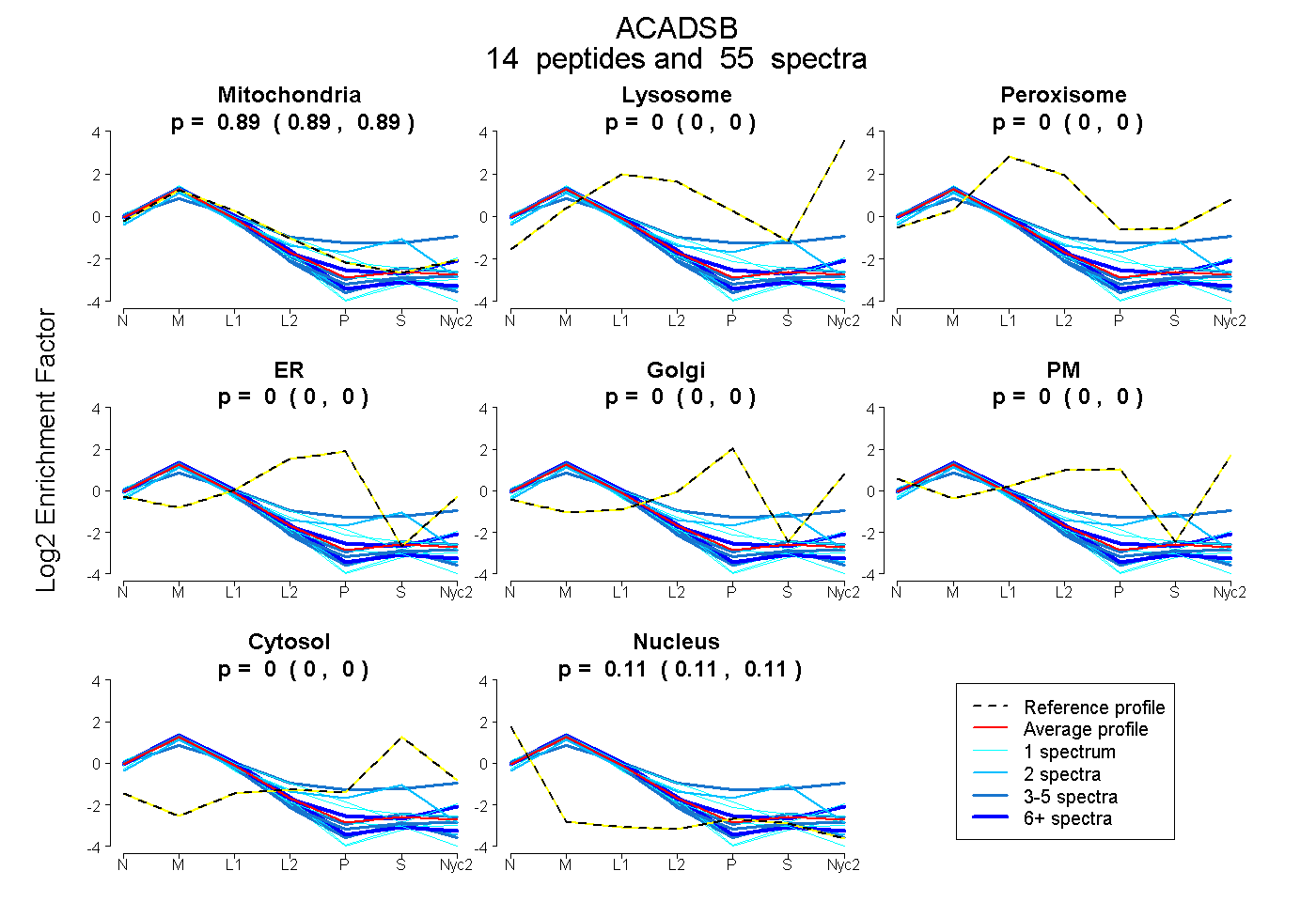
0.887 | 0.893
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.107 | 0.113
peptides
spectra
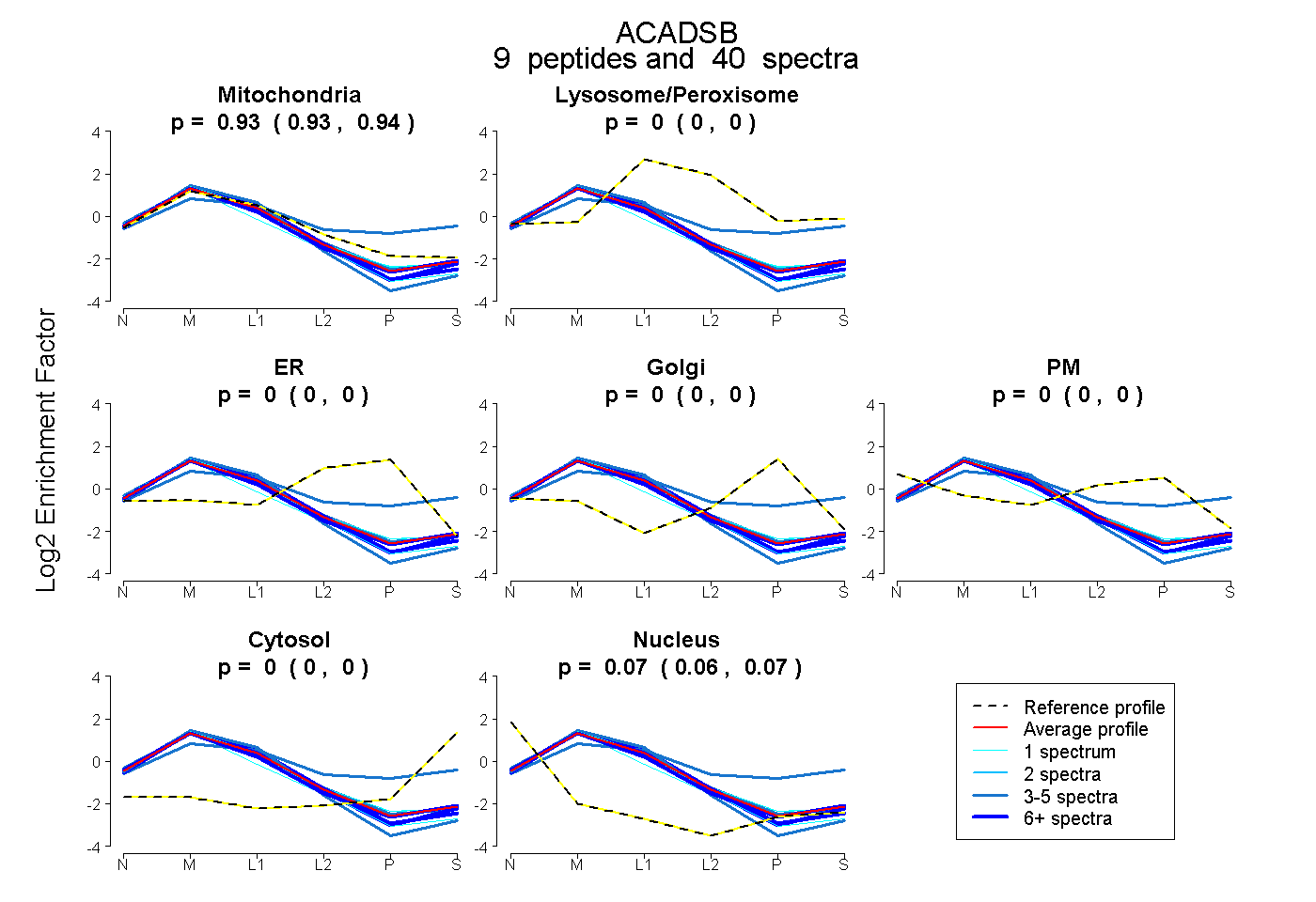
0.929 | 0.937
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.062 | 0.070
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
55 spectra |
 |
0.890 0.887 | 0.893 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.110 0.107 | 0.113 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
40 spectra |
 |
0.934 0.929 | 0.937 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.066 0.062 | 0.070 |
| 1 spectrum, EASMAK | 0.945 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.055 | |||
| 10 spectra, LLTYNAAR | 0.928 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.072 | |||
| 8 spectra, GITCFLVDR | 0.944 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.056 | |||
| 1 spectrum, ASSTCQLTFENVK | 0.864 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.136 | |||
| 3 spectra, LVEAGRPFIK | 0.926 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.074 | |||
| 4 spectra, DTEGFQIGR | 0.930 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.070 | |||
| 3 spectra, IFDFQGLQHQVAHVATQLEAAR | 0.509 | 0.255 | 0.000 | 0.074 | 0.000 | 0.162 | 0.000 | |||
| 1 spectrum, VPETSVLGK | 0.910 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.090 | |||
| 9 spectra, YAIGSLNEGR | 0.904 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.096 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
266 spectra |
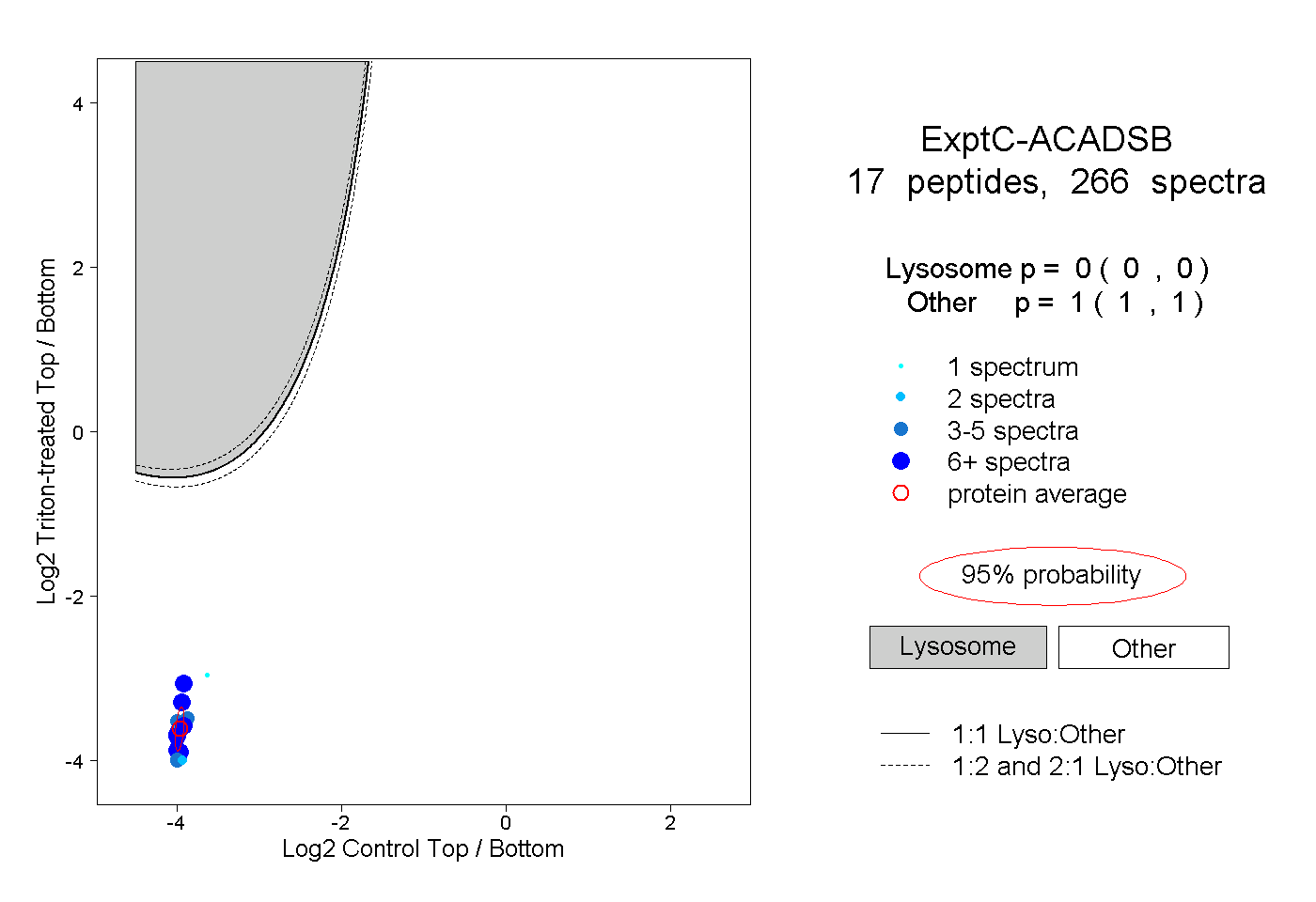 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
20 spectra |
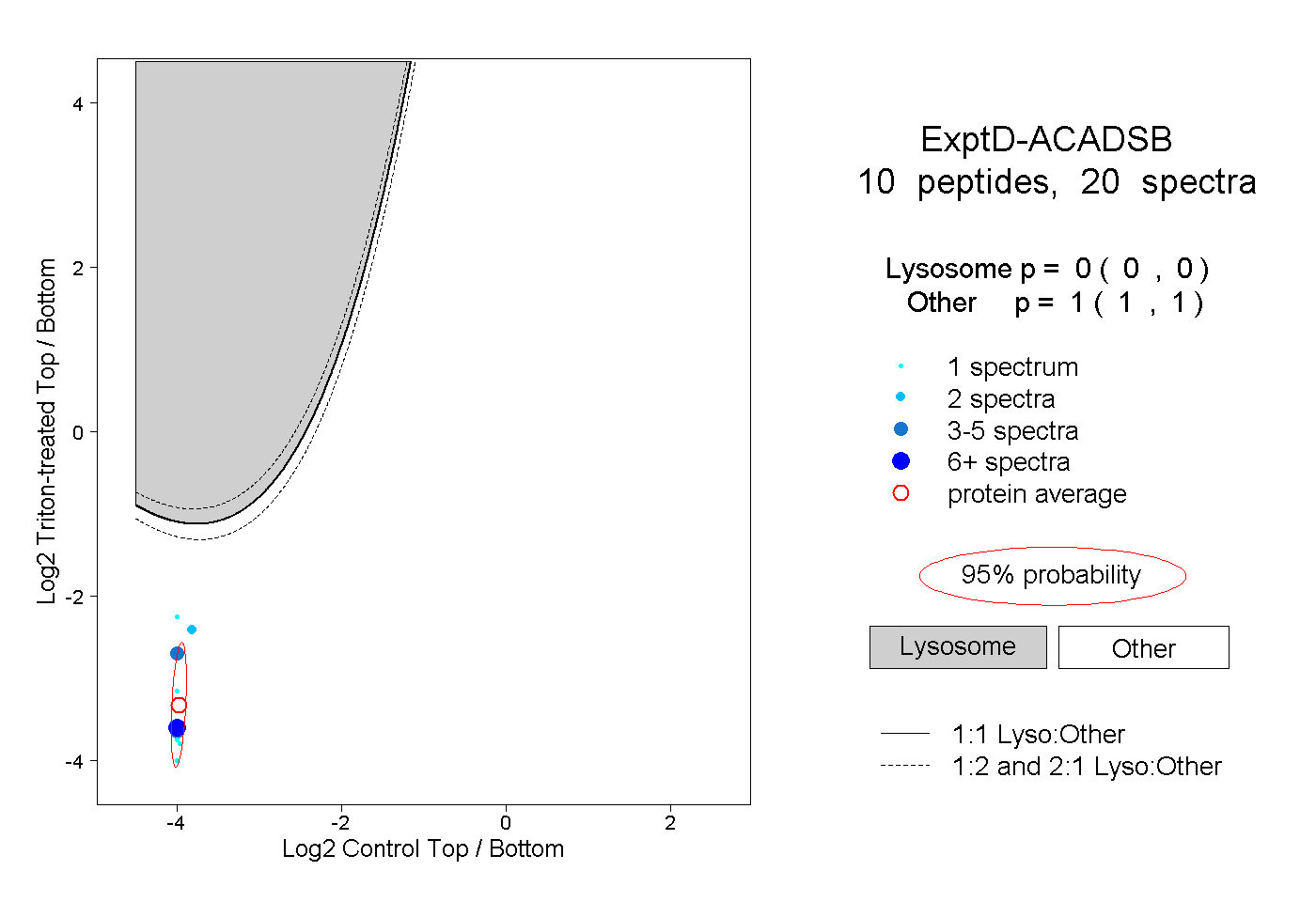 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |