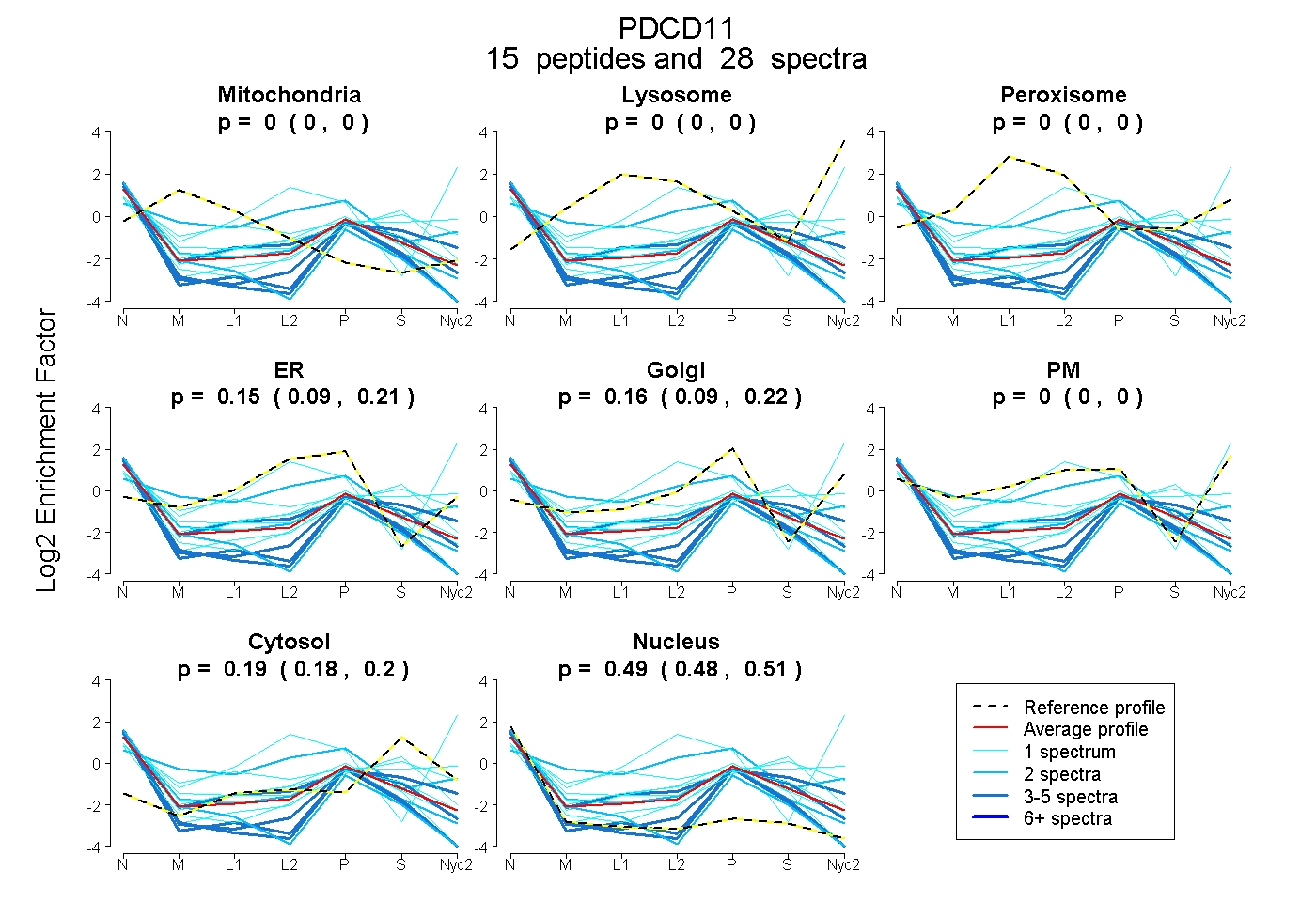
peptides
spectra
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.086 | 0.208
0.093 | 0.223
0.000 | 0.000
0.177 | 0.204
0.476 | 0.507
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
28 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.154 0.086 | 0.208 |
0.162 0.093 | 0.223 |
0.000 0.000 | 0.000 |
0.192 0.177 | 0.204 |
0.492 0.476 | 0.507 |
| 1 spectrum, FLPISHPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.990 | 0.000 | 0.010 | ||
| 2 spectra, SIIAAPFLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.132 | 0.000 | 0.013 | 0.856 | ||
| 3 spectra, FQIGQAIK | 0.000 | 0.000 | 0.000 | 0.070 | 0.022 | 0.218 | 0.325 | 0.364 | ||
| 4 spectra, HILLCR | 0.000 | 0.000 | 0.000 | 0.064 | 0.075 | 0.000 | 0.070 | 0.791 | ||
| 3 spectra, MLLSLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.107 | 0.000 | 0.246 | 0.647 | ||
| 1 spectrum, VVVLHVDALK | 0.000 | 0.000 | 0.000 | 0.000 | 0.093 | 0.000 | 0.532 | 0.375 | ||
| 1 spectrum, QESESEQELVNK | 0.000 | 0.000 | 0.062 | 0.222 | 0.043 | 0.000 | 0.218 | 0.455 | ||
| 2 spectra, ACILCVHPR | 0.138 | 0.000 | 0.000 | 0.400 | 0.000 | 0.224 | 0.171 | 0.067 | ||
| 1 spectrum, GSTVNTGQLVDVK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.283 | 0.492 | 0.224 | ||
| 1 spectrum, ILGCVK | 0.000 | 0.000 | 0.000 | 0.364 | 0.000 | 0.000 | 0.164 | 0.472 | ||
| 4 spectra, MLALSLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.114 | 0.000 | 0.029 | 0.857 | ||
| 1 spectrum, ILDDVPEGVSPTTTLK | 0.000 | 0.000 | 0.000 | 0.284 | 0.000 | 0.000 | 0.094 | 0.621 | ||
| 1 spectrum, LPELFSPGMLVR | 0.000 | 0.000 | 0.000 | 0.239 | 0.000 | 0.000 | 0.014 | 0.747 | ||
| 1 spectrum, SLSEIQPGMLLIGFVK | 0.000 | 0.000 | 0.128 | 0.000 | 0.000 | 0.374 | 0.340 | 0.158 | ||
| 2 spectra, ALEYVEAK | 0.000 | 0.000 | 0.000 | 0.345 | 0.000 | 0.000 | 0.081 | 0.574 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
4 spectra |
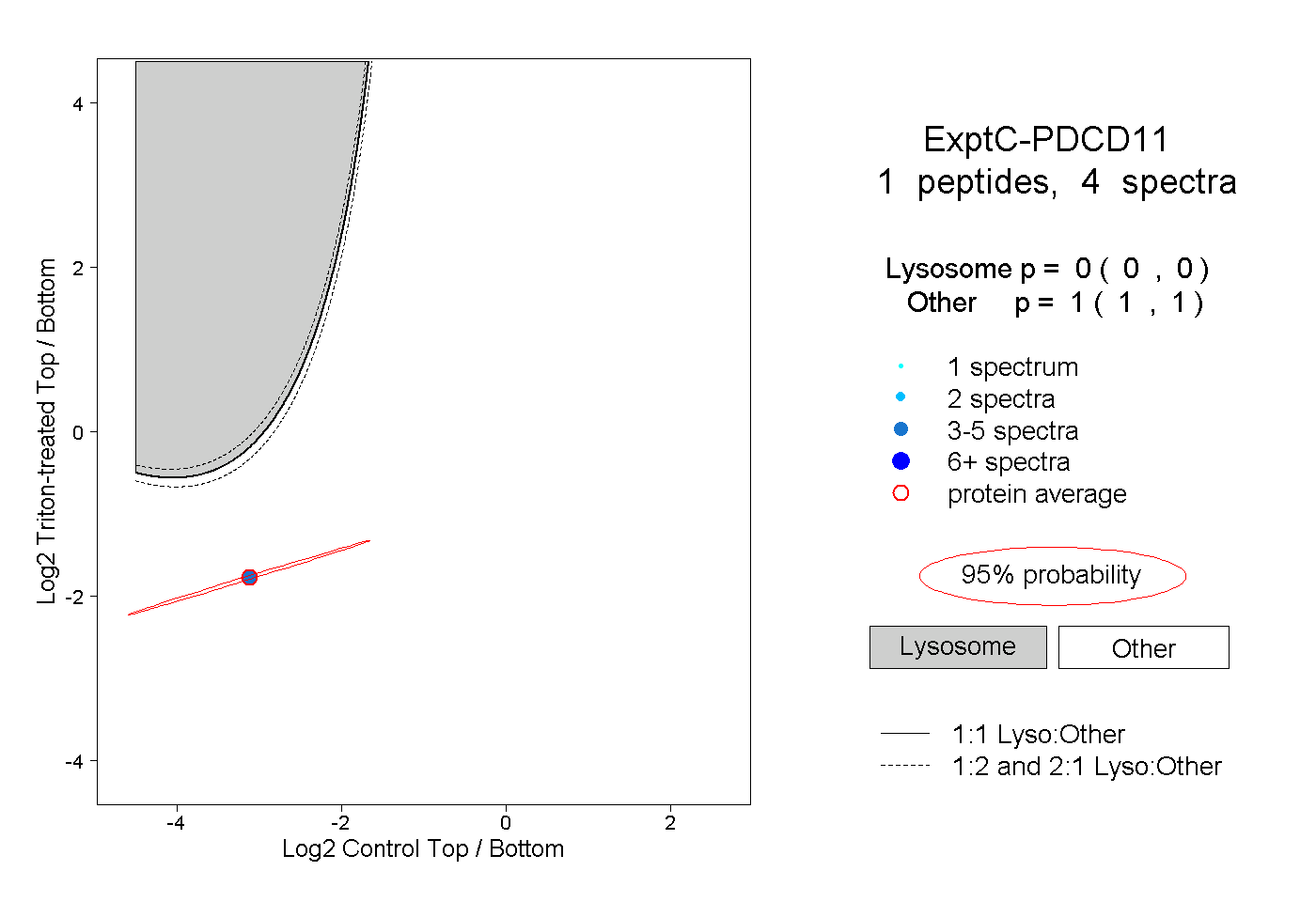 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |