peptides
spectra
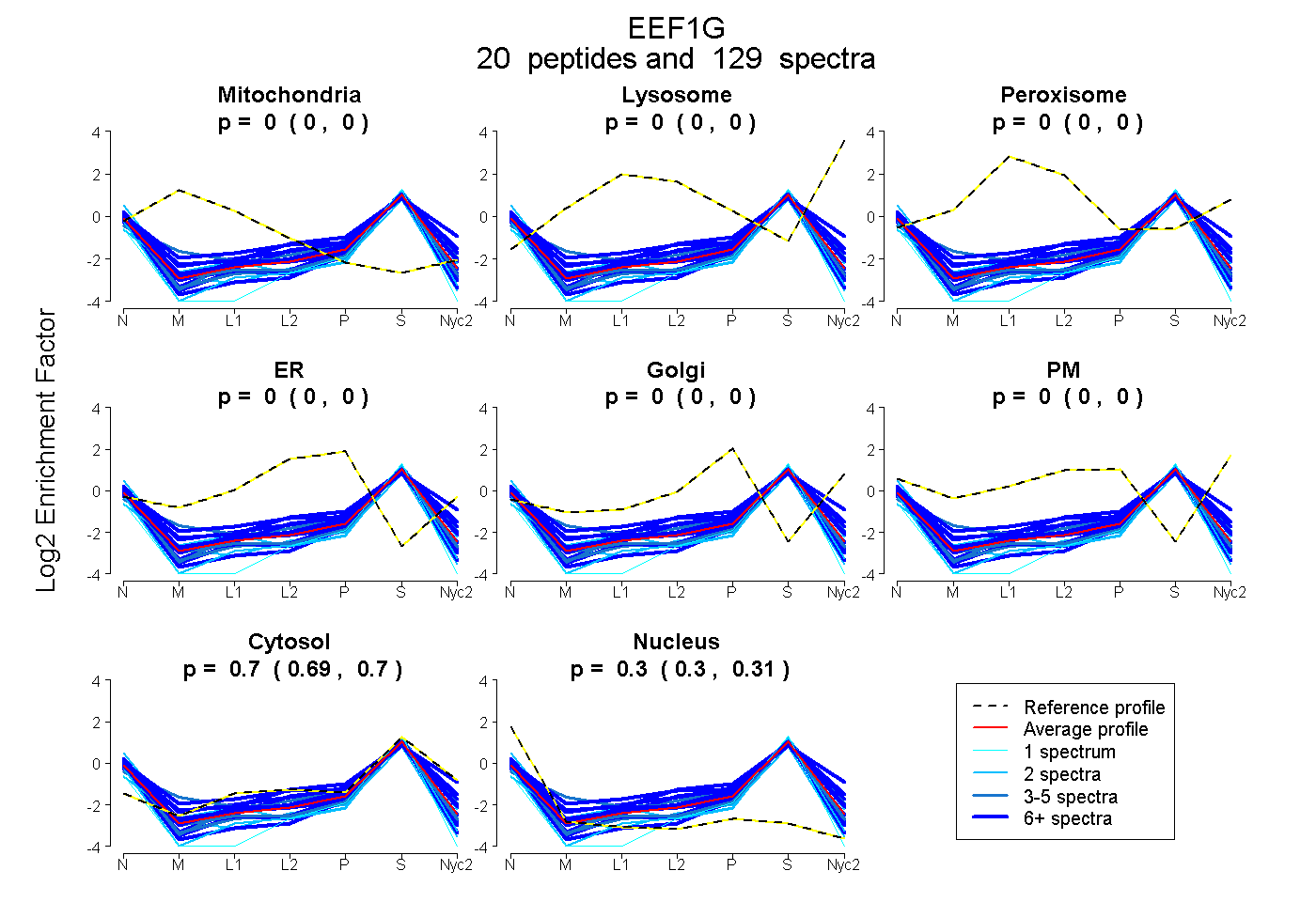
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.693 | 0.697
0.302 | 0.306
peptides
spectra
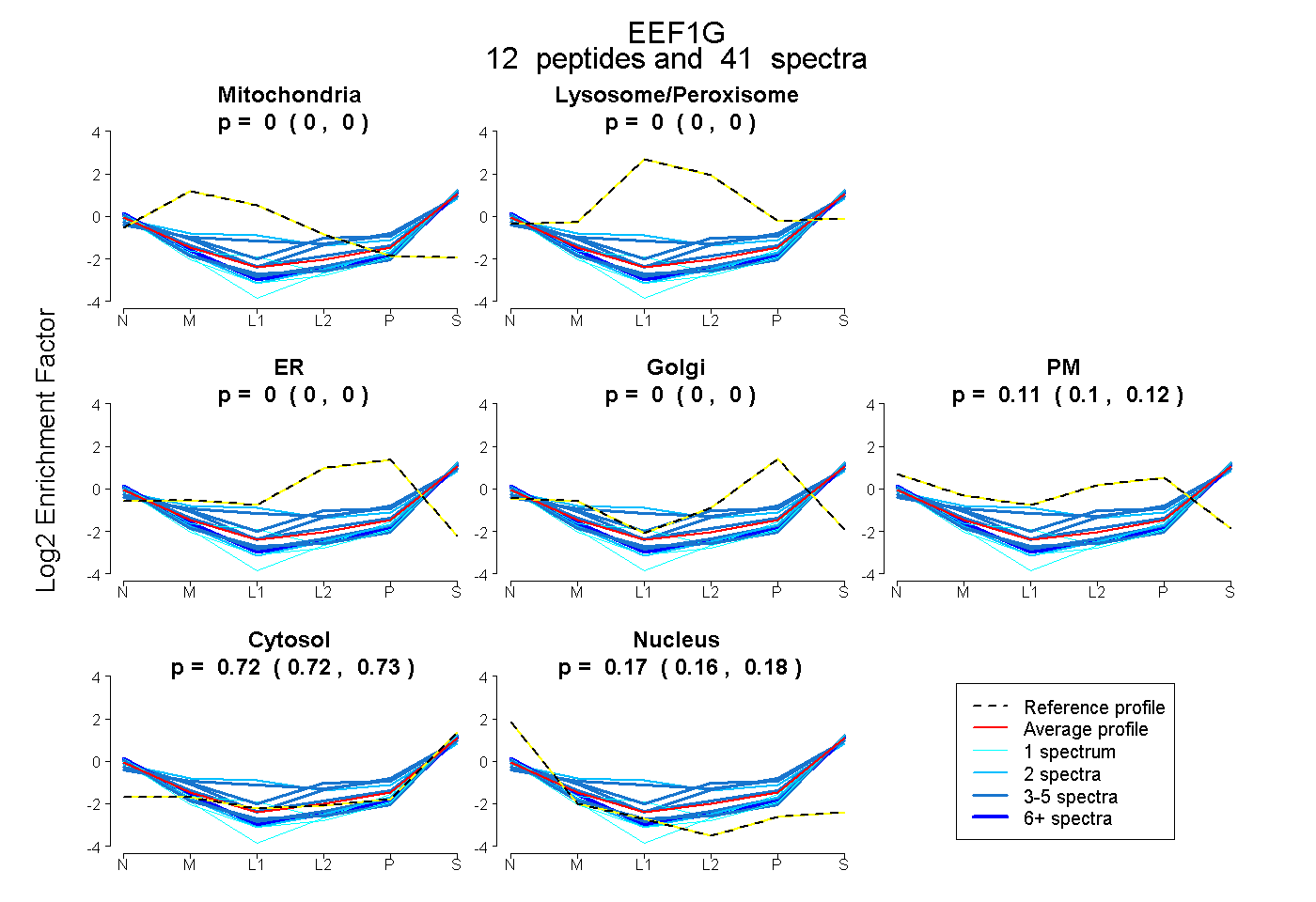
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.097 | 0.116
0.719 | 0.726
0.161 | 0.177
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
129 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.695 0.693 | 0.697 |
0.305 0.302 | 0.306 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
41 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.107 0.097 | 0.116 |
0.723 0.719 | 0.726 |
0.170 0.161 | 0.177 |
| 1 spectrum, QKPQTER | 0.000 | 0.050 | 0.000 | 0.000 | 0.000 | 0.684 | 0.266 | |||
| 1 spectrum, TPEFLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.727 | 0.273 | |||
| 5 spectra, TFLVGER | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.734 | 0.266 | |||
| 5 spectra, QVLEPSFR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.742 | 0.258 | |||
| 1 spectrum, LDPGSEETQTLVR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.731 | 0.269 | |||
| 4 spectra, VLSAPPHFHFGQTNR | 0.000 | 0.156 | 0.000 | 0.000 | 0.190 | 0.633 | 0.022 | |||
| 10 spectra, ILGLLDTHLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.719 | 0.281 | |||
| 2 spectra, ALIAAQYSGAQIR | 0.000 | 0.248 | 0.000 | 0.000 | 0.080 | 0.539 | 0.132 | |||
| 3 spectra, EYFSWEGAFQHVGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.300 | 0.669 | 0.032 | |||
| 4 spectra, WFLTCINQPQFR | 0.000 | 0.007 | 0.000 | 0.000 | 0.328 | 0.665 | 0.000 | |||
| 3 spectra, QAFPNTNR | 0.000 | 0.000 | 0.000 | 0.000 | 0.149 | 0.704 | 0.148 | |||
| 2 spectra, STFVLDEFK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.744 | 0.256 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
95 spectra |
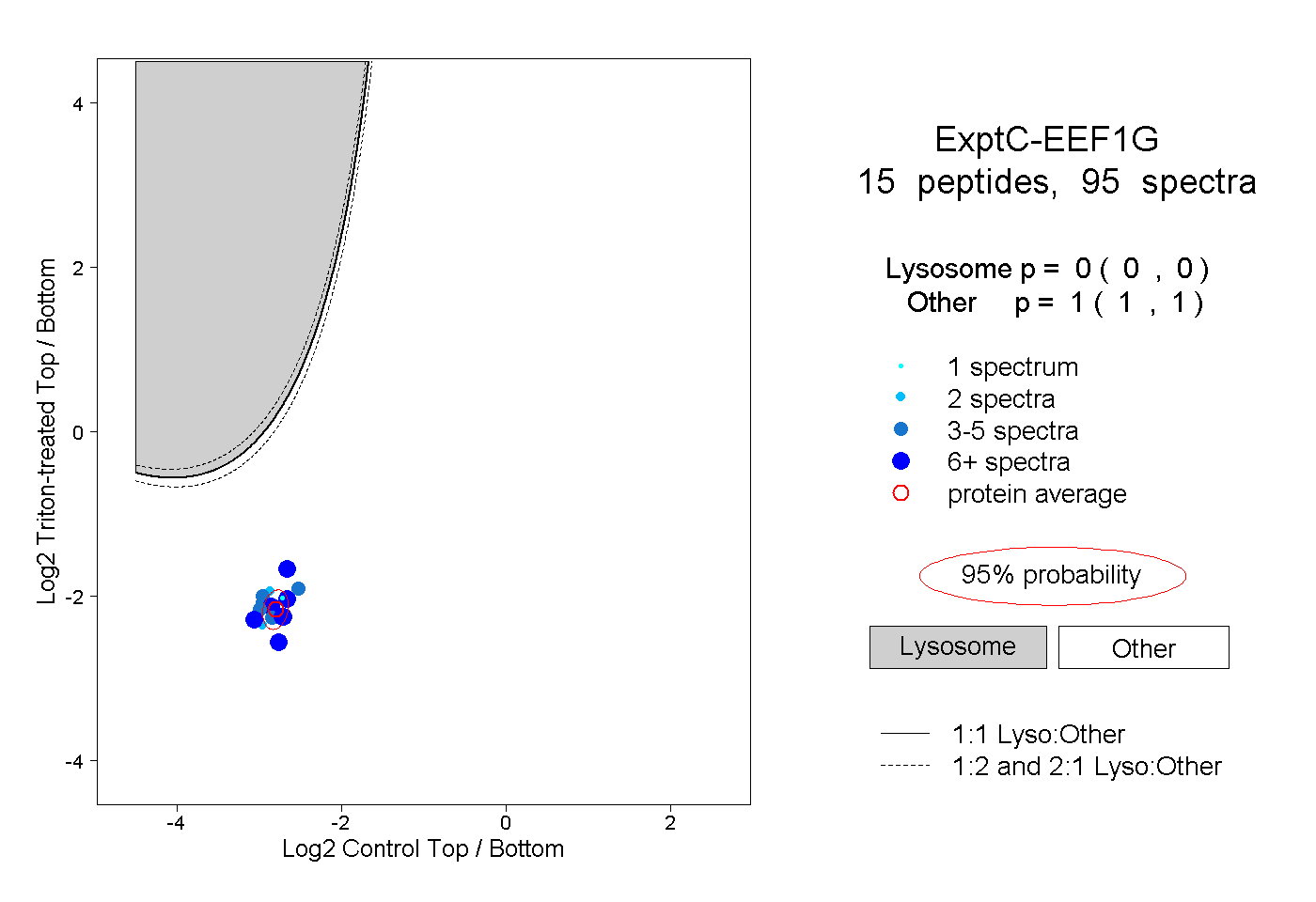 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
24 spectra |
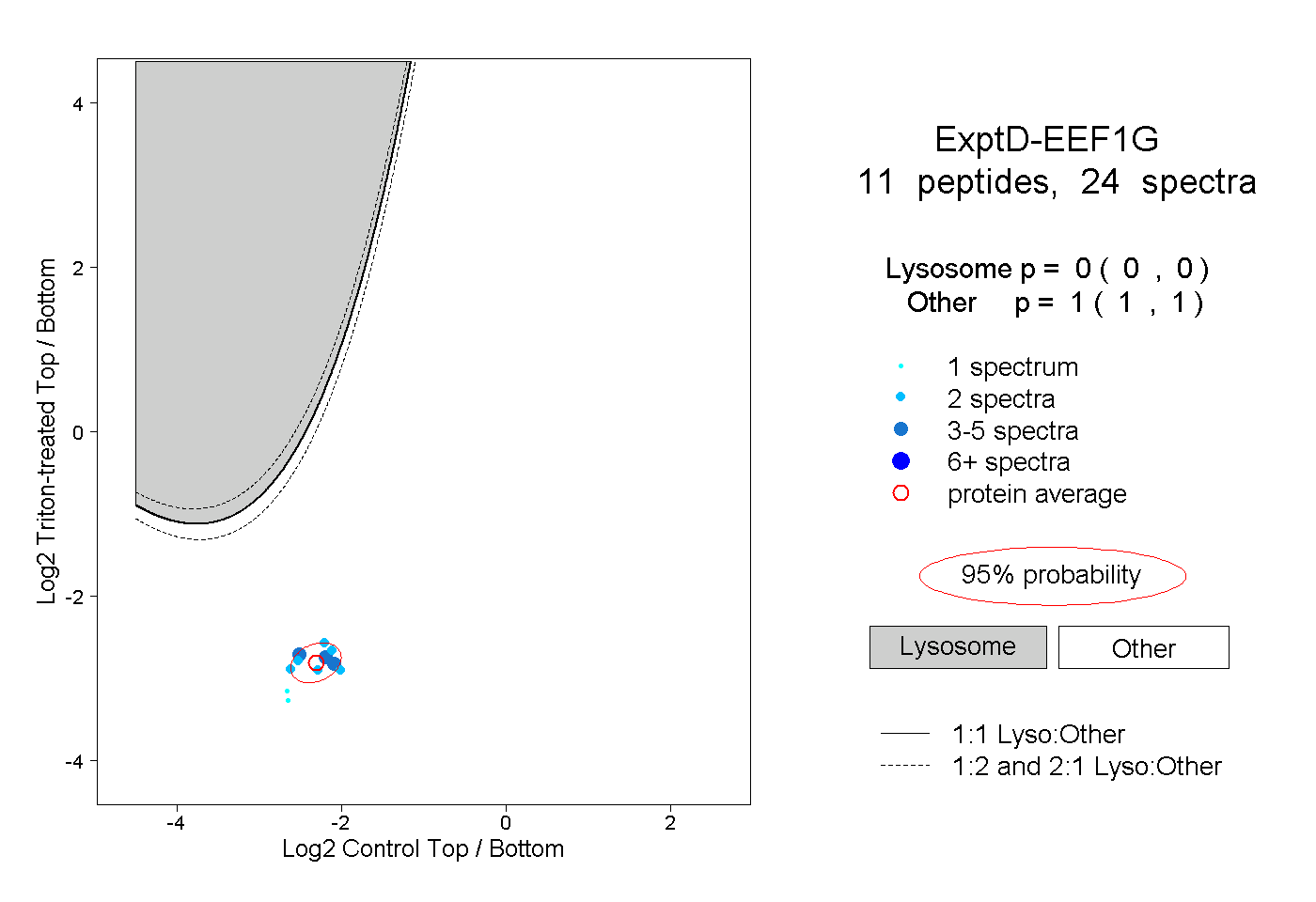 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |