peptides
spectra
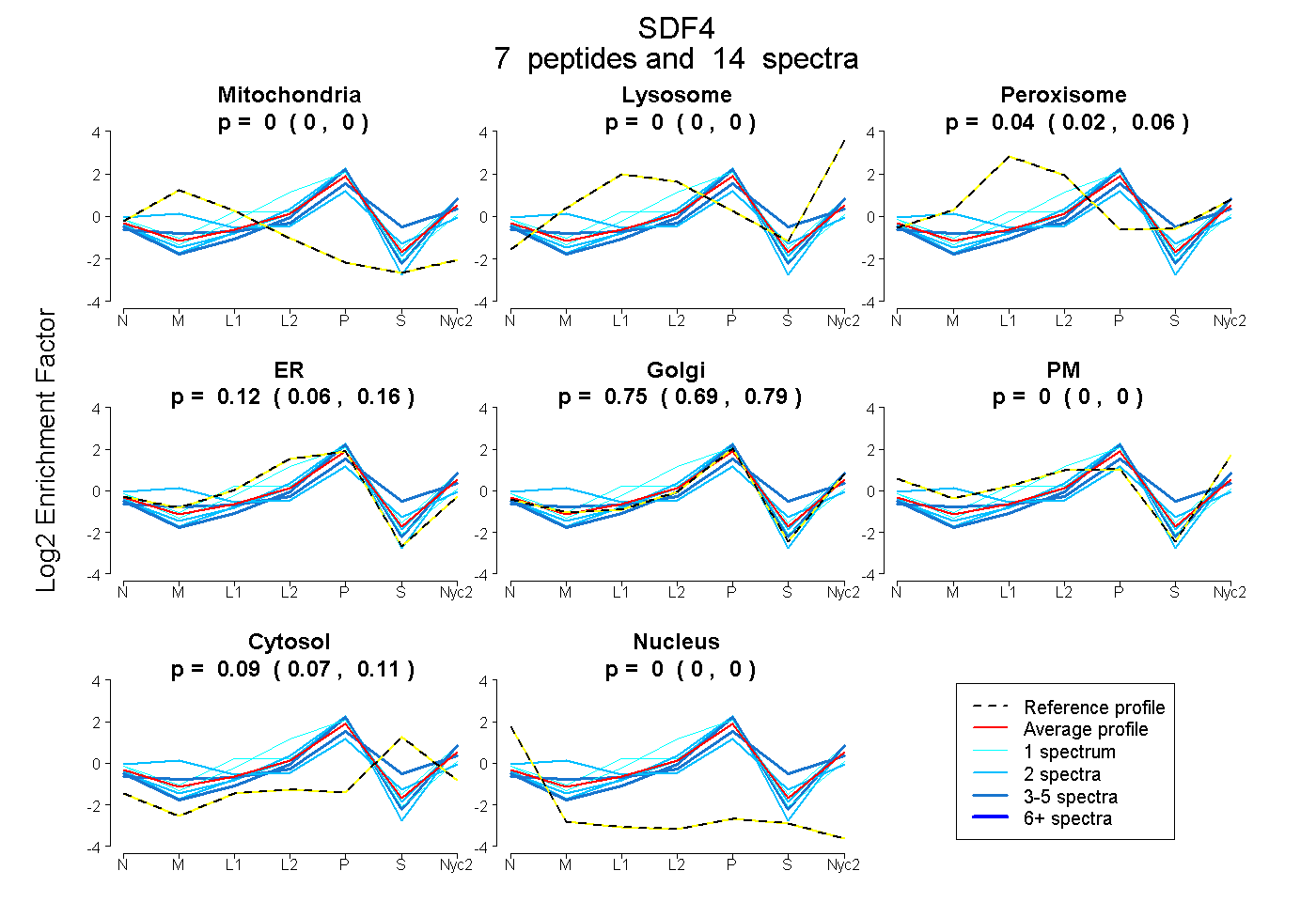
0.000 | 0.000
0.000 | 0.000
0.017 | 0.060
0.062 | 0.165
0.691 | 0.787
0.000 | 0.000
0.071 | 0.114
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
14 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.040 0.017 | 0.060 |
0.118 0.062 | 0.165 |
0.748 0.691 | 0.787 |
0.000 0.000 | 0.000 |
0.094 0.071 | 0.114 |
0.000 0.000 | 0.000 |
| 2 spectra, YSEFFTGSK | 0.202 | 0.000 | 0.078 | 0.000 | 0.629 | 0.000 | 0.090 | 0.000 | ||
| 2 spectra, EIADAIK | 0.000 | 0.000 | 0.000 | 0.044 | 0.888 | 0.000 | 0.069 | 0.000 | ||
| 1 spectrum, VDEETQEVLGNLR | 0.000 | 0.000 | 0.000 | 0.697 | 0.247 | 0.003 | 0.054 | 0.000 | ||
| 2 spectra, DLDQDGDK | 0.000 | 0.000 | 0.000 | 0.135 | 0.865 | 0.000 | 0.000 | 0.000 | ||
| 3 spectra, LMVIFSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.961 | 0.000 | 0.039 | 0.000 | ||
| 3 spectra, EMQHWIMEK | 0.000 | 0.017 | 0.085 | 0.000 | 0.632 | 0.000 | 0.265 | 0.000 | ||
| 1 spectrum, DFHQEVFLGK | 0.000 | 0.000 | 0.218 | 0.000 | 0.770 | 0.000 | 0.012 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
3 spectra |
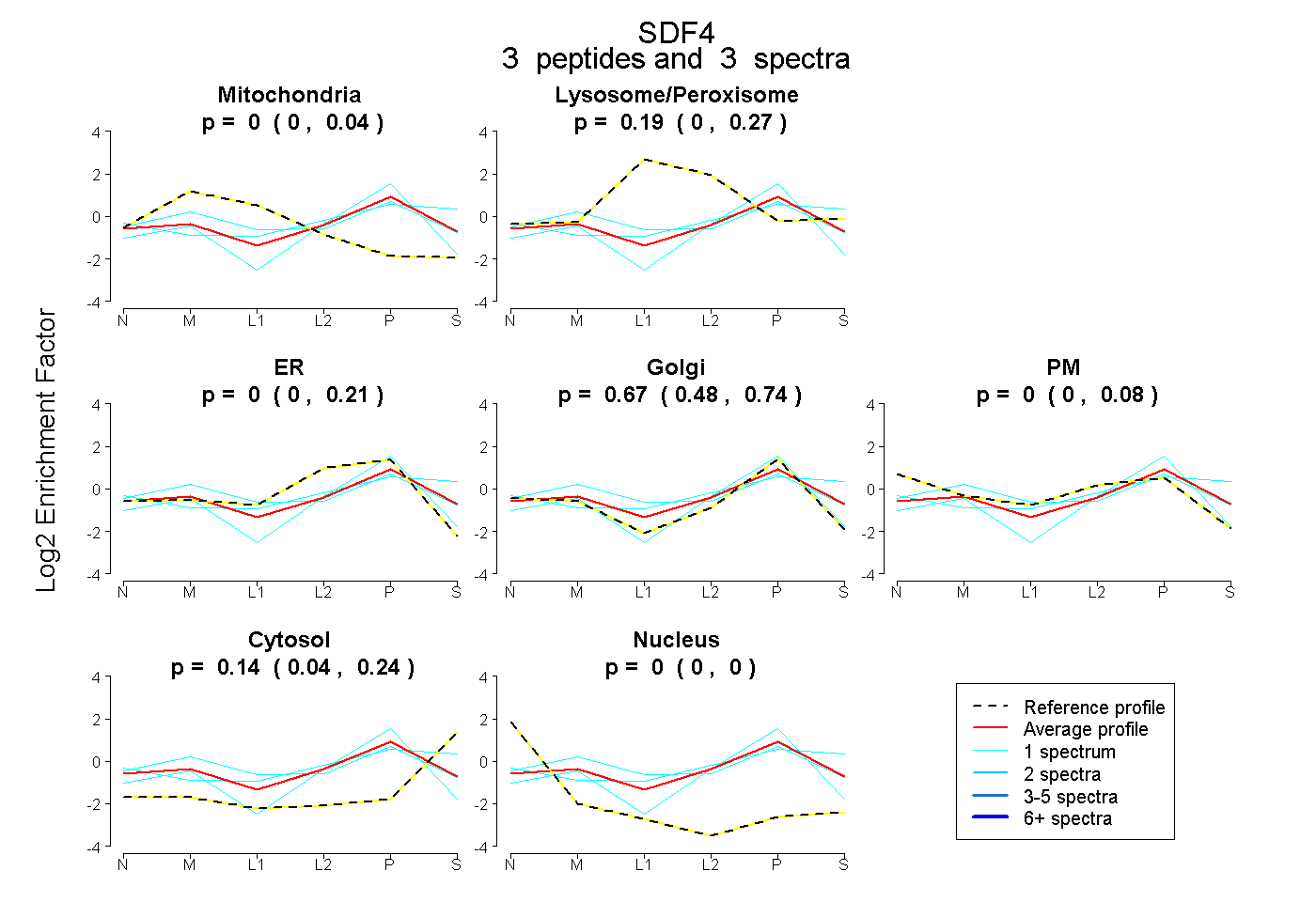 |
0.000 0.000 | 0.044 |
0.189 0.000 | 0.265 |
0.000 0.000 | 0.210 |
0.674 0.482 | 0.739 |
0.000 0.000 | 0.078 |
0.136 0.035 | 0.238 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
15 spectra |
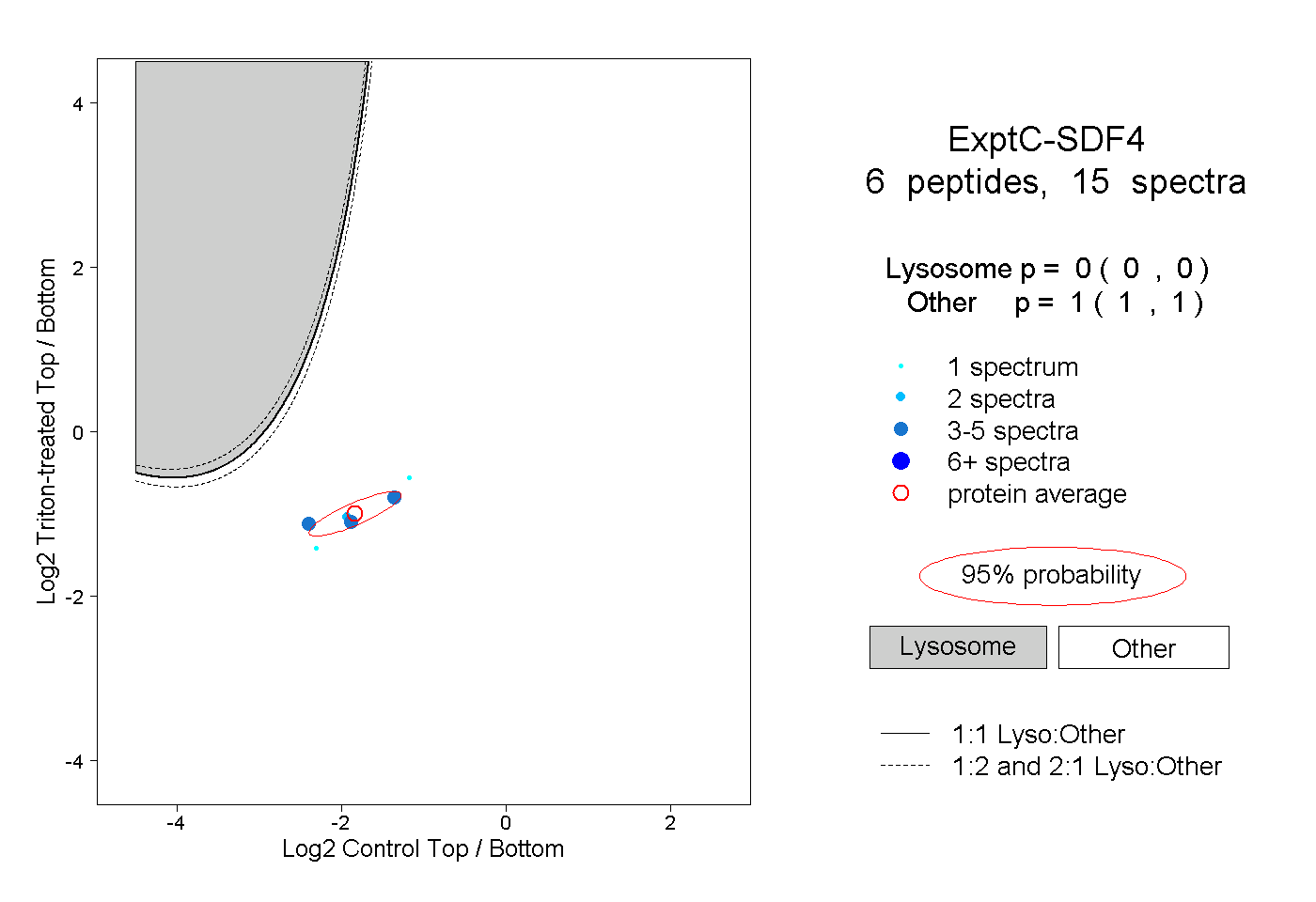 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
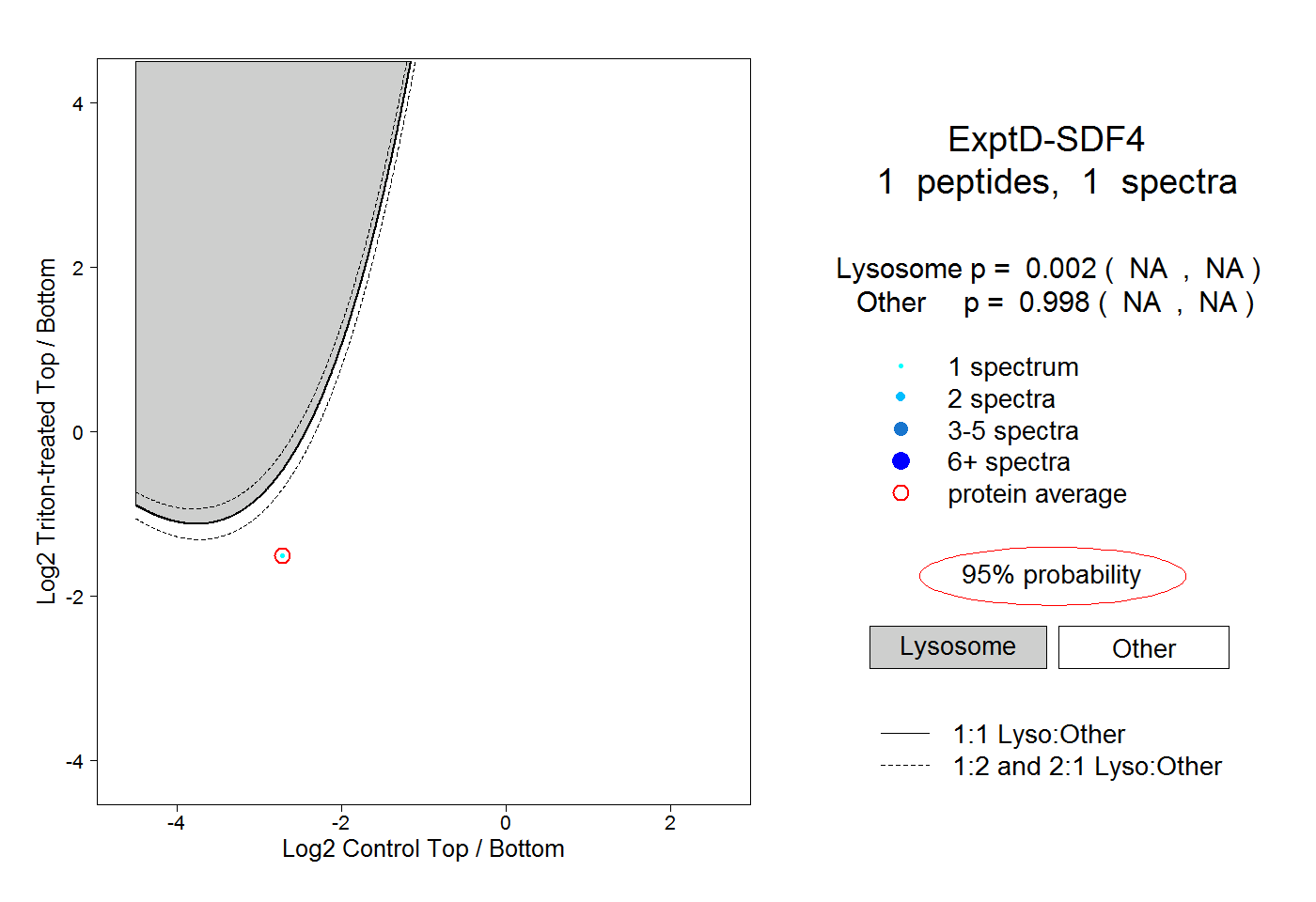 |
0.002 NA | NA |
0.998 NA | NA |