peptides
spectra
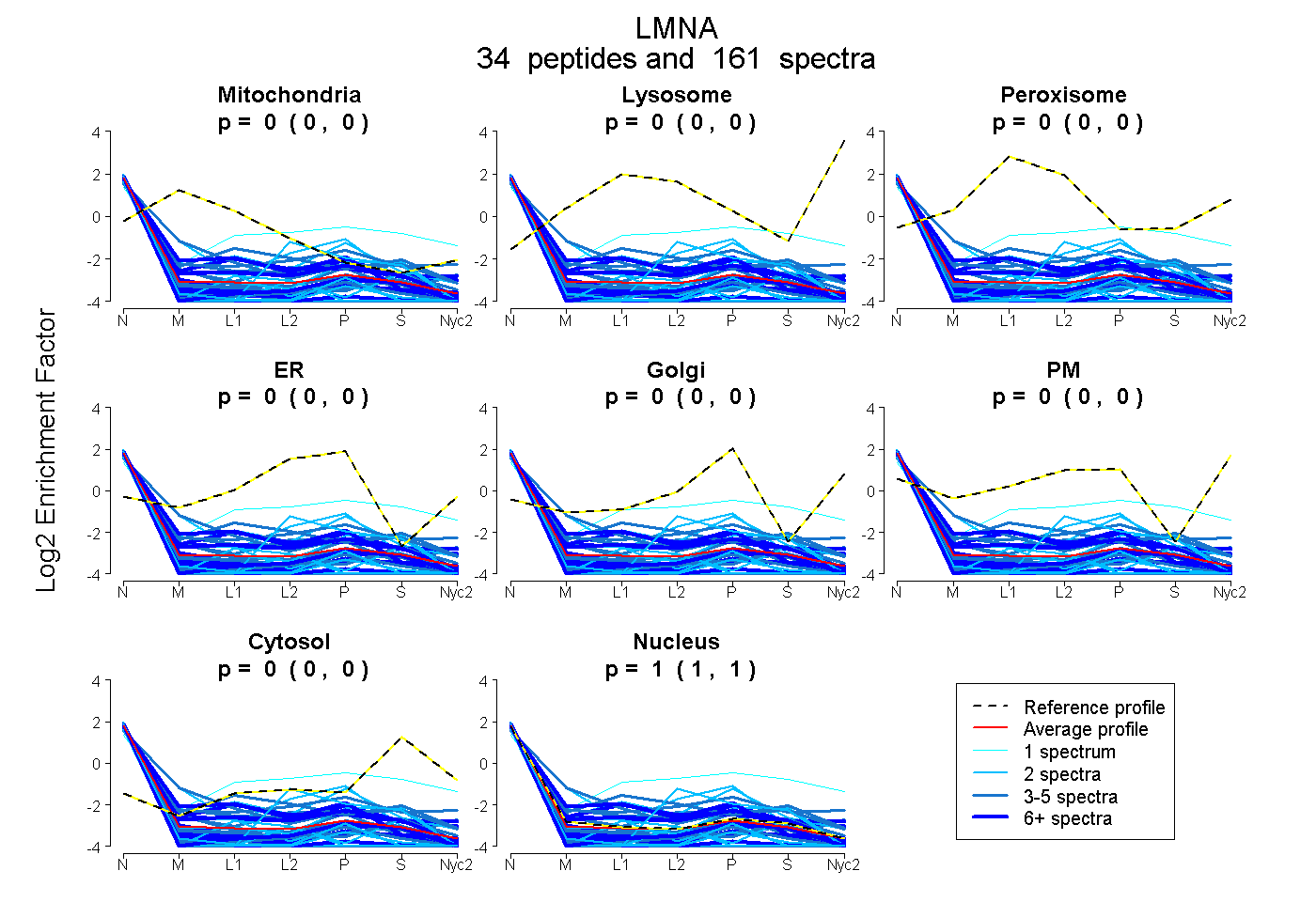
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
1.000 | 1.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
161 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
| 9 spectra, LADALQELR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, MQQQLDEYQELLDIK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 3 spectra, DLEALLNSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 5 spectra, EELDFQK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, LESSESR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.050 | 0.950 | ||
| 4 spectra, SLETENAGLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 3 spectra, AQNTWGCGSSLR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 12 spectra, TLEGELHDLR | 0.000 | 0.000 | 0.021 | 0.043 | 0.000 | 0.000 | 0.000 | 0.936 | ||
| 2 spectra, SVSGLK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 7 spectra, ITESEEVVSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, TVLCGTCGQPADK | 0.000 | 0.000 | 0.000 | 0.056 | 0.000 | 0.000 | 0.058 | 0.886 | ||
| 6 spectra, DLEDSLAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.039 | 0.081 | 0.000 | 0.880 | ||
| 2 spectra, SVGGSGGGSFGDNLVTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, VDAENR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, AQHEDQVEQYK | 0.094 | 0.000 | 0.000 | 0.187 | 0.000 | 0.000 | 0.000 | 0.720 | ||
| 4 spectra, SNEDQSMGNWQIR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, NIYSEELR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 5 spectra, QLQDEMLR | 0.000 | 0.000 | 0.206 | 0.000 | 0.000 | 0.000 | 0.000 | 0.794 | ||
| 7 spectra, EDLQELNDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, EMAEMR | 0.000 | 0.000 | 0.005 | 0.213 | 0.000 | 0.000 | 0.000 | 0.783 | ||
| 4 spectra, EGDLLAAQAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.039 | 0.961 | ||
| 1 spectrum, GSHCSSSGDPAEYNLR | 0.000 | 0.000 | 0.096 | 0.119 | 0.000 | 0.169 | 0.264 | 0.352 | ||
| 4 spectra, SGAQASSTPLSPTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 10 spectra, LEAALGEAK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 4 spectra, LQLELSK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 15 spectra, LSPSPTSQR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 5 spectra, AAYEAELGDAR | 0.000 | 0.000 | 0.000 | 0.090 | 0.000 | 0.000 | 0.000 | 0.910 | ||
| 5 spectra, NSNLVGAAHEELQQSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.227 | 0.060 | 0.712 | ||
| 6 spectra, TALINATGEEVAMR | 0.129 | 0.000 | 0.000 | 0.079 | 0.000 | 0.000 | 0.000 | 0.792 | ||
| 7 spectra, LALDMEIHAYR | 0.000 | 0.000 | 0.115 | 0.000 | 0.000 | 0.034 | 0.000 | 0.851 | ||
| 6 spectra, VAVEEVDEEGK | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 2 spectra, LAVYIDR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | ||
| 5 spectra, EAALSTALSEK | 0.052 | 0.000 | 0.000 | 0.000 | 0.000 | 0.108 | 0.000 | 0.840 | ||
| 4 spectra, LVEIDNGK | 0.287 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.019 | 0.693 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
49 spectra |
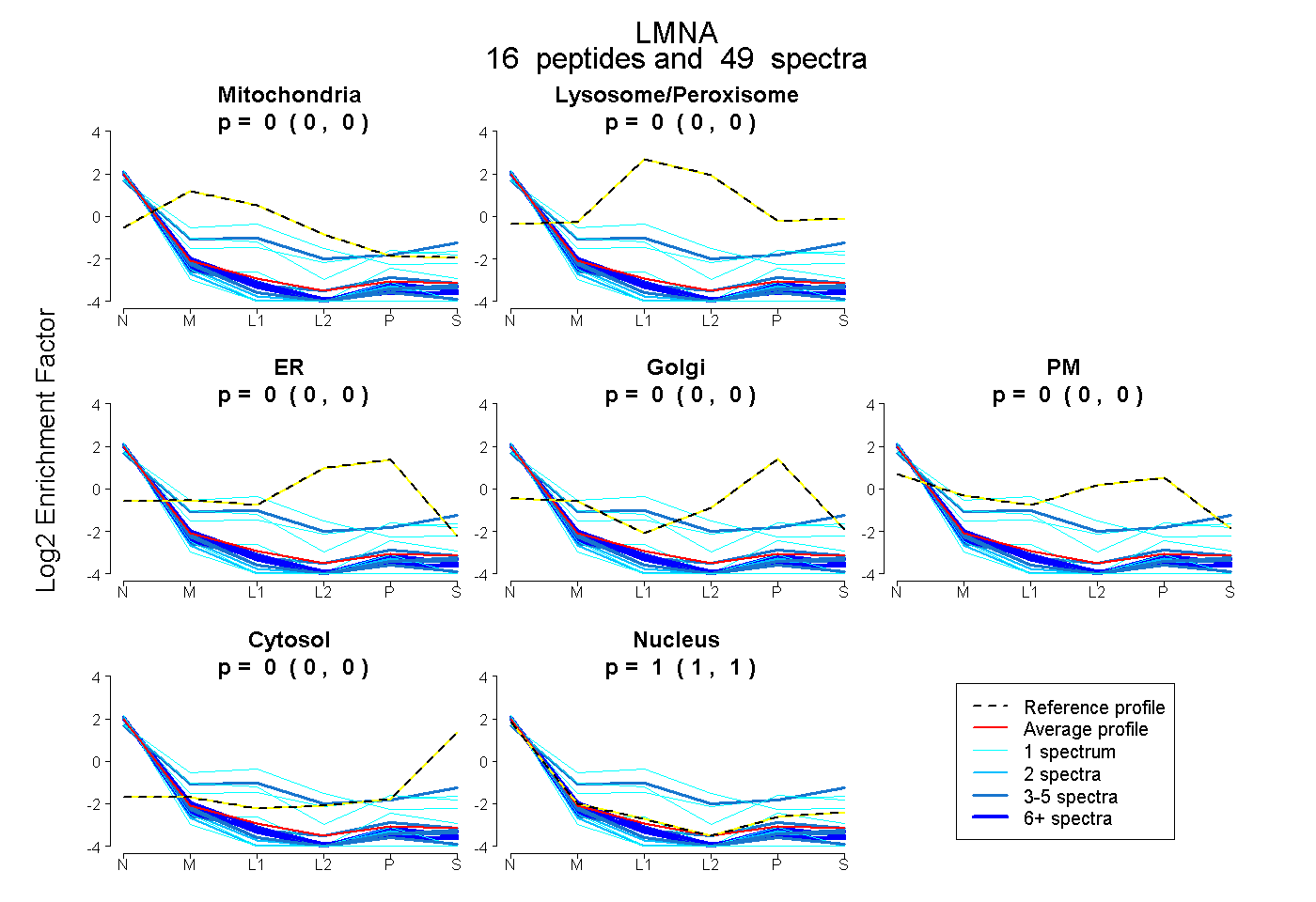 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
13 spectra |
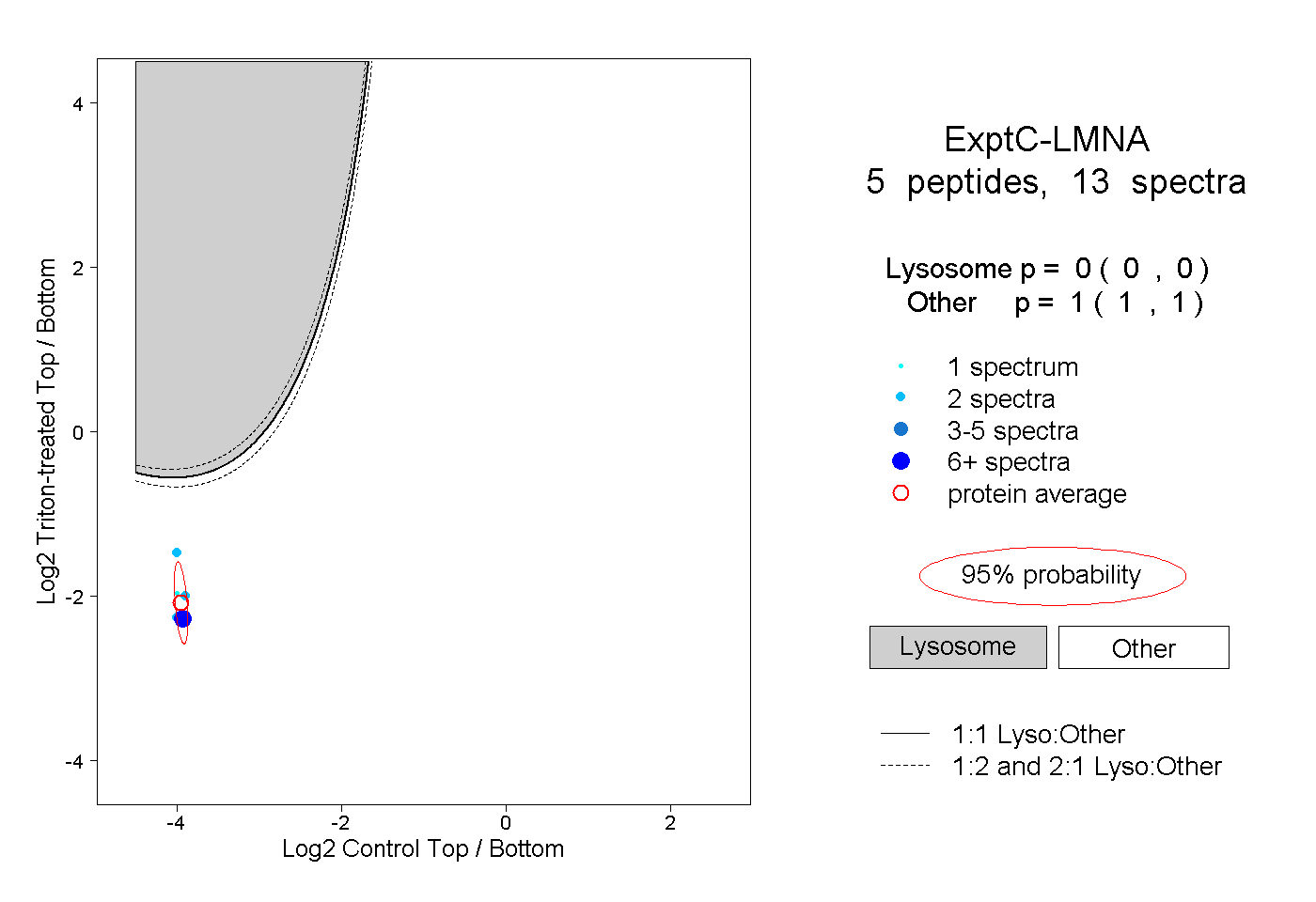 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
5 spectra |
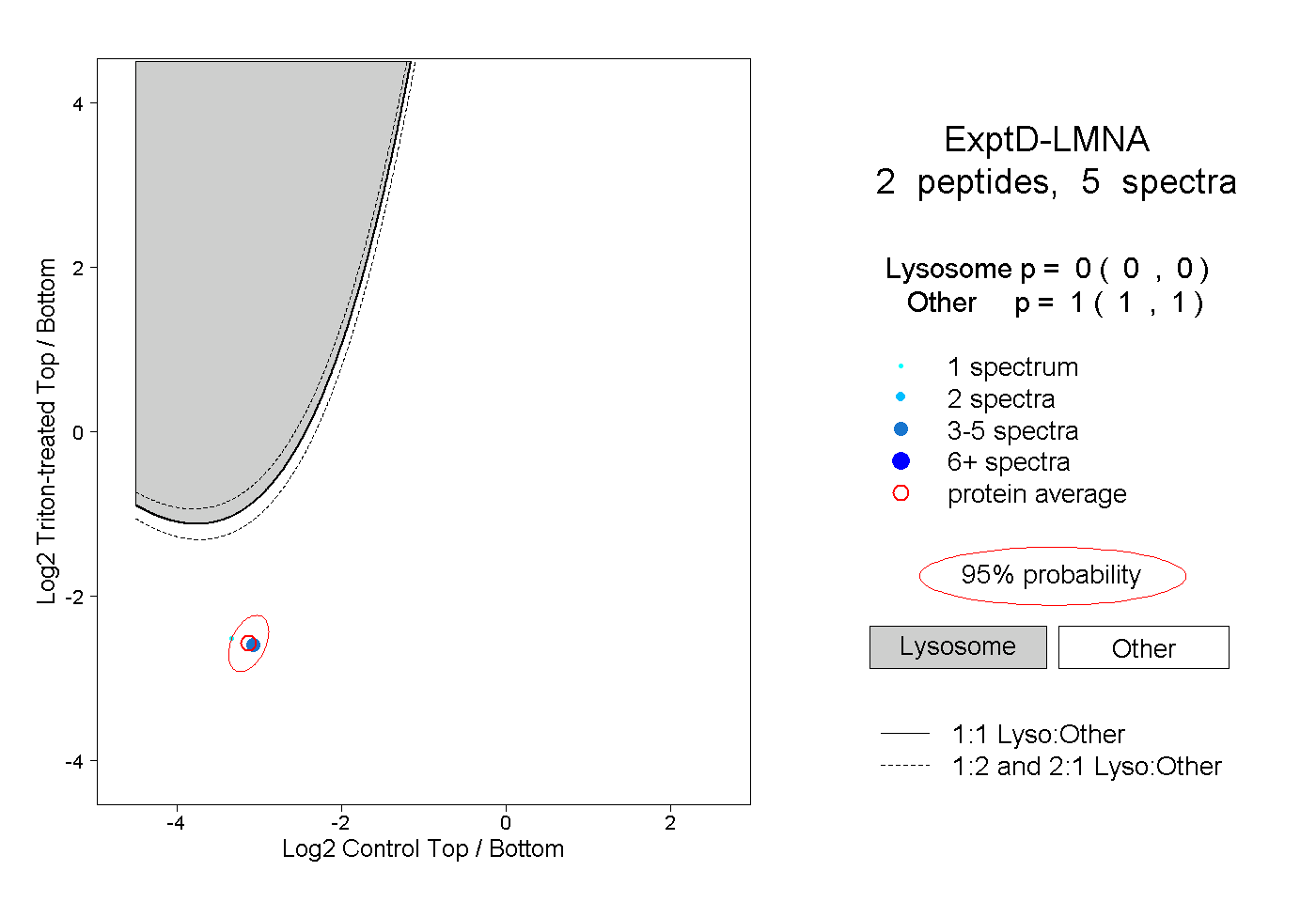 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |