peptides
spectra
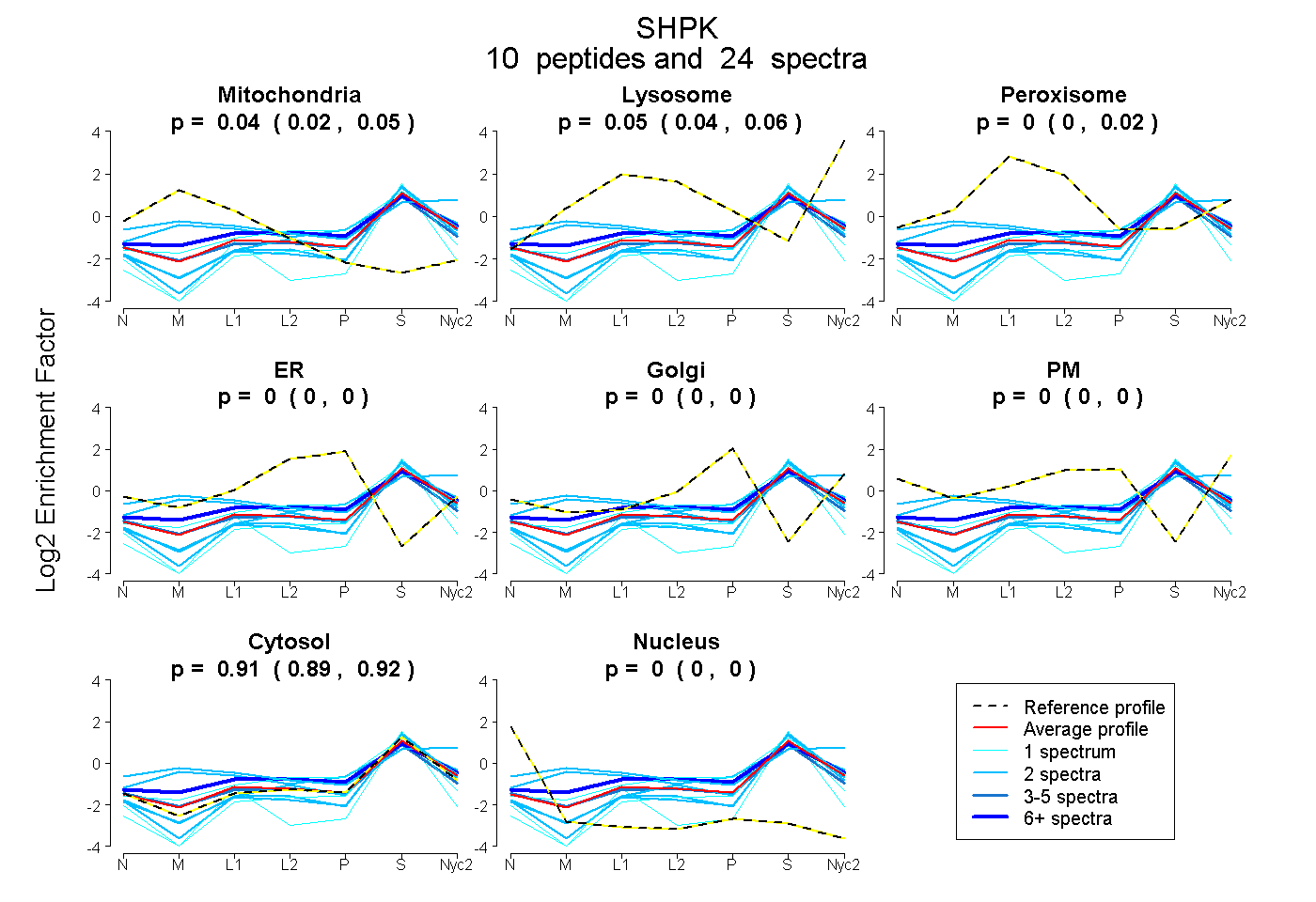
0.018 | 0.054
0.035 | 0.062
0.000 | 0.015
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.889 | 0.923
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
24 spectra |
 |
0.039 0.018 | 0.054 |
0.054 0.035 | 0.062 |
0.000 0.000 | 0.015 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.907 0.889 | 0.923 |
0.000 0.000 | 0.000 |
| 2 spectra, AAGAETESAAAGPQGR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 2 spectra, VVGSGSALSR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, TGQGCEWTER | 0.000 | 0.096 | 0.022 | 0.053 | 0.000 | 0.000 | 0.829 | 0.000 | ||
| 1 spectrum, AALLEAAPGHPSGFVVLASCAR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.914 | 0.086 | ||
| 2 spectra, NSPEFLK | 0.149 | 0.309 | 0.000 | 0.000 | 0.000 | 0.000 | 0.542 | 0.000 | ||
| 7 spectra, MIQAAAQQK | 0.054 | 0.071 | 0.099 | 0.000 | 0.020 | 0.000 | 0.756 | 0.000 | ||
| 2 spectra, DTHLTITPTVLGER | 0.173 | 0.188 | 0.003 | 0.000 | 0.002 | 0.000 | 0.634 | 0.000 | ||
| 2 spectra, EQDVTR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 1.000 | 0.000 | ||
| 1 spectrum, GSAPVFEPR | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.985 | 0.015 | ||
| 4 spectra, AVSHLVTWQDNR | 0.096 | 0.005 | 0.000 | 0.000 | 0.000 | 0.000 | 0.899 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
8 spectra |
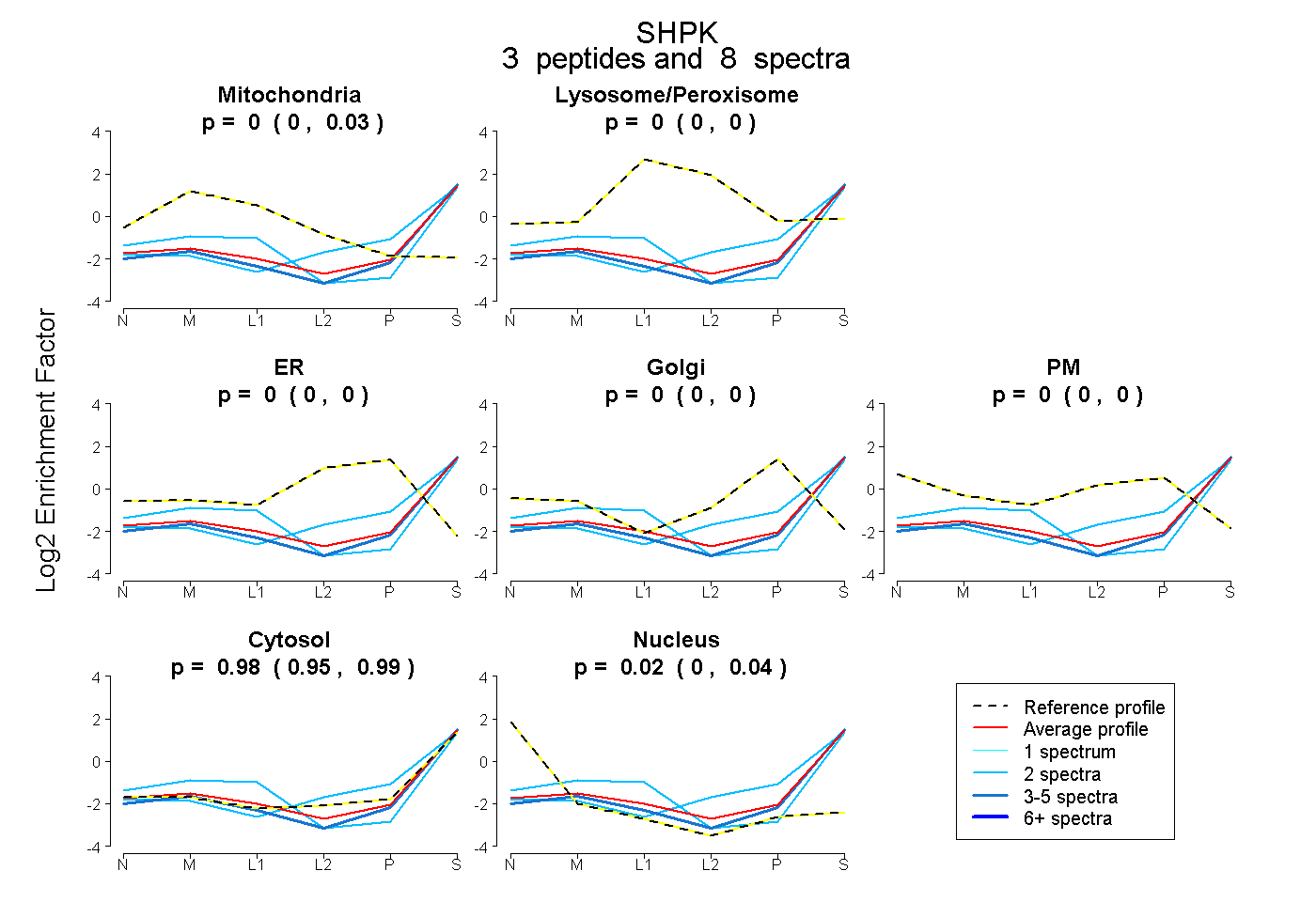 |
0.000 0.000 | 0.032 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.979 0.951 | 0.992 |
0.021 0.000 | 0.042 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
34 spectra |
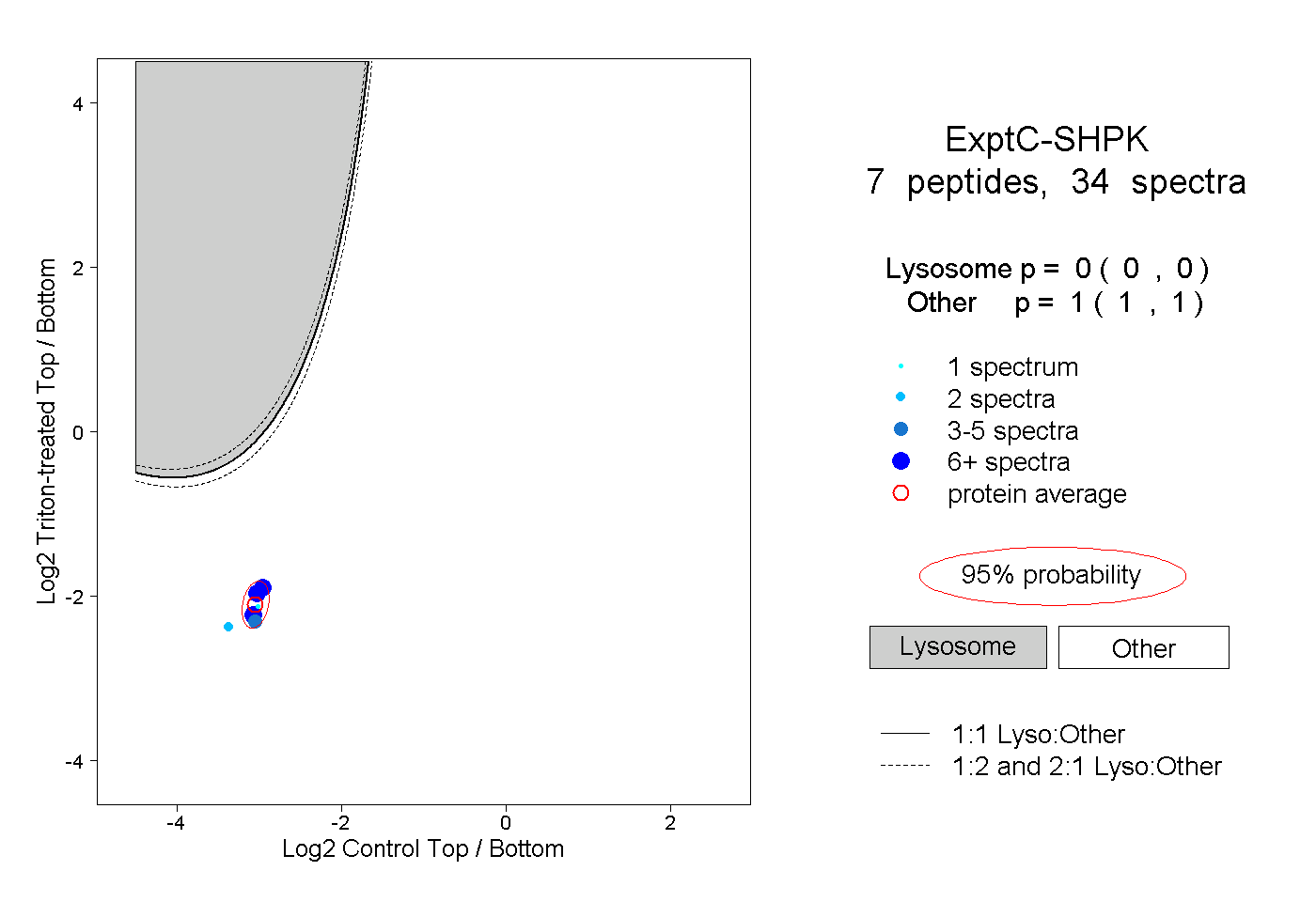 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
2 spectra |
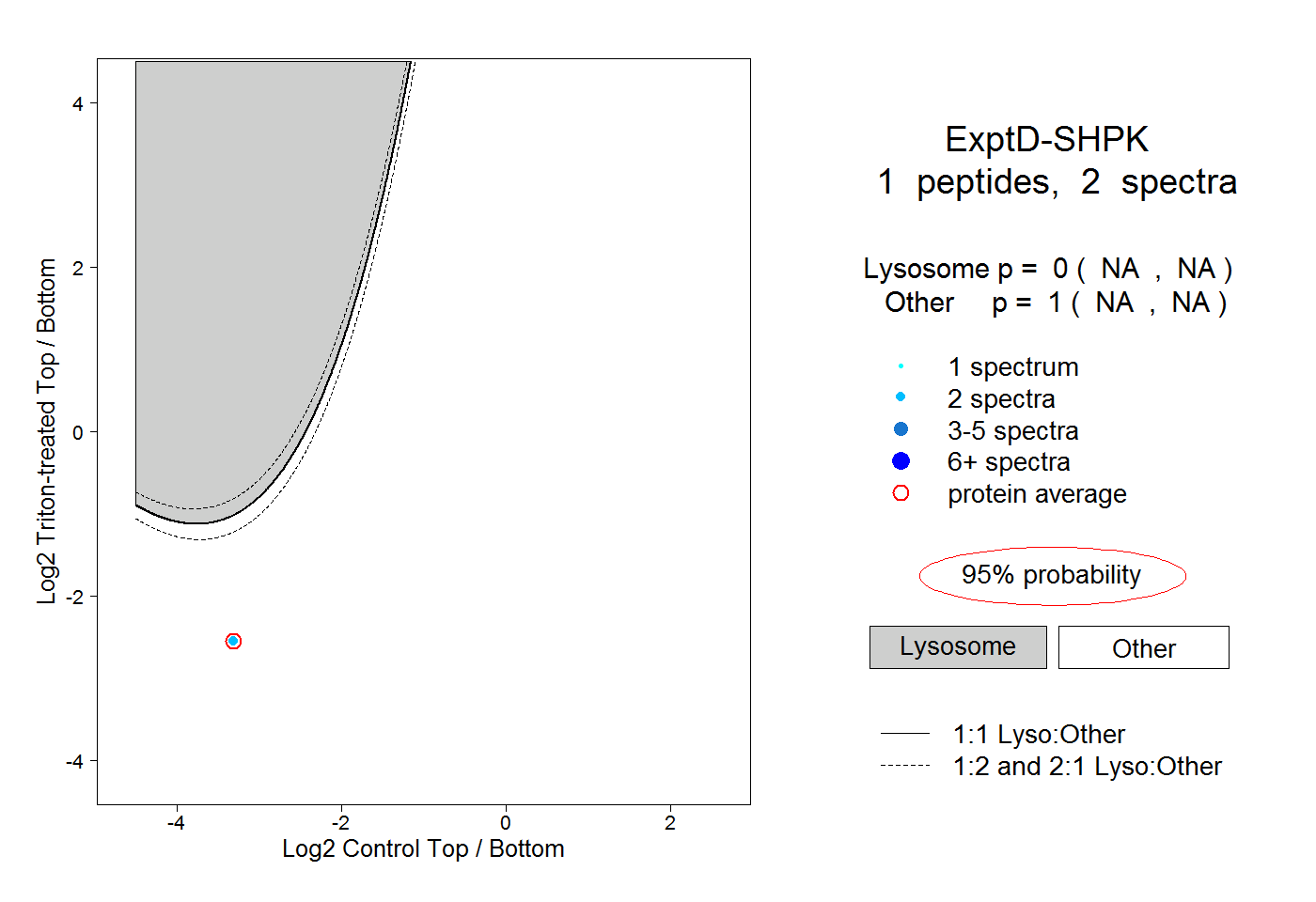 |
0.000 NA | NA |
1.000 NA | NA |