peptides
spectra
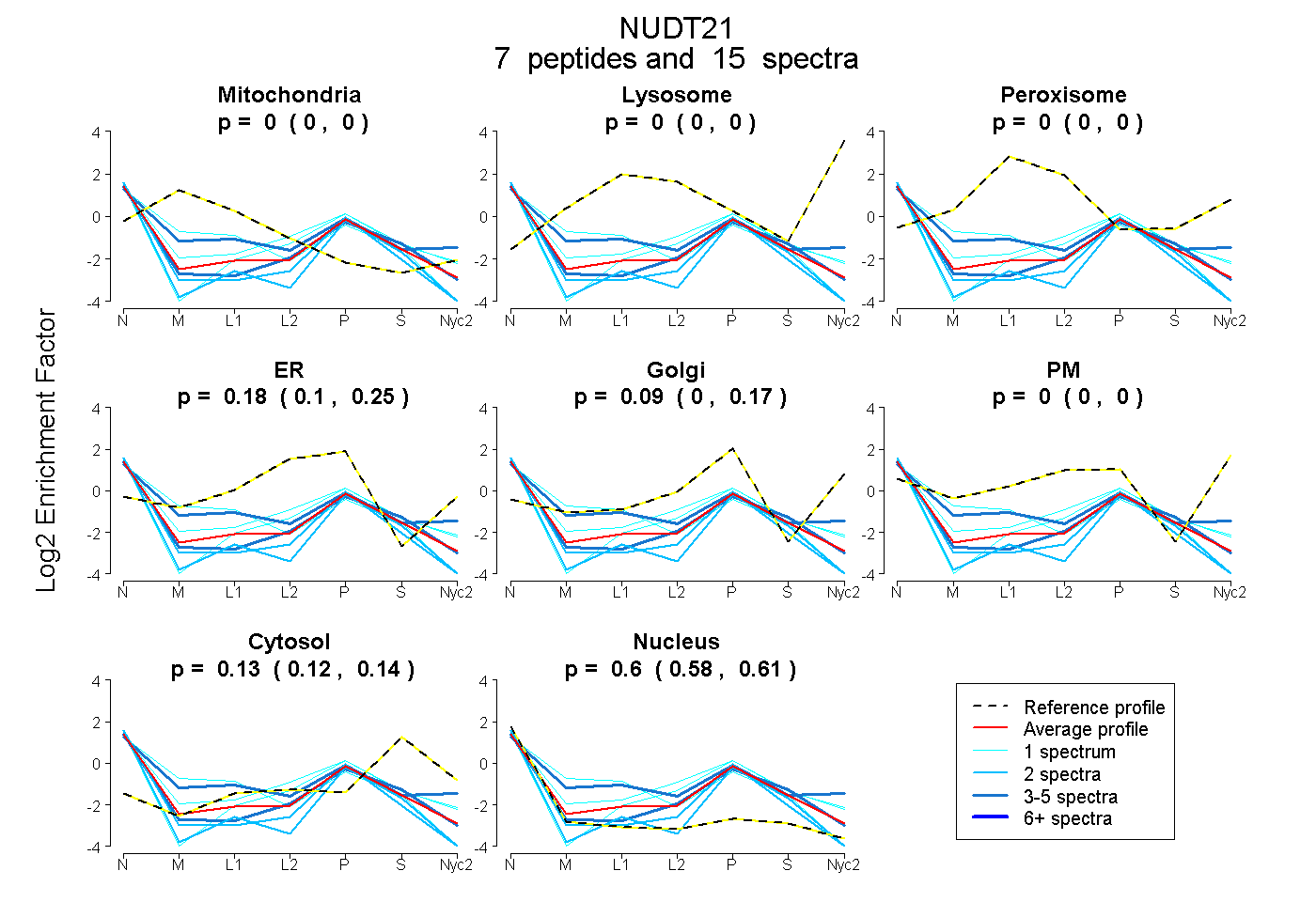
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.102 | 0.253
0.000 | 0.168
0.000 | 0.000
0.117 | 0.141
0.575 | 0.613
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
15 spectra |
 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.185 0.102 | 0.253 |
0.089 0.000 | 0.168 |
0.000 0.000 | 0.000 |
0.130 0.117 | 0.141 |
0.596 0.575 | 0.613 |
| 4 spectra, LFLVQLQEK | 0.000 | 0.000 | 0.000 | 0.087 | 0.119 | 0.000 | 0.181 | 0.613 | ||
| 1 spectrum, DSSVAAR | 0.000 | 0.000 | 0.000 | 0.400 | 0.000 | 0.000 | 0.164 | 0.436 | ||
| 2 spectra, LMTEILGR | 0.000 | 0.000 | 0.000 | 0.101 | 0.095 | 0.000 | 0.006 | 0.797 | ||
| 1 spectrum, FNFIYN | 0.000 | 0.000 | 0.000 | 0.171 | 0.128 | 0.000 | 0.202 | 0.499 | ||
| 1 spectrum, EPLYEK | 0.307 | 0.000 | 0.000 | 0.177 | 0.000 | 0.000 | 0.037 | 0.479 | ||
| 2 spectra, YIQQTKPLTLER | 0.000 | 0.000 | 0.000 | 0.000 | 0.089 | 0.000 | 0.105 | 0.806 | ||
| 4 spectra, GVNQFGNK | 0.000 | 0.000 | 0.183 | 0.000 | 0.341 | 0.000 | 0.023 | 0.453 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptide |
1 spectrum |
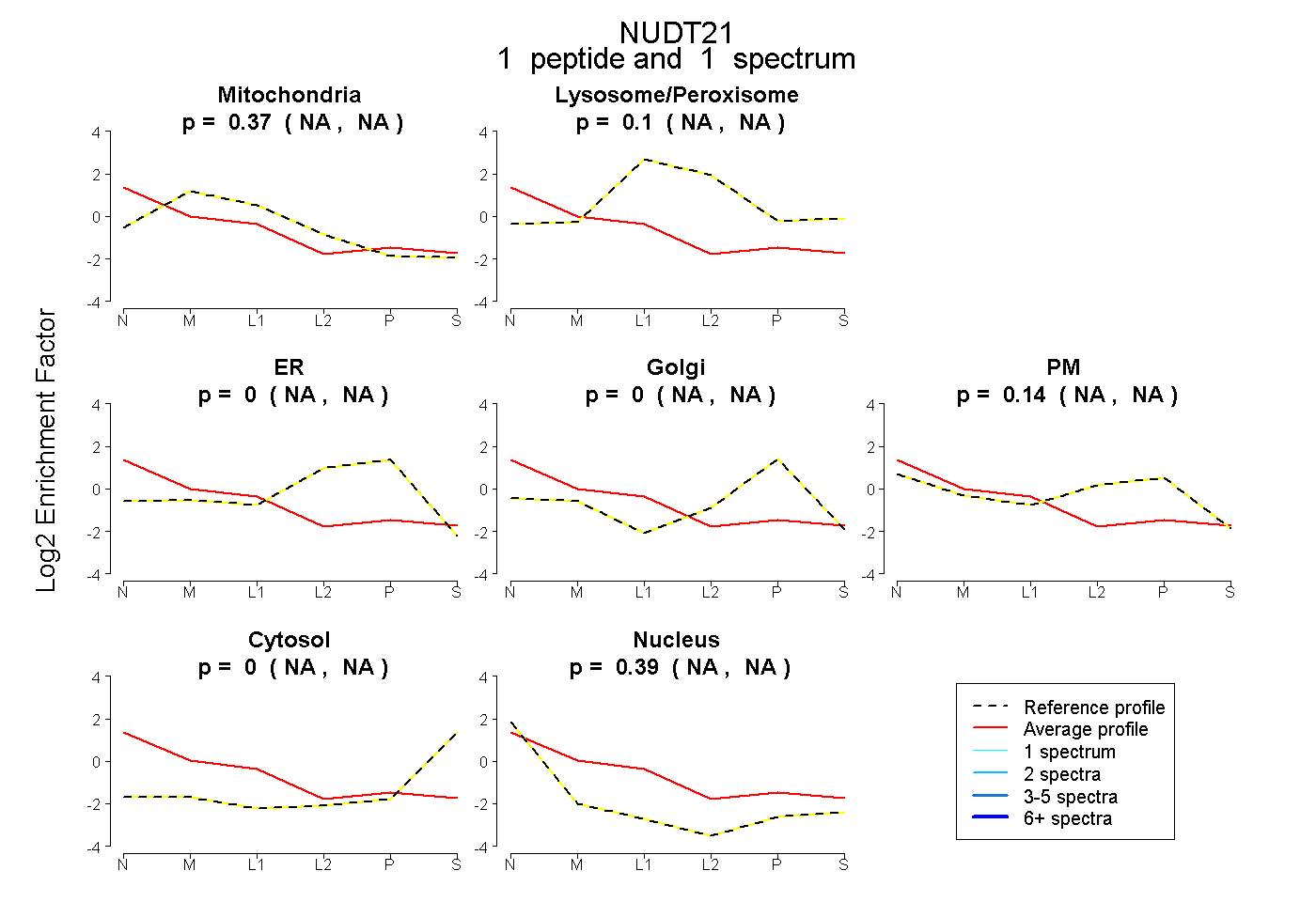 |
0.366 NA | NA |
0.100 NA | NA |
0.000 NA | NA |
0.000 NA | NA |
0.143 NA | NA |
0.000 NA | NA |
0.390 NA | NA |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptide |
2 spectra |
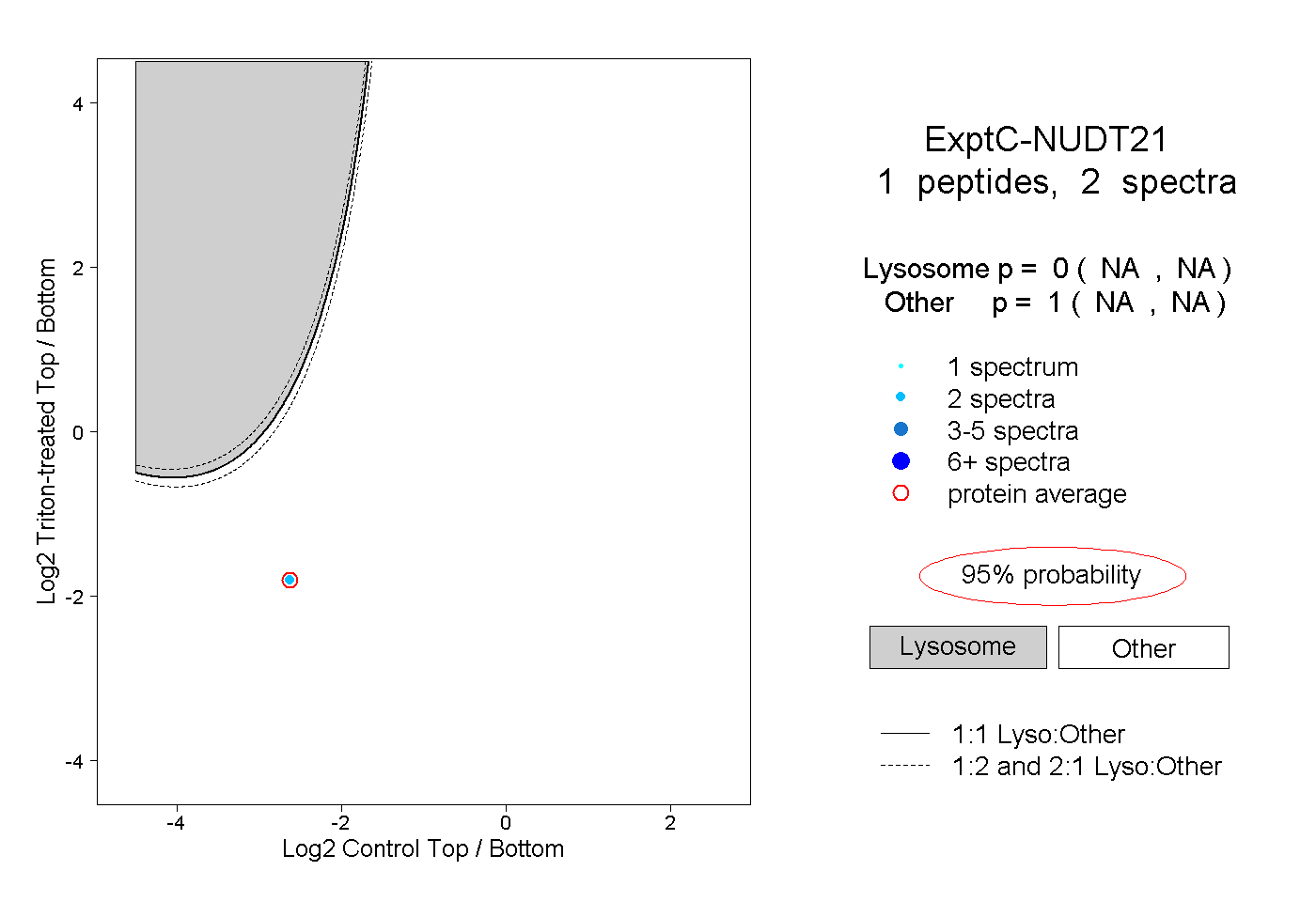 |
0.000 NA | NA |
1.000 NA | NA |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptide |
1 spectrum |
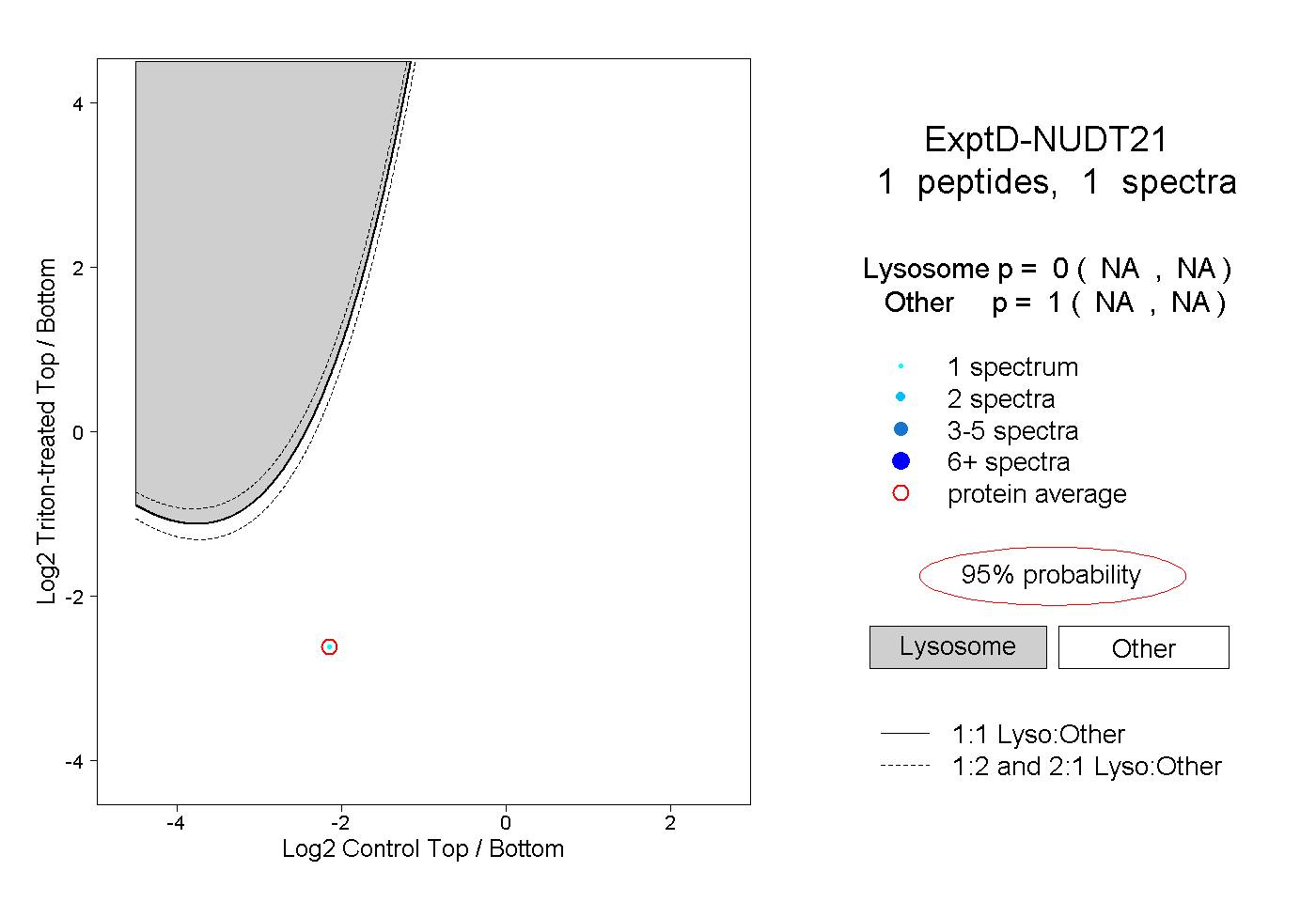 |
0.000 NA | NA |
1.000 NA | NA |